peptides
spectra
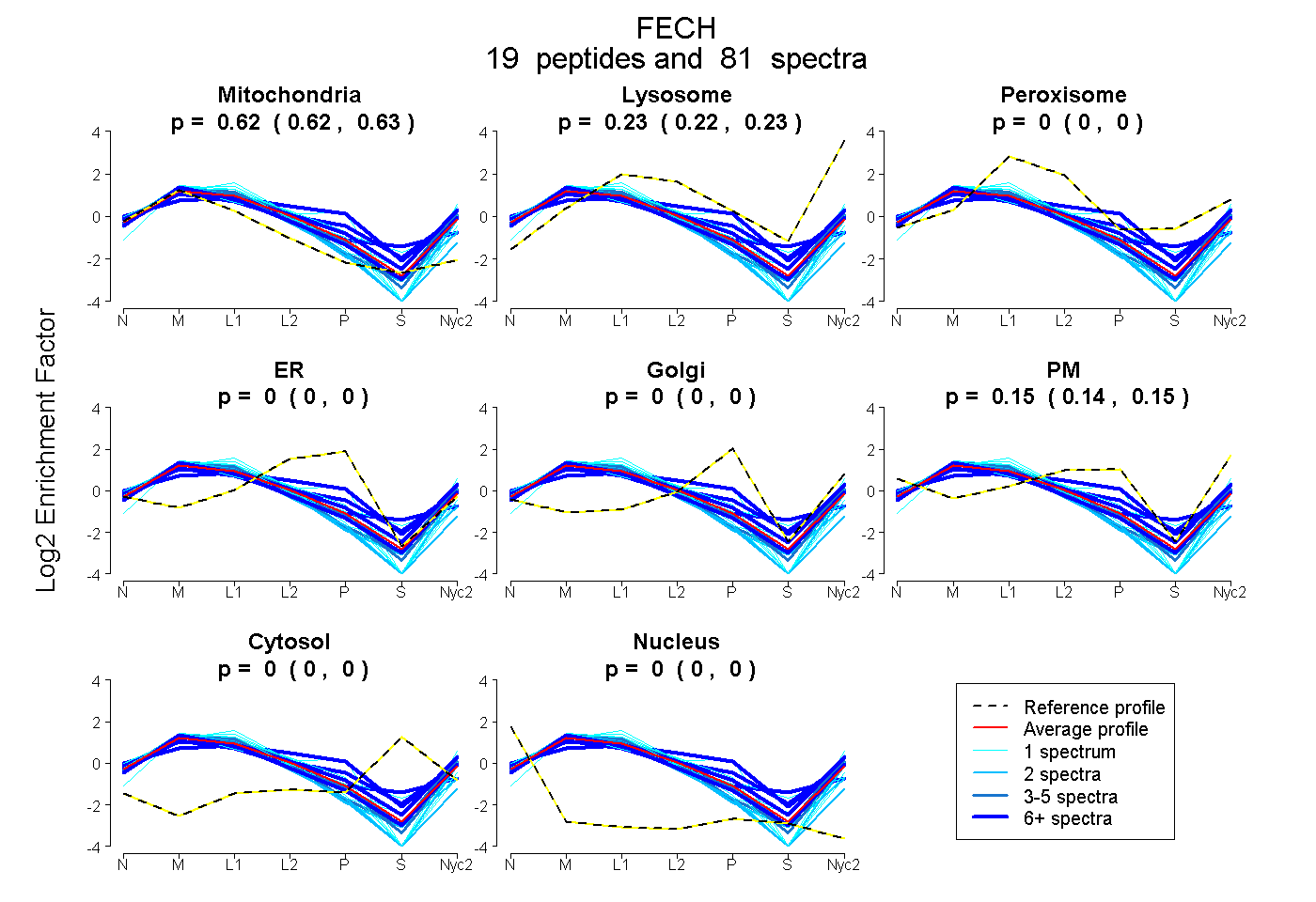
0.618 | 0.626
0.224 | 0.234
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.141 | 0.155
0.000 | 0.000
0.000 | 0.000
peptides
spectra
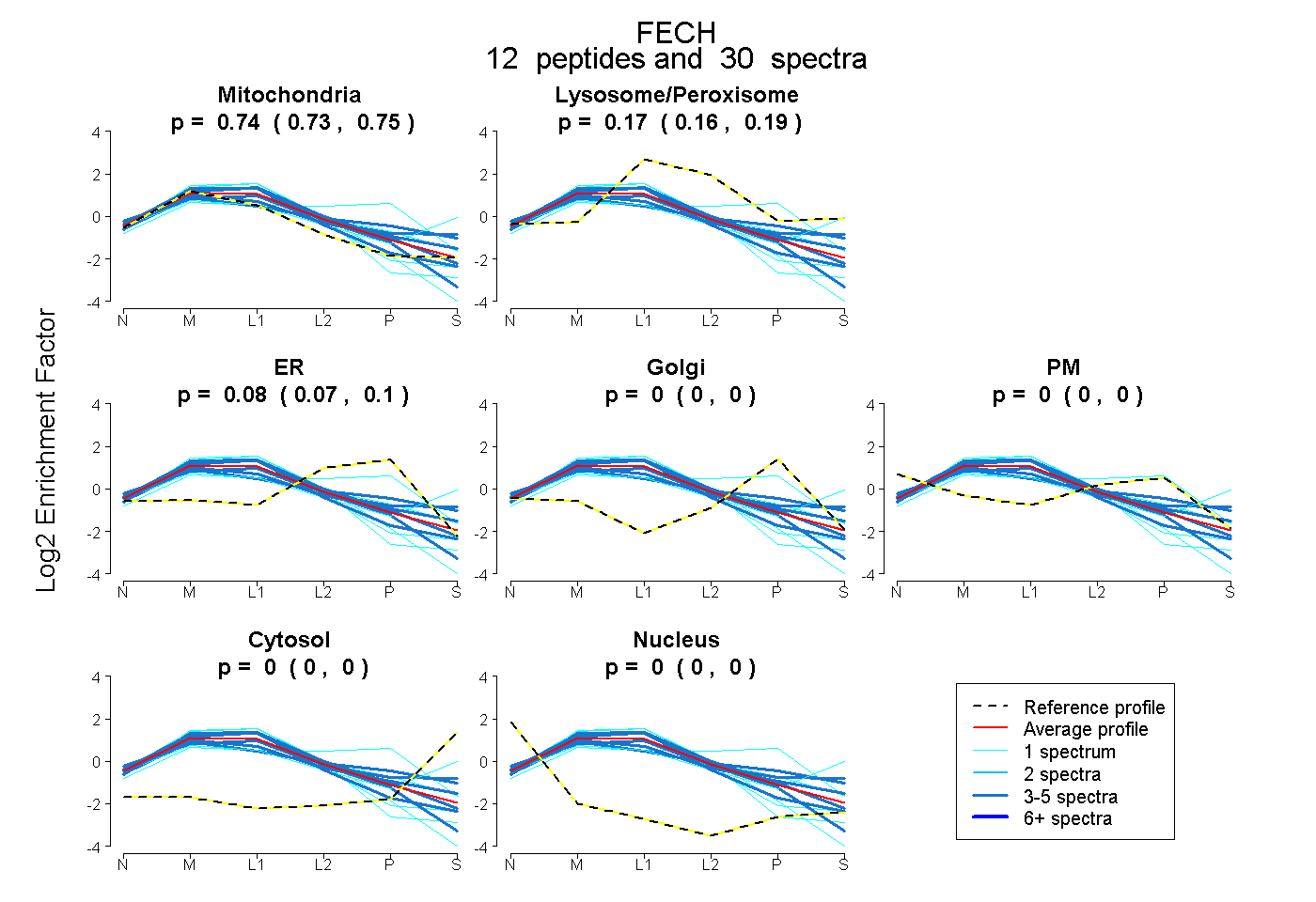
0.732 | 0.755
0.156 | 0.186
0.066 | 0.096
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
81 spectra |
 |
0.622 0.618 | 0.626 |
0.229 0.224 | 0.234 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.149 0.141 | 0.155 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
30 spectra |
 |
0.745 0.732 | 0.755 |
0.173 0.156 | 0.186 |
0.082 0.066 | 0.096 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 5 spectra, YYNEVGR | 0.721 | 0.213 | 0.065 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, YYIGFR | 0.895 | 0.105 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, CGAENIR | 0.627 | 0.230 | 0.081 | 0.000 | 0.062 | 0.000 | 0.000 | |||
| 3 spectra, YVHPLTEEAIEEMER | 0.677 | 0.204 | 0.000 | 0.119 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, ELDHFPEEK | 0.977 | 0.011 | 0.012 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, LLDELSPDTAPHK | 0.486 | 0.286 | 0.000 | 0.215 | 0.000 | 0.014 | 0.000 | |||
| 4 spectra, TTKPQAQPER | 0.846 | 0.046 | 0.109 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, AESLNGNPLFSK | 0.294 | 0.201 | 0.505 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, GDPYPQEVGATVHR | 0.540 | 0.322 | 0.000 | 0.069 | 0.028 | 0.041 | 0.000 | |||
| 1 spectrum, LAPFIAK | 0.946 | 0.054 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, VGPVPWLGPQTDEAIK | 0.472 | 0.294 | 0.000 | 0.000 | 0.000 | 0.234 | 0.000 | |||
| 1 spectrum, LVWQSK | 0.910 | 0.090 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
340 spectra |
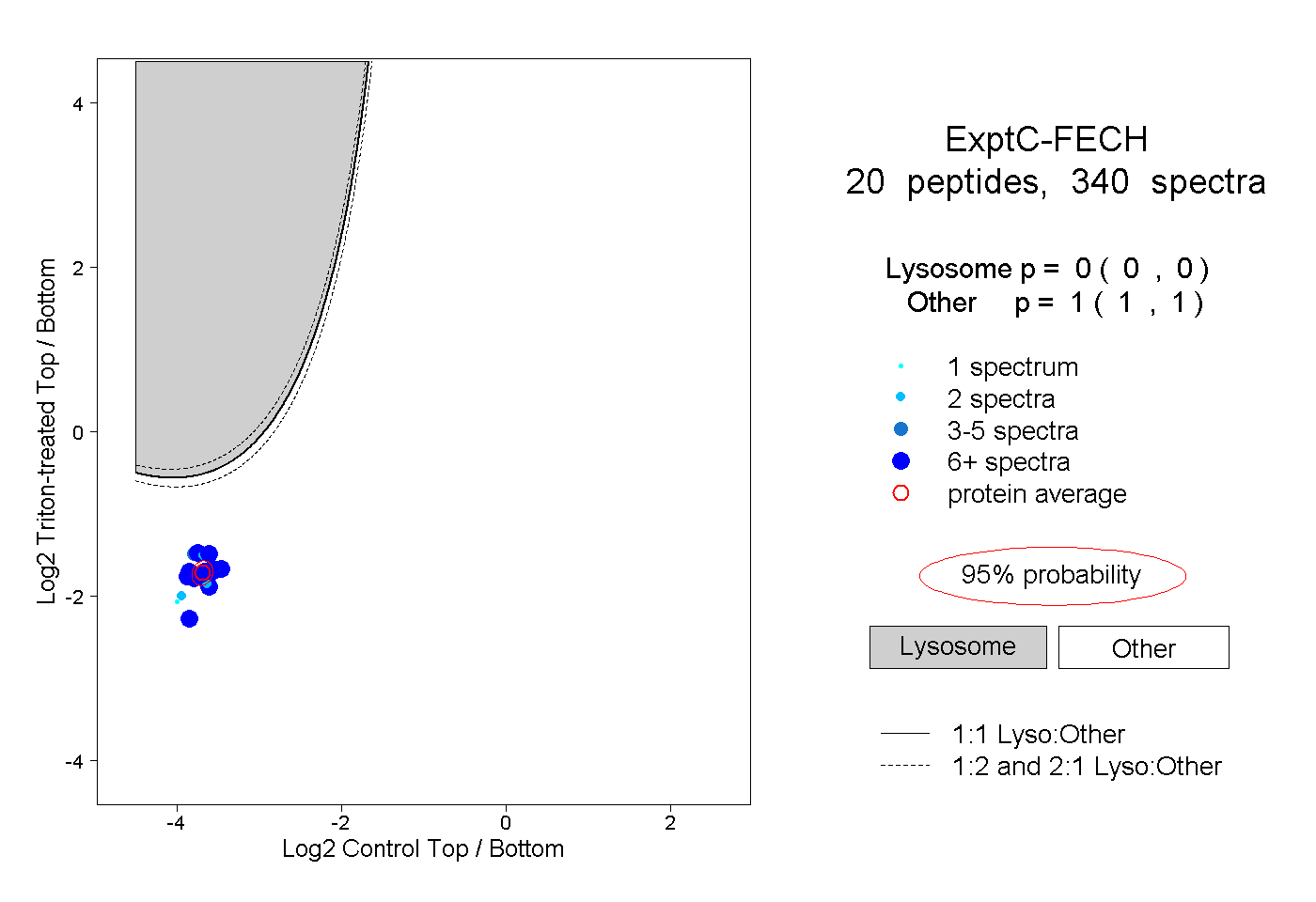 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
21 spectra |
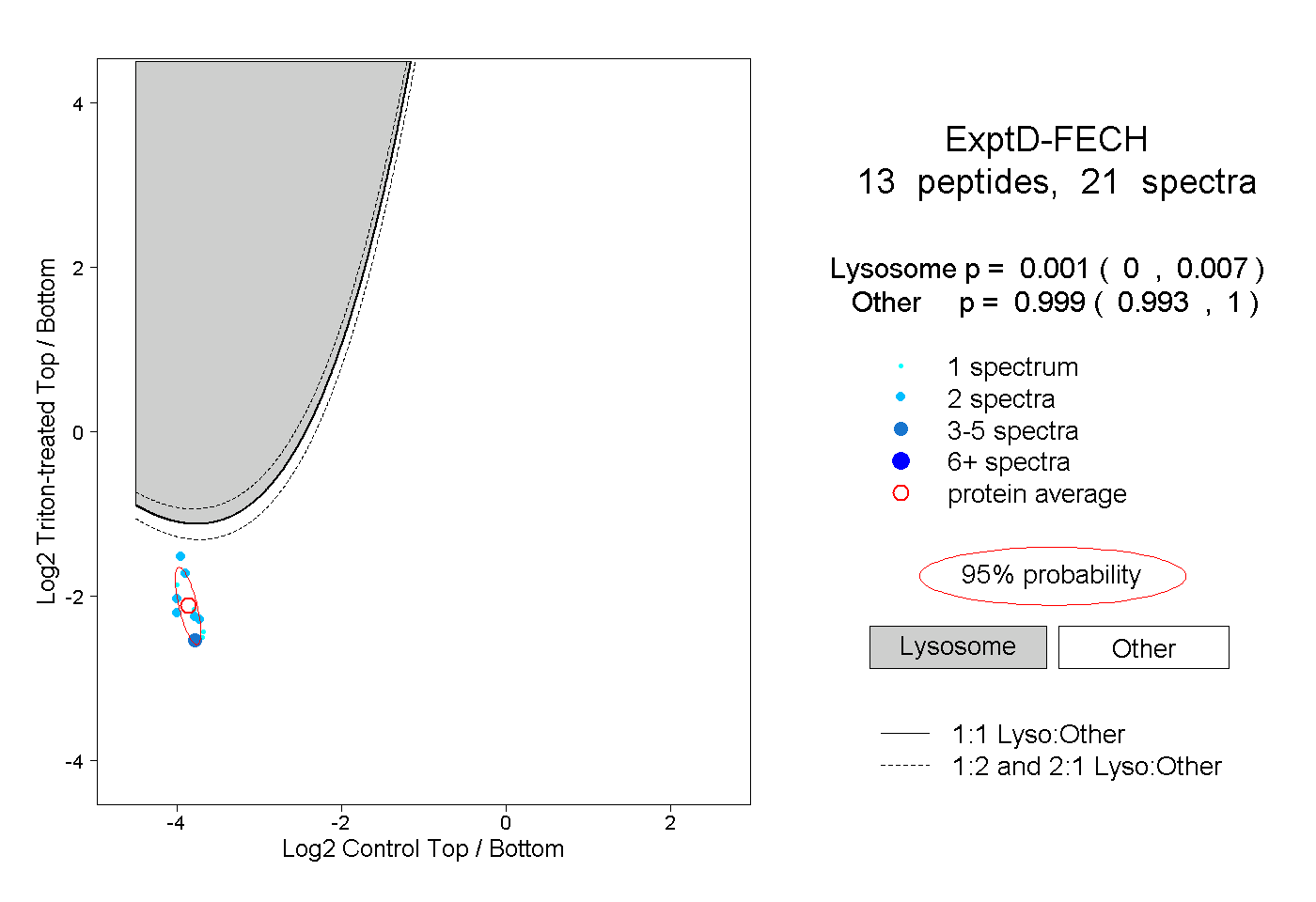 |
0.001 0.000 | 0.007 |
0.999 0.993 | 1.000 |