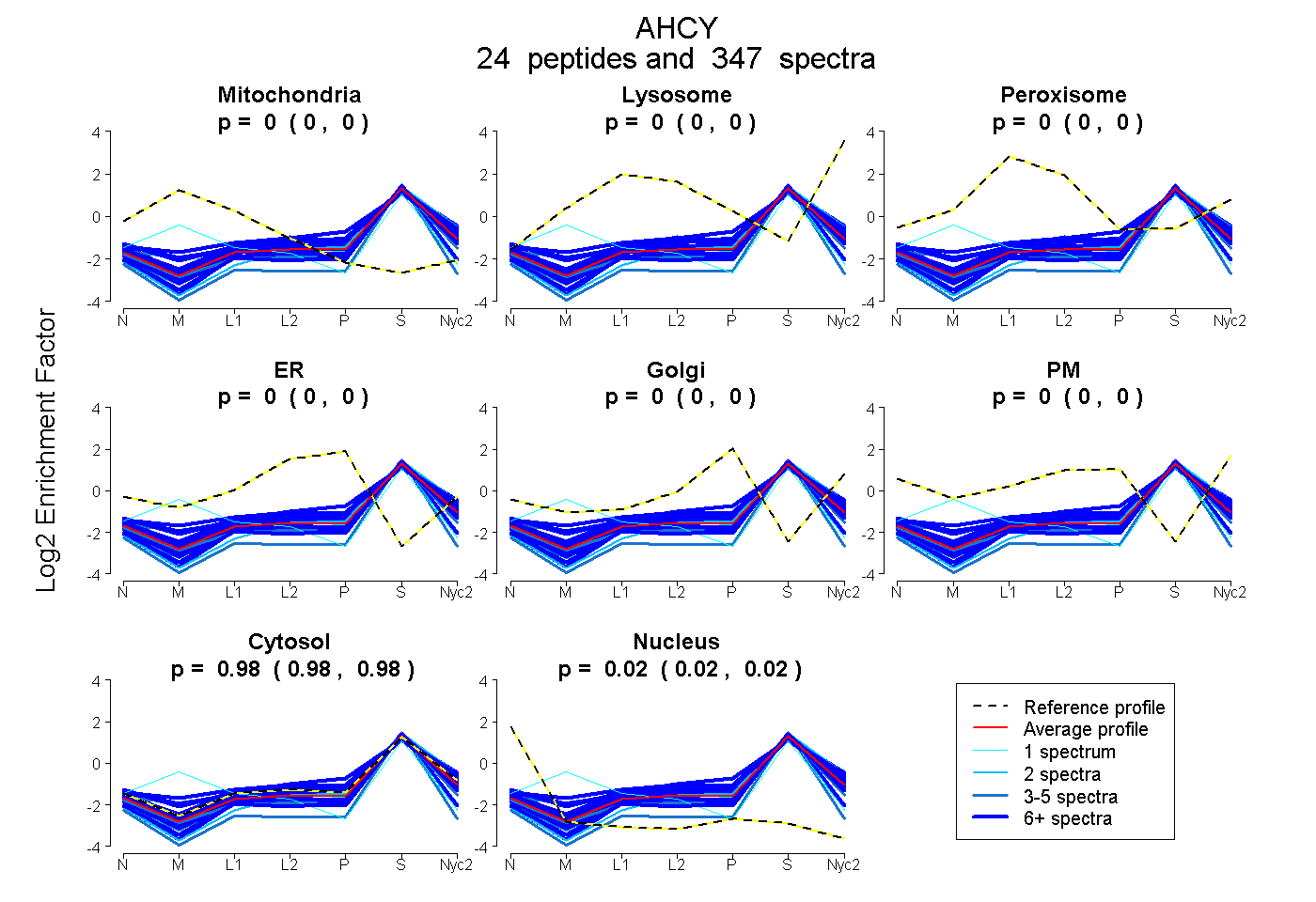
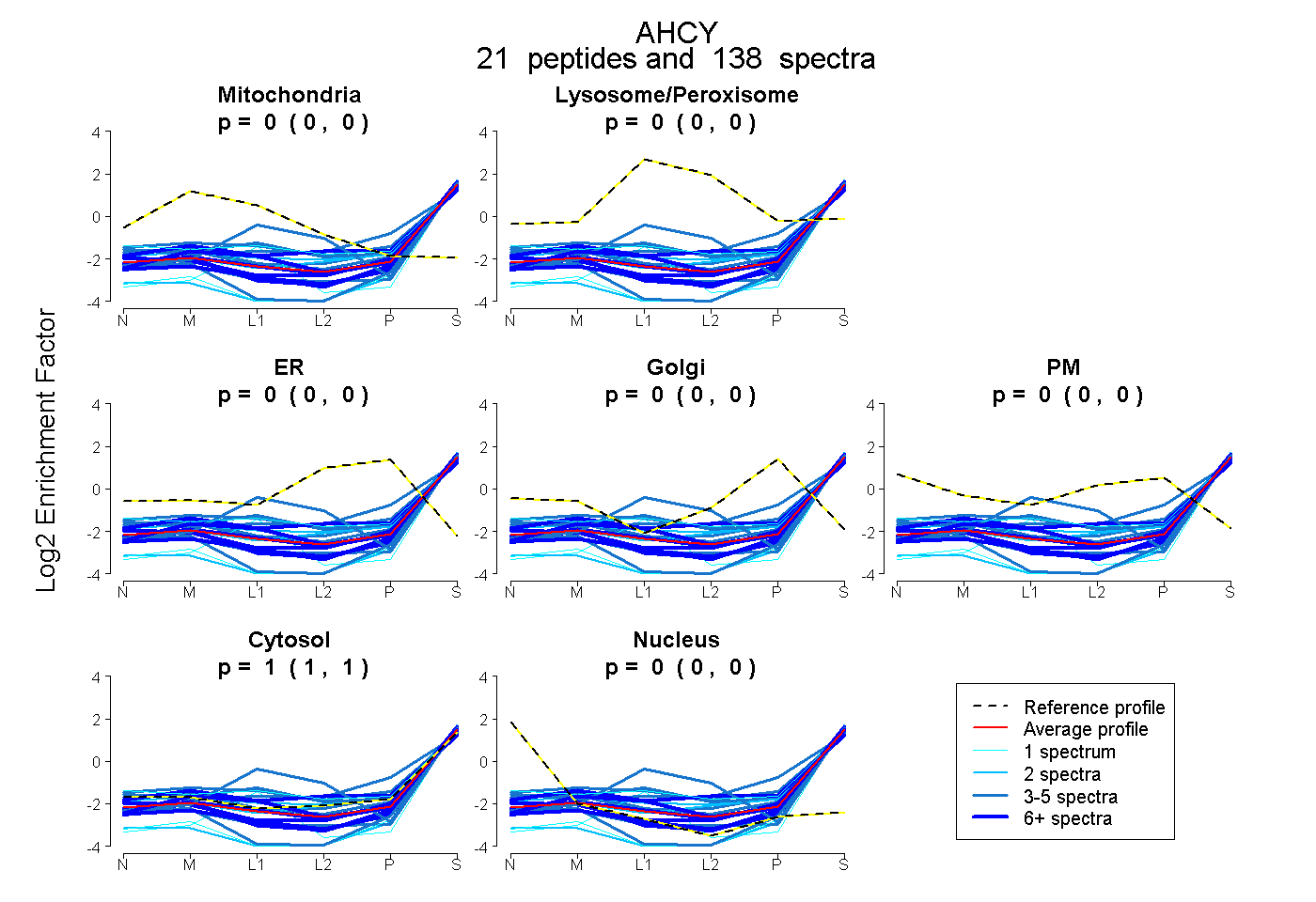
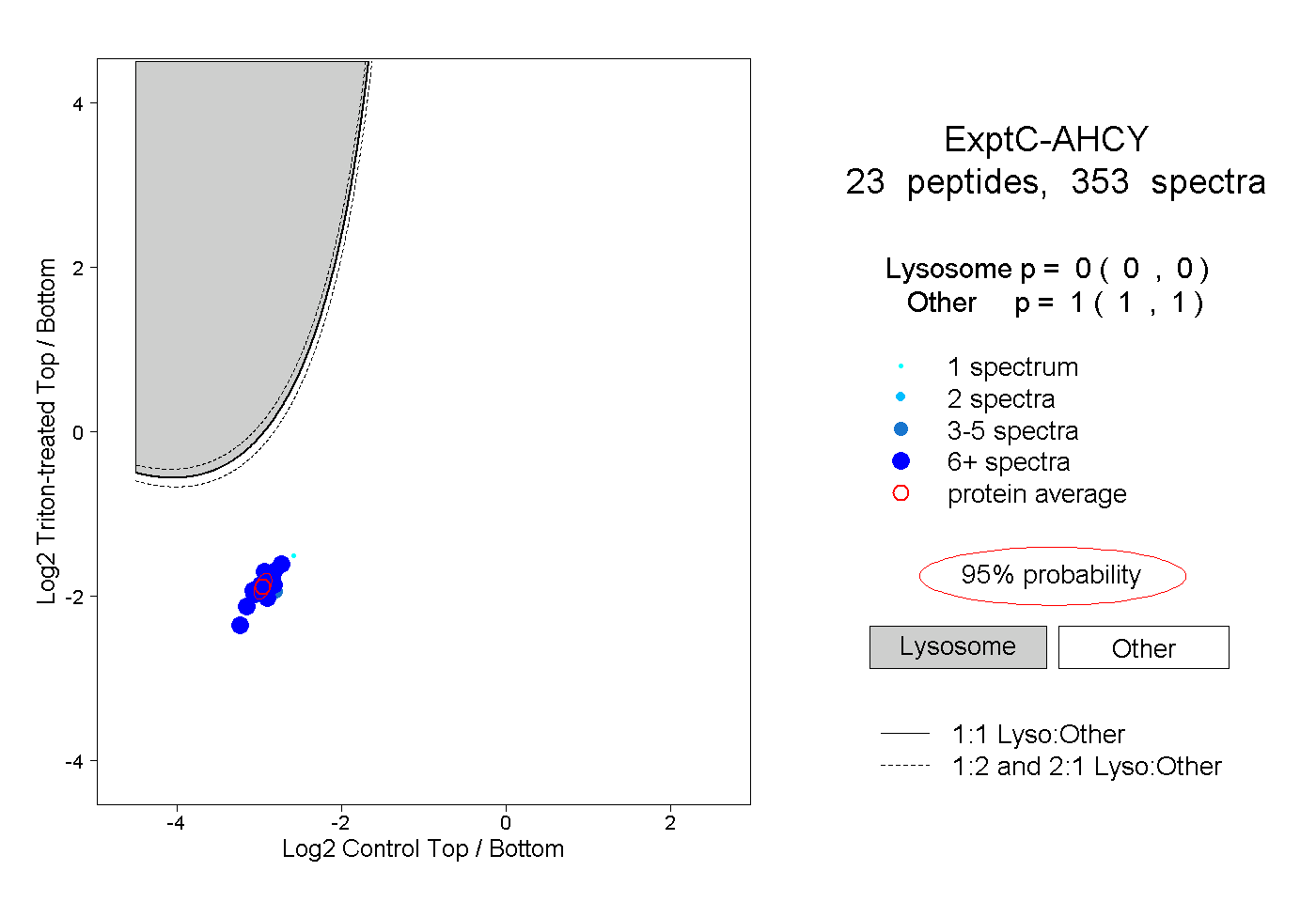
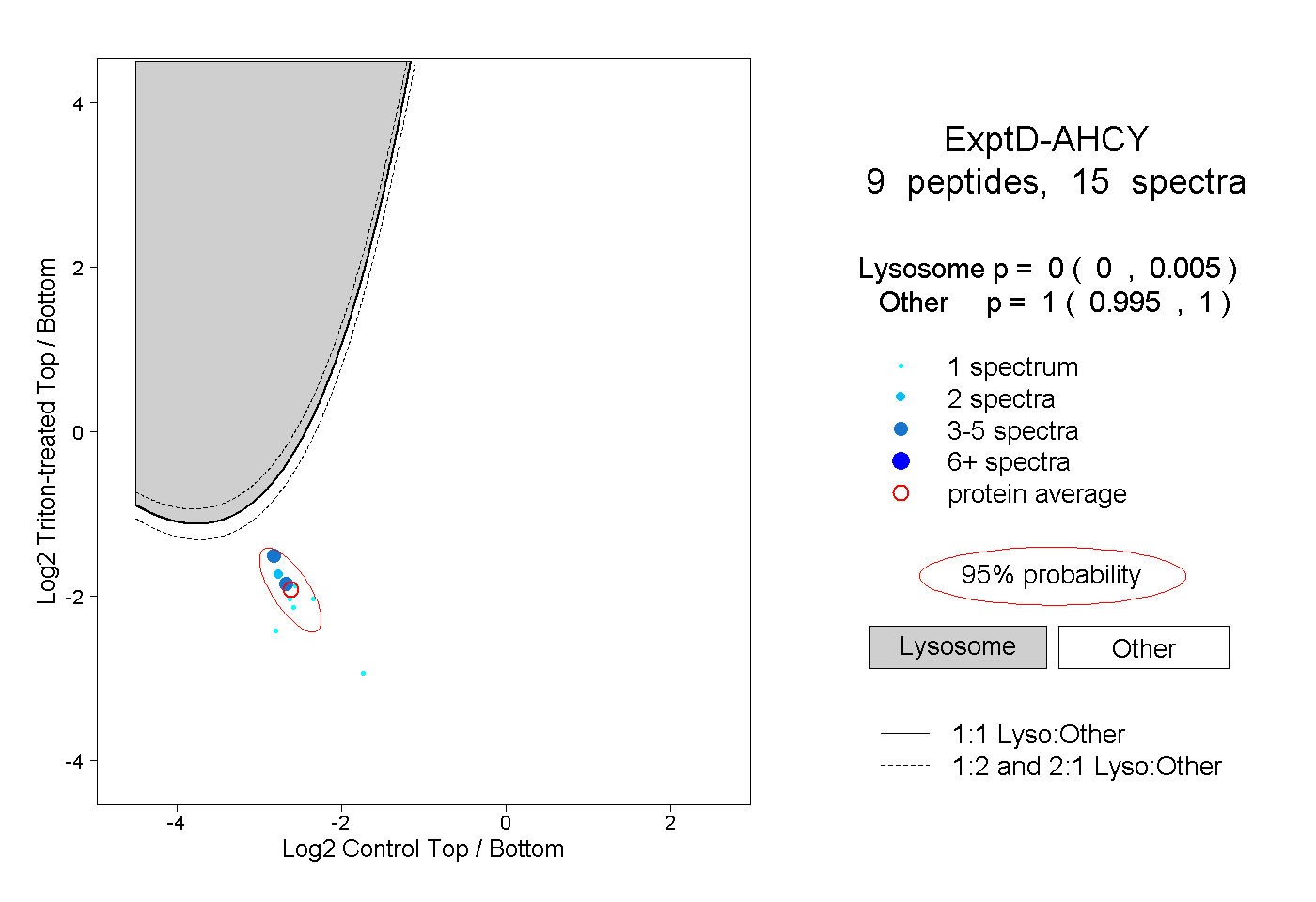
| 19 spectra, LDEAVAEAHLGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, FDNLYGCR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 34 spectra, AGIPVFAWK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, MMANGILK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 20 spectra, DGPLNMILDDGGDLTNLIHTK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, EMYSASKPLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 13 spectra, WLNENAVEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 38 spectra, VNIKPQVDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, GISEETTTGVHNLYK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, EGNIFVTTTGCVDIILGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, QAQYLGMPINGPFKPDHYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, GETDEEYLWCIEQTLHFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, ALDIAENEMPGLMR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 16 spectra, HPQLLSGIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, VPAINVNDSVTK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, VAVVAGYGDVGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, VADIGLAAWGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, HFEQMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 49 spectra, IILLAEGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 36 spectra, ATDVMIAGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 11 spectra, ESILDGLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 17 spectra, YPVGVHFLPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 14 spectra, GCAQALR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |