peptides
spectra
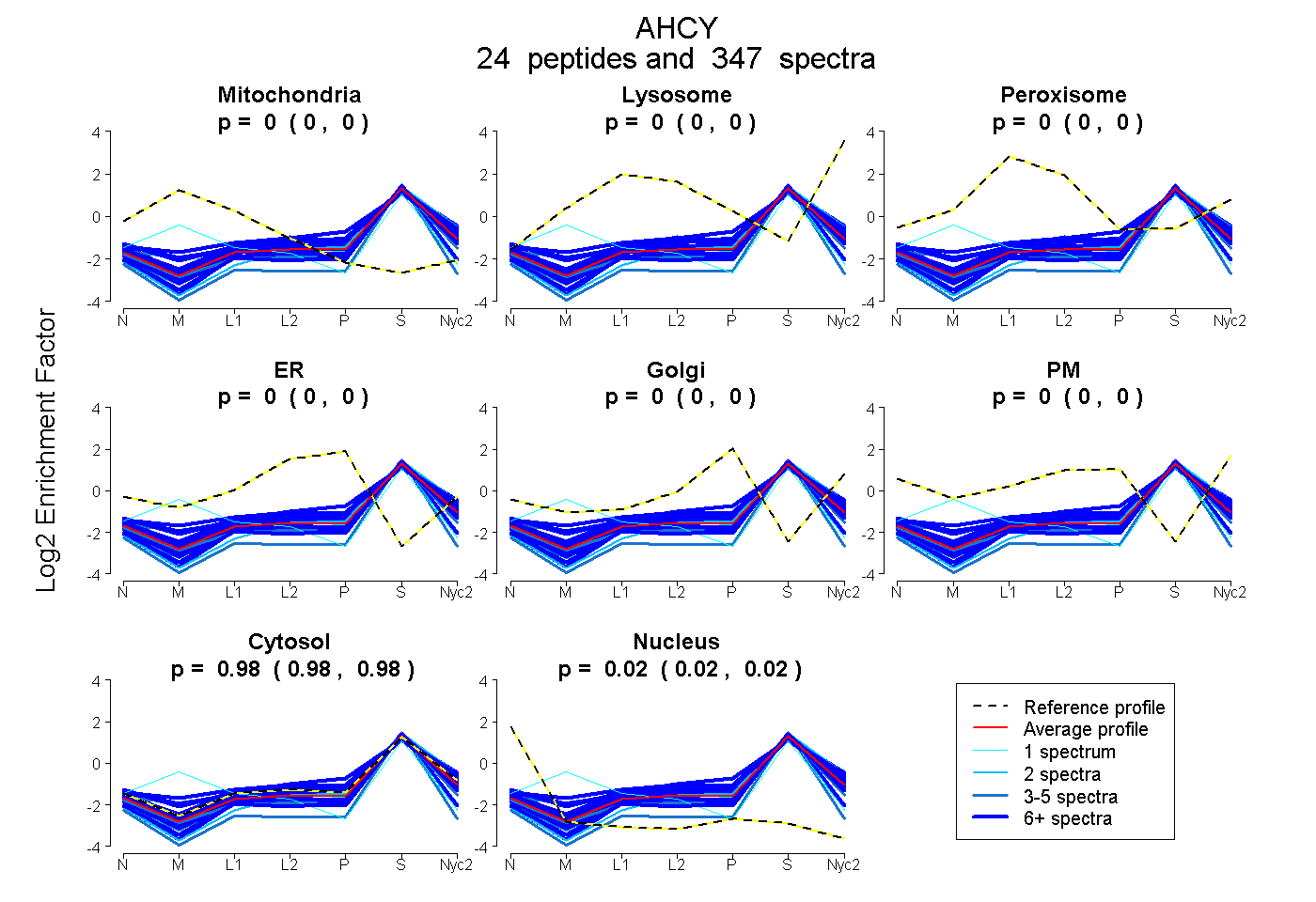
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.980 | 0.982
0.018 | 0.020
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
347 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.981 0.980 | 0.982 |
0.019 0.018 | 0.020 |
| 11 spectra, LDEAVAEAHLGK | 0.023 | 0.060 | 0.000 | 0.000 | 0.000 | 0.000 | 0.917 | 0.000 | ||
| 4 spectra, FDNLYGCR | 0.035 | 0.028 | 0.000 | 0.000 | 0.000 | 0.000 | 0.938 | 0.000 | ||
| 24 spectra, AGIPVFAWK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.986 | 0.014 | ||
| 9 spectra, MMANGILK | 0.000 | 0.000 | 0.000 | 0.080 | 0.035 | 0.000 | 0.885 | 0.000 | ||
| 5 spectra, DGPLNMILDDGGDLTNLIHTK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.973 | 0.027 | ||
| 6 spectra, EMYSASKPLK | 0.000 | 0.000 | 0.000 | 0.034 | 0.000 | 0.000 | 0.966 | 0.000 | ||
| 10 spectra, WLNENAVEK | 0.067 | 0.061 | 0.002 | 0.004 | 0.004 | 0.000 | 0.862 | 0.000 | ||
| 33 spectra, VNIKPQVDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.965 | 0.035 | ||
| 7 spectra, GISEETTTGVHNLYK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.993 | 0.007 | ||
| 3 spectra, EGNIFVTTTGCVDIILGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.822 | 0.178 | ||
| 2 spectra, QAQYLGMPINGPFKPDHYR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 1 spectrum, GETDEEYLWCIEQTLHFK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.874 | 0.126 | ||
| 25 spectra, ALDIAENEMPGLMR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 40 spectra, HPQLLSGIR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.993 | 0.007 | ||
| 3 spectra, VPAINVNDSVTK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.927 | 0.073 | ||
| 15 spectra, VAVVAGYGDVGK | 0.000 | 0.024 | 0.000 | 0.000 | 0.033 | 0.000 | 0.943 | 0.000 | ||
| 17 spectra, VADIGLAAWGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.973 | 0.027 | ||
| 7 spectra, HFEQMK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 27 spectra, IILLAEGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.974 | 0.026 | ||
| 12 spectra, ATDVMIAGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.960 | 0.040 | ||
| 1 spectrum, WSSCNIFSTQDHAAAAIAK | 0.312 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.683 | 0.005 | ||
| 18 spectra, ESILDGLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 28 spectra, YPVGVHFLPK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.954 | 0.046 | ||
| 39 spectra, GCAQALR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.916 | 0.084 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
138 spectra |
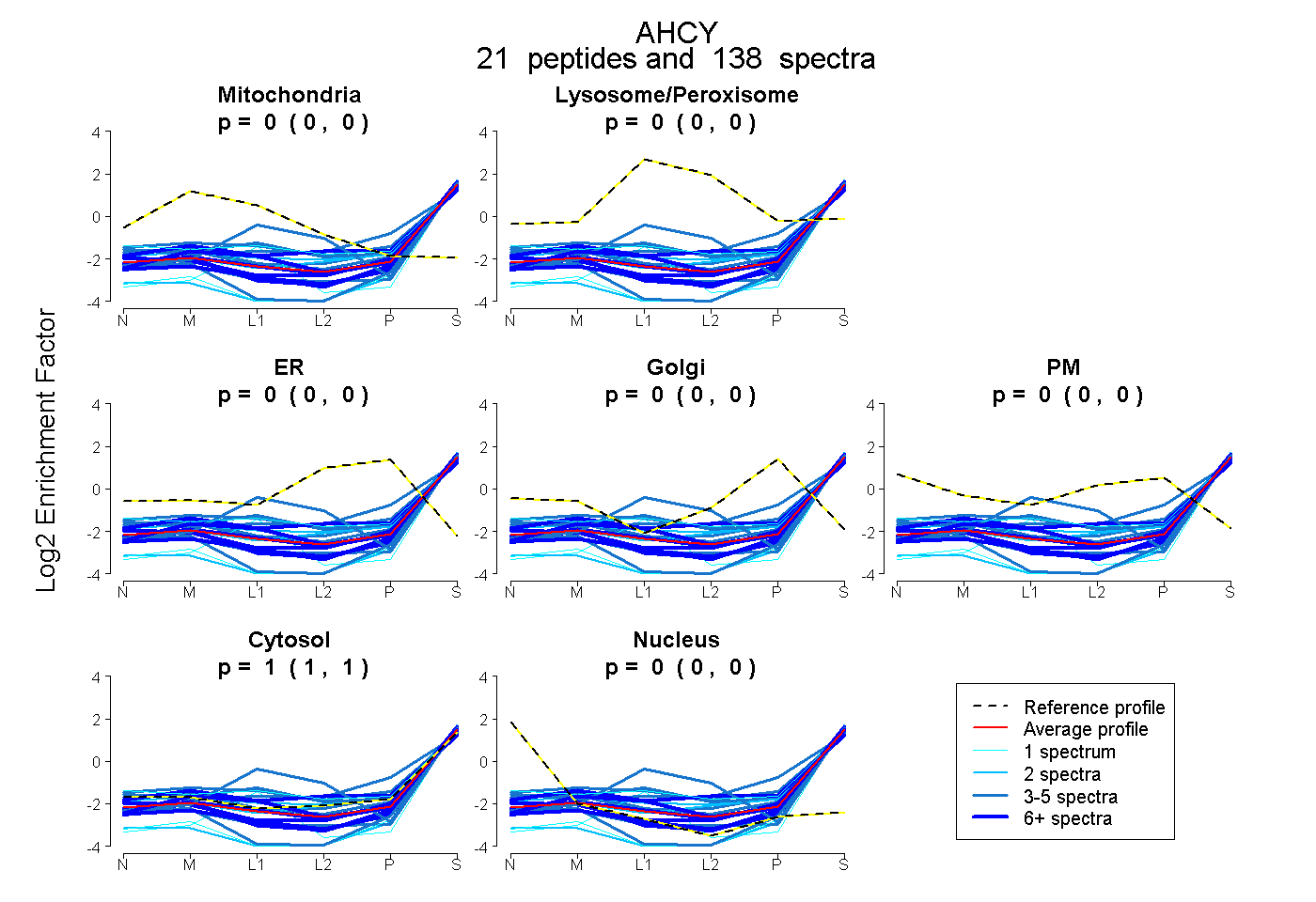 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
353 spectra |
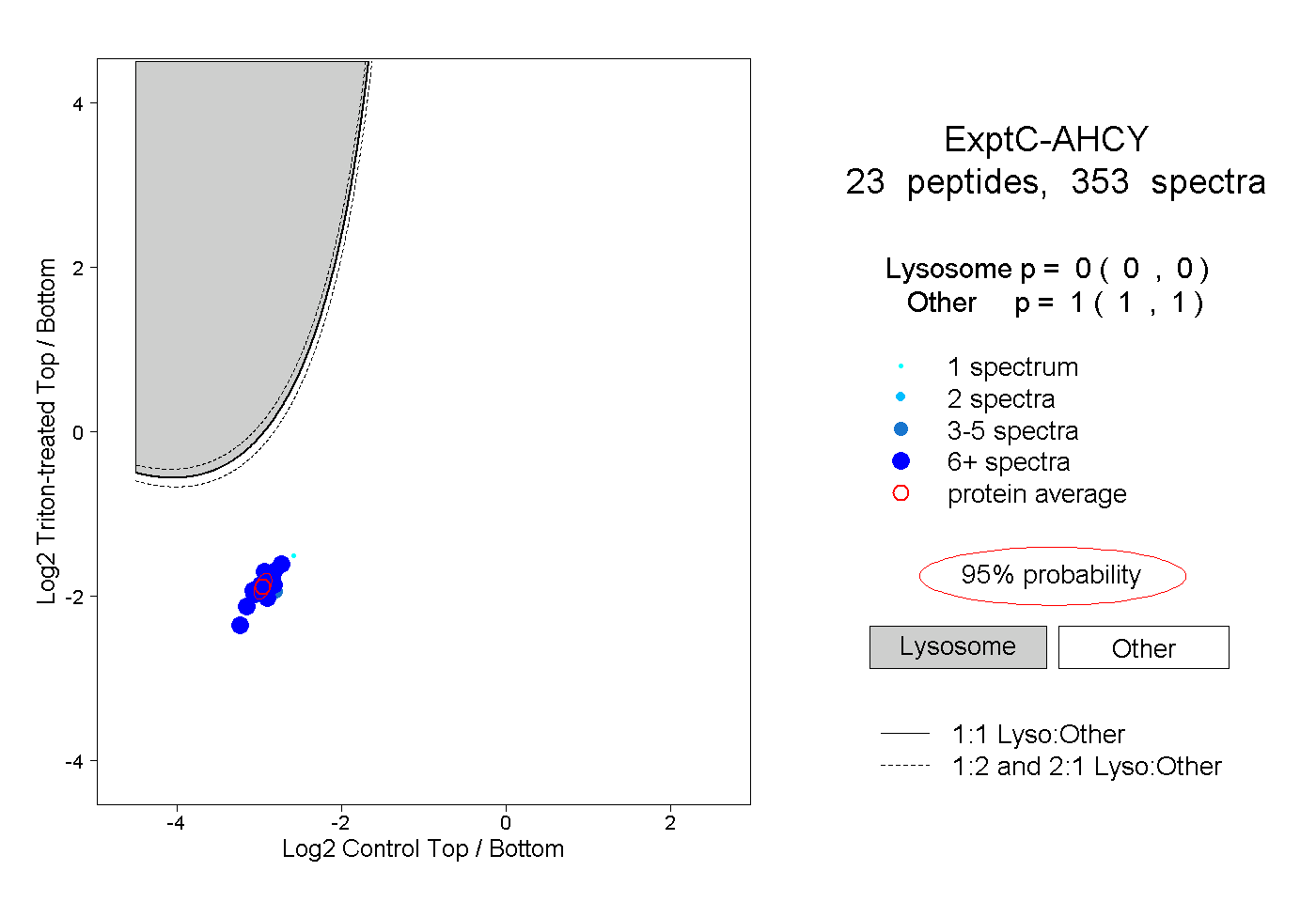 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
15 spectra |
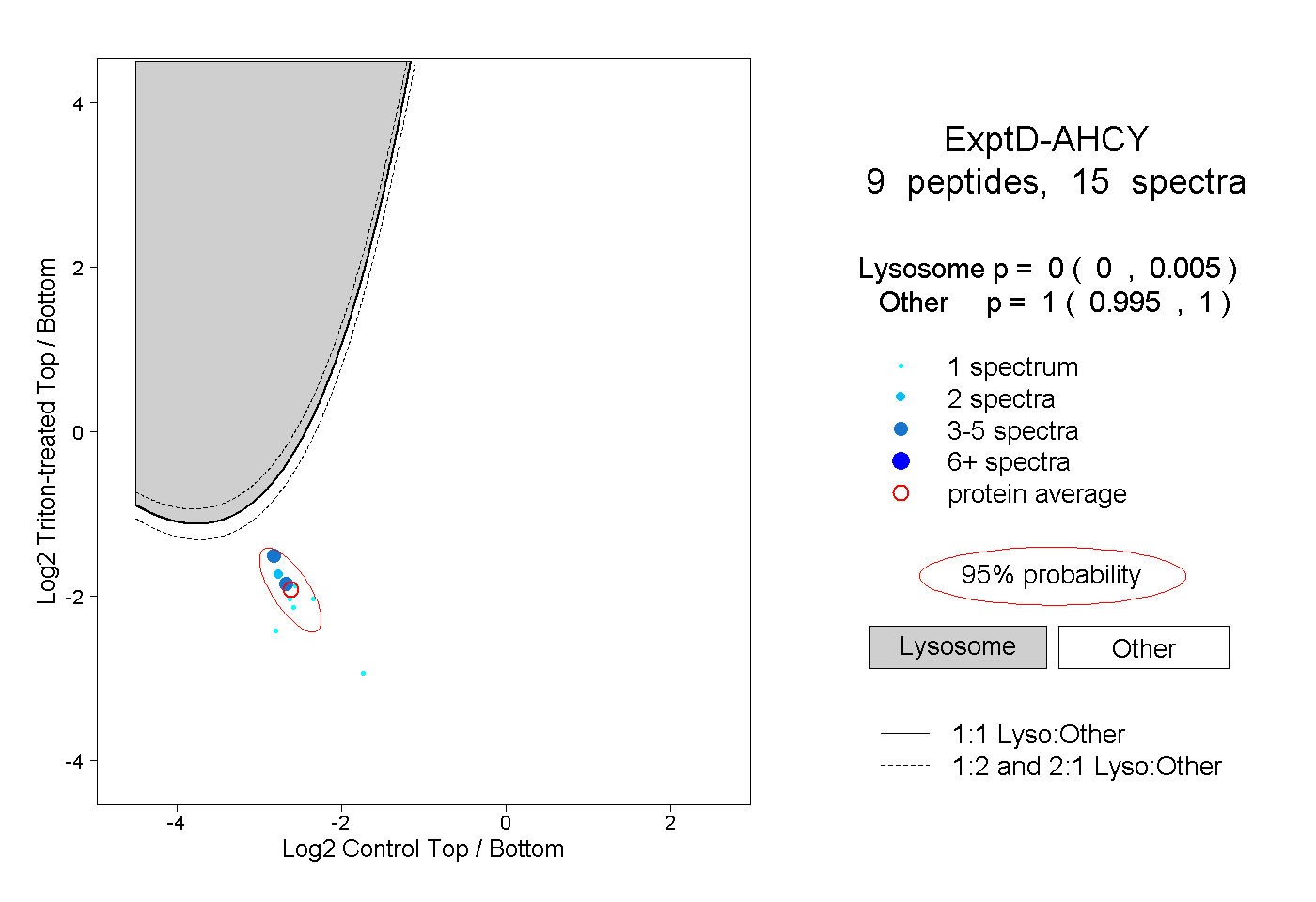 |
0.000 0.000 | 0.005 |
1.000 0.995 | 1.000 |