peptides
spectra
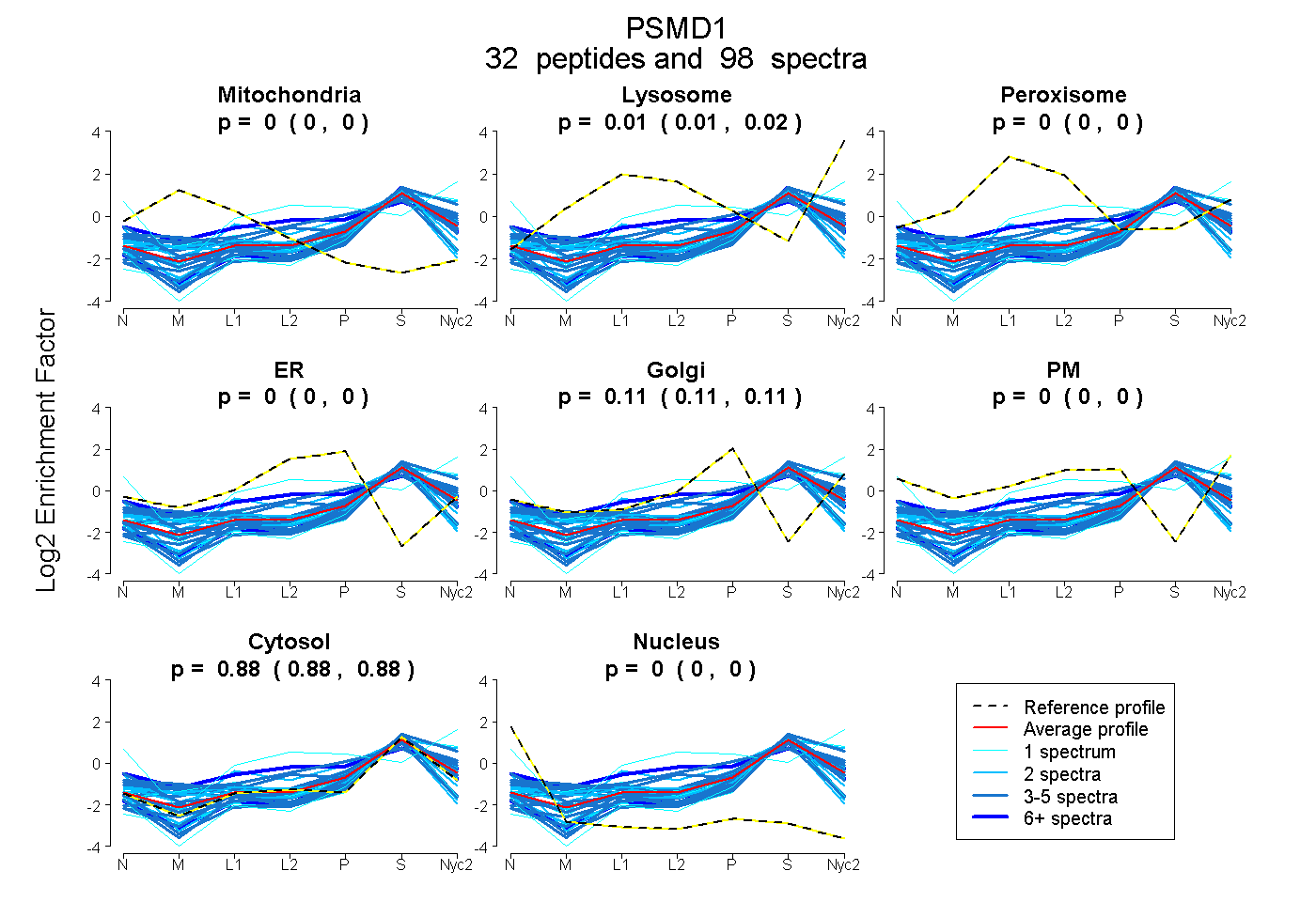
0.000 | 0.000
0.008 | 0.015
0.000 | 0.000
0.000 | 0.000
0.106 | 0.113
0.000 | 0.000
0.875 | 0.880
0.000 | 0.000
peptides
spectra
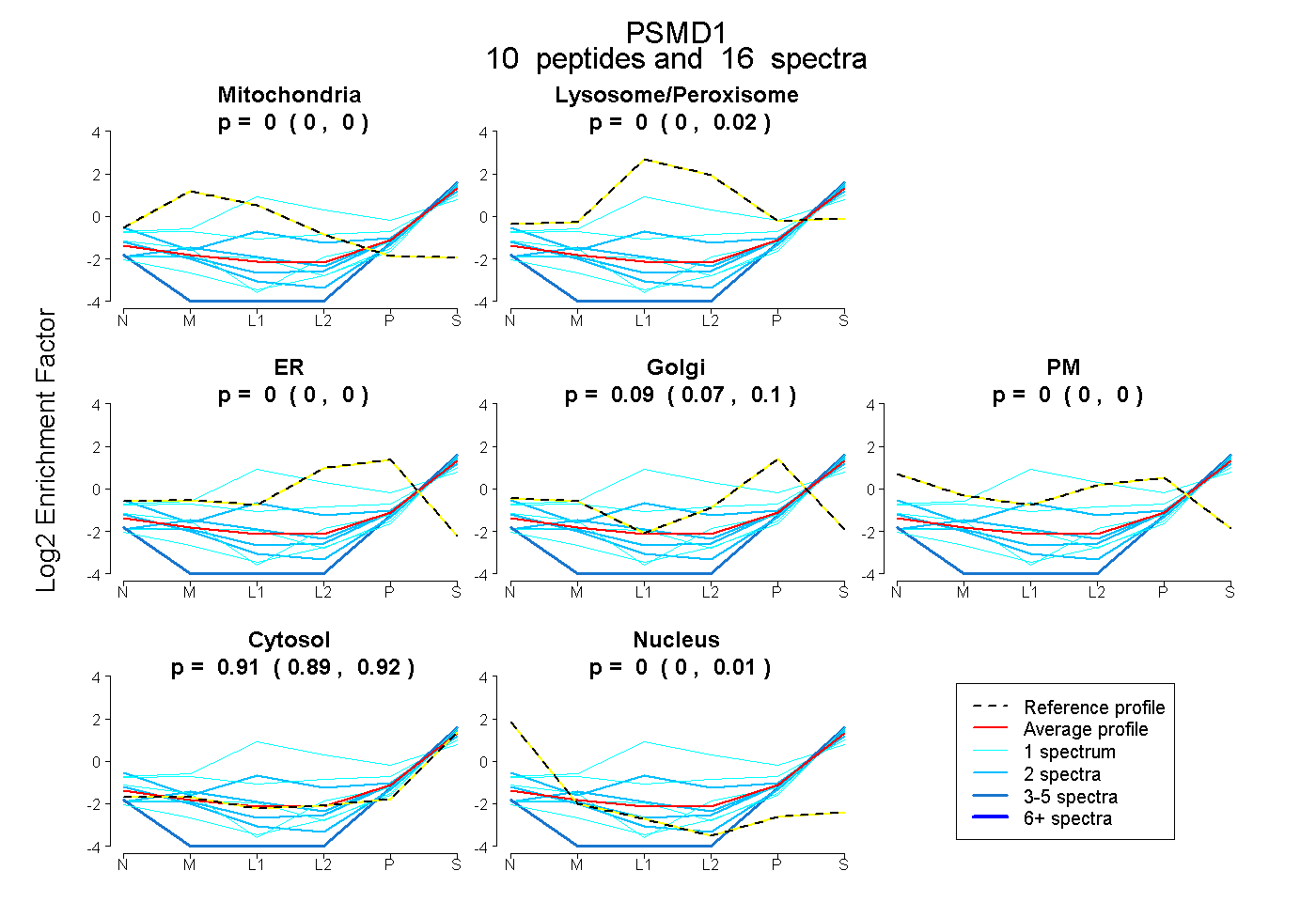
0.000 | 0.000
0.000 | 0.020
0.000 | 0.000
0.072 | 0.104
0.000 | 0.000
0.886 | 0.918
0.000 | 0.006
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
98 spectra |
 |
0.000 0.000 | 0.000 |
0.012 0.008 | 0.015 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.110 0.106 | 0.113 |
0.000 0.000 | 0.000 |
0.878 0.875 | 0.880 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
16 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.020 |
0.000 0.000 | 0.000 |
0.094 0.072 | 0.104 |
0.000 0.000 | 0.000 |
0.906 0.886 | 0.918 |
0.000 0.000 | 0.006 |
| 1 spectrum, TPEQCPSVVSLLSESYNPHVR | 0.000 | 0.000 | 0.000 | 0.091 | 0.000 | 0.879 | 0.031 | |||
| 2 spectra, EFALHK | 0.000 | 0.005 | 0.000 | 0.067 | 0.000 | 0.928 | 0.000 | |||
| 2 spectra, CIDHYTK | 0.000 | 0.285 | 0.000 | 0.000 | 0.000 | 0.644 | 0.071 | |||
| 1 spectrum, VLSMTETCR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, LEGIVNK | 0.000 | 0.622 | 0.000 | 0.046 | 0.000 | 0.331 | 0.000 | |||
| 1 spectrum, FTATASLGVIHK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 2 spectra, QDVYDLLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.883 | 0.117 | |||
| 2 spectra, DNLEWLAR | 0.000 | 0.000 | 0.000 | 0.034 | 0.000 | 0.966 | 0.000 | |||
| 1 spectrum, LLHVAVSDVNDDVR | 0.000 | 0.219 | 0.000 | 0.020 | 0.145 | 0.616 | 0.000 | |||
| 3 spectra, QAIGIALETR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.915 | 0.085 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
53 spectra |
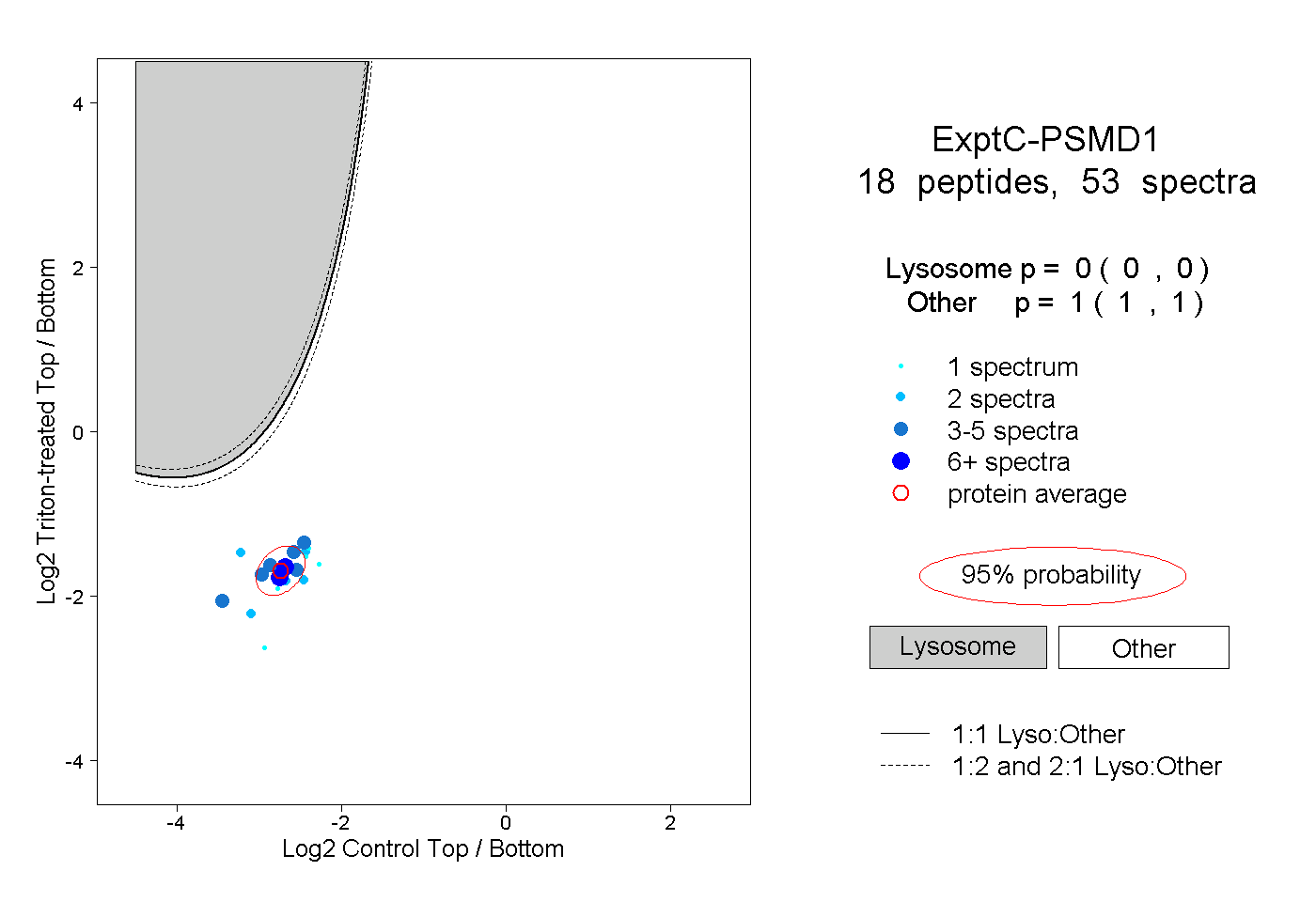 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
8 spectra |
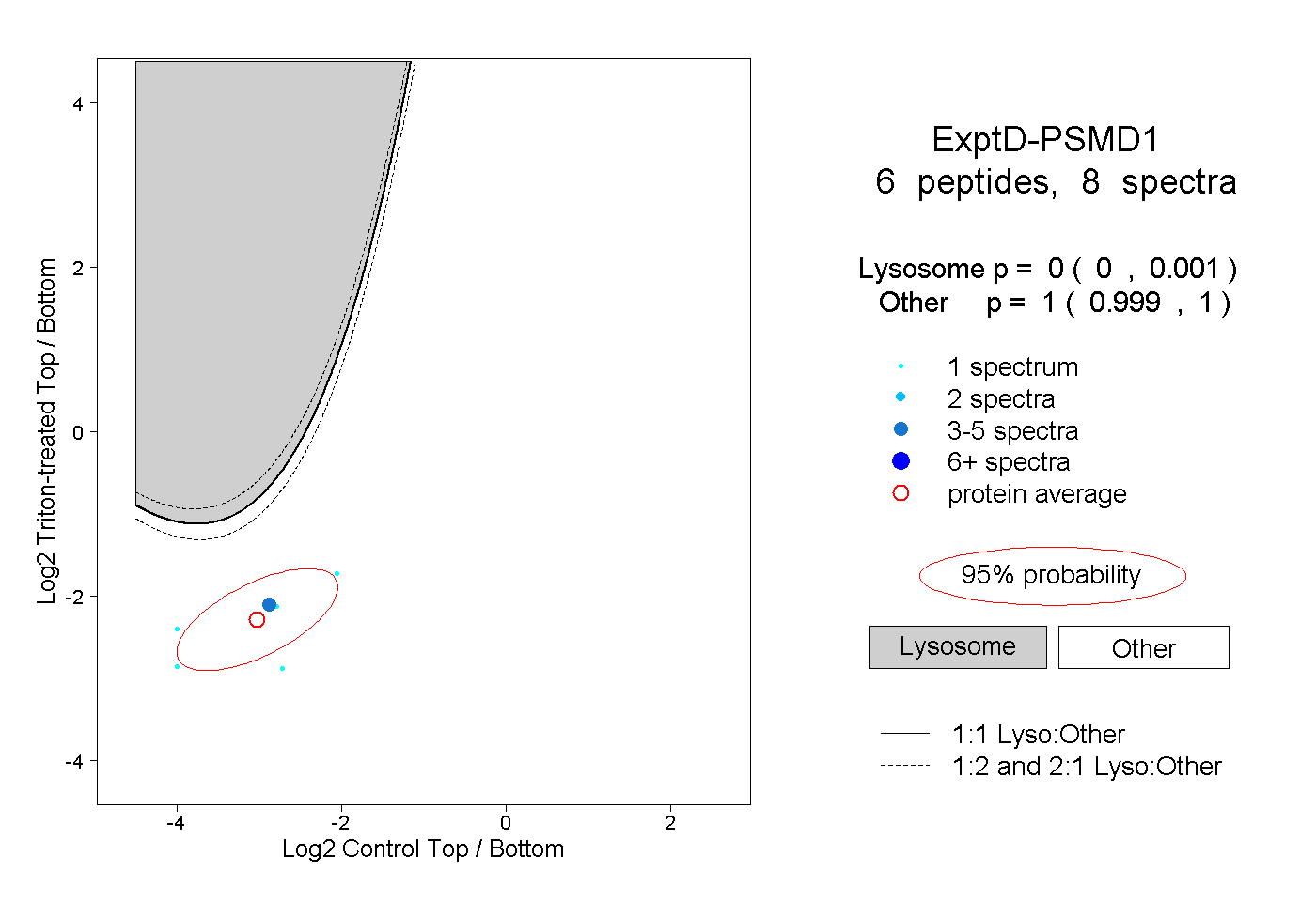 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |