peptides
spectra
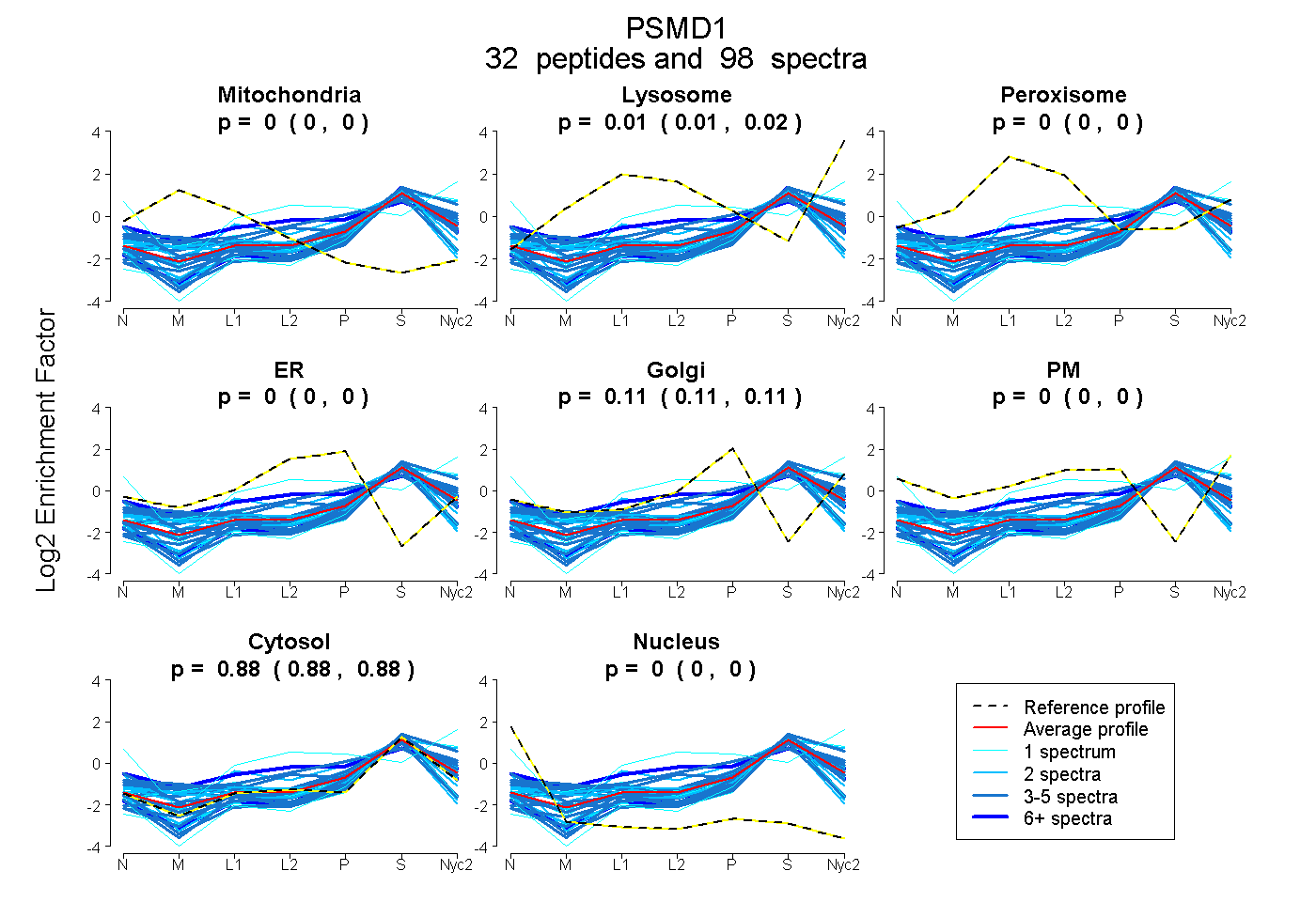
0.000 | 0.000
0.008 | 0.015
0.000 | 0.000
0.000 | 0.000
0.106 | 0.113
0.000 | 0.000
0.875 | 0.880
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
98 spectra |
 |
0.000 0.000 | 0.000 |
0.012 0.008 | 0.015 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.110 0.106 | 0.113 |
0.000 0.000 | 0.000 |
0.878 0.875 | 0.880 |
0.000 0.000 | 0.000 |
| 5 spectra, ATNWAK | 0.035 | 0.045 | 0.000 | 0.000 | 0.072 | 0.000 | 0.848 | 0.000 | ||
| 3 spectra, QFAALVASK | 0.000 | 0.000 | 0.093 | 0.122 | 0.141 | 0.000 | 0.644 | 0.000 | ||
| 1 spectrum, HDDVMAK | 0.000 | 0.027 | 0.000 | 0.000 | 0.133 | 0.000 | 0.840 | 0.000 | ||
| 2 spectra, TPEQCPSVVSLLSESYNPHVR | 0.060 | 0.000 | 0.020 | 0.044 | 0.000 | 0.000 | 0.875 | 0.000 | ||
| 2 spectra, EFALHK | 0.000 | 0.000 | 0.000 | 0.000 | 0.024 | 0.000 | 0.976 | 0.000 | ||
| 4 spectra, VMPAQLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 9 spectra, HGGSLGLGLAAMGTAR | 0.000 | 0.000 | 0.187 | 0.061 | 0.073 | 0.087 | 0.593 | 0.000 | ||
| 7 spectra, AAVESLGFILFR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 5 spectra, LEGIVNK | 0.023 | 0.113 | 0.000 | 0.000 | 0.119 | 0.000 | 0.745 | 0.000 | ||
| 3 spectra, NAQAIEDMVGYAQETQHEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.002 | 0.000 | 0.998 | 0.000 | ||
| 1 spectrum, DTSEDIEELVEPVAAHGPK | 0.000 | 0.001 | 0.000 | 0.000 | 0.106 | 0.000 | 0.893 | 0.000 | ||
| 1 spectrum, MITSAAGIISLLDEEEPQLK | 0.000 | 0.226 | 0.000 | 0.000 | 0.000 | 0.000 | 0.774 | 0.000 | ||
| 2 spectra, FTATASLGVIHK | 0.000 | 0.240 | 0.000 | 0.000 | 0.038 | 0.000 | 0.721 | 0.000 | ||
| 5 spectra, DNLEWLAR | 0.028 | 0.117 | 0.000 | 0.000 | 0.001 | 0.000 | 0.853 | 0.000 | ||
| 2 spectra, CLDDHK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.951 | 0.049 | ||
| 3 spectra, QAIGIALETR | 0.000 | 0.012 | 0.000 | 0.000 | 0.043 | 0.000 | 0.945 | 0.000 | ||
| 1 spectrum, MEVDEAEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 5 spectra, LCMSLMQNK | 0.163 | 0.000 | 0.000 | 0.000 | 0.050 | 0.000 | 0.787 | 0.000 | ||
| 2 spectra, GLAVGIALVMYGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.114 | 0.000 | 0.831 | 0.056 | ||
| 3 spectra, QCVENADLPEGEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.894 | 0.106 | ||
| 4 spectra, MEEADALIESLCR | 0.000 | 0.000 | 0.000 | 0.000 | 0.126 | 0.000 | 0.874 | 0.000 | ||
| 1 spectrum, SNCKPSTFAYPAPLEVPK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.924 | 0.076 | ||
| 2 spectra, CIDHYTK | 0.139 | 0.000 | 0.000 | 0.045 | 0.000 | 0.000 | 0.816 | 0.000 | ||
| 1 spectrum, TILESNDVPGMLAYSLK | 0.000 | 0.068 | 0.000 | 0.000 | 0.000 | 0.549 | 0.383 | 0.000 | ||
| 5 spectra, VLSMTETCR | 0.000 | 0.000 | 0.000 | 0.000 | 0.102 | 0.089 | 0.795 | 0.014 | ||
| 2 spectra, EALQLMATYLPK | 0.000 | 0.122 | 0.000 | 0.000 | 0.122 | 0.000 | 0.756 | 0.000 | ||
| 2 spectra, LDVFEK | 0.000 | 0.063 | 0.000 | 0.000 | 0.043 | 0.000 | 0.894 | 0.000 | ||
| 2 spectra, LLHVAVSDVNDDVR | 0.034 | 0.042 | 0.000 | 0.000 | 0.139 | 0.000 | 0.786 | 0.000 | ||
| 3 spectra, IEVLYEDEGFR | 0.001 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.999 | 0.000 | ||
| 2 spectra, TAGAVAGK | 0.048 | 0.008 | 0.000 | 0.000 | 0.097 | 0.000 | 0.847 | 0.000 | ||
| 4 spectra, QDVYDLLK | 0.000 | 0.056 | 0.000 | 0.000 | 0.000 | 0.000 | 0.944 | 0.000 | ||
| 4 spectra, NNNTDLMILK | 0.023 | 0.114 | 0.000 | 0.000 | 0.000 | 0.148 | 0.715 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
16 spectra |
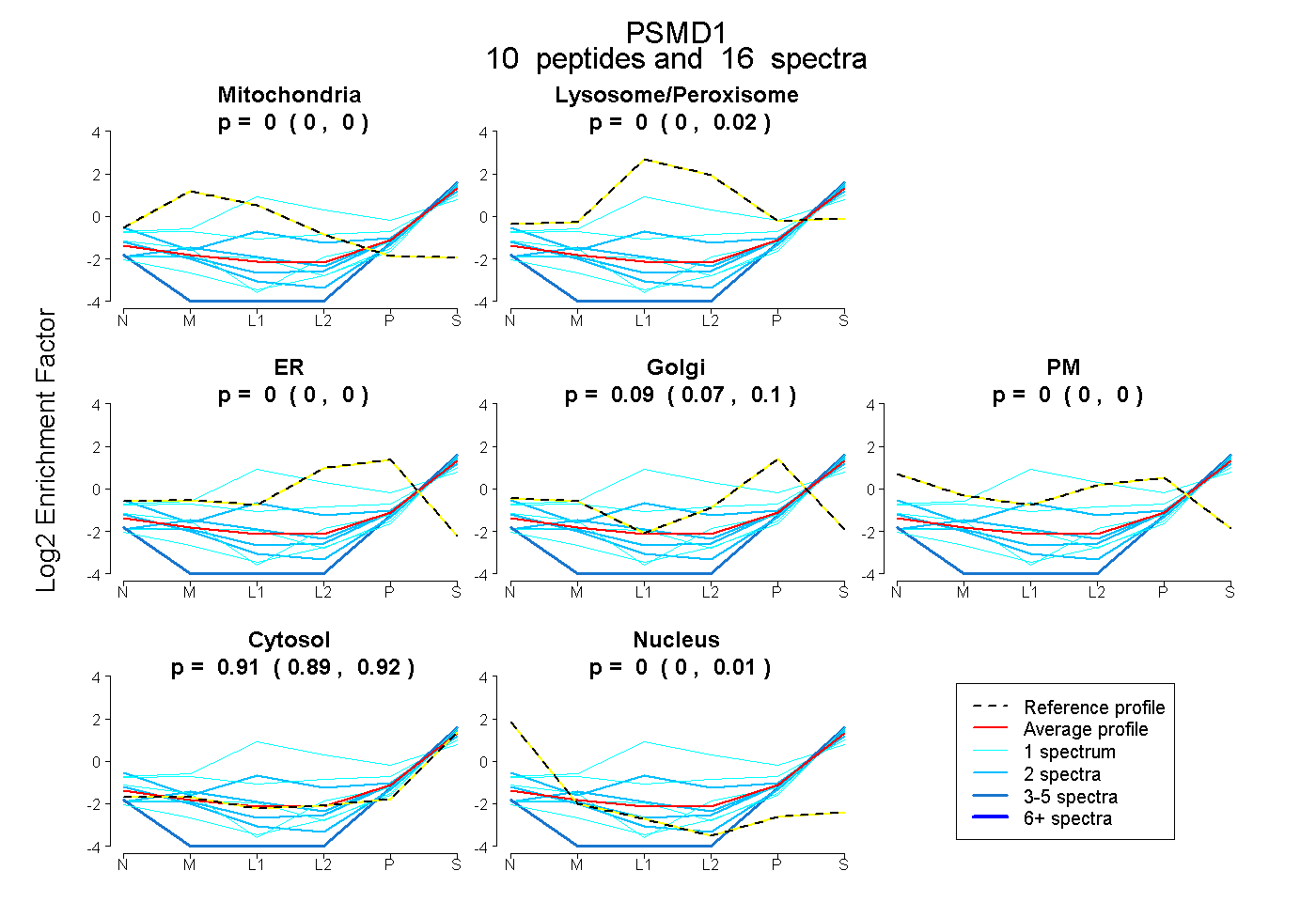 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.020 |
0.000 0.000 | 0.000 |
0.094 0.072 | 0.104 |
0.000 0.000 | 0.000 |
0.906 0.886 | 0.918 |
0.000 0.000 | 0.006 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
53 spectra |
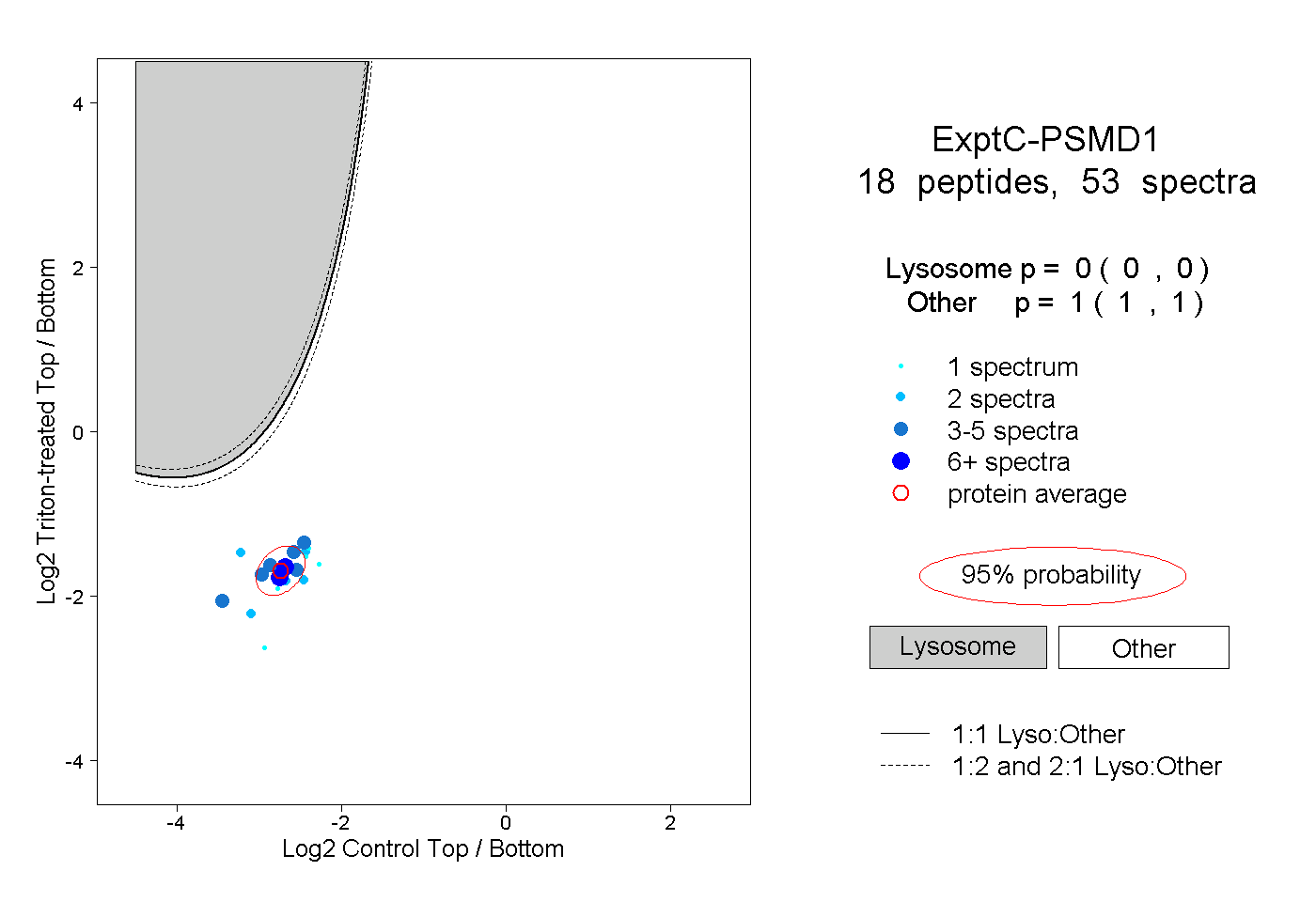 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
8 spectra |
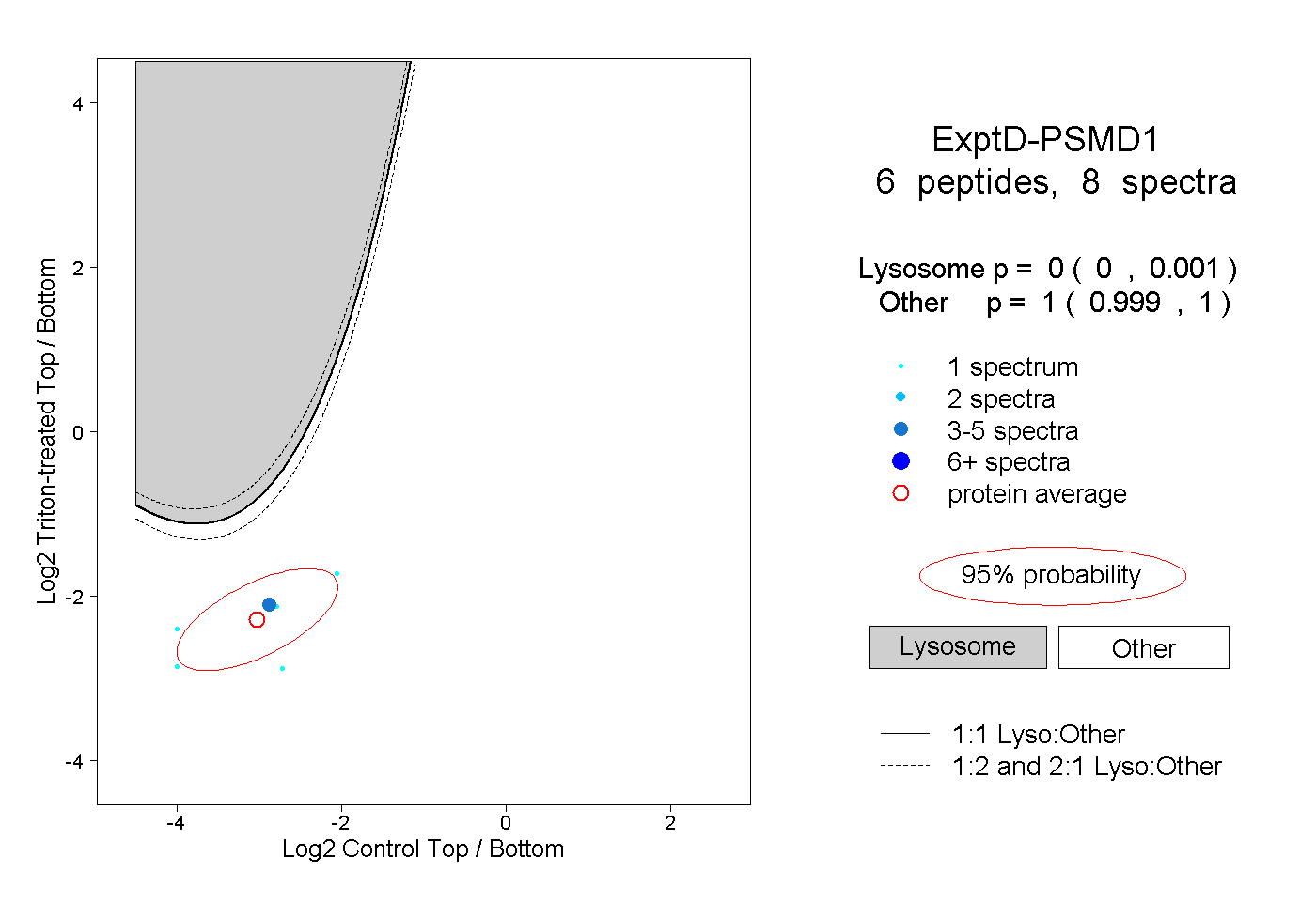 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |