peptides
spectra
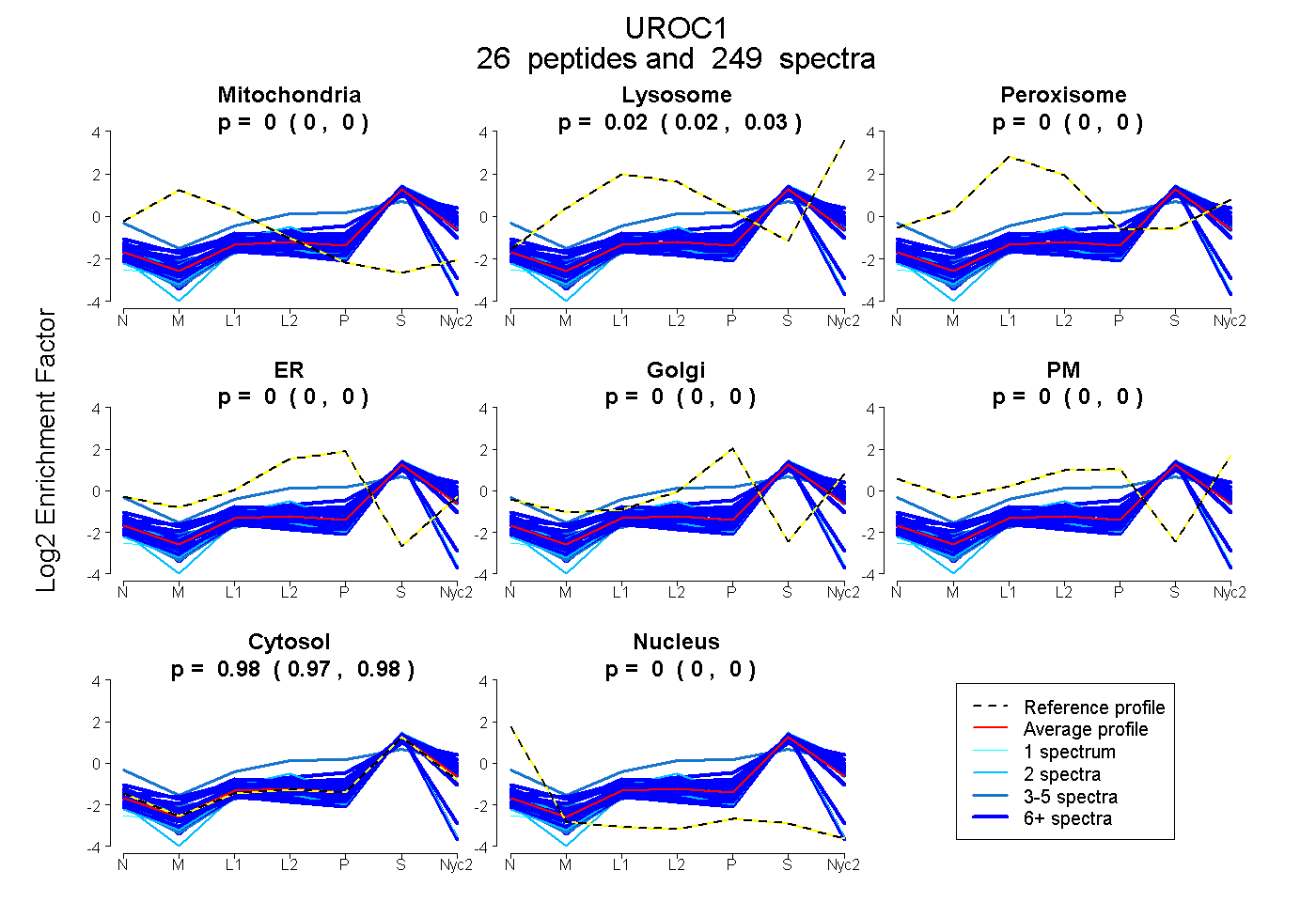
0.000 | 0.000
0.021 | 0.026
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.974 | 0.978
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
249 spectra |
 |
0.000 0.000 | 0.000 |
0.024 0.021 | 0.026 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.976 0.974 | 0.978 |
0.000 0.000 | 0.000 |
| 14 spectra, QFGHIYMYR | 0.000 | 0.206 | 0.000 | 0.000 | 0.068 | 0.000 | 0.726 | 0.000 | ||
| 17 spectra, LLALEFAQELR | 0.000 | 0.057 | 0.000 | 0.000 | 0.000 | 0.000 | 0.943 | 0.000 | ||
| 4 spectra, EVLSLGYHGNVVDLWER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, AGADVEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 10 spectra, HISAINR | 0.021 | 0.047 | 0.033 | 0.000 | 0.000 | 0.079 | 0.819 | 0.000 | ||
| 3 spectra, CWSGNPK | 0.000 | 0.037 | 0.000 | 0.000 | 0.000 | 0.000 | 0.963 | 0.000 | ||
| 15 spectra, MMLSWDVSNGVAR | 0.000 | 0.082 | 0.000 | 0.000 | 0.000 | 0.000 | 0.918 | 0.000 | ||
| 7 spectra, LQYMDNIR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 40 spectra, HQLVVGSQAR | 0.000 | 0.038 | 0.000 | 0.000 | 0.000 | 0.058 | 0.904 | 0.000 | ||
| 4 spectra, ILYSDQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 14 spectra, TPDLSPEEEQLALR | 0.000 | 0.077 | 0.000 | 0.000 | 0.000 | 0.000 | 0.923 | 0.000 | ||
| 19 spectra, AAVIVGCIGVIAEVDK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.818 | 0.182 | ||
| 5 spectra, DHHDVSGTDSPFR | 0.000 | 0.000 | 0.136 | 0.063 | 0.000 | 0.244 | 0.557 | 0.000 | ||
| 8 spectra, FCPSIEMR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 18 spectra, WAGVPHAPVR | 0.000 | 0.075 | 0.000 | 0.000 | 0.059 | 0.000 | 0.866 | 0.000 | ||
| 2 spectra, SSLQELCSGLPLRPLPENR | 0.000 | 0.038 | 0.069 | 0.000 | 0.000 | 0.000 | 0.894 | 0.000 | ||
| 4 spectra, APVVLSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 6 spectra, YLGIEDLAGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 6 spectra, HQQGWLMEVTDSLDHCIAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.891 | 0.109 | ||
| 6 spectra, VAIAVAINQAIASGK | 0.000 | 0.135 | 0.000 | 0.000 | 0.000 | 0.000 | 0.865 | 0.000 | ||
| 12 spectra, AYPIEQYPCR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 13 spectra, VFVTSGLGGMSGAQAK | 0.000 | 0.158 | 0.000 | 0.000 | 0.000 | 0.000 | 0.842 | 0.000 | ||
| 8 spectra, AIADGVK | 0.000 | 0.040 | 0.000 | 0.000 | 0.000 | 0.000 | 0.960 | 0.000 | ||
| 1 spectrum, AYEIICQTMQENSGLVVTLPHEVADEQVLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.898 | 0.102 | ||
| 9 spectra, YFPPDVQK | 0.000 | 0.024 | 0.000 | 0.000 | 0.000 | 0.000 | 0.976 | 0.000 | ||
| 2 spectra, LVITNGMVIPNYSSR | 0.000 | 0.005 | 0.000 | 0.000 | 0.000 | 0.000 | 0.995 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
93 spectra |
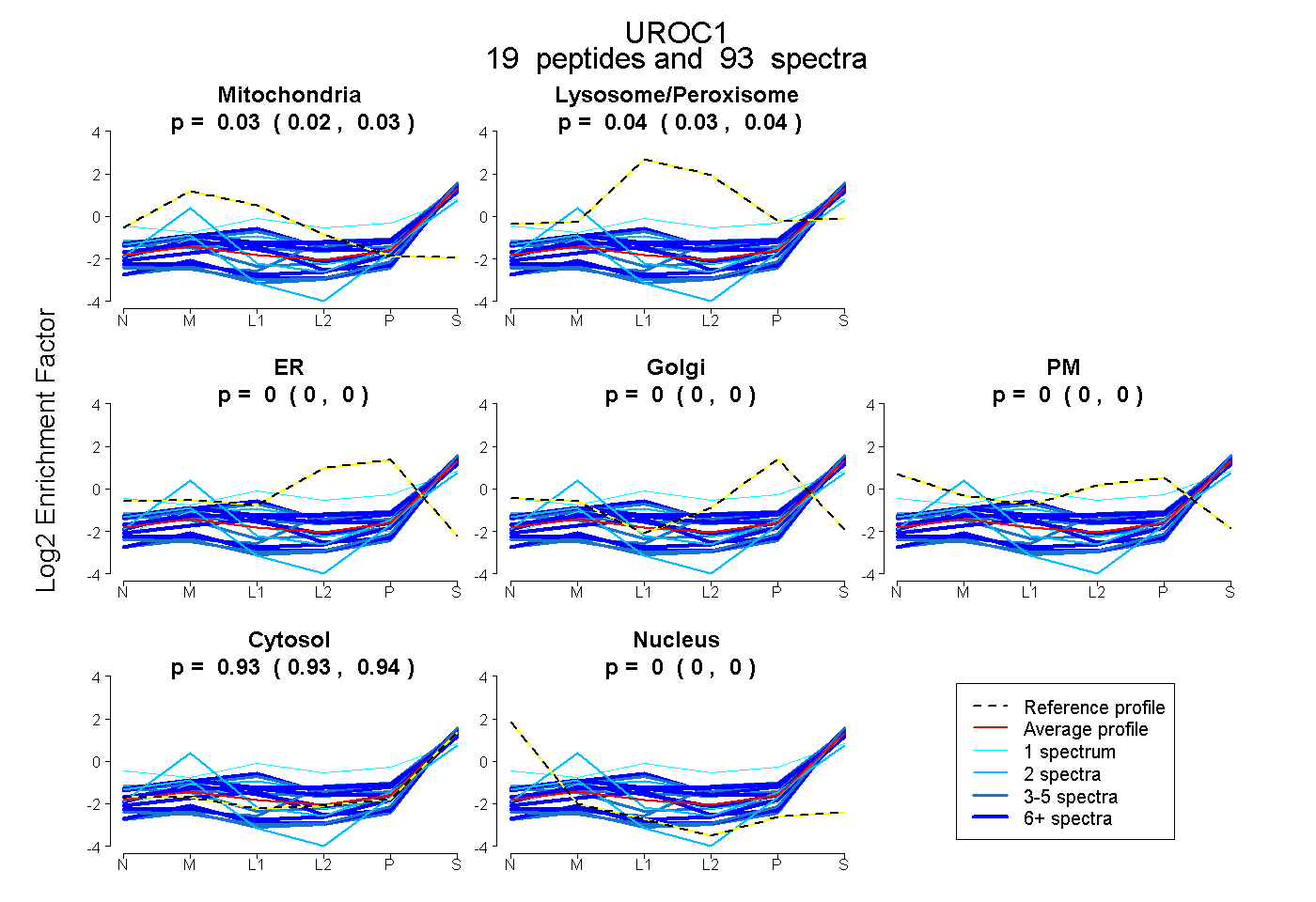 |
0.028 0.022 | 0.034 |
0.037 0.030 | 0.044 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.934 0.929 | 0.939 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
300 spectra |
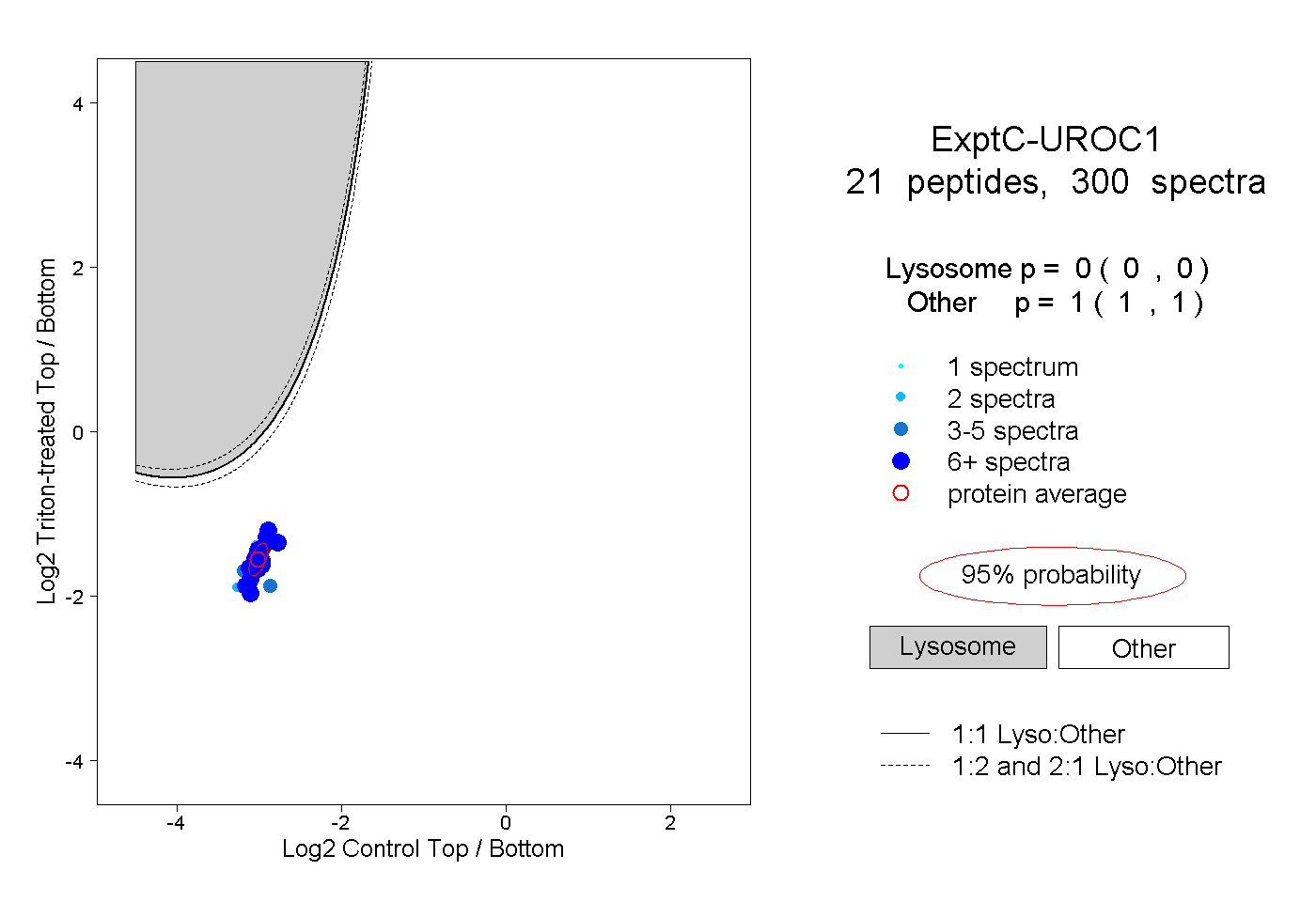 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
28 spectra |
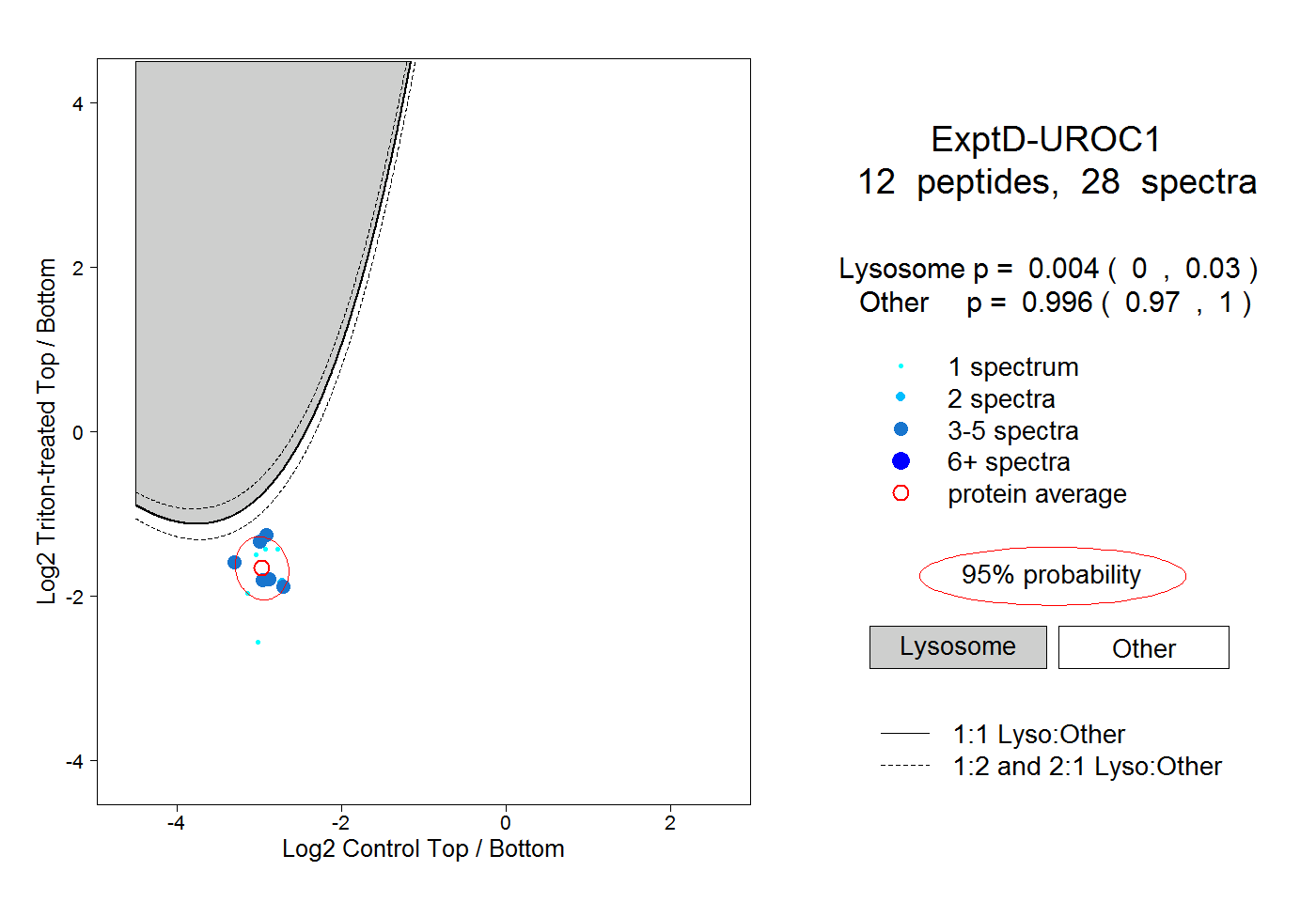 |
0.004 0.000 | 0.030 |
0.996 0.970 | 1.000 |