peptides
spectra
0.000 | 0.000
0.087 | 0.116
0.000 | 0.000
0.005 | 0.043
0.000 | 0.000
0.845 | 0.893
0.000 | 0.000
0.000 | 0.000
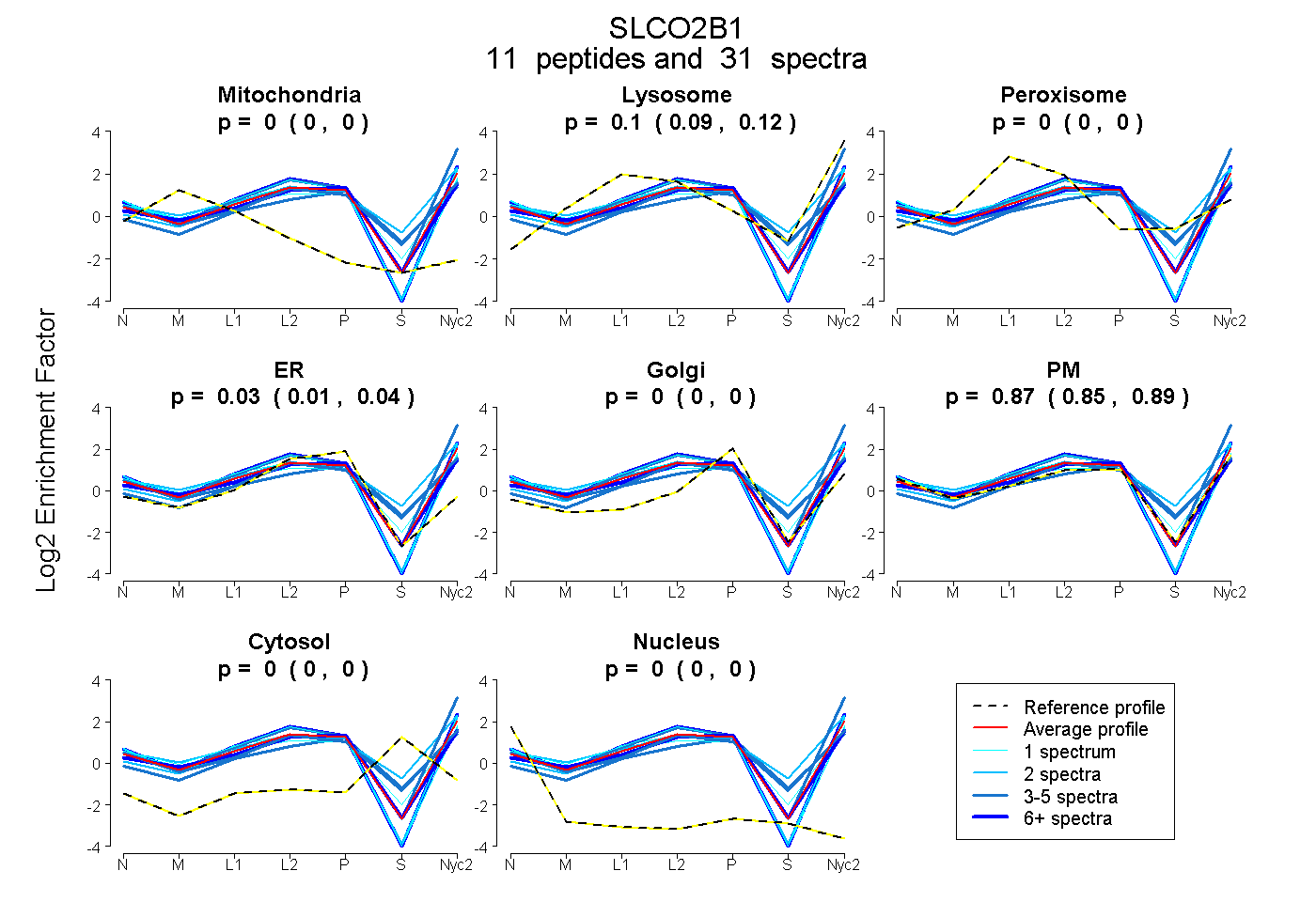
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
31 spectra |
 |
0.000 0.000 | 0.000 |
0.102 0.087 | 0.116 |
0.000 0.000 | 0.000 |
0.026 0.005 | 0.043 |
0.000 0.000 | 0.000 |
0.872 0.845 | 0.893 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 2 spectra, LYVDIDR | 0.000 | 0.032 | 0.000 | 0.000 | 0.000 | 0.968 | 0.000 | 0.000 | ||
| 3 spectra, ATMGAEDIHER | 0.000 | 0.159 | 0.066 | 0.060 | 0.237 | 0.352 | 0.125 | 0.000 | ||
| 1 spectrum, SSDLQEL | 0.000 | 0.000 | 0.117 | 0.000 | 0.000 | 0.883 | 0.000 | 0.000 | ||
| 1 spectrum, VLAGGASIGSK | 0.000 | 0.001 | 0.000 | 0.075 | 0.000 | 0.923 | 0.000 | 0.000 | ||
| 1 spectrum, MPEGGINLTTK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | ||
| 6 spectra, DSHQDAQPR | 0.000 | 0.017 | 0.000 | 0.000 | 0.000 | 0.983 | 0.000 | 0.000 | ||
| 6 spectra, YELHFR | 0.000 | 0.079 | 0.000 | 0.188 | 0.000 | 0.733 | 0.000 | 0.000 | ||
| 2 spectra, GMFQNIK | 0.000 | 0.361 | 0.016 | 0.000 | 0.000 | 0.525 | 0.098 | 0.000 | ||
| 1 spectrum, QAGLPQIAPDLTVVQFIK | 0.000 | 0.000 | 0.000 | 0.071 | 0.000 | 0.929 | 0.000 | 0.000 | ||
| 4 spectra, TLAVGMQFMLLR | 0.000 | 0.271 | 0.000 | 0.000 | 0.000 | 0.729 | 0.000 | 0.000 | ||
| 4 spectra, YYDHDLLR | 0.000 | 0.051 | 0.102 | 0.010 | 0.000 | 0.762 | 0.075 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
9 spectra |
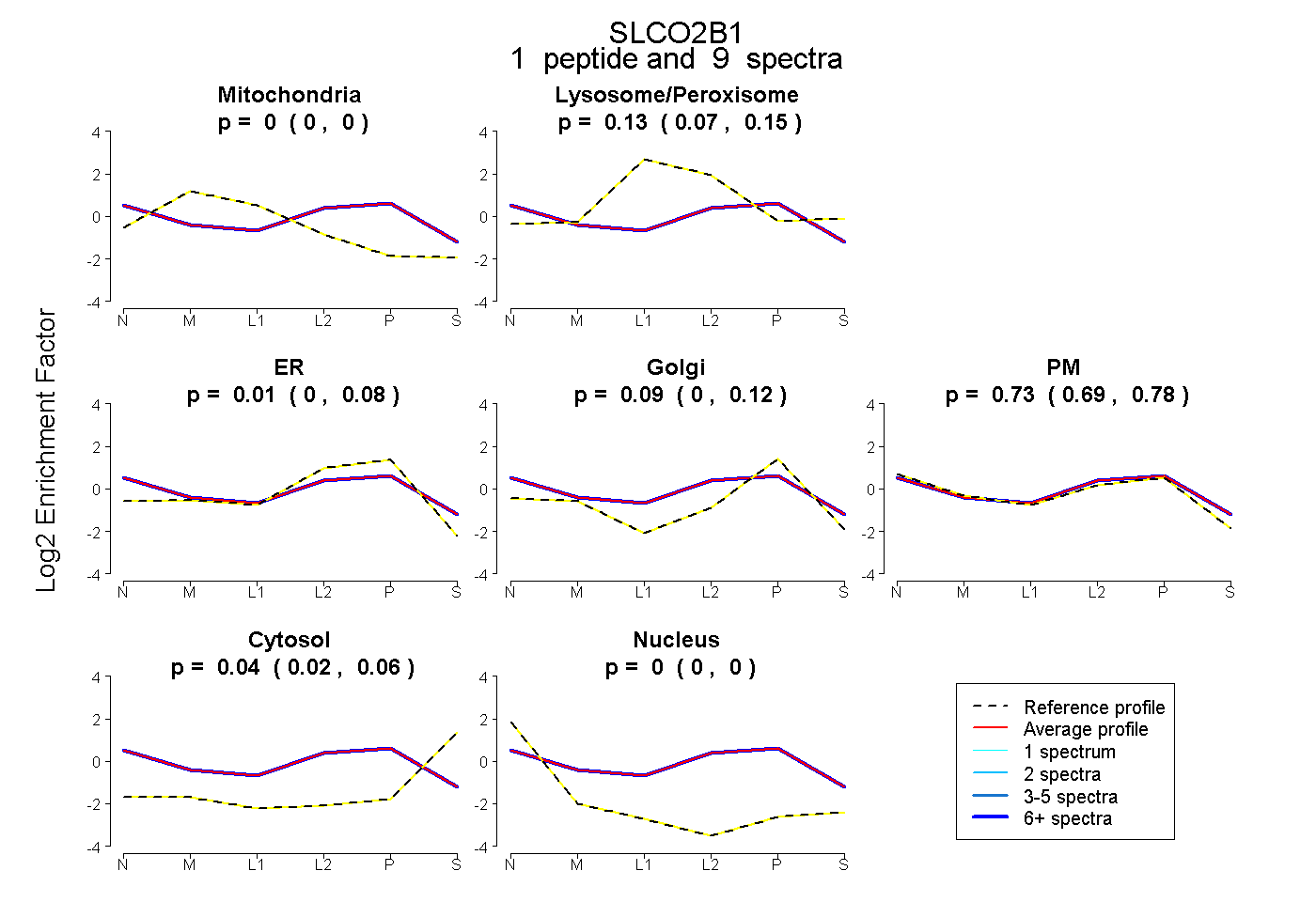 |
0.000 0.000 | 0.000 |
0.126 0.070 | 0.148 |
0.006 0.000 | 0.080 |
0.092 0.004 | 0.117 |
0.733 0.688 | 0.778 |
0.043 0.024 | 0.065 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
51 spectra |
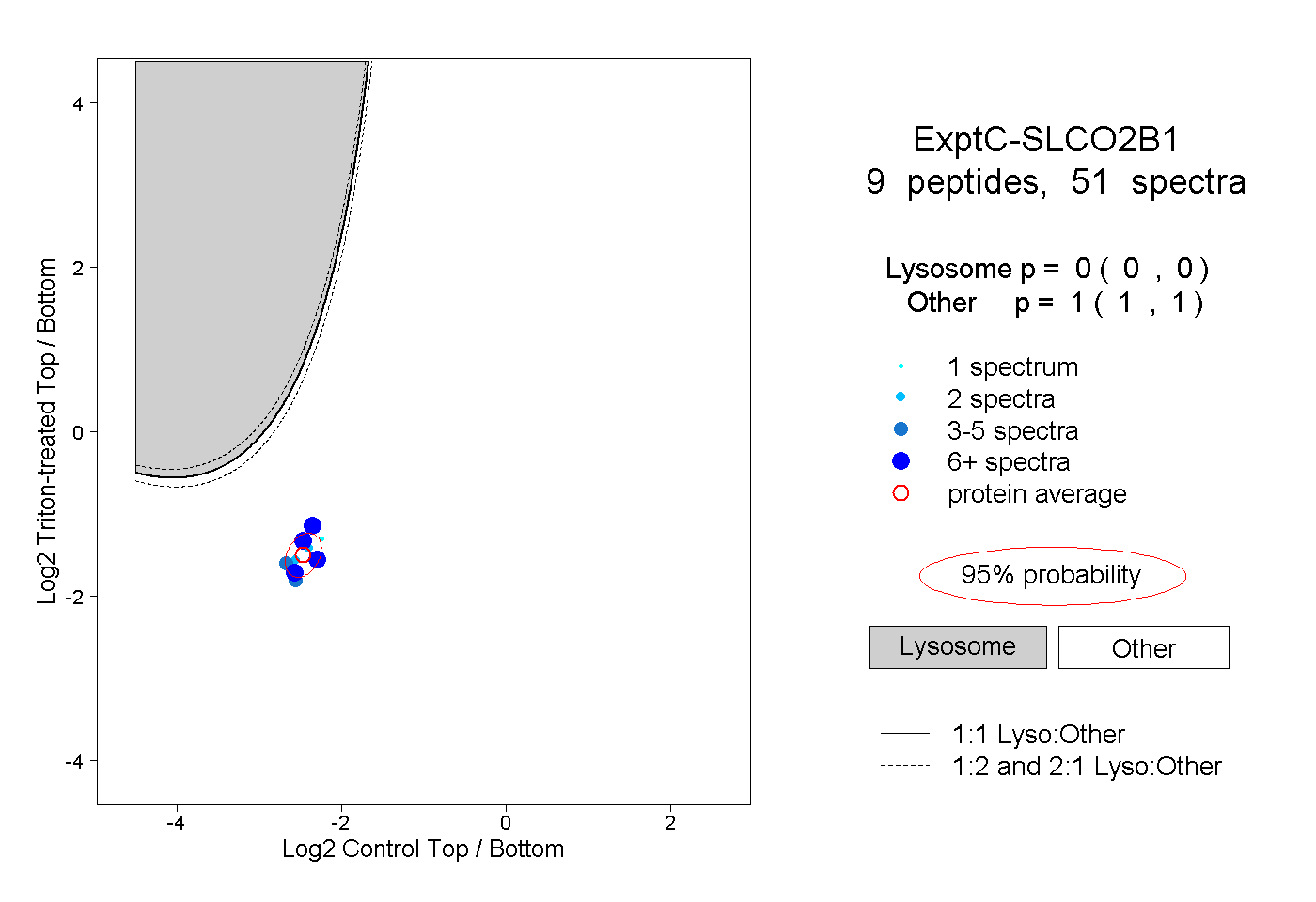 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
4 spectra |
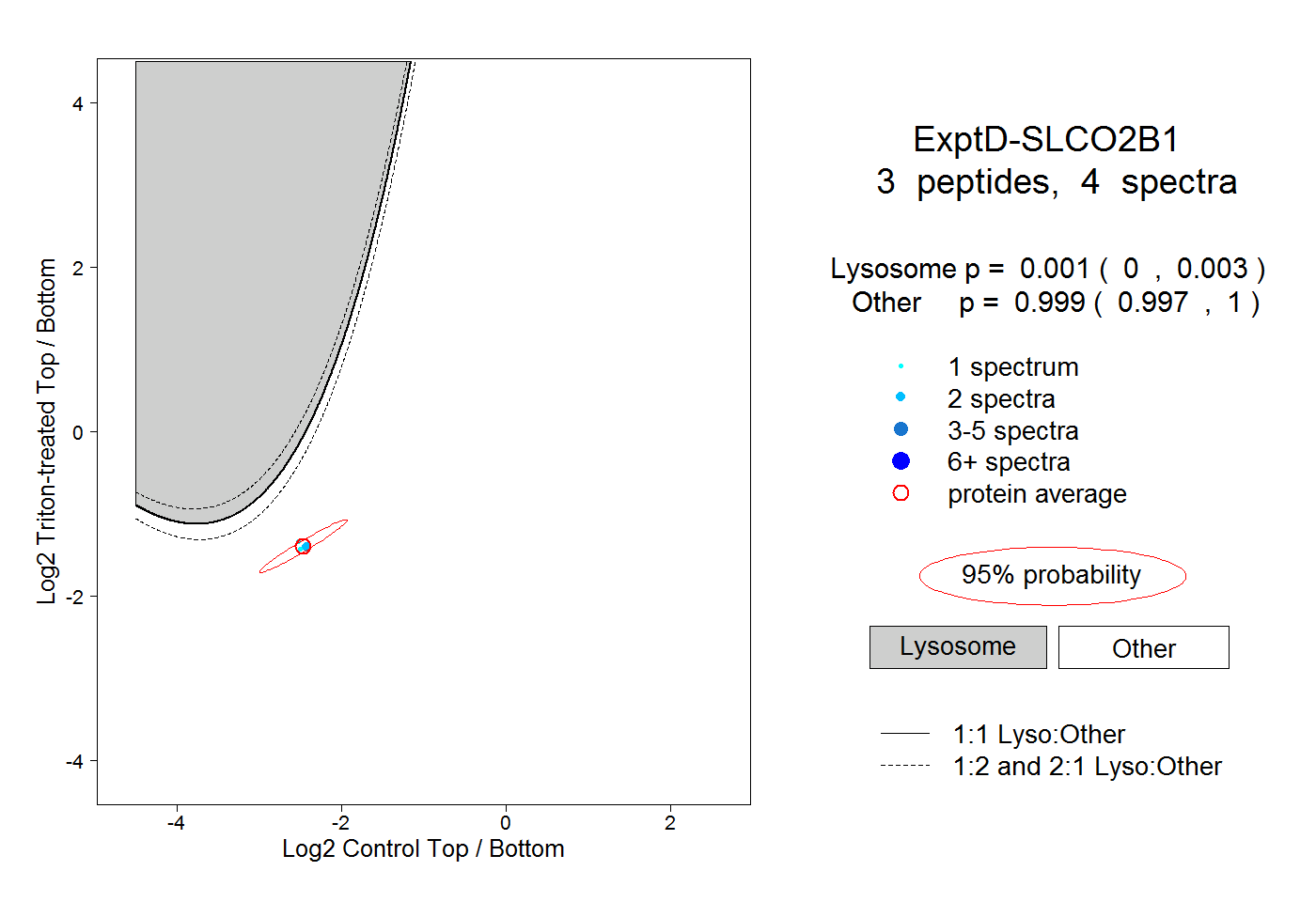 |
0.001 0.000 | 0.003 |
0.999 0.997 | 1.000 |