peptides
spectra
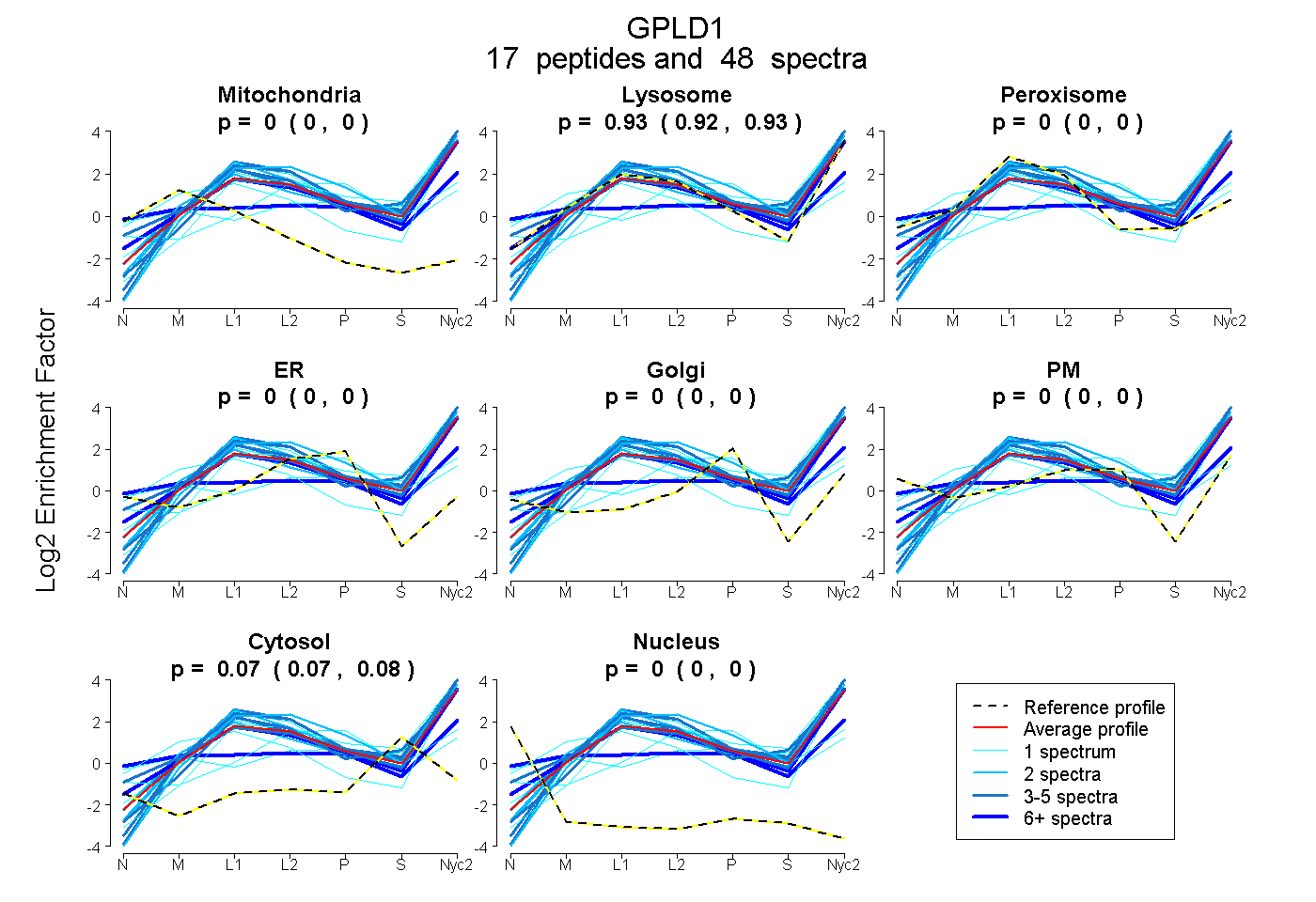
0.000 | 0.000
0.920 | 0.932
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.067 | 0.079
0.000 | 0.000
peptides
spectra
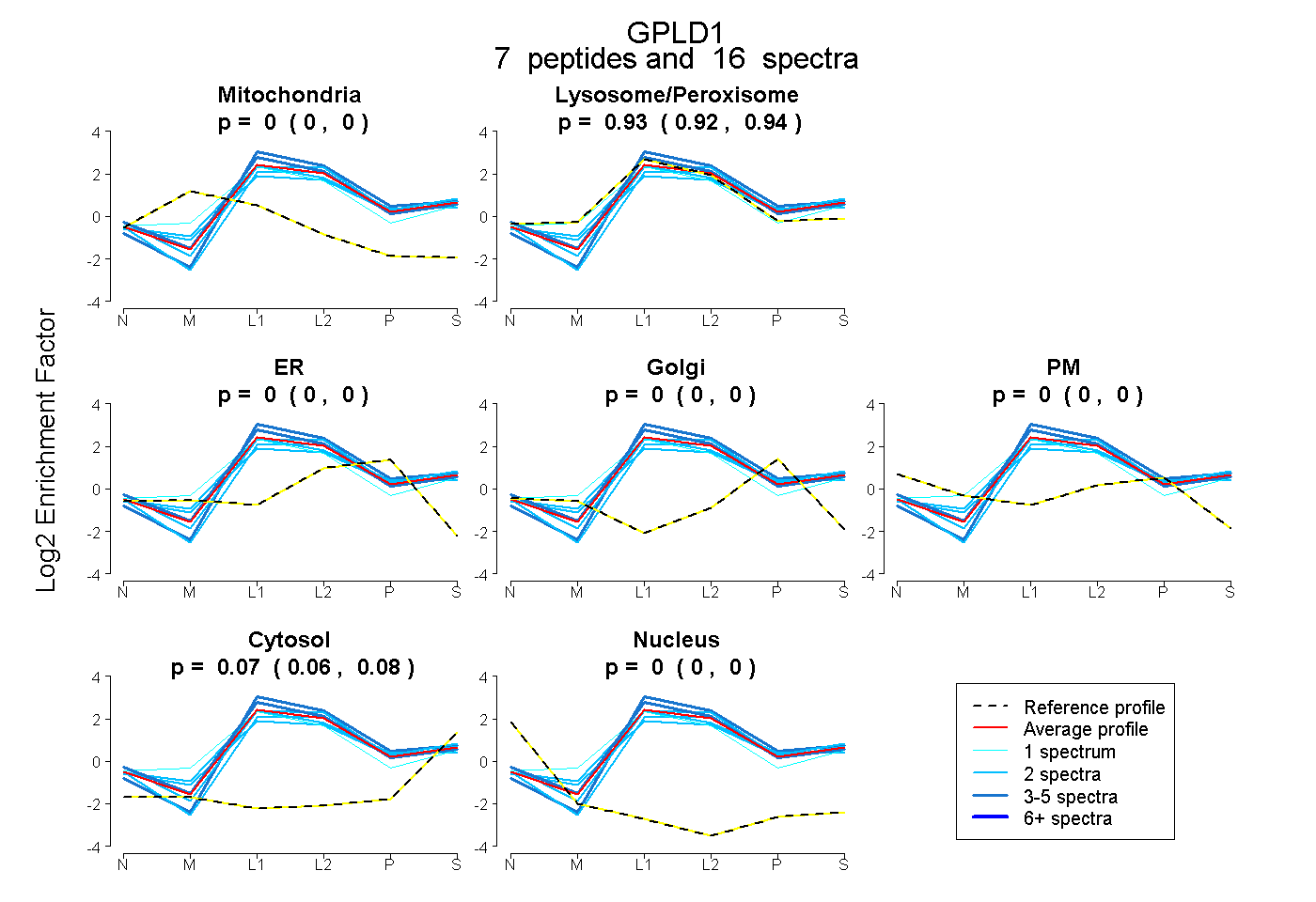
0.000 | 0.000
0.919 | 0.936
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.062 | 0.080
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
48 spectra |
 |
0.000 0.000 | 0.000 |
0.927 0.920 | 0.932 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.073 0.067 | 0.079 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
16 spectra |
 |
0.000 0.000 | 0.000 |
0.928 0.919 | 0.936 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.072 0.062 | 0.080 |
0.000 0.000 | 0.000 |
| 4 spectra, NQVVVAAGR | 0.000 | 0.977 | 0.000 | 0.000 | 0.000 | 0.023 | 0.000 | |||
| 3 spectra, ALQFLQLQDGR | 0.000 | 0.993 | 0.000 | 0.000 | 0.000 | 0.007 | 0.000 | |||
| 1 spectrum, MAFLTMTLHQGGATR | 0.000 | 0.913 | 0.000 | 0.000 | 0.000 | 0.087 | 0.000 | |||
| 2 spectra, IYDNLYGR | 0.000 | 0.926 | 0.012 | 0.000 | 0.000 | 0.062 | 0.000 | |||
| 2 spectra, LGTSLSSGYVR | 0.000 | 0.866 | 0.000 | 0.000 | 0.000 | 0.134 | 0.000 | |||
| 2 spectra, FGSSLVSVR | 0.000 | 0.939 | 0.000 | 0.000 | 0.000 | 0.061 | 0.000 | |||
| 2 spectra, GIVAAFYSHPR | 0.000 | 0.850 | 0.019 | 0.000 | 0.000 | 0.131 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
94 spectra |
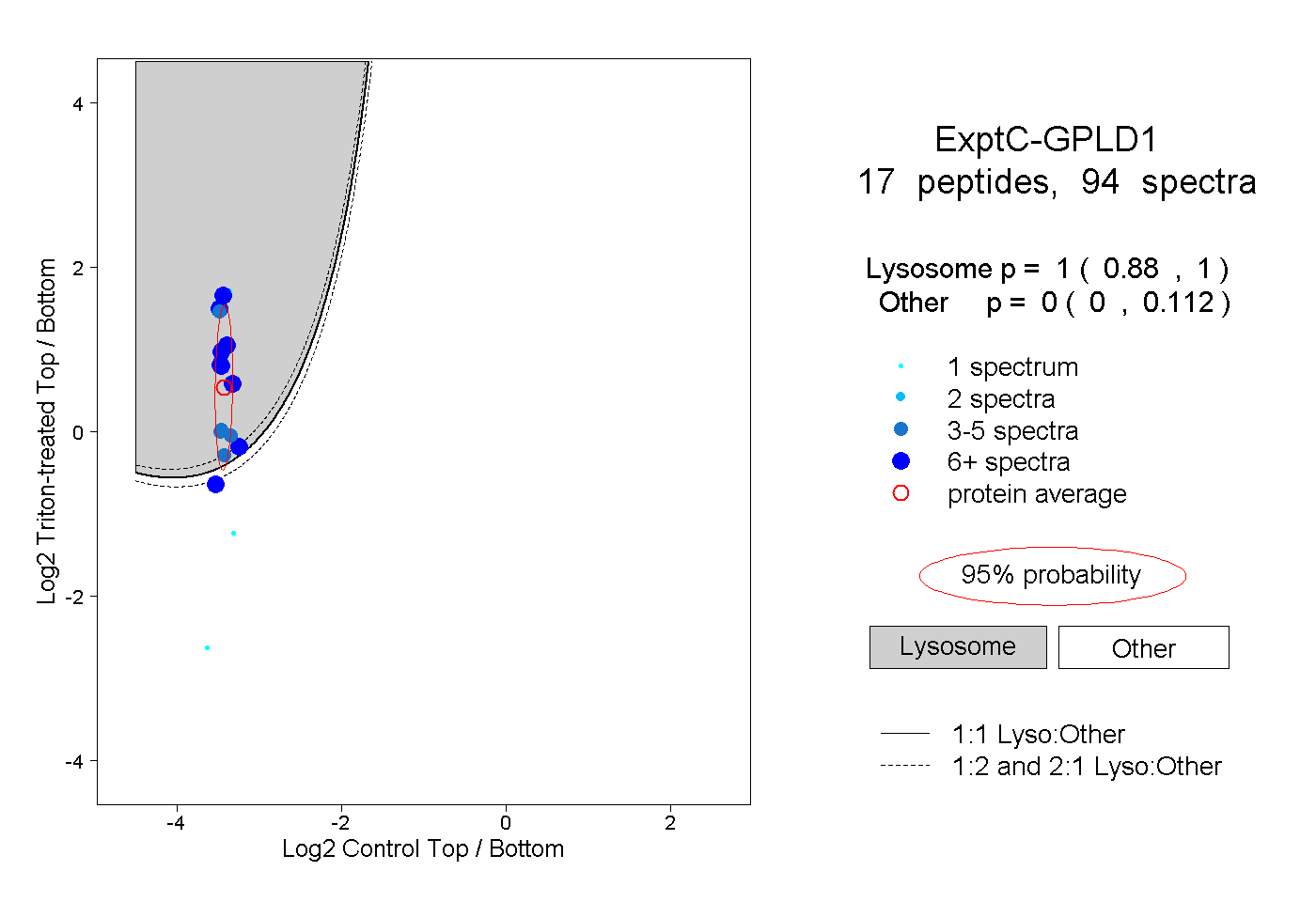 |
1.000 0.880 | 1.000 |
0.000 0.000 | 0.112 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
17 spectra |
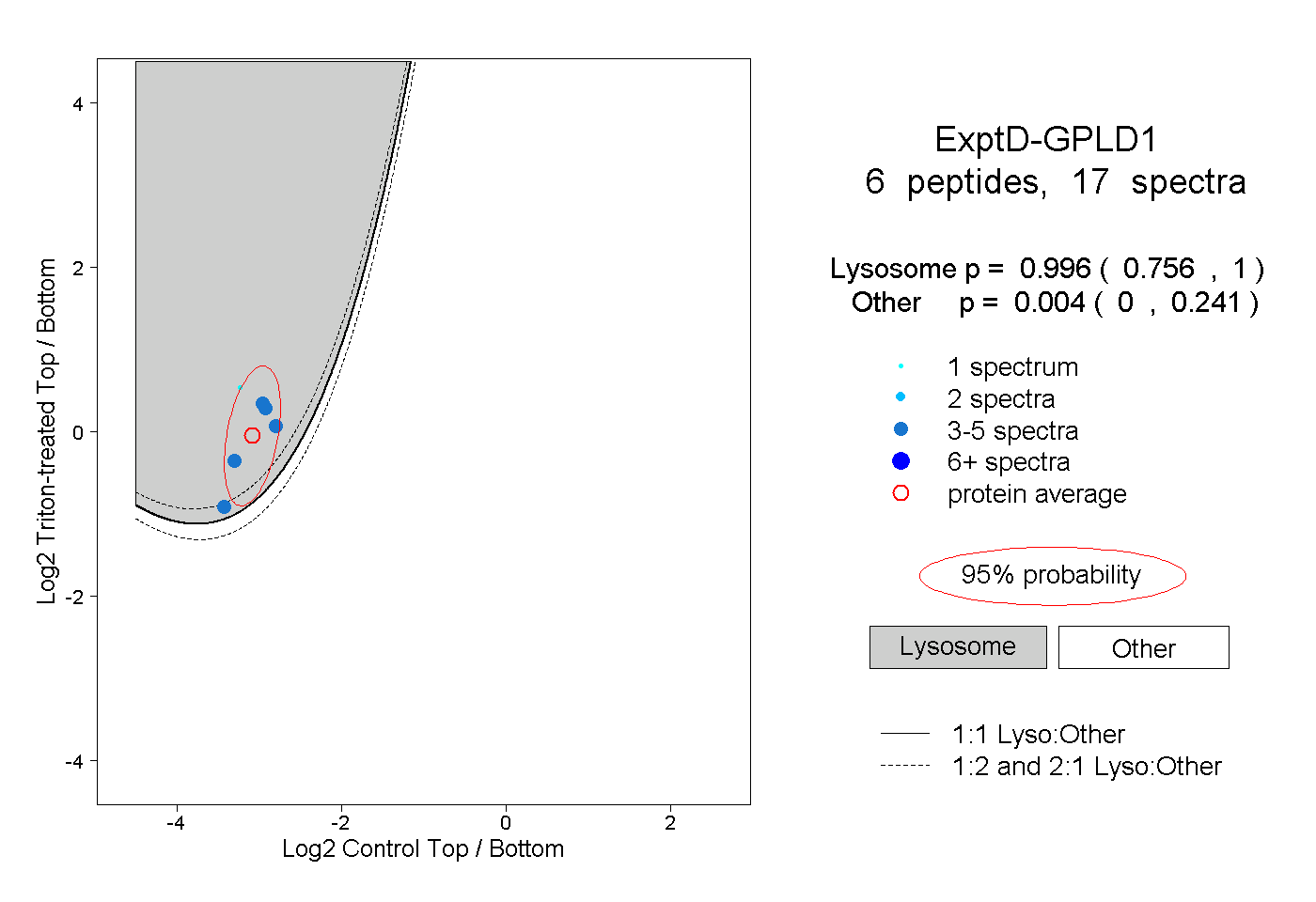 |
0.996 0.756 | 1.000 |
0.004 0.000 | 0.241 |