peptides
spectra
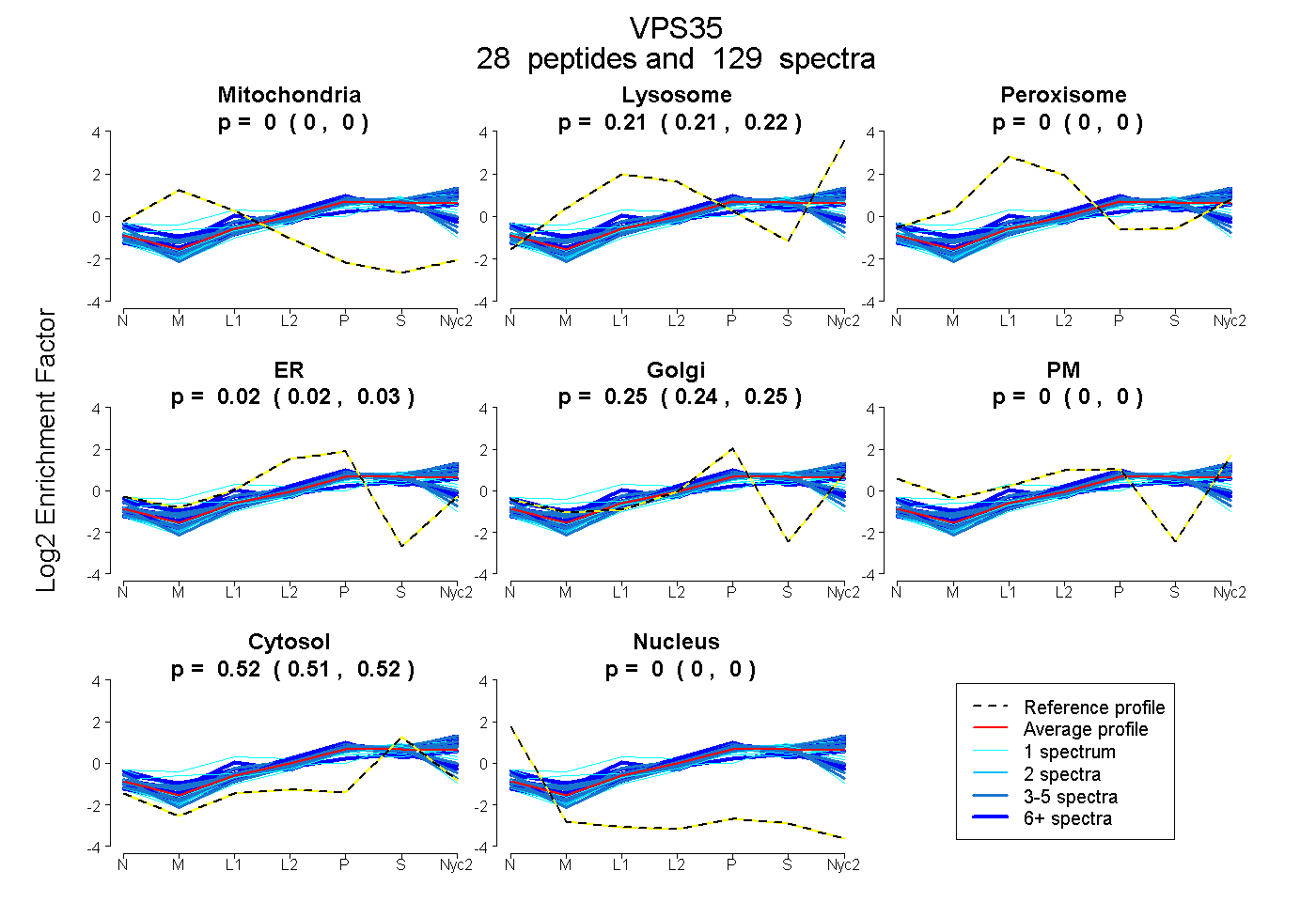
0.000 | 0.000
0.210 | 0.215
0.000 | 0.000
0.016 | 0.029
0.242 | 0.253
0.000 | 0.000
0.514 | 0.517
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
129 spectra |
 |
0.000 0.000 | 0.000 |
0.213 0.210 | 0.215 |
0.000 0.000 | 0.000 |
0.024 0.016 | 0.029 |
0.248 0.242 | 0.253 |
0.000 0.000 | 0.000 |
0.516 0.514 | 0.517 |
0.000 0.000 | 0.000 |
| 2 spectra, LMDALK | 0.000 | 0.250 | 0.000 | 0.000 | 0.224 | 0.000 | 0.526 | 0.000 | ||
| 23 spectra, ILVGTNLVR | 0.000 | 0.289 | 0.000 | 0.000 | 0.261 | 0.000 | 0.450 | 0.000 | ||
| 6 spectra, GVQHPLR | 0.000 | 0.113 | 0.129 | 0.000 | 0.397 | 0.000 | 0.361 | 0.000 | ||
| 3 spectra, LNLEHIATSSAVSK | 0.000 | 0.249 | 0.000 | 0.054 | 0.212 | 0.000 | 0.485 | 0.000 | ||
| 4 spectra, NYLLQCTR | 0.000 | 0.101 | 0.069 | 0.167 | 0.149 | 0.000 | 0.514 | 0.000 | ||
| 1 spectrum, QIVLTGILEQVVNCR | 0.000 | 0.211 | 0.075 | 0.000 | 0.296 | 0.000 | 0.417 | 0.000 | ||
| 1 spectrum, FLLLHR | 0.000 | 0.015 | 0.120 | 0.109 | 0.014 | 0.236 | 0.506 | 0.000 | ||
| 1 spectrum, YIYFYEK | 0.000 | 0.126 | 0.045 | 0.000 | 0.257 | 0.000 | 0.571 | 0.000 | ||
| 6 spectra, AVSTCAHLFWSGR | 0.000 | 0.000 | 0.246 | 0.018 | 0.255 | 0.000 | 0.481 | 0.000 | ||
| 3 spectra, DLVEMCR | 0.000 | 0.000 | 0.040 | 0.337 | 0.000 | 0.000 | 0.623 | 0.000 | ||
| 1 spectrum, EDGPGIPAEIK | 0.000 | 0.185 | 0.000 | 0.000 | 0.258 | 0.000 | 0.557 | 0.000 | ||
| 3 spectra, VQSFQMK | 0.000 | 0.190 | 0.000 | 0.000 | 0.201 | 0.093 | 0.516 | 0.000 | ||
| 1 spectrum, QDMPSEDVVSLQVSLINLAMK | 0.000 | 0.194 | 0.043 | 0.000 | 0.052 | 0.118 | 0.593 | 0.000 | ||
| 5 spectra, VLETTVEIFNK | 0.000 | 0.238 | 0.000 | 0.000 | 0.286 | 0.000 | 0.476 | 0.000 | ||
| 4 spectra, TQCALAASK | 0.000 | 0.049 | 0.122 | 0.071 | 0.261 | 0.000 | 0.497 | 0.000 | ||
| 11 spectra, LALFAHR | 0.000 | 0.224 | 0.000 | 0.000 | 0.240 | 0.000 | 0.536 | 0.000 | ||
| 1 spectrum, SEDPDQQYLILNTAR | 0.000 | 0.236 | 0.000 | 0.000 | 0.218 | 0.000 | 0.547 | 0.000 | ||
| 8 spectra, CFSEENHEPLR | 0.000 | 0.000 | 0.243 | 0.000 | 0.244 | 0.034 | 0.478 | 0.000 | ||
| 5 spectra, TSMLSPK | 0.000 | 0.279 | 0.000 | 0.000 | 0.228 | 0.000 | 0.493 | 0.000 | ||
| 9 spectra, FIHLLR | 0.000 | 0.248 | 0.000 | 0.000 | 0.267 | 0.000 | 0.486 | 0.000 | ||
| 1 spectrum, HFHNTLEHLR | 0.000 | 0.095 | 0.290 | 0.000 | 0.162 | 0.116 | 0.336 | 0.000 | ||
| 9 spectra, NIIIALIDR | 0.000 | 0.274 | 0.000 | 0.000 | 0.258 | 0.000 | 0.468 | 0.000 | ||
| 1 spectrum, ACAELHQNVNVK | 0.000 | 0.000 | 0.000 | 0.308 | 0.000 | 0.000 | 0.692 | 0.000 | ||
| 4 spectra, AELAELPLR | 0.000 | 0.228 | 0.000 | 0.000 | 0.223 | 0.000 | 0.548 | 0.000 | ||
| 3 spectra, VDYVDK | 0.000 | 0.151 | 0.000 | 0.000 | 0.311 | 0.000 | 0.537 | 0.000 | ||
| 4 spectra, LSQLEGVNVER | 0.000 | 0.289 | 0.000 | 0.000 | 0.230 | 0.000 | 0.481 | 0.000 | ||
| 3 spectra, VMECLK | 0.000 | 0.000 | 0.121 | 0.158 | 0.169 | 0.000 | 0.552 | 0.000 | ||
| 6 spectra, LLDEAIQAVK | 0.000 | 0.223 | 0.000 | 0.000 | 0.270 | 0.000 | 0.508 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
75 spectra |
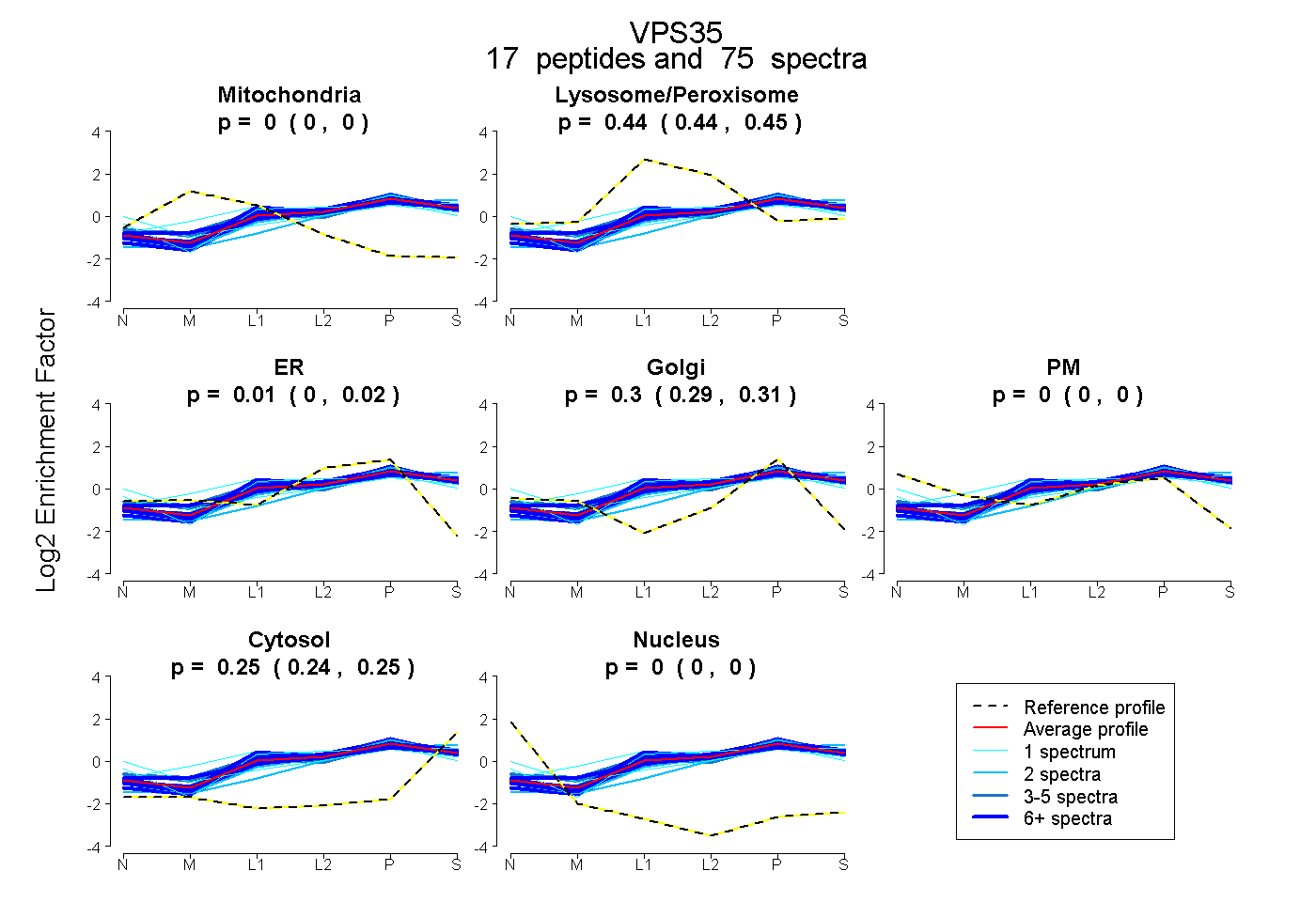 |
0.000 0.000 | 0.000 |
0.441 0.435 | 0.446 |
0.008 0.000 | 0.020 |
0.304 0.290 | 0.311 |
0.000 0.000 | 0.000 |
0.247 0.244 | 0.251 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
200 spectra |
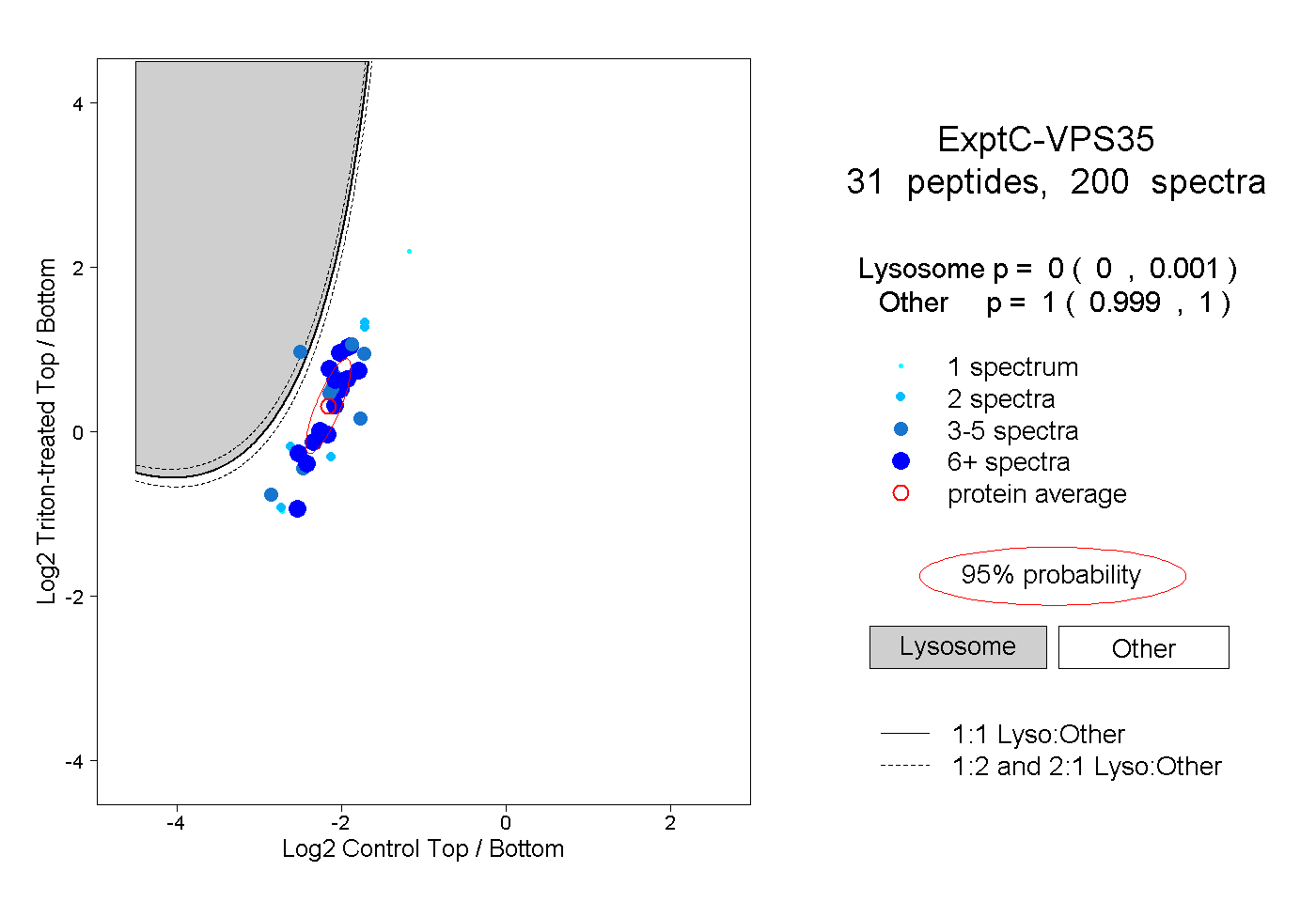 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
21 spectra |
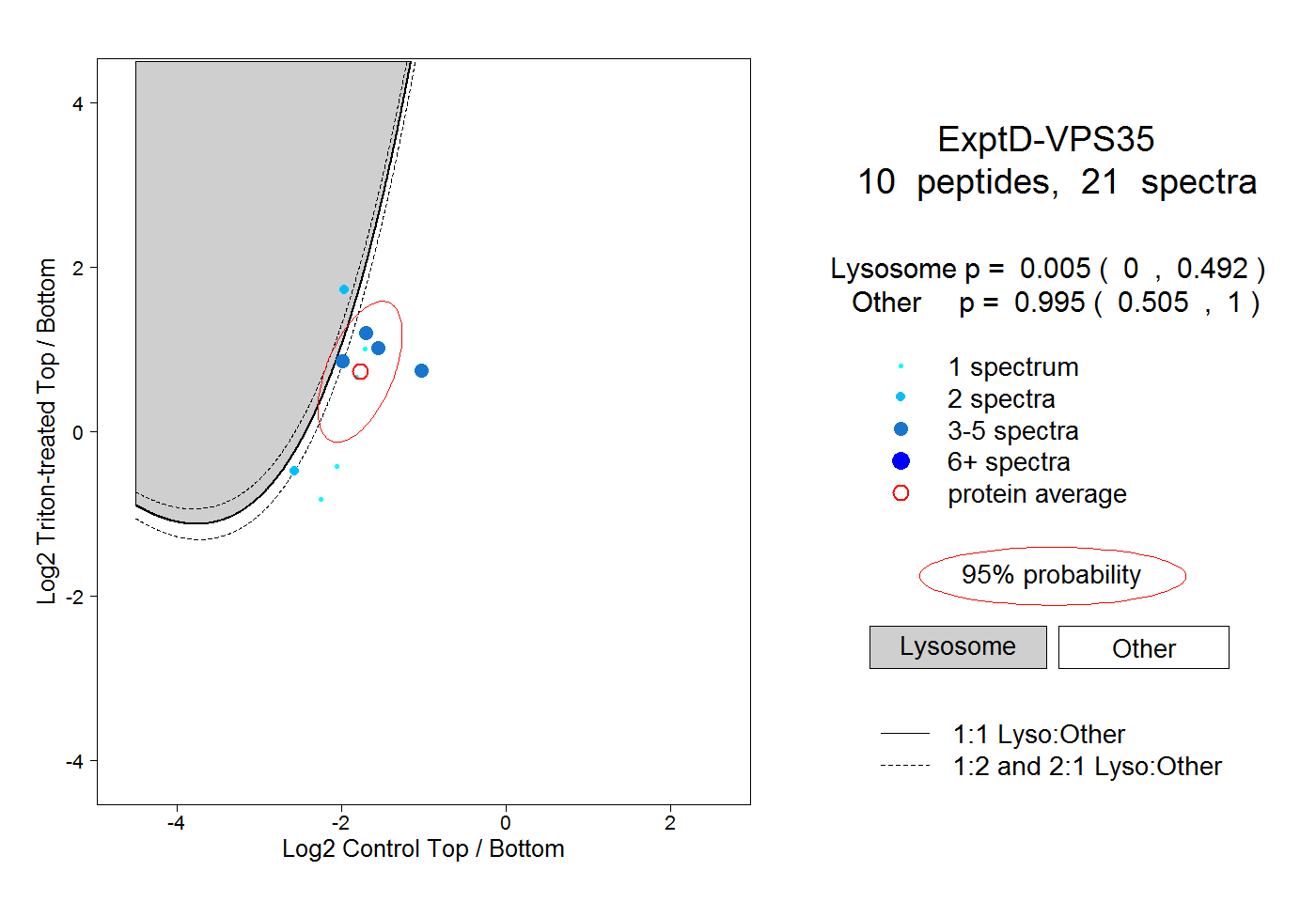 |
0.005 0.000 | 0.492 |
0.995 0.505 | 1.000 |