peptides
spectra
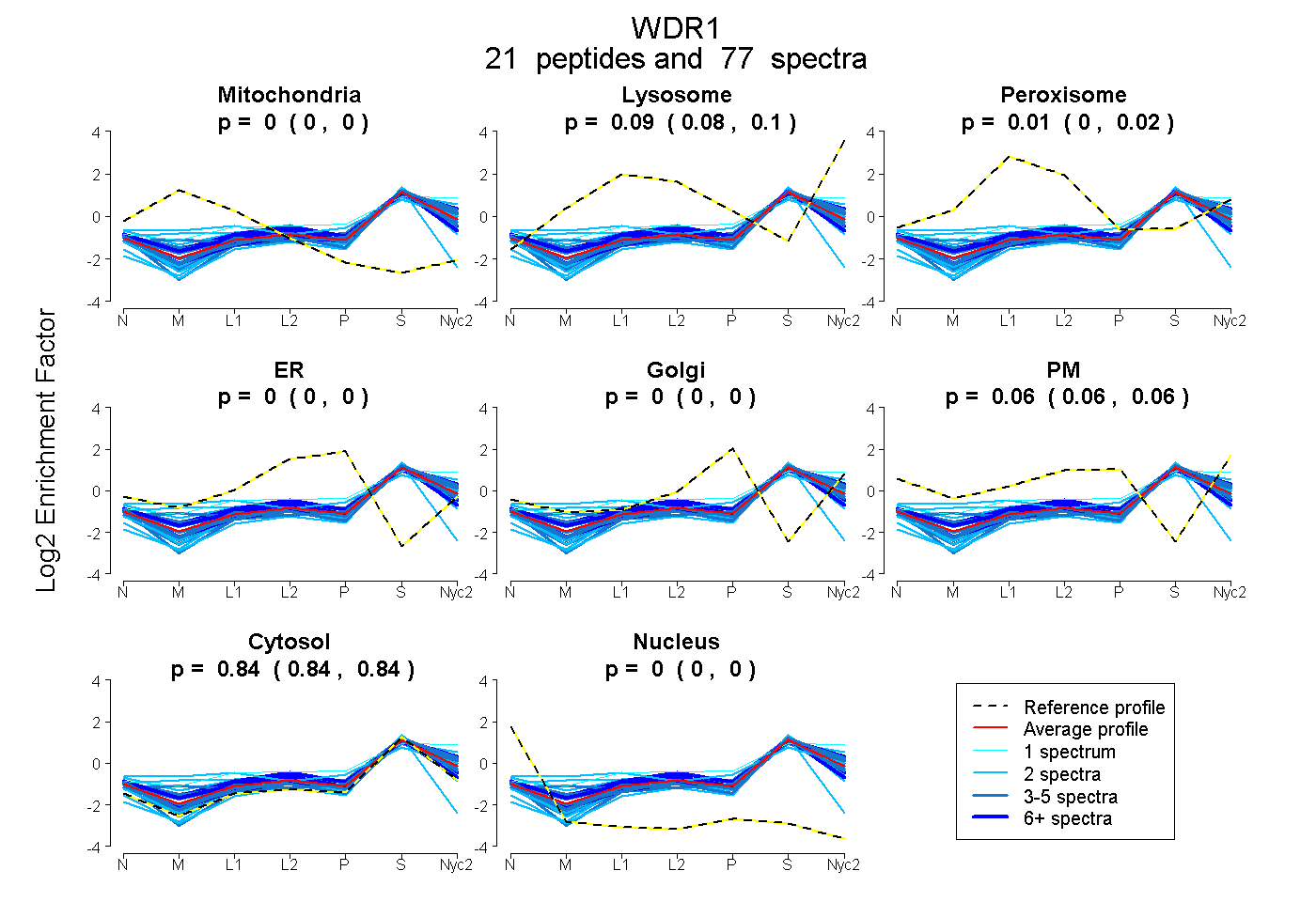
0.000 | 0.000
0.077 | 0.095
0.004 | 0.019
0.000 | 0.000
0.000 | 0.000
0.055 | 0.061
0.840 | 0.844
0.000 | 0.000
peptides
spectra
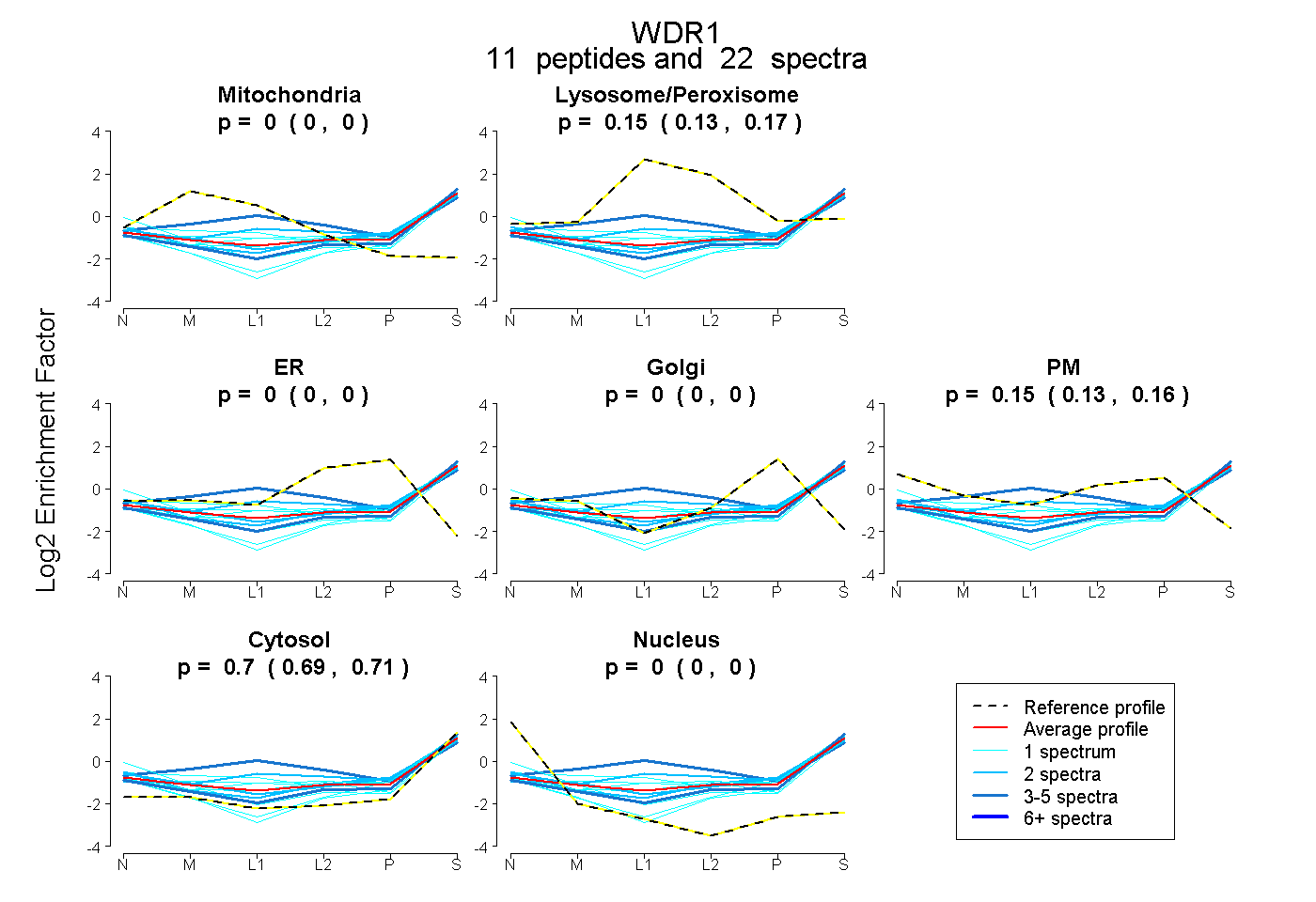
0.000 | 0.000
0.128 | 0.169
0.000 | 0.000
0.000 | 0.000
0.129 | 0.160
0.694 | 0.711
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
77 spectra |
 |
0.000 0.000 | 0.000 |
0.087 0.077 | 0.095 |
0.012 0.004 | 0.019 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.059 0.055 | 0.061 |
0.842 0.840 | 0.844 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
22 spectra |
 |
0.000 0.000 | 0.000 |
0.150 0.128 | 0.169 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.147 0.129 | 0.160 |
0.703 0.694 | 0.711 |
0.000 0.000 | 0.000 |
| 3 spectra, LATGSDDNCAAFFEGPPFK | 0.000 | 0.107 | 0.000 | 0.000 | 0.183 | 0.710 | 0.000 | |||
| 1 spectrum, VYSILGATLK | 0.000 | 0.238 | 0.000 | 0.000 | 0.062 | 0.700 | 0.000 | |||
| 1 spectrum, FGAVFLWDTGSSVGEITGHNK | 0.000 | 0.227 | 0.000 | 0.019 | 0.063 | 0.691 | 0.000 | |||
| 1 spectrum, VFASLPQVER | 0.000 | 0.000 | 0.000 | 0.092 | 0.000 | 0.859 | 0.049 | |||
| 4 spectra, FTIGDHSR | 0.090 | 0.412 | 0.000 | 0.000 | 0.013 | 0.485 | 0.000 | |||
| 1 spectrum, FATASADGQIFIYDGK | 0.044 | 0.225 | 0.000 | 0.000 | 0.108 | 0.609 | 0.013 | |||
| 5 spectra, YTNLTLR | 0.000 | 0.049 | 0.000 | 0.000 | 0.138 | 0.813 | 0.000 | |||
| 1 spectrum, YEYQPFAGK | 0.000 | 0.000 | 0.000 | 0.163 | 0.003 | 0.825 | 0.008 | |||
| 2 spectra, GHTNQVSR | 0.000 | 0.298 | 0.000 | 0.000 | 0.109 | 0.593 | 0.000 | |||
| 1 spectrum, IAVVGEGR | 0.000 | 0.049 | 0.000 | 0.000 | 0.158 | 0.680 | 0.113 | |||
| 2 spectra, YAPSGFYIASGDISGK | 0.000 | 0.129 | 0.000 | 0.061 | 0.108 | 0.701 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
108 spectra |
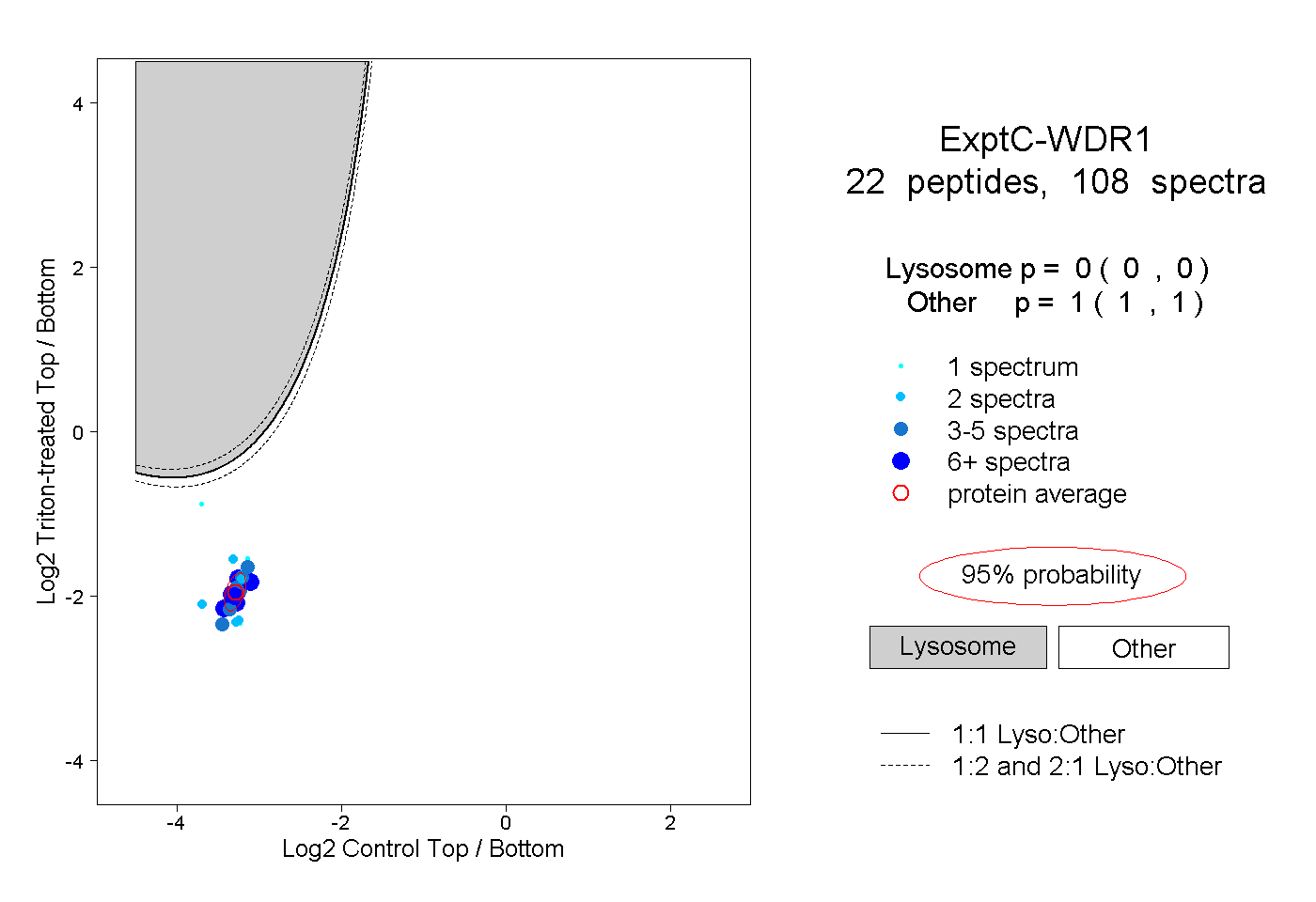 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
10 spectra |
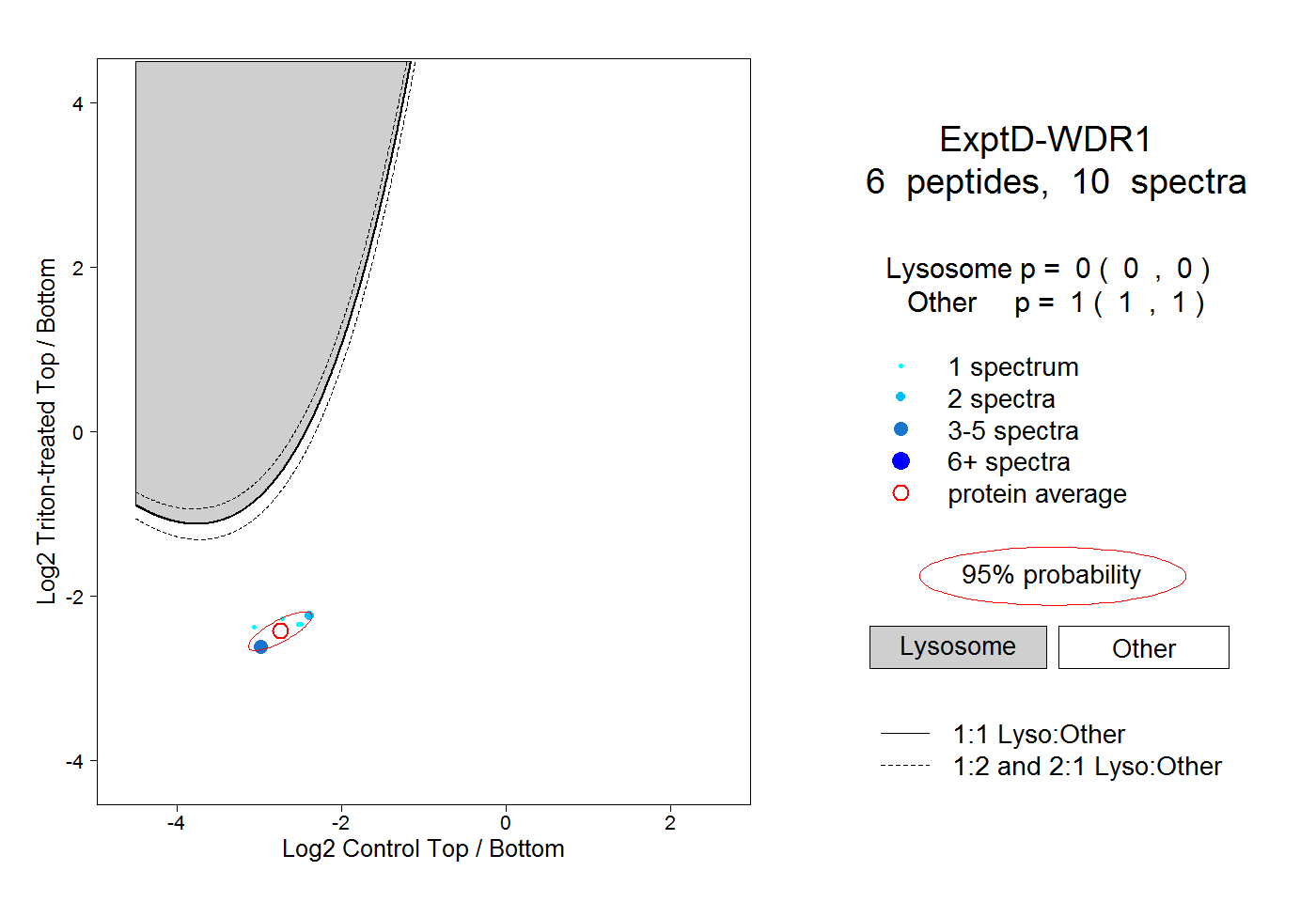 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |