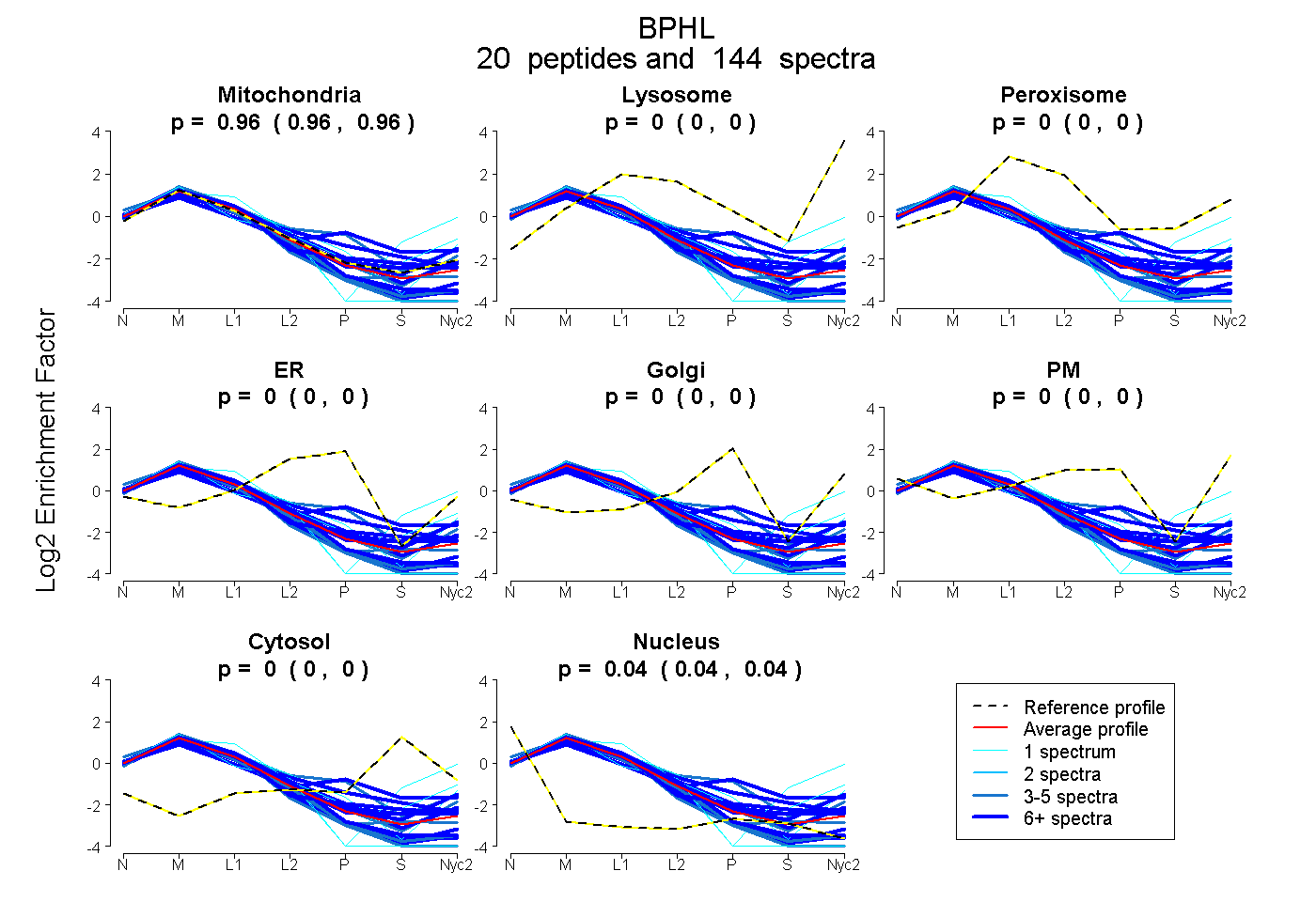
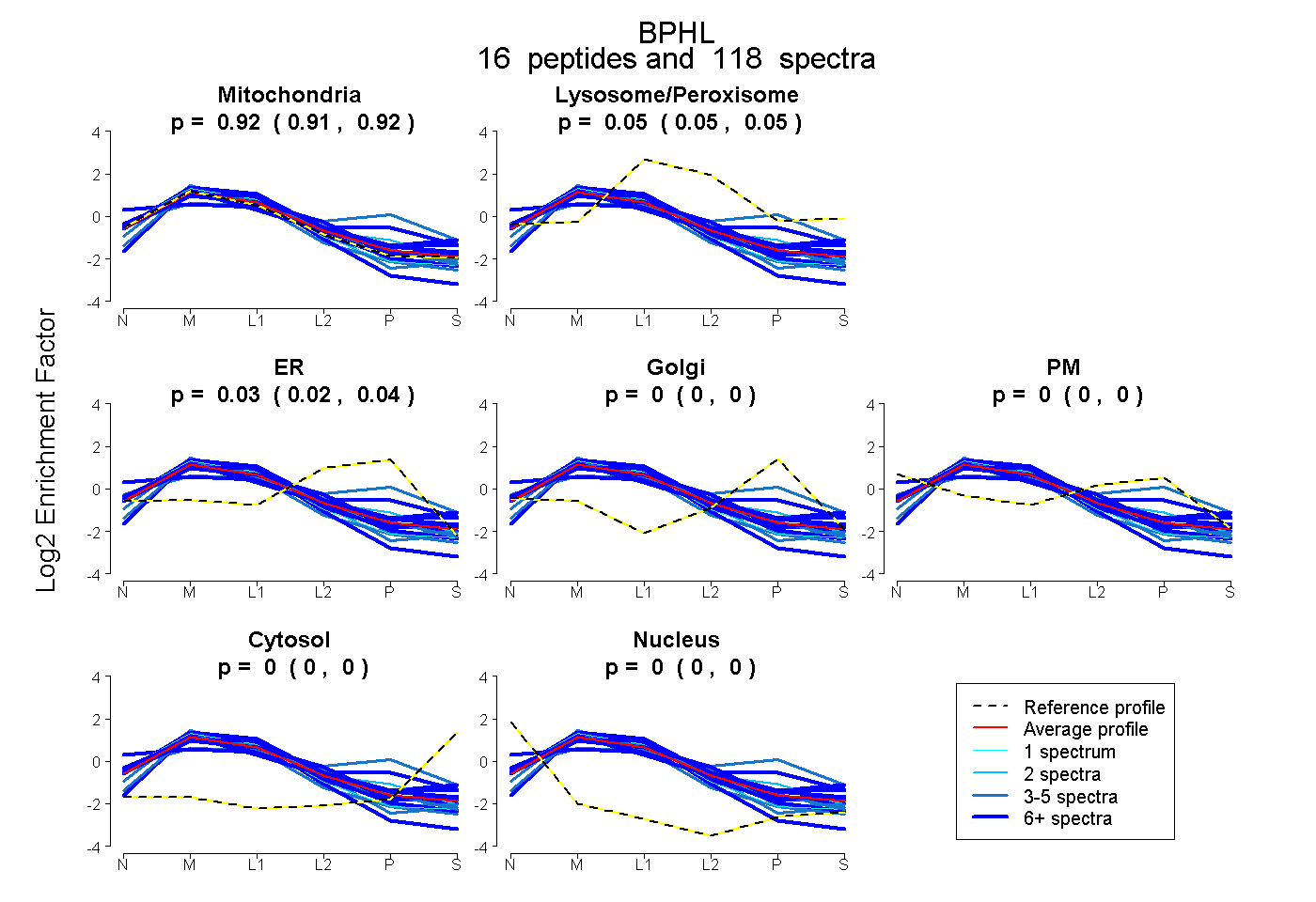
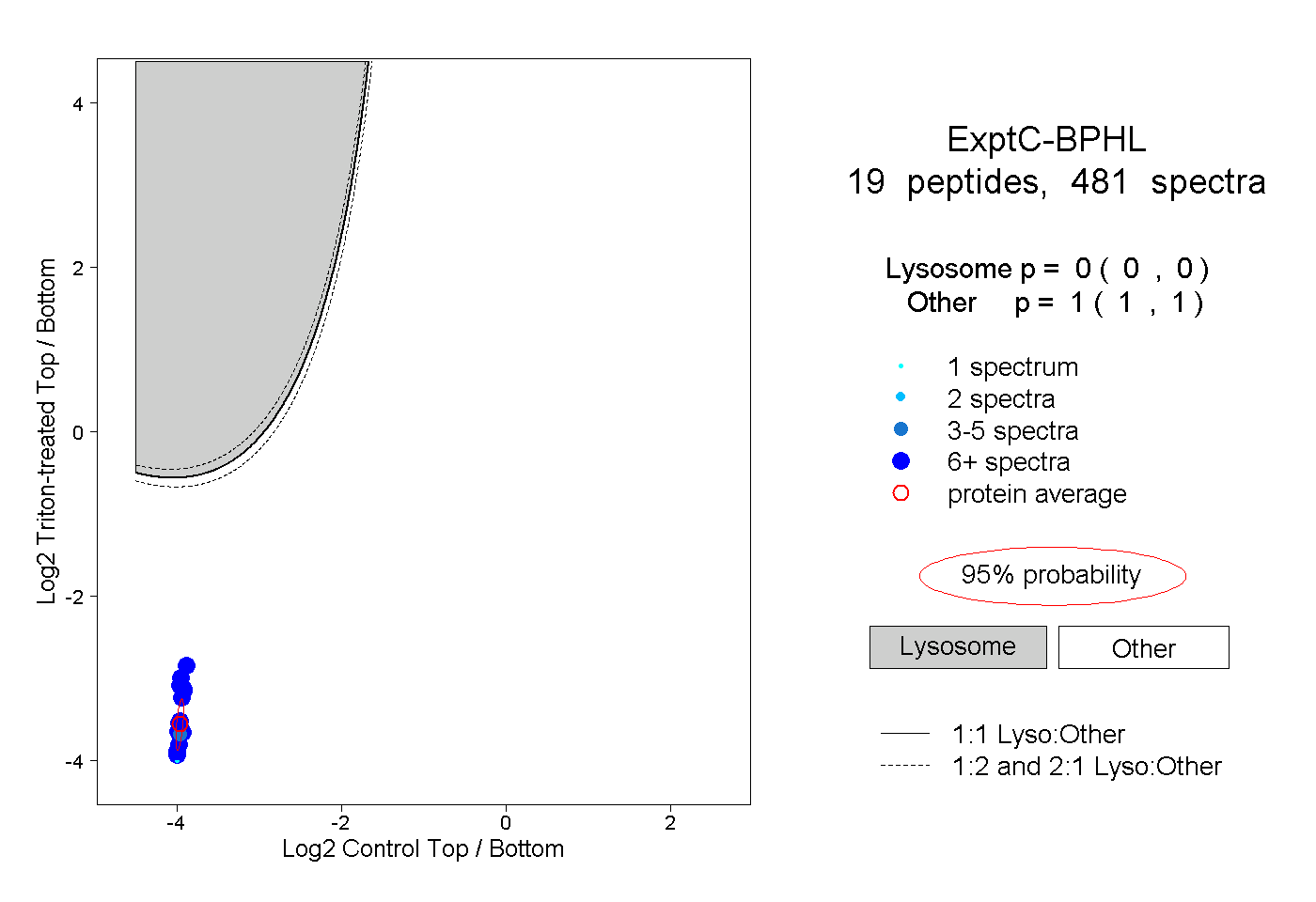
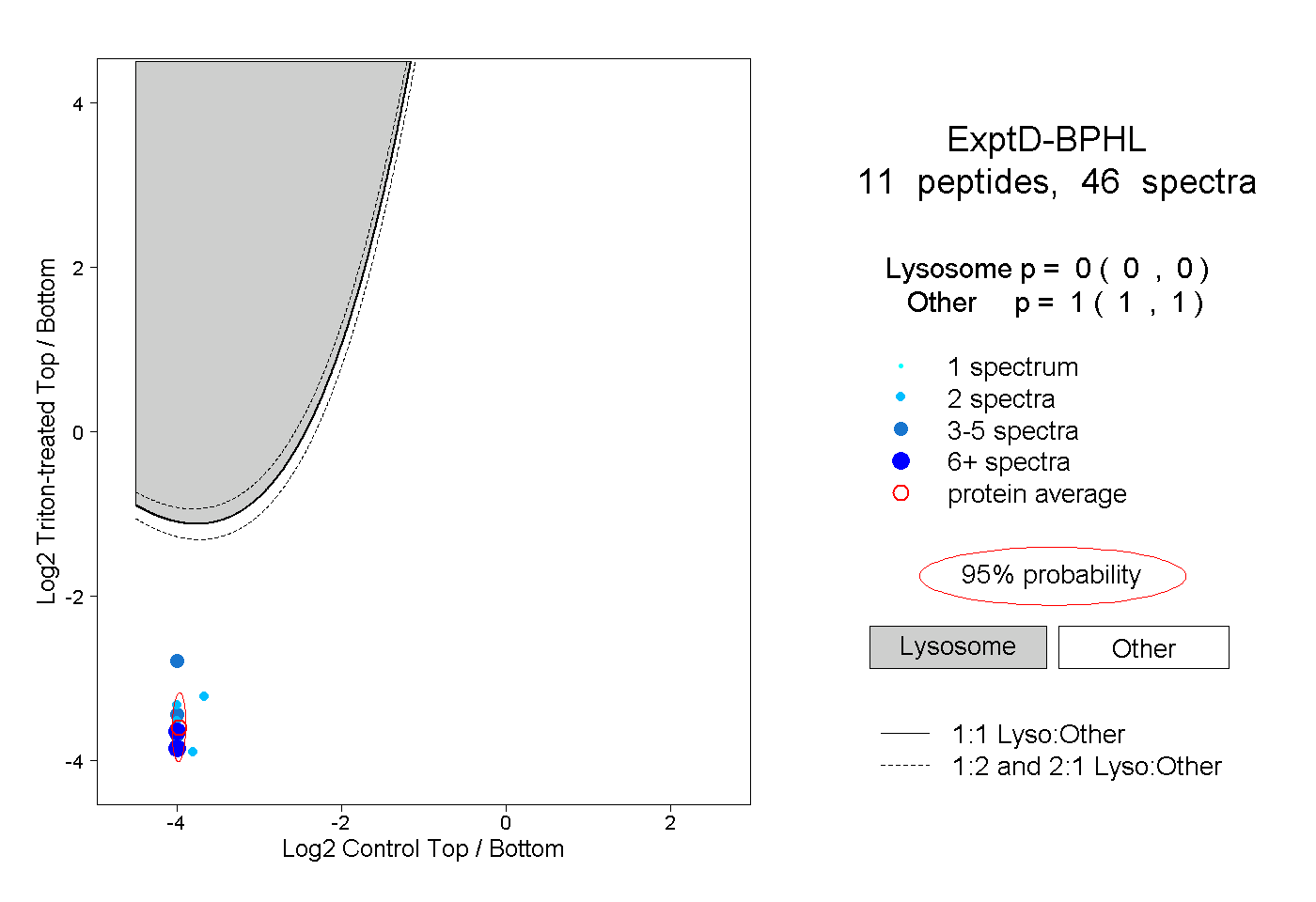
| 1 spectrum, MVIWGANAYVTEEDSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 54 spectra, FHADFLLEHVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 38 spectra, HLPDGNICR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 15 spectra, GYGESRPPDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 44 spectra, FADEFNR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 45 spectra, LHLMPEGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 13 spectra, TDFAPQLQSLNK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, AAVNGIHLHYQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 30 spectra, KPLEALYGHDYFAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 22 spectra, FTLVAWDPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 26 spectra, DPLVPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 40 spectra, YPSYIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 36 spectra, IYQGIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 39 spectra, DAVDLMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, HNLHLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, VGEGEHAVLLLPGMLGSGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 41 spectra, WVDGINQFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, LVEDFLQ |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, HLLPLIQCPTLIVHGEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |