peptides
spectra
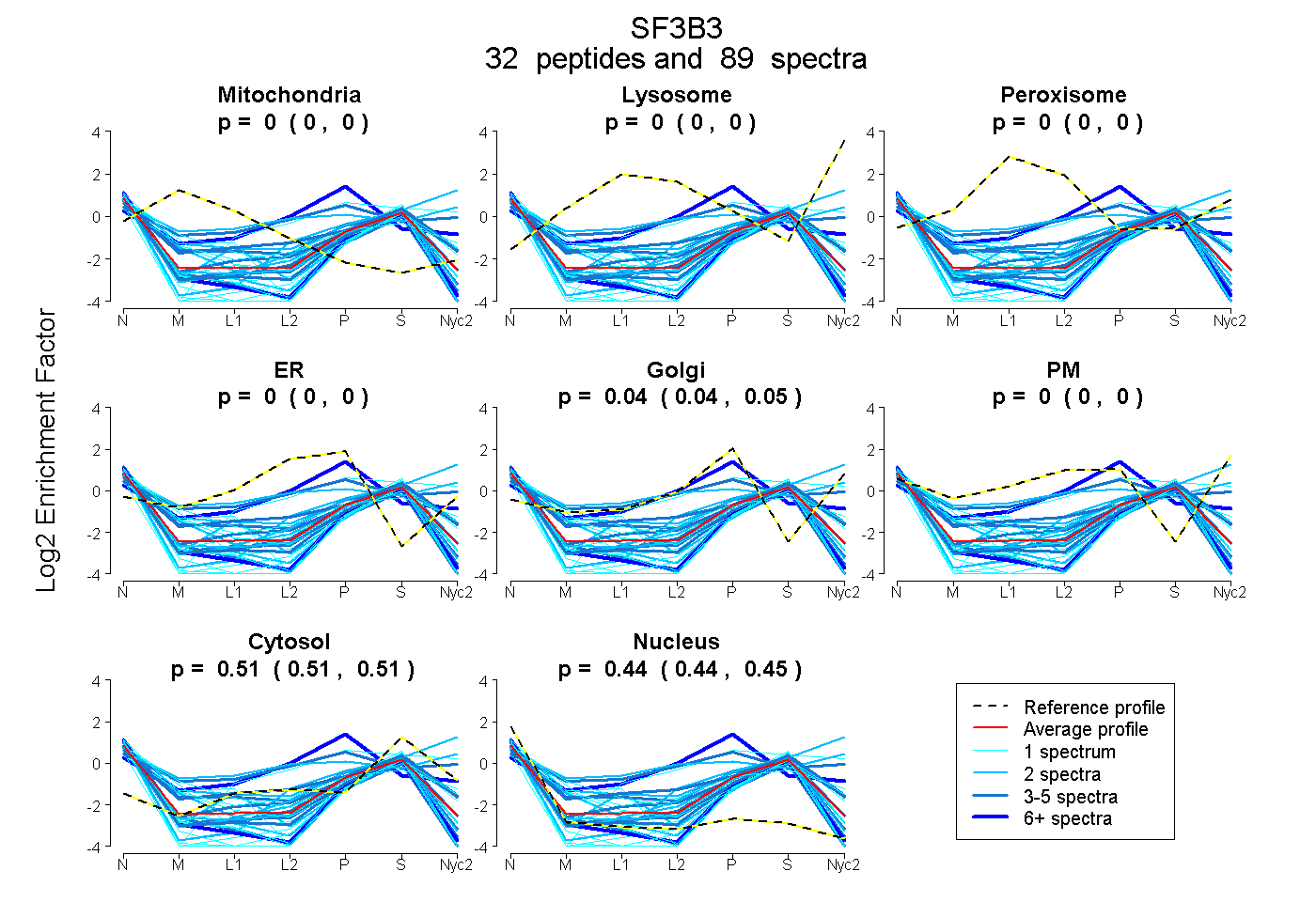
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.039 | 0.049
0.000 | 0.000
0.509 | 0.514
0.438 | 0.449
peptides
spectra
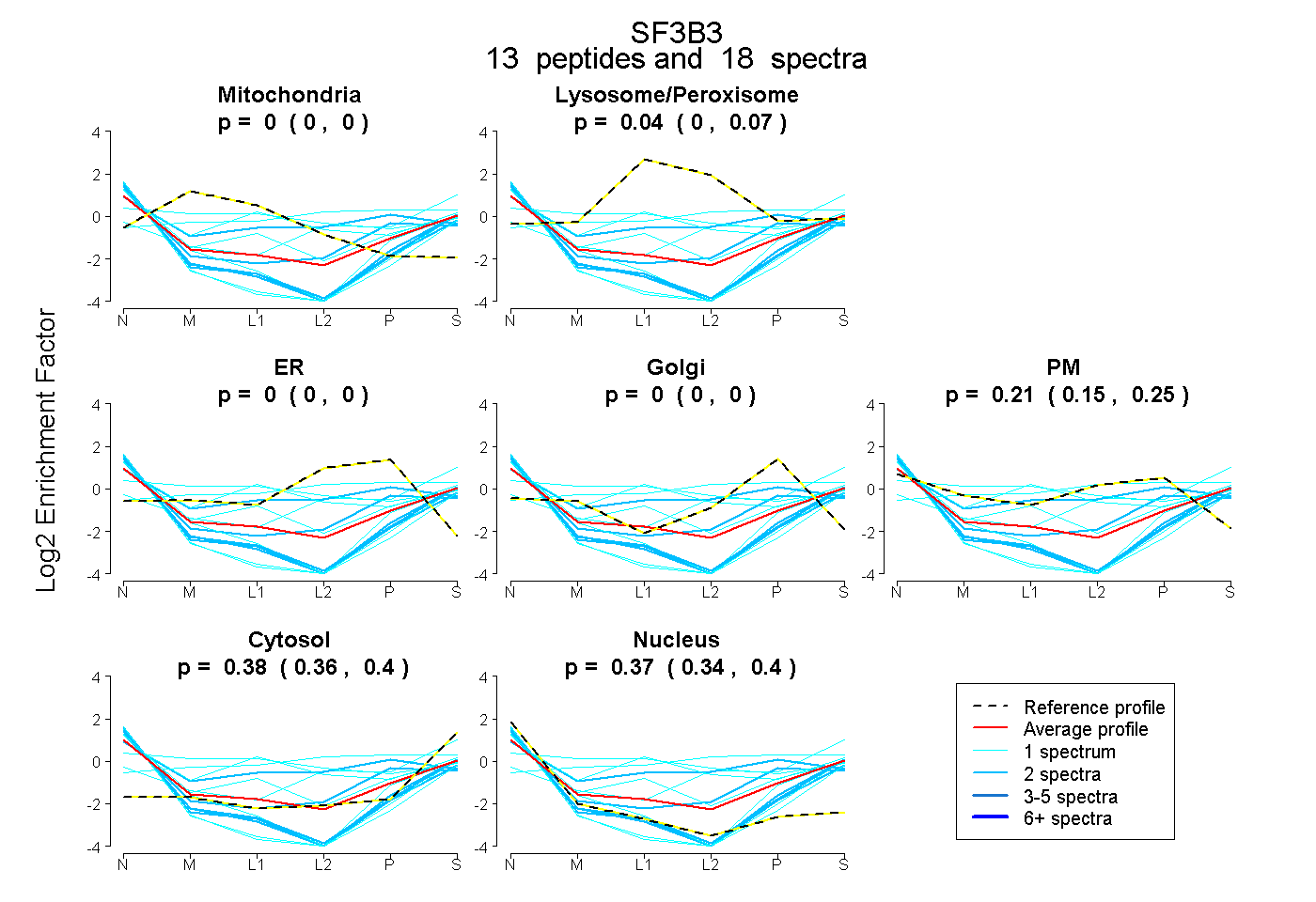
0.000 | 0.000
0.000 | 0.073
0.000 | 0.000
0.000 | 0.000
0.150 | 0.250
0.361 | 0.404
0.339 | 0.399
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
89 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.044 0.039 | 0.049 |
0.000 0.000 | 0.000 |
0.512 0.509 | 0.514 |
0.444 0.438 | 0.449 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
18 spectra |
 |
0.000 0.000 | 0.000 |
0.038 0.000 | 0.073 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.207 0.150 | 0.250 |
0.384 0.361 | 0.404 |
0.371 0.339 | 0.399 |
| 2 spectra, NVSEELDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.365 | 0.635 | |||
| 1 spectrum, TVLDPVTGDLSDTR | 0.000 | 0.242 | 0.000 | 0.000 | 0.089 | 0.240 | 0.428 | |||
| 1 spectrum, IVPGQFLAVDPK | 0.000 | 0.508 | 0.000 | 0.000 | 0.019 | 0.164 | 0.310 | |||
| 2 spectra, HIANYISGIQTIGHR | 0.000 | 0.183 | 0.000 | 0.000 | 0.529 | 0.179 | 0.109 | |||
| 1 spectrum, QQEIVVSR | 0.155 | 0.301 | 0.000 | 0.000 | 0.292 | 0.205 | 0.047 | |||
| 1 spectrum, LVYILNR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.267 | 0.733 | |||
| 1 spectrum, CPIPR | 0.000 | 0.080 | 0.000 | 0.000 | 0.319 | 0.601 | 0.000 | |||
| 2 spectra, FLAVGLVDNTVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.306 | 0.694 | |||
| 1 spectrum, NDLDDPER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.325 | 0.675 | |||
| 2 spectra, DLILSPR | 0.000 | 0.000 | 0.000 | 0.147 | 0.245 | 0.246 | 0.363 | |||
| 1 spectrum, LPPNTNDEVDEDPTGNK | 0.000 | 0.000 | 0.000 | 0.037 | 0.000 | 0.373 | 0.590 | |||
| 1 spectrum, LTGGTK | 0.000 | 0.443 | 0.000 | 0.317 | 0.000 | 0.241 | 0.000 | |||
| 2 spectra, FGNICVVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.364 | 0.636 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
15 spectra |
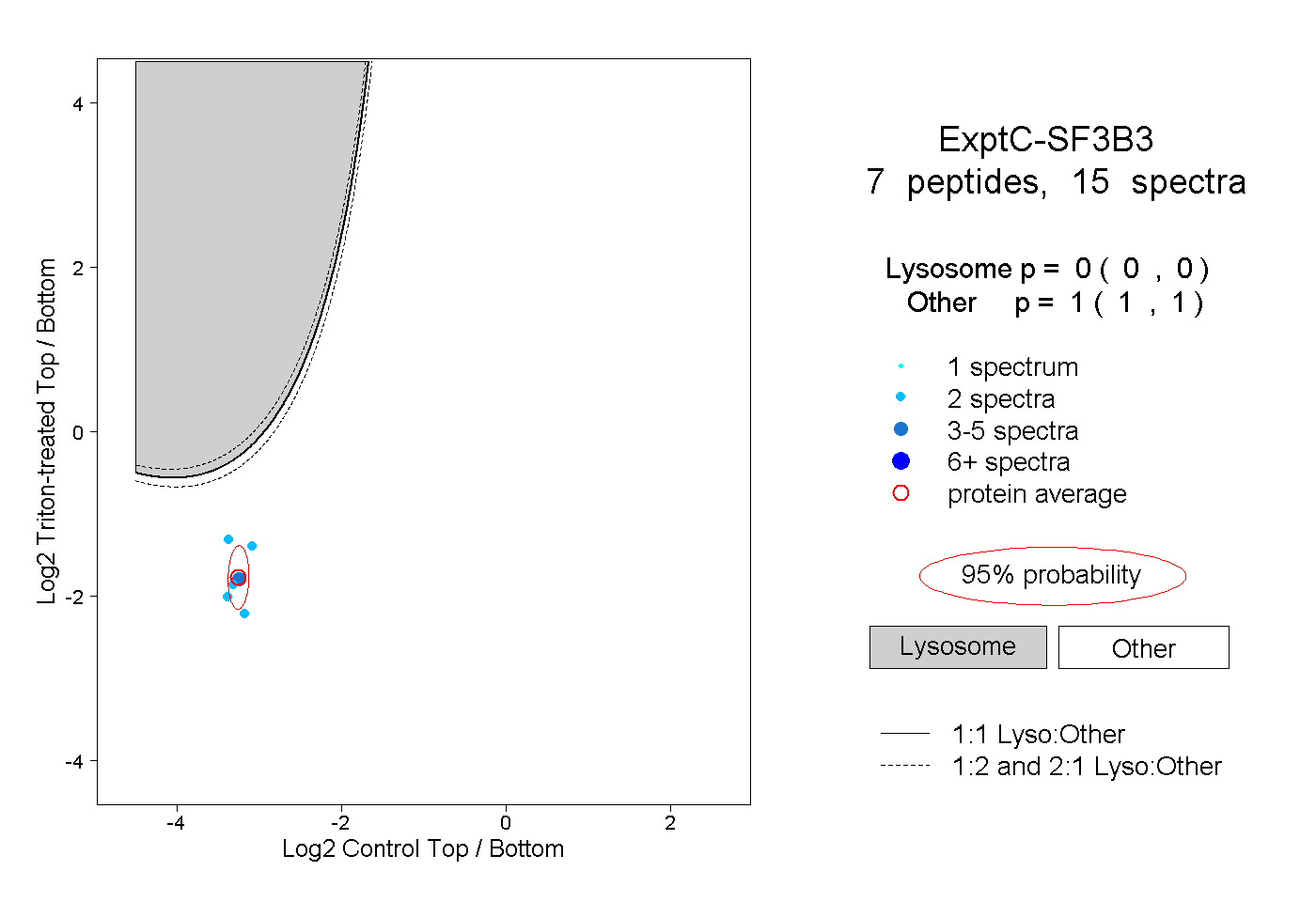 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
2 spectra |
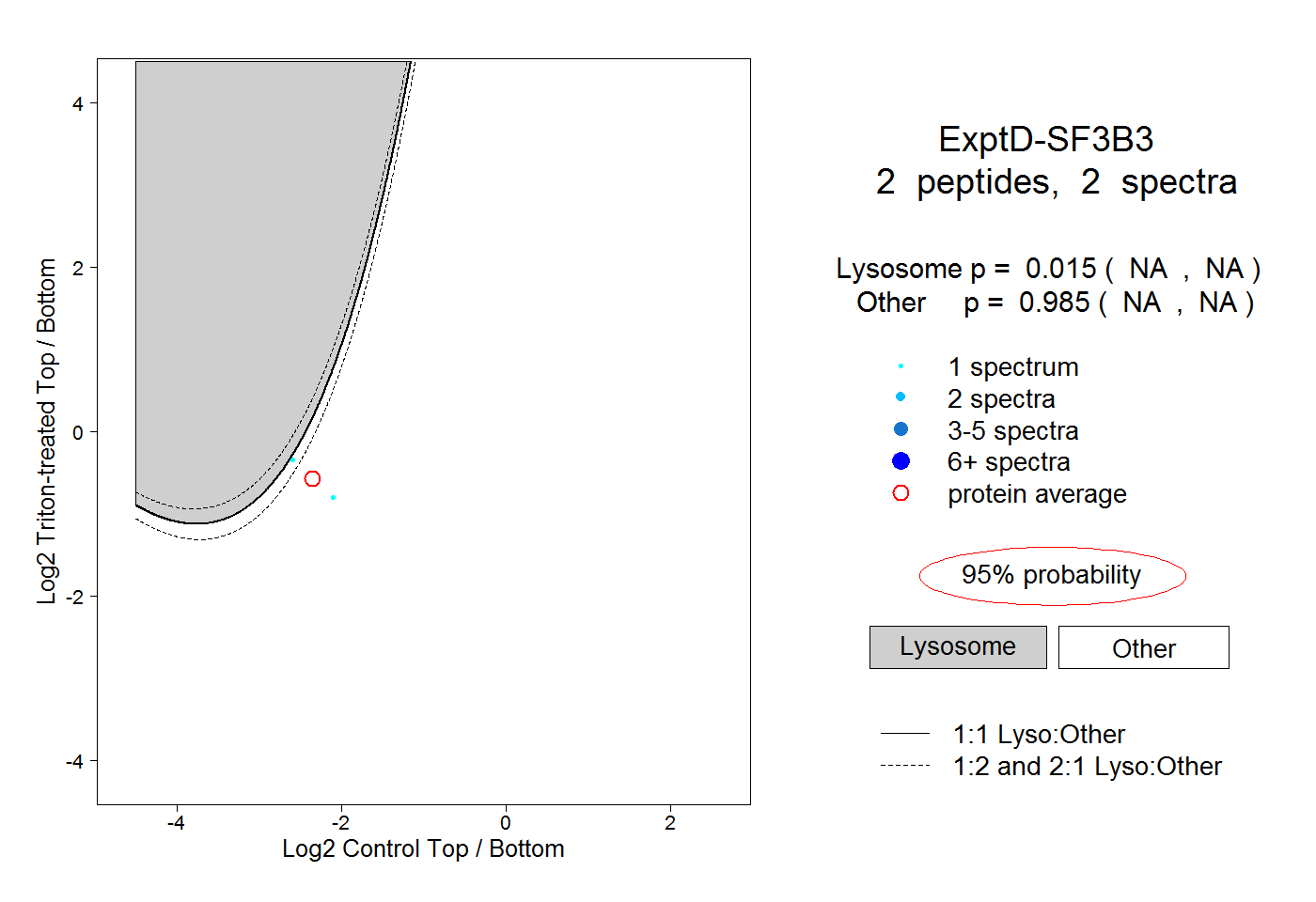 |
0.015 NA | NA |
0.985 NA | NA |