peptides
spectra
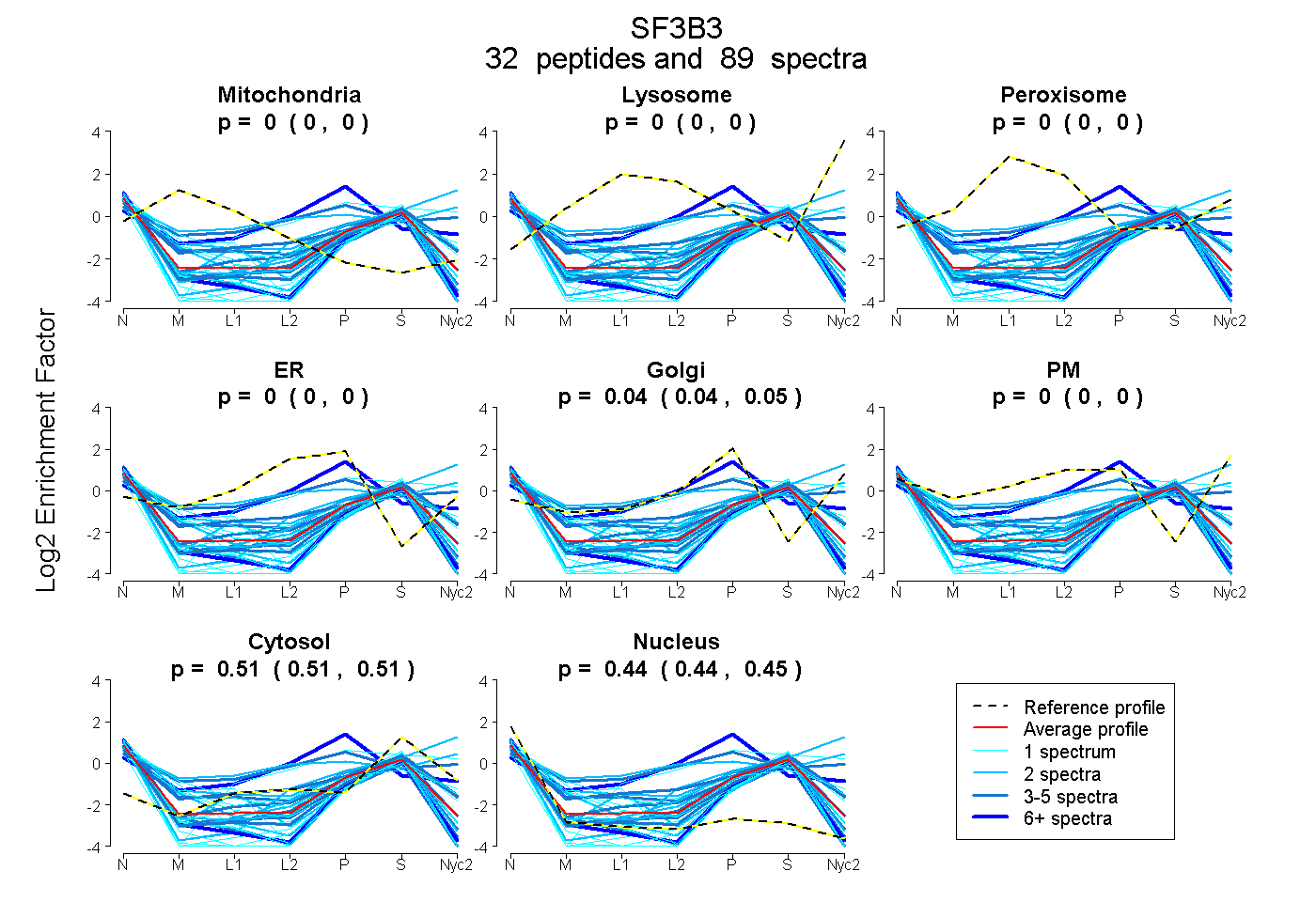
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.039 | 0.049
0.000 | 0.000
0.509 | 0.514
0.438 | 0.449
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
89 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.044 0.039 | 0.049 |
0.000 0.000 | 0.000 |
0.512 0.509 | 0.514 |
0.444 0.438 | 0.449 |
| 4 spectra, SYYFPVK | 0.000 | 0.000 | 0.051 | 0.087 | 0.000 | 0.066 | 0.537 | 0.258 | ||
| 2 spectra, CAVNQR | 0.119 | 0.000 | 0.000 | 0.124 | 0.000 | 0.000 | 0.345 | 0.412 | ||
| 6 spectra, MFLYNLTLQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.345 | 0.655 | ||
| 3 spectra, LVYILNR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.436 | 0.564 | ||
| 1 spectrum, VIVSDVQESFIWVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.349 | 0.651 | ||
| 1 spectrum, SVAGGFVYTYK | 0.099 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.458 | 0.444 | ||
| 3 spectra, LTISSPLEAHK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.550 | 0.450 | ||
| 1 spectrum, WVTTASLLDYDTVAGADK | 0.000 | 0.000 | 0.000 | 0.000 | 0.041 | 0.000 | 0.553 | 0.406 | ||
| 1 spectrum, FLAVGLVDNTVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.292 | 0.708 | ||
| 2 spectra, IVILEYQPSK | 0.000 | 0.003 | 0.000 | 0.000 | 0.000 | 0.192 | 0.610 | 0.195 | ||
| 1 spectrum, AGNGQWASVIR | 0.014 | 0.000 | 0.000 | 0.000 | 0.116 | 0.000 | 0.525 | 0.346 | ||
| 3 spectra, ILELLRPDPNTGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.306 | 0.694 | ||
| 2 spectra, NVIDGDLCEQFNSMEPNK | 0.000 | 0.000 | 0.050 | 0.000 | 0.000 | 0.527 | 0.392 | 0.031 | ||
| 1 spectrum, TVLDPVTGDLSDTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.336 | 0.664 | ||
| 3 spectra, HIANYISGIQTIGHR | 0.000 | 0.000 | 0.000 | 0.106 | 0.001 | 0.443 | 0.419 | 0.031 | ||
| 2 spectra, VYDLGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.483 | 0.517 | ||
| 5 spectra, MQGQEAVLAMSSR | 0.000 | 0.000 | 0.003 | 0.000 | 0.138 | 0.077 | 0.498 | 0.284 | ||
| 2 spectra, DLILSPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.332 | 0.668 | ||
| 1 spectrum, SWLSYSYQSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.438 | 0.562 | ||
| 1 spectrum, YLGSRPVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.021 | 0.240 | 0.387 | 0.353 | ||
| 1 spectrum, FGNICVVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.330 | 0.670 | ||
| 2 spectra, NVSEELDR | 0.000 | 0.000 | 0.000 | 0.013 | 0.000 | 0.000 | 0.477 | 0.510 | ||
| 1 spectrum, SLMAFR | 0.151 | 0.000 | 0.000 | 0.000 | 0.005 | 0.118 | 0.451 | 0.274 | ||
| 2 spectra, DYIVVGSDSGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.373 | 0.627 | ||
| 5 spectra, VLIGVGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.451 | 0.549 | ||
| 1 spectrum, LEFLHK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.306 | 0.694 | ||
| 21 spectra, CPIPR | 0.000 | 0.000 | 0.000 | 0.423 | 0.200 | 0.000 | 0.321 | 0.056 | ||
| 5 spectra, NFGDQPDIR | 0.000 | 0.000 | 0.000 | 0.000 | 0.100 | 0.000 | 0.588 | 0.311 | ||
| 2 spectra, LPPNTNDEVDEDPTGNK | 0.000 | 0.000 | 0.000 | 0.007 | 0.000 | 0.000 | 0.474 | 0.519 | ||
| 2 spectra, IHQETFGK | 0.008 | 0.000 | 0.000 | 0.070 | 0.002 | 0.000 | 0.495 | 0.424 | ||
| 1 spectrum, FSNTGEDWYVLVGVAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.277 | 0.112 | 0.611 | 0.000 | ||
| 1 spectrum, QDELGER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.507 | 0.493 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
18 spectra |
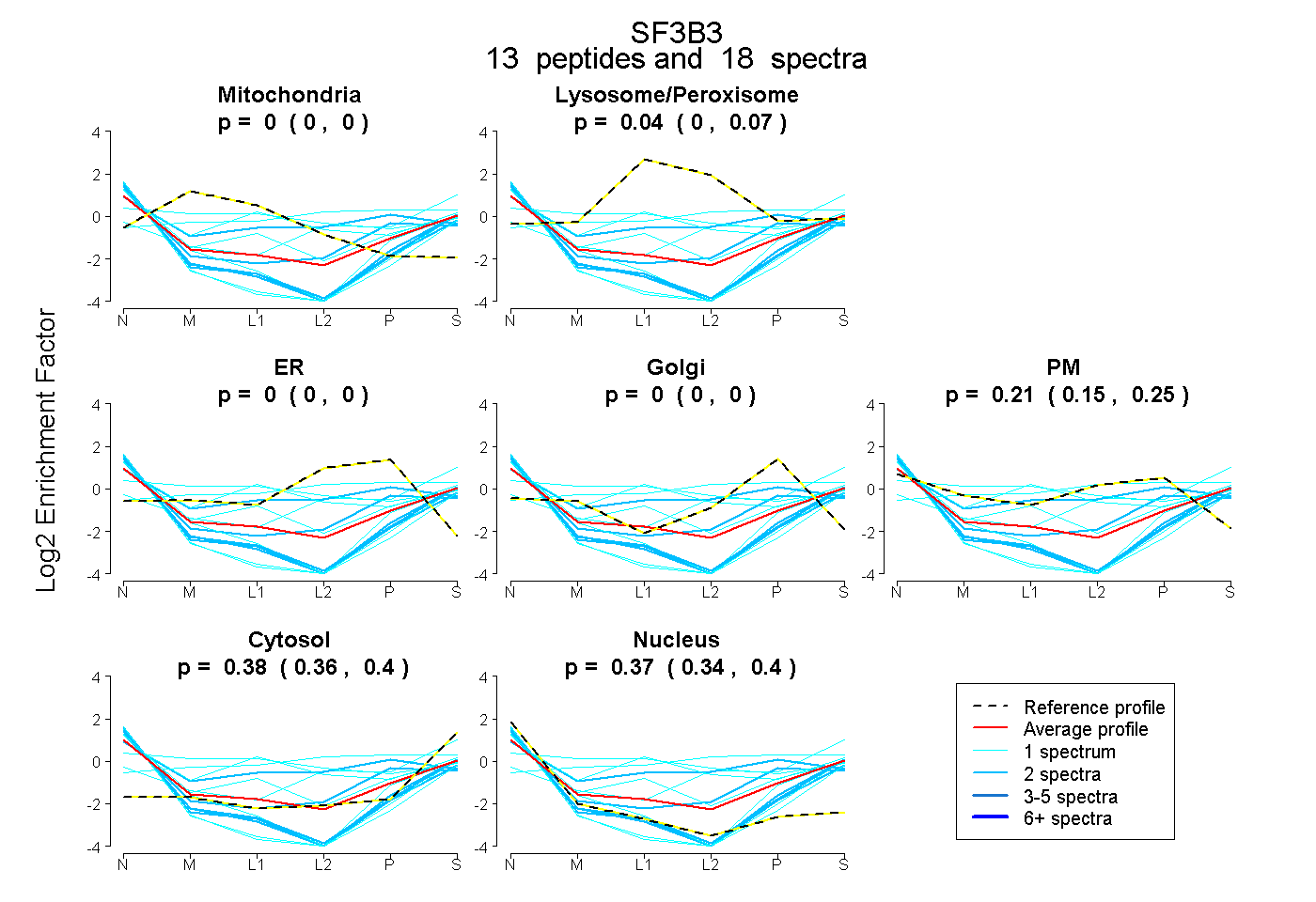 |
0.000 0.000 | 0.000 |
0.038 0.000 | 0.073 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.207 0.150 | 0.250 |
0.384 0.361 | 0.404 |
0.371 0.339 | 0.399 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
15 spectra |
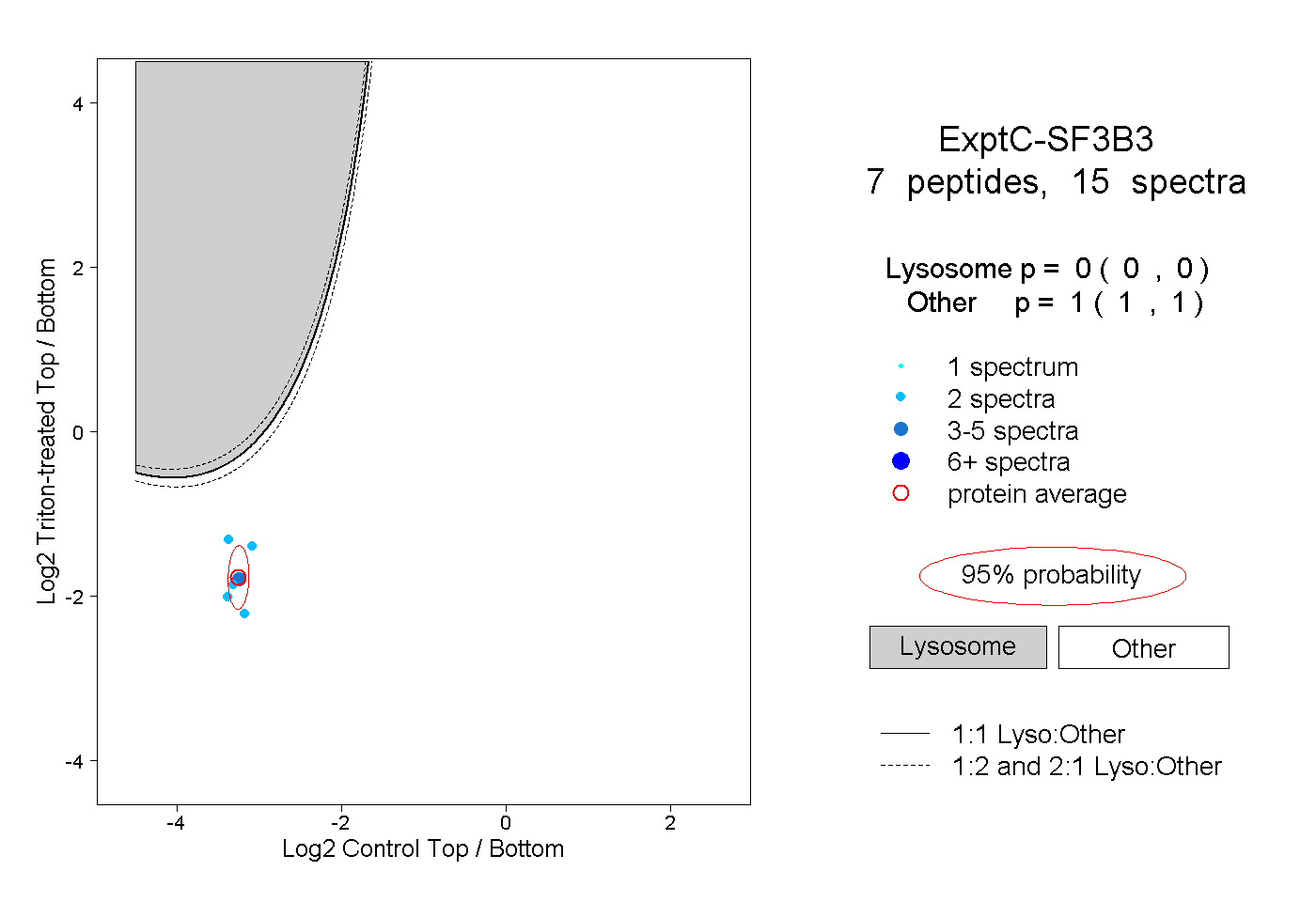 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
2 spectra |
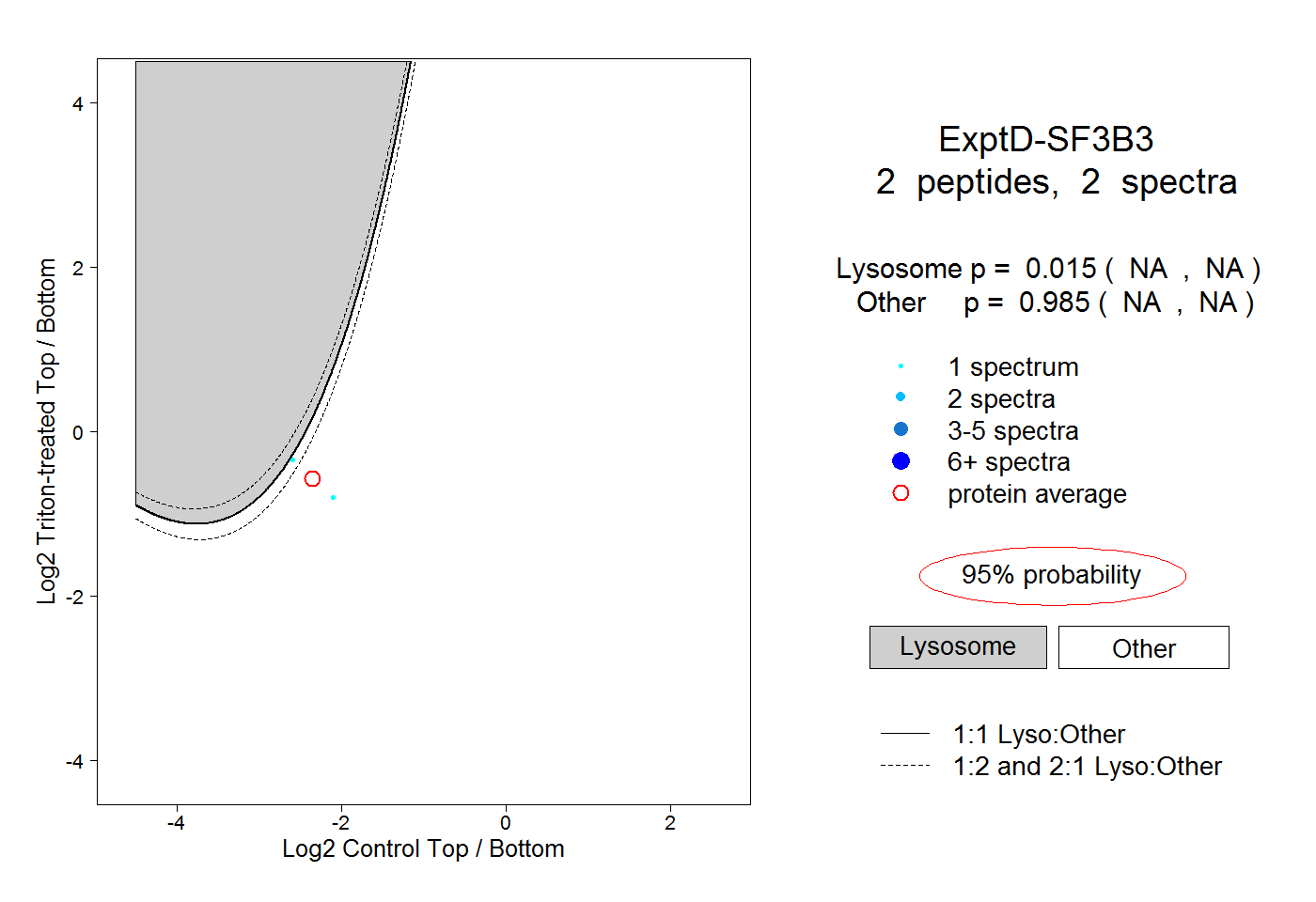 |
0.015 NA | NA |
0.985 NA | NA |