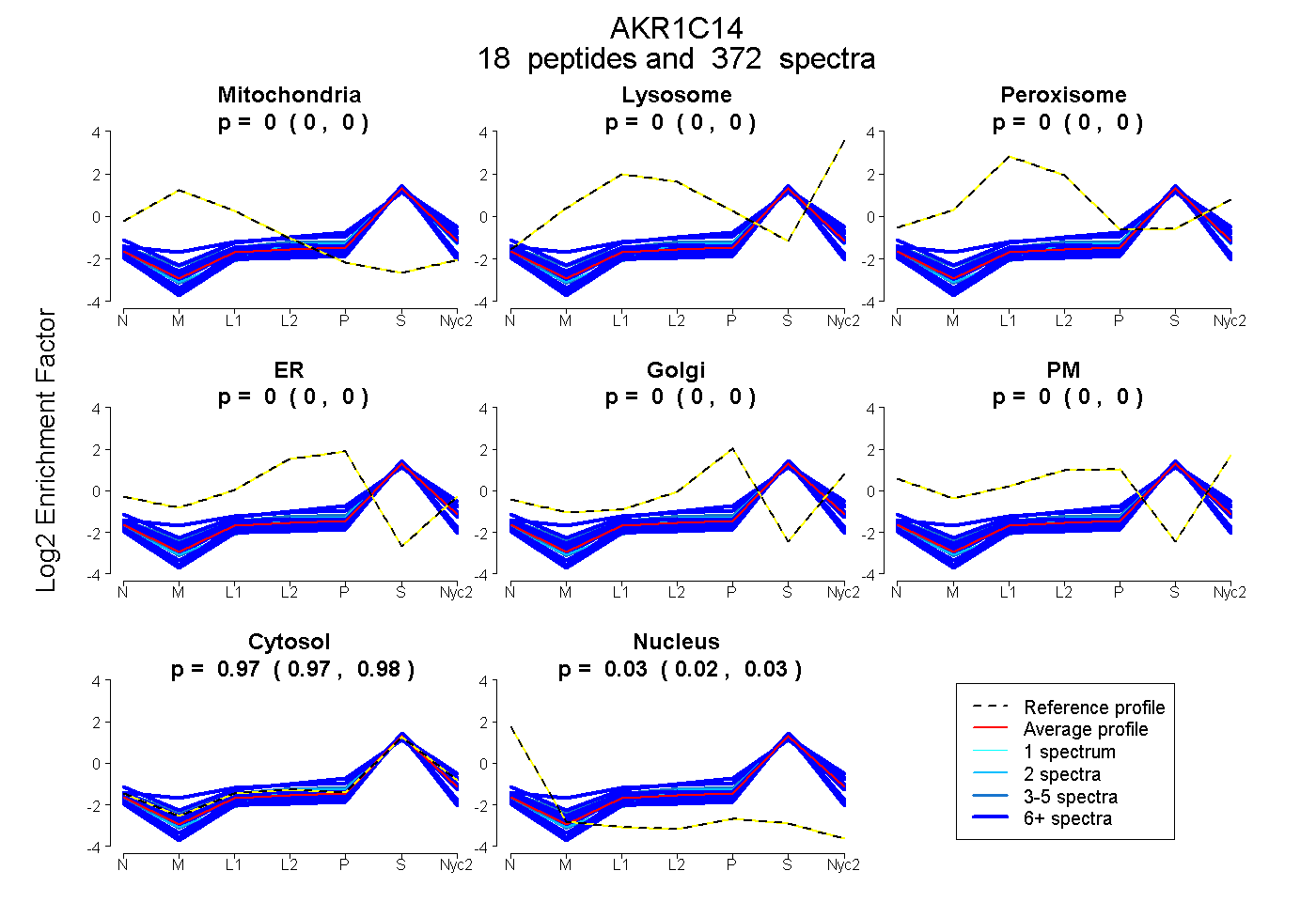
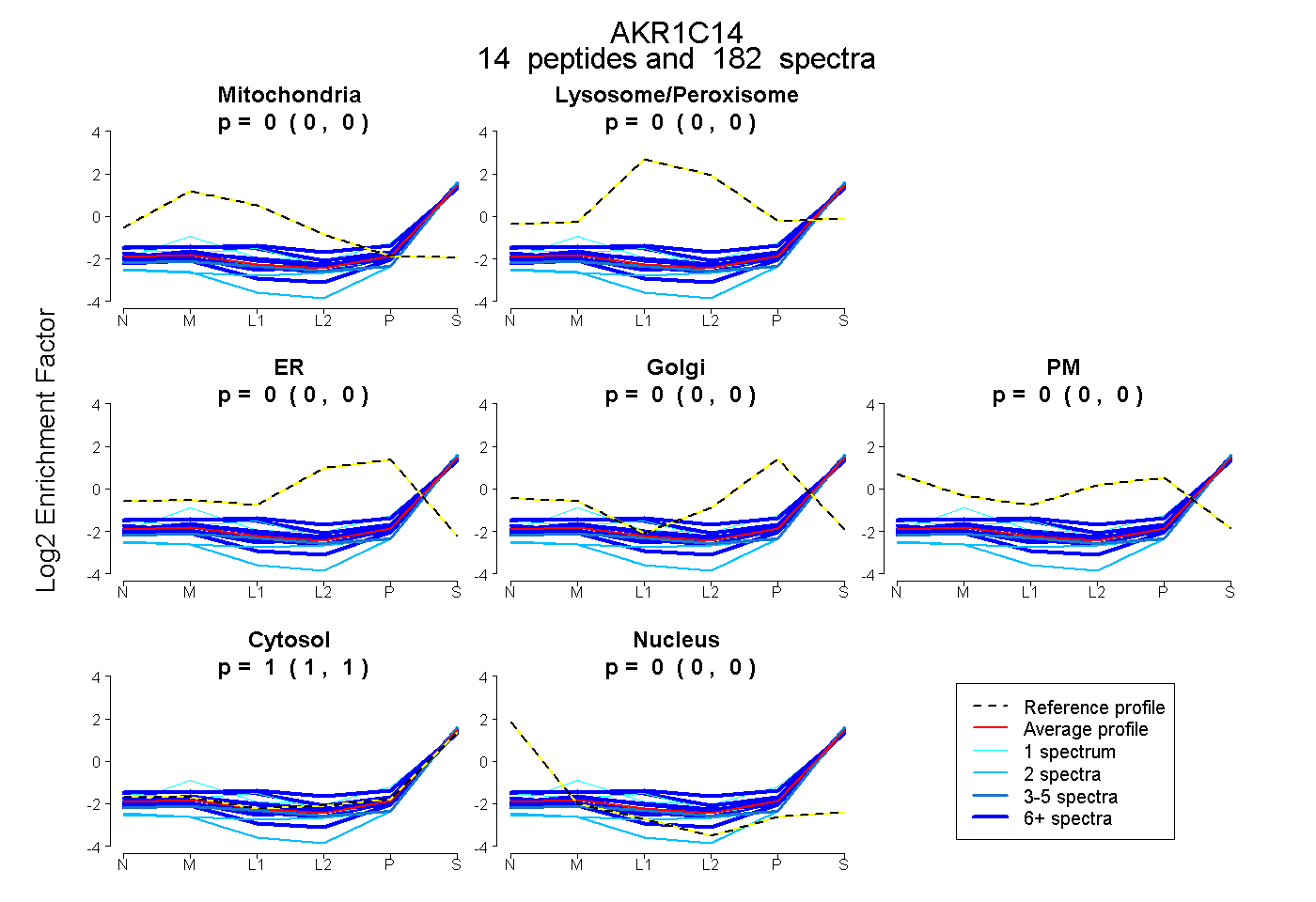
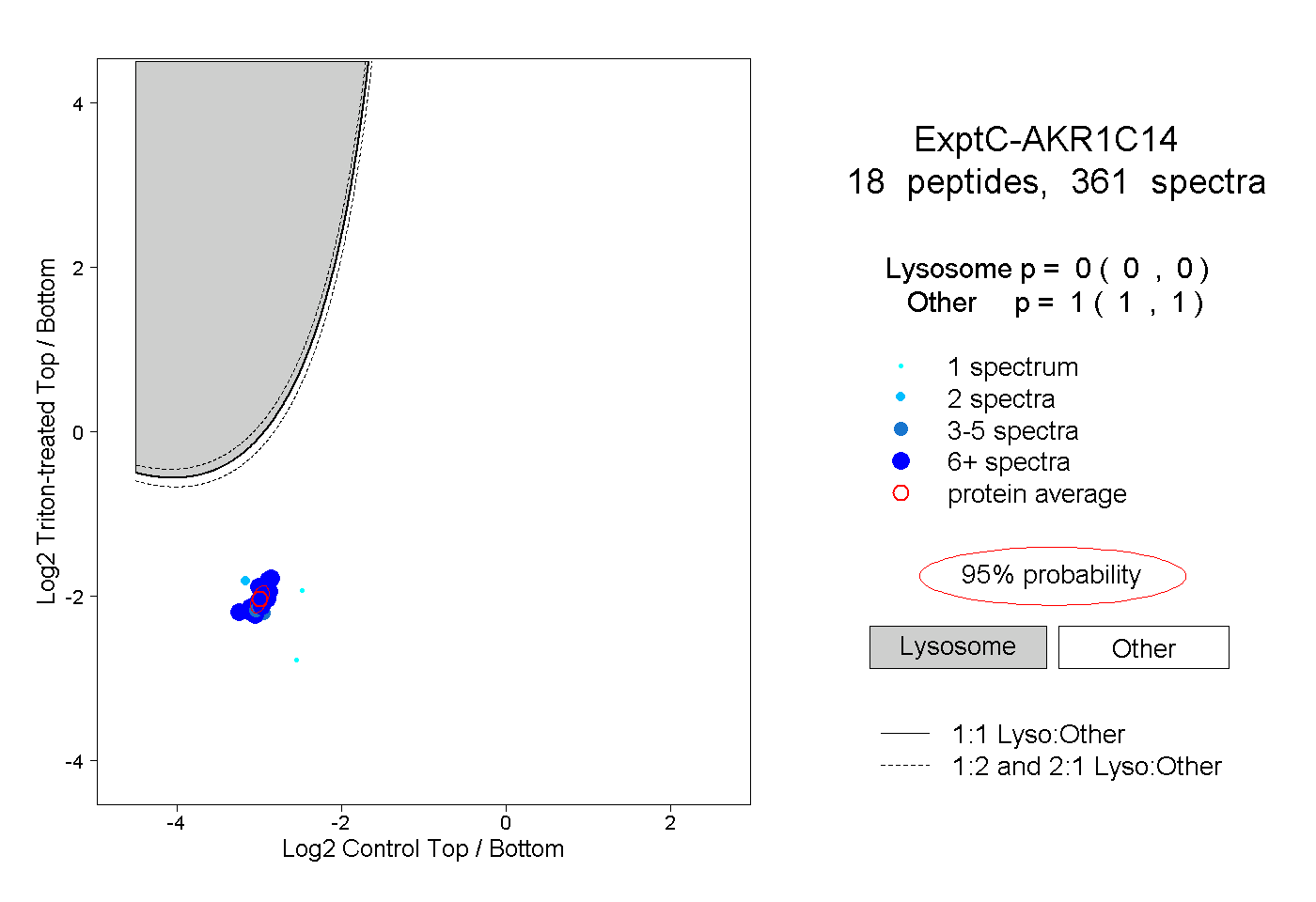
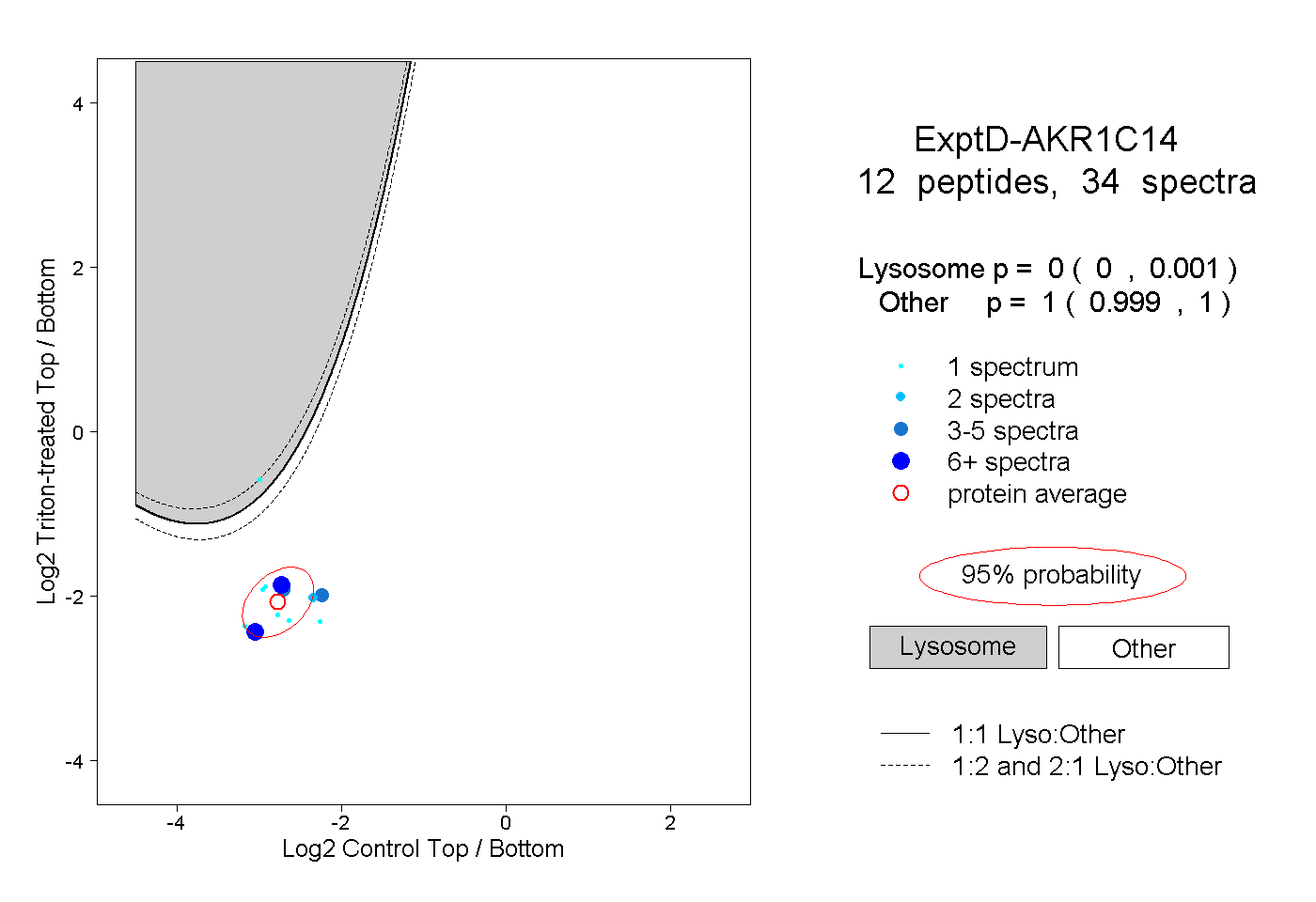
| 1 spectrum, ELTQVFEFQLASEDMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 27 spectra, MLDYCK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 22 spectra, IAIDNGFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 47 spectra, ALDGLNR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 35 spectra, YFDDHPNHPFTDE |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, YKPVCNQVECHLYLNQSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, TWVDQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 62 spectra, LLNKPGLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 19 spectra, SFNAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 21 spectra, EDIFYTSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 15 spectra, DAGLAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 29 spectra, GVVPLIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 28 spectra, SIGVSNFNCR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, DSLSIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 16 spectra, QTPALVALR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, SPVLLDDPVLCAIAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 22 spectra, IEDGTVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, DIILVSYCTLGSSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |