peptides
spectra
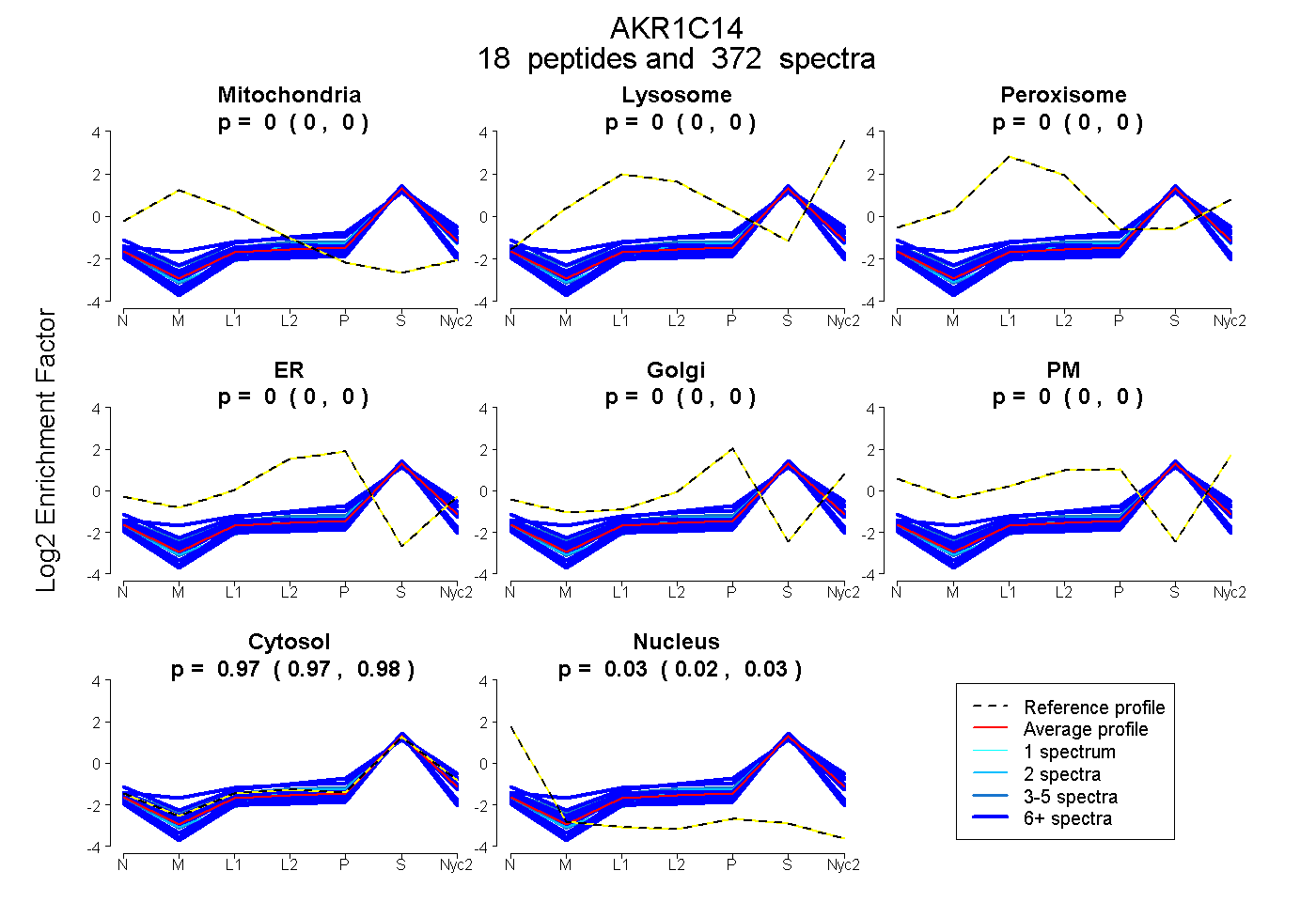
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.974 | 0.976
0.024 | 0.026
peptides
spectra
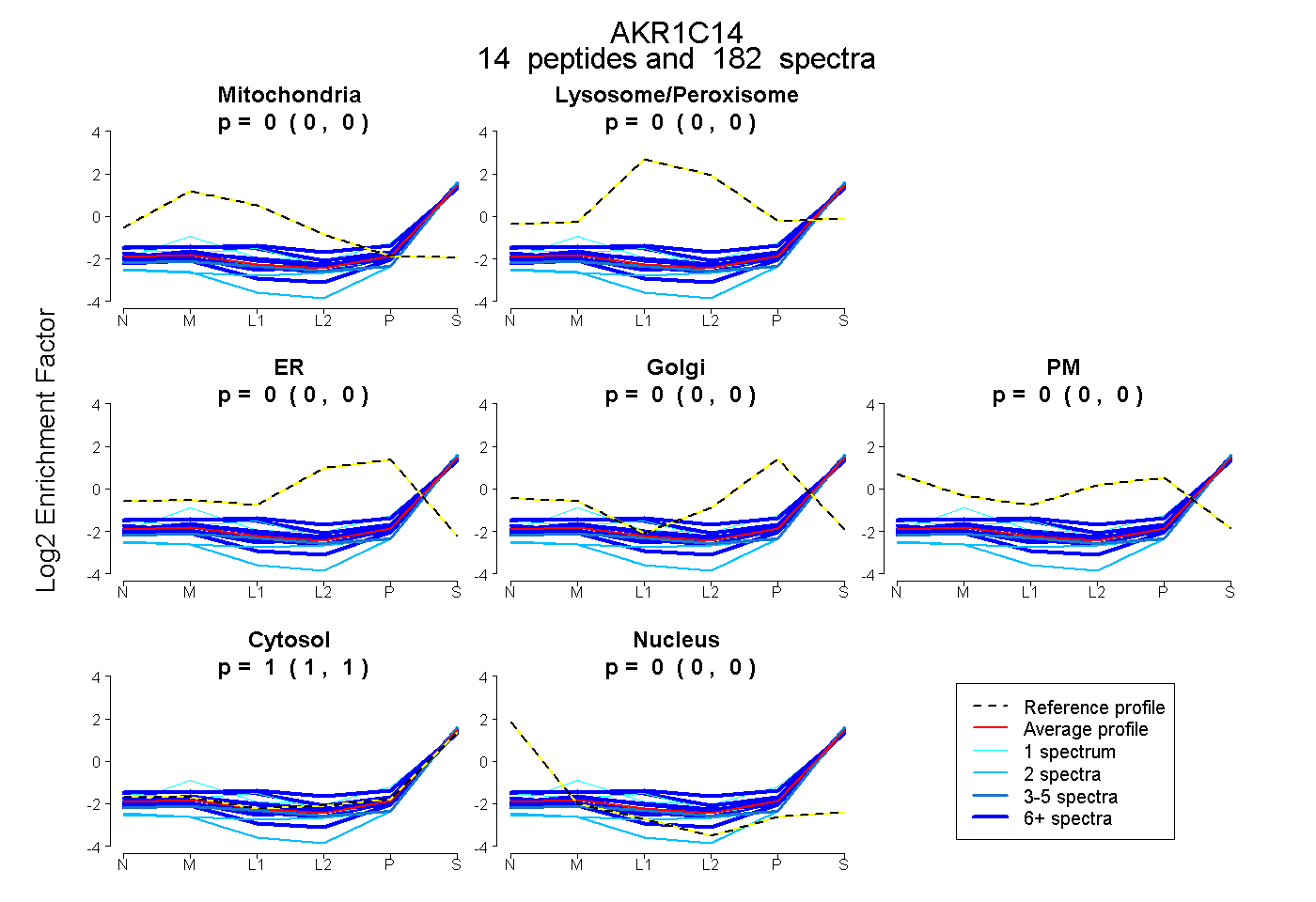
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
1.000 | 1.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
372 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.975 0.974 | 0.976 |
0.025 0.024 | 0.026 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
182 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
| 1 spectrum, ELTQVFEFQLASEDMK | 0.052 | 0.013 | 0.000 | 0.052 | 0.000 | 0.883 | 0.000 | |||
| 1 spectrum, MLDYCK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 11 spectra, IAIDNGFR | 0.033 | 0.067 | 0.000 | 0.000 | 0.000 | 0.899 | 0.000 | |||
| 24 spectra, ALDGLNR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 13 spectra, YFDDHPNHPFTDE | 0.000 | 0.145 | 0.000 | 0.000 | 0.000 | 0.855 | 0.000 | |||
| 3 spectra, YKPVCNQVECHLYLNQSK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, LLNKPGLK | 0.000 | 0.056 | 0.000 | 0.000 | 0.000 | 0.933 | 0.011 | |||
| 2 spectra, EDIFYTSK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.992 | 0.008 | |||
| 30 spectra, GVVPLIR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 19 spectra, SIGVSNFNCR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.994 | 0.006 | |||
| 15 spectra, QTPALVALR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 11 spectra, SPVLLDDPVLCAIAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 2 spectra, MDSISLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 49 spectra, LWSTFHRPELVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
361 spectra |
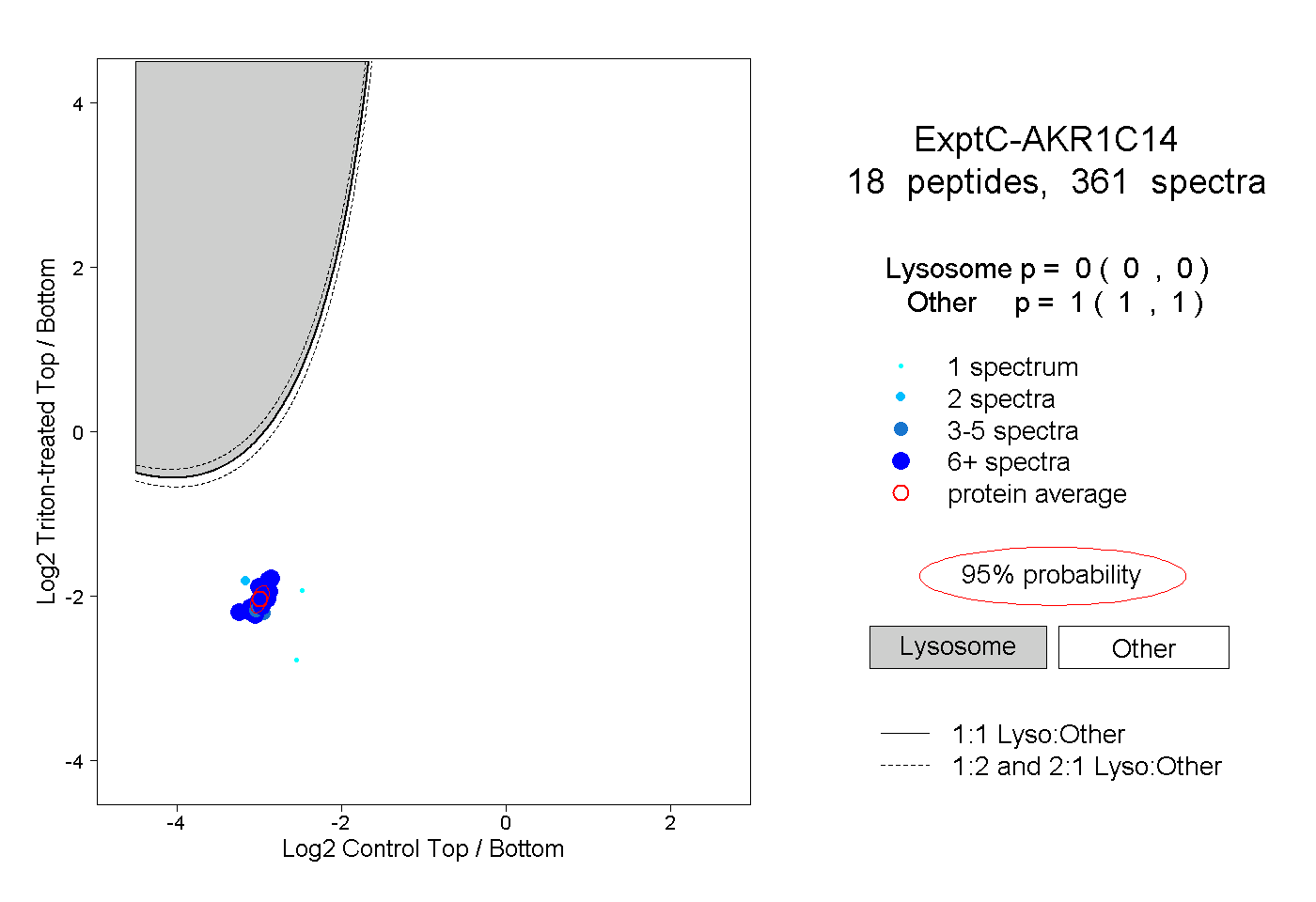 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
34 spectra |
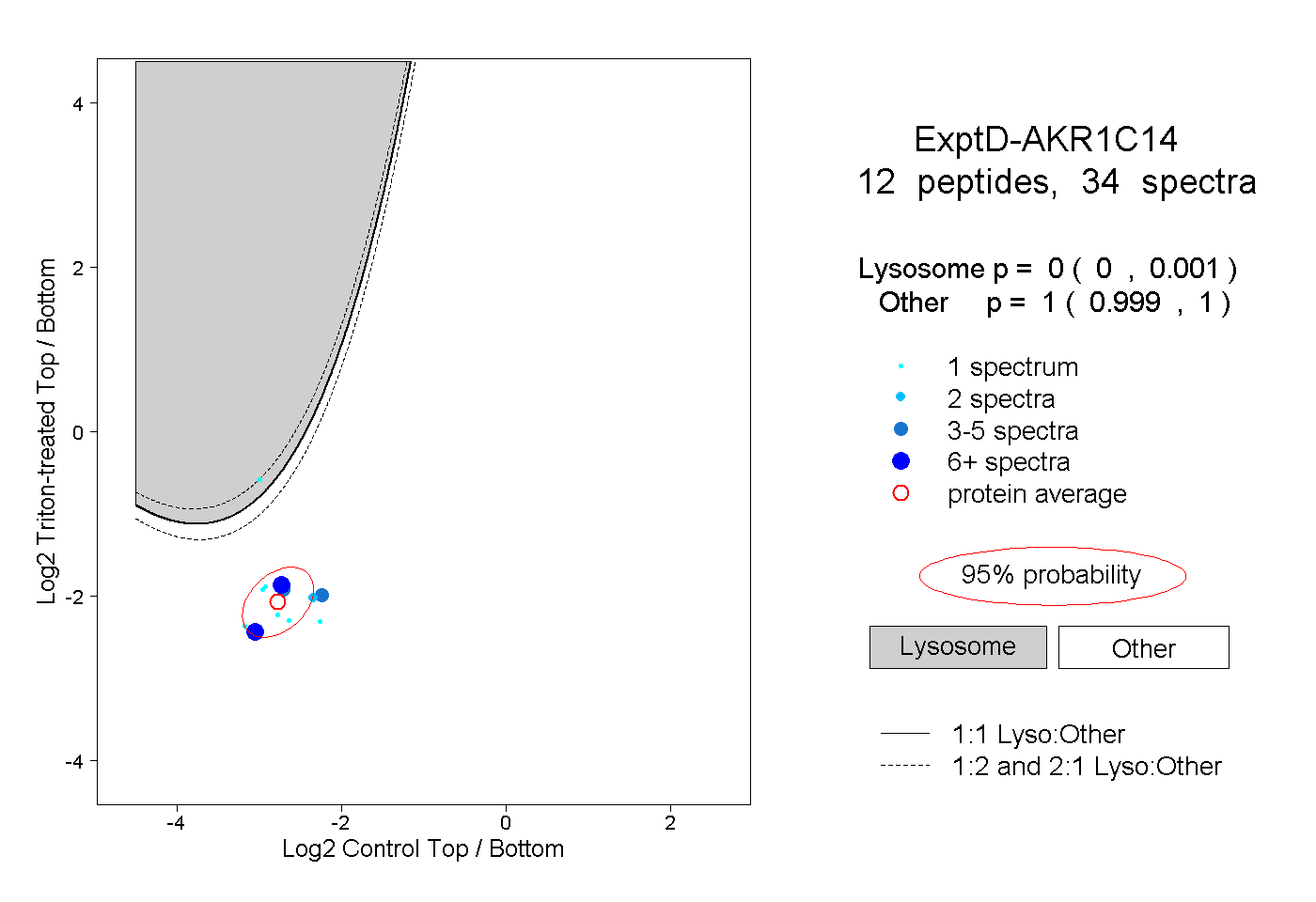 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |