peptides
spectra
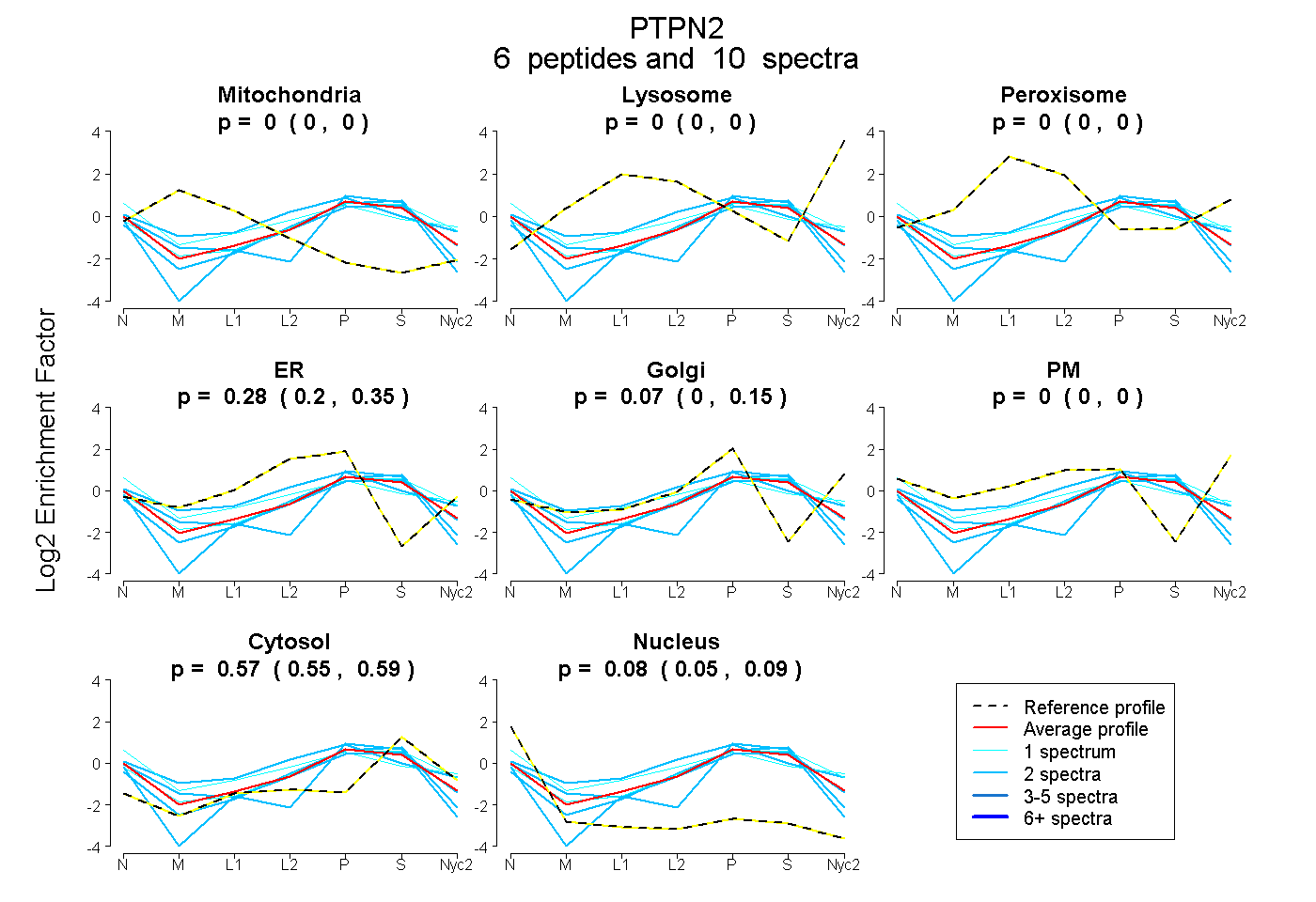
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.197 | 0.345
0.000 | 0.147
0.000 | 0.000
0.553 | 0.591
0.053 | 0.095
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
10 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.279 0.197 | 0.345 |
0.071 0.000 | 0.147 |
0.000 0.000 | 0.000 |
0.574 0.553 | 0.591 |
0.076 0.053 | 0.095 |
| 2 spectra, VPDTVEESSESILR | 0.000 | 0.000 | 0.000 | 0.000 | 0.117 | 0.000 | 0.654 | 0.229 | ||
| 2 spectra, EDLSPVCDHSQNR | 0.000 | 0.000 | 0.012 | 0.462 | 0.000 | 0.072 | 0.454 | 0.000 | ||
| 1 spectrum, NESHDYPHR | 0.000 | 0.000 | 0.000 | 0.101 | 0.278 | 0.000 | 0.615 | 0.006 | ||
| 1 spectrum, IGSEDEK | 0.000 | 0.000 | 0.000 | 0.201 | 0.000 | 0.301 | 0.424 | 0.074 | ||
| 2 spectra, MGLIQTPDQLR | 0.000 | 0.000 | 0.000 | 0.277 | 0.051 | 0.000 | 0.589 | 0.082 | ||
| 2 spectra, EFEELDAQCR | 0.000 | 0.000 | 0.000 | 0.252 | 0.000 | 0.000 | 0.654 | 0.093 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptide |
2 spectra |
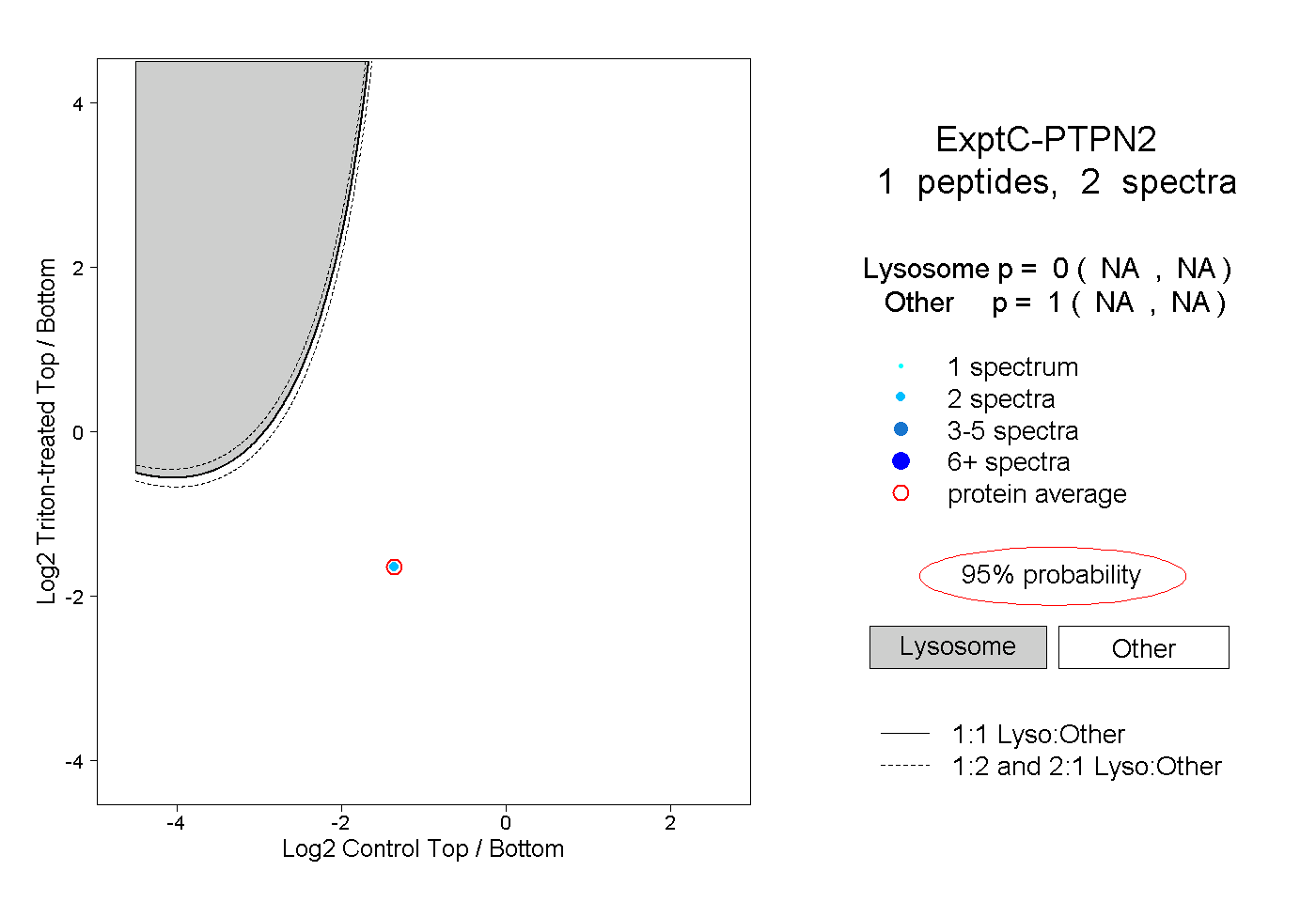 |
0.000 NA | NA |
1.000 NA | NA |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
1 spectrum |
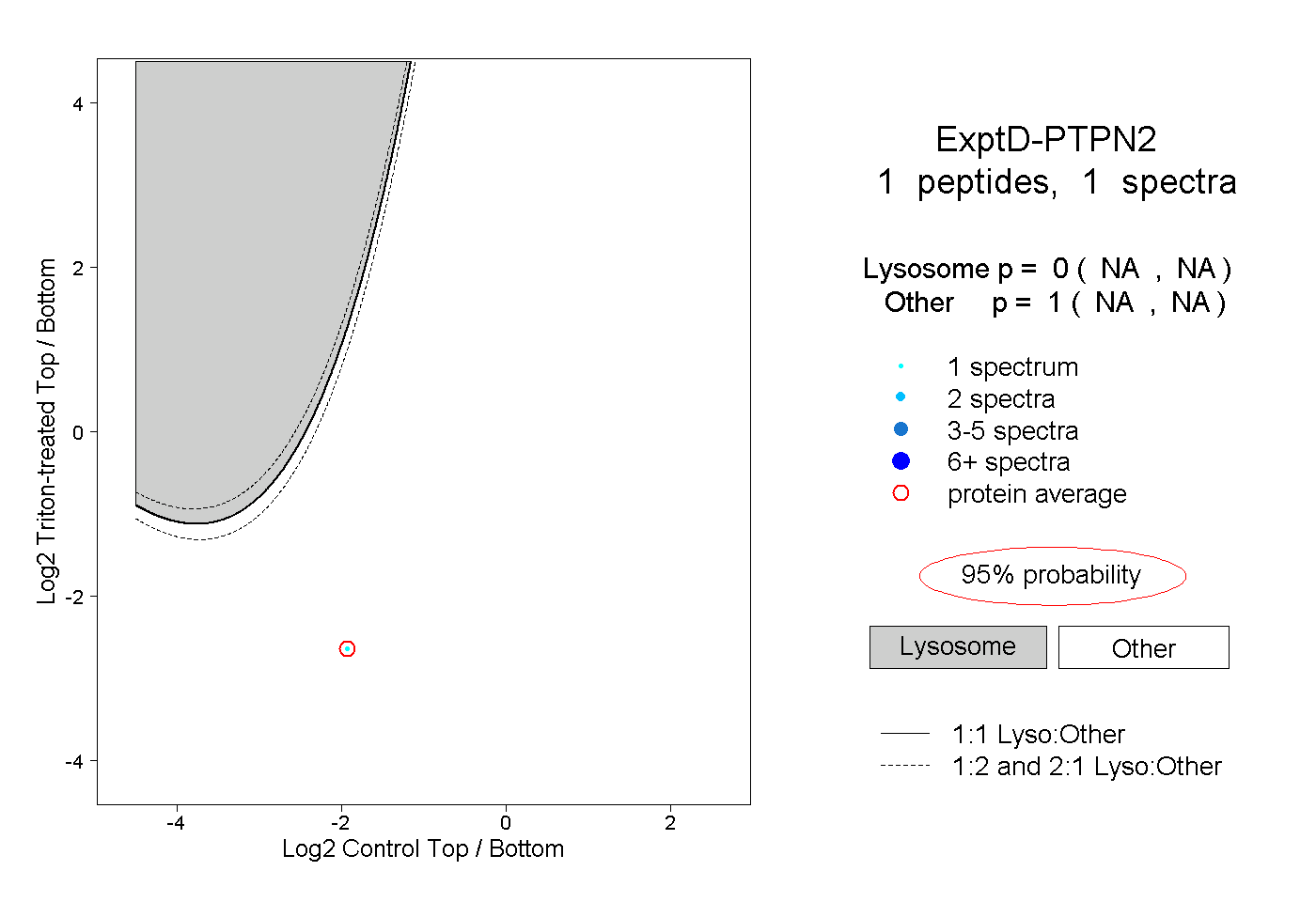 |
0.000 NA | NA |
1.000 NA | NA |