peptides
spectra
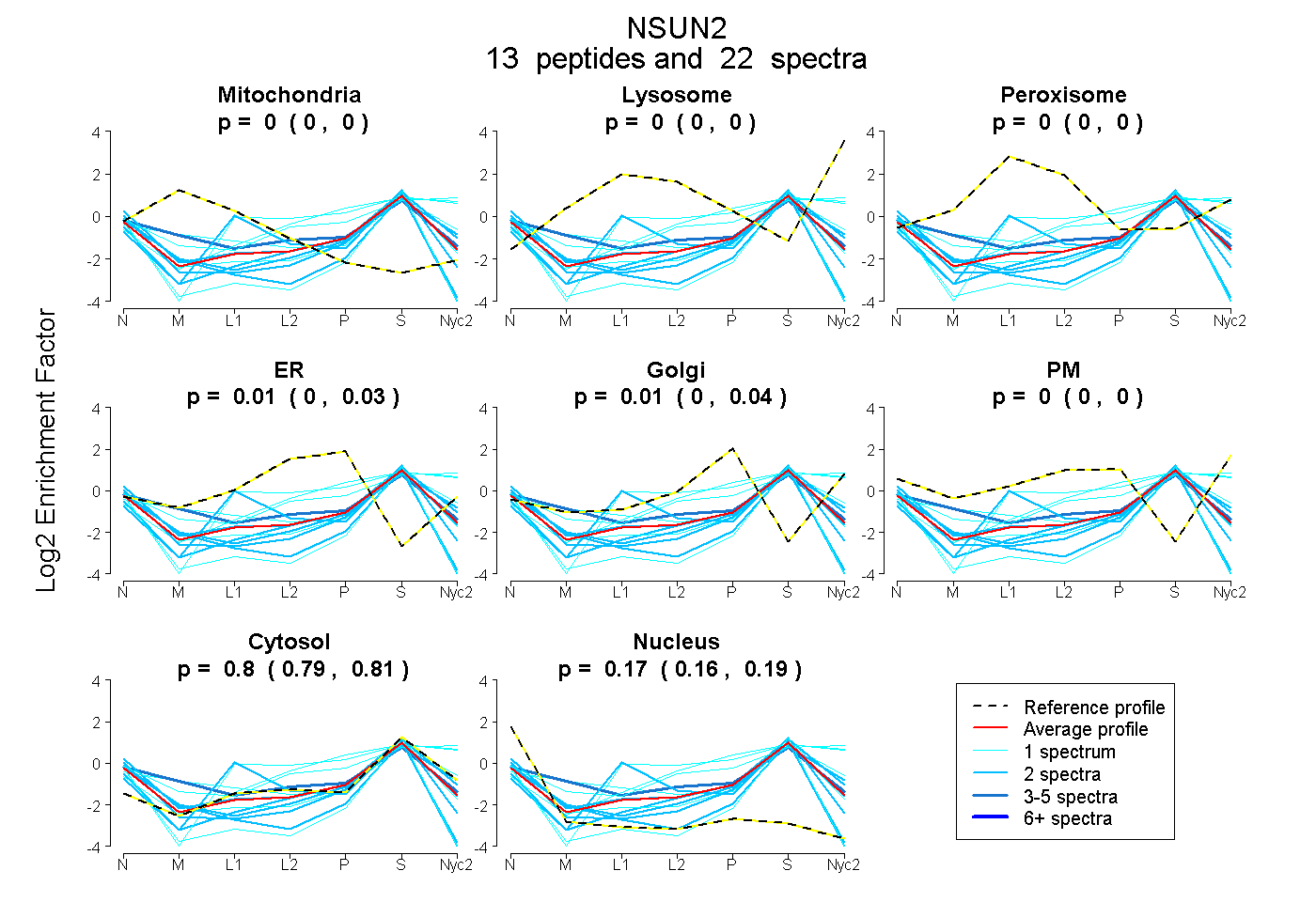
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.032
0.000 | 0.037
0.000 | 0.002
0.791 | 0.807
0.157 | 0.187
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
22 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.013 0.000 | 0.032 |
0.013 0.000 | 0.037 |
0.000 0.000 | 0.002 |
0.800 0.791 | 0.807 |
0.174 0.157 | 0.187 |
| 1 spectrum, LSSEAYSQVK | 0.000 | 0.072 | 0.000 | 0.000 | 0.289 | 0.004 | 0.635 | 0.000 | ||
| 2 spectra, EPLPATLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.861 | 0.139 | ||
| 2 spectra, WMPGVSQWK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.774 | 0.226 | ||
| 1 spectrum, APMPWNK | 0.214 | 0.004 | 0.000 | 0.000 | 0.000 | 0.056 | 0.725 | 0.000 | ||
| 2 spectra, IITVSMEDVK | 0.000 | 0.000 | 0.079 | 0.000 | 0.000 | 0.000 | 0.796 | 0.125 | ||
| 2 spectra, MNILTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.109 | 0.721 | 0.171 | ||
| 1 spectrum, YEPDSANPDTLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.513 | 0.487 | ||
| 1 spectrum, FYALDPSFPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.777 | 0.223 | ||
| 1 spectrum, WTTLNSLQLHGLQLR | 0.000 | 0.006 | 0.000 | 0.000 | 0.000 | 0.358 | 0.636 | 0.000 | ||
| 2 spectra, TLLTQENPFFR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.529 | 0.471 | ||
| 4 spectra, GAEQLAEGGR | 0.210 | 0.000 | 0.000 | 0.000 | 0.016 | 0.049 | 0.682 | 0.043 | ||
| 2 spectra, NNSGEEFDCAFR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.582 | 0.418 | ||
| 1 spectrum, FHQFLVSETESGNISR | 0.000 | 0.042 | 0.000 | 0.000 | 0.000 | 0.266 | 0.692 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
1 spectrum |
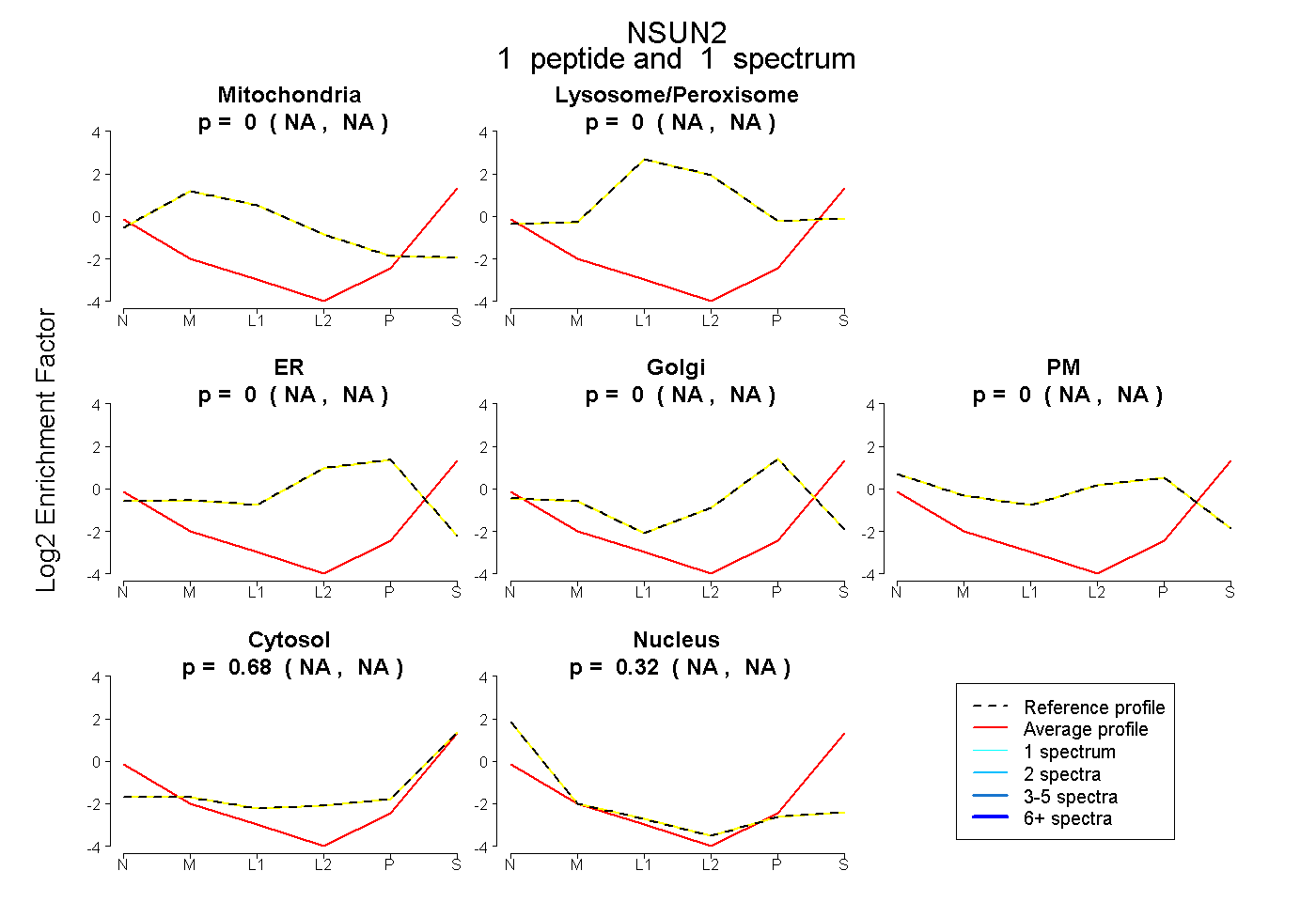 |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.680 NA | NA |
0.320 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
11 spectra |
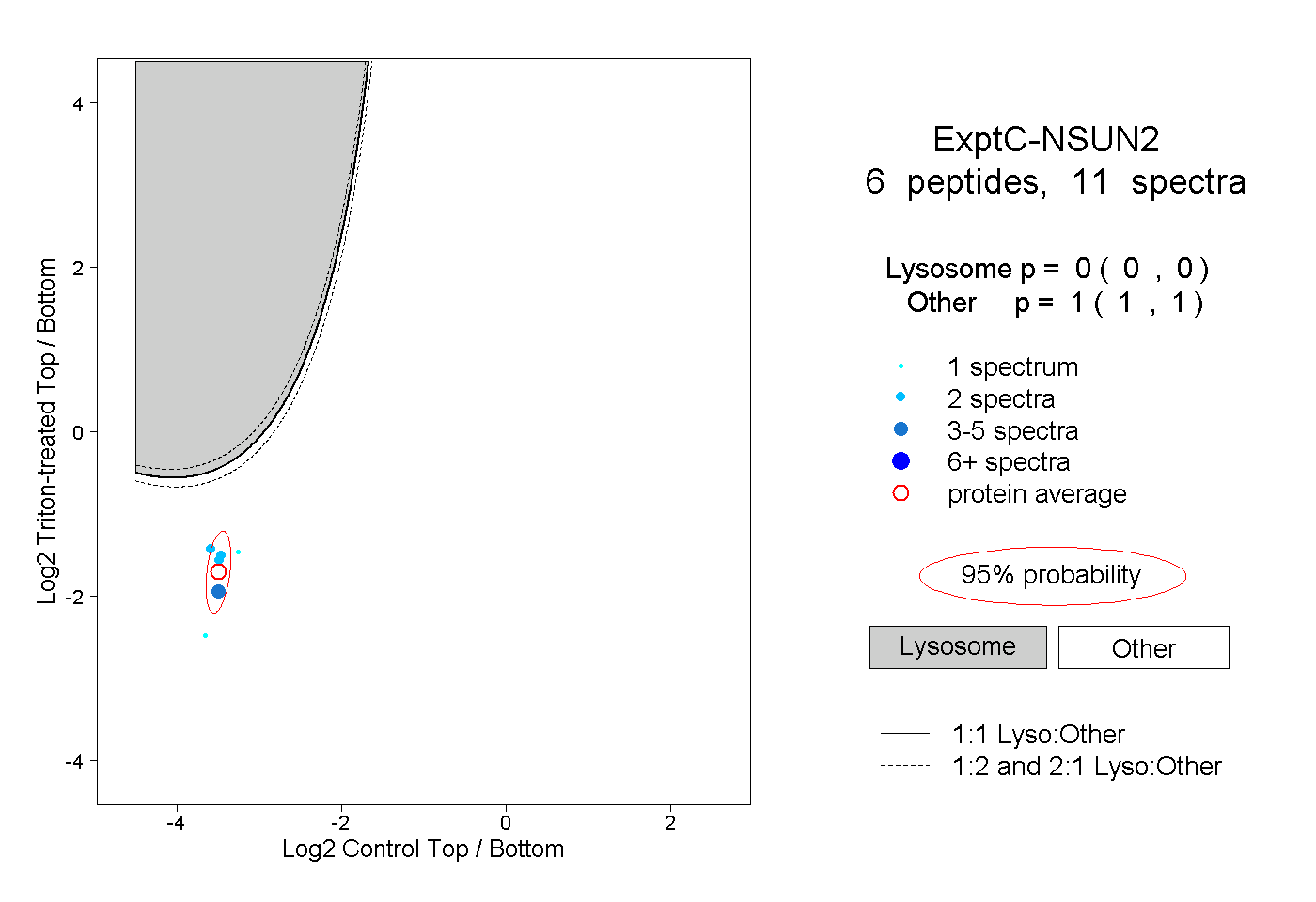 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |