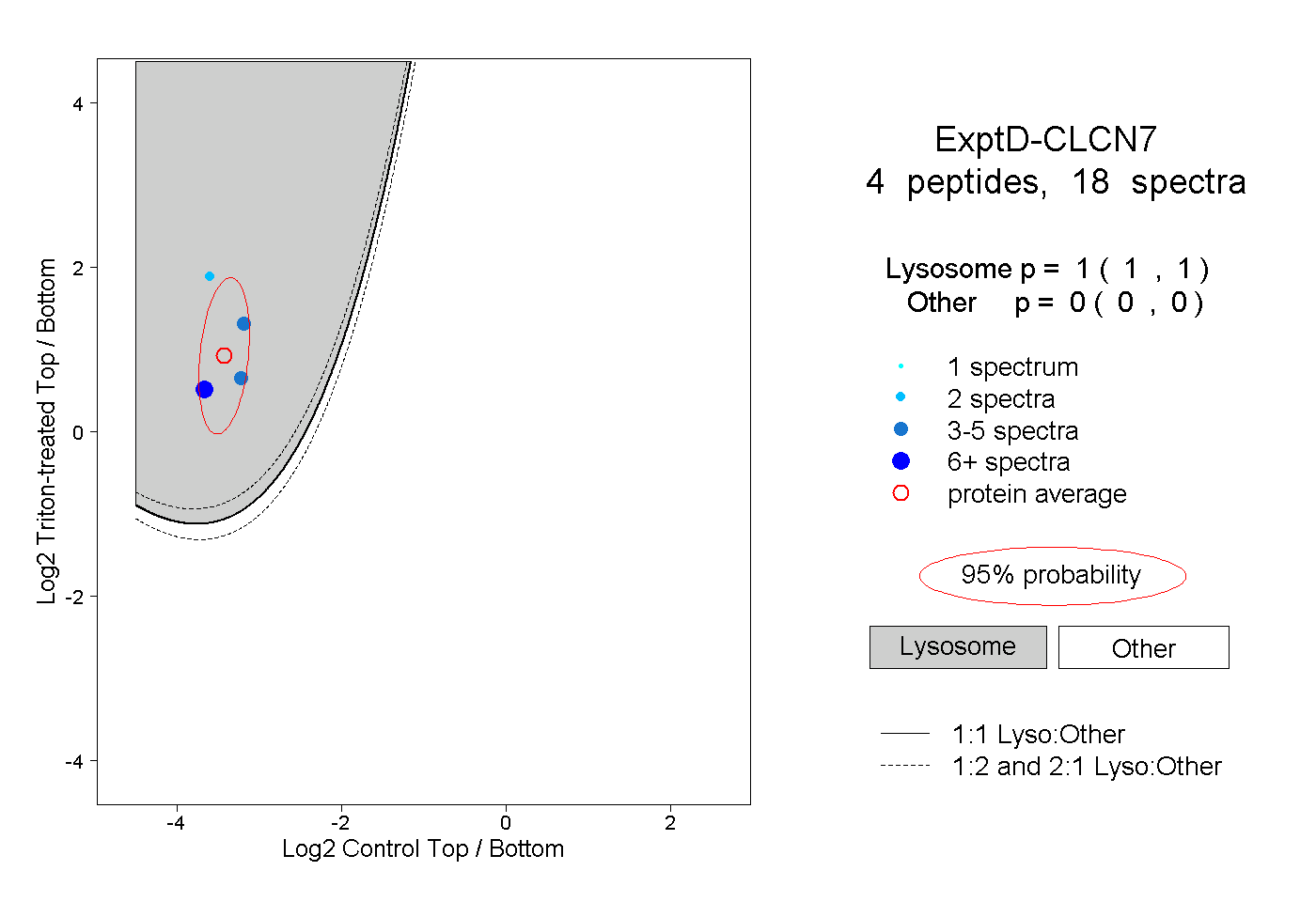
peptides
spectra
0.000 | 0.000
0.985 | 1.000
0.000 | 0.002
0.000 | 0.012
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
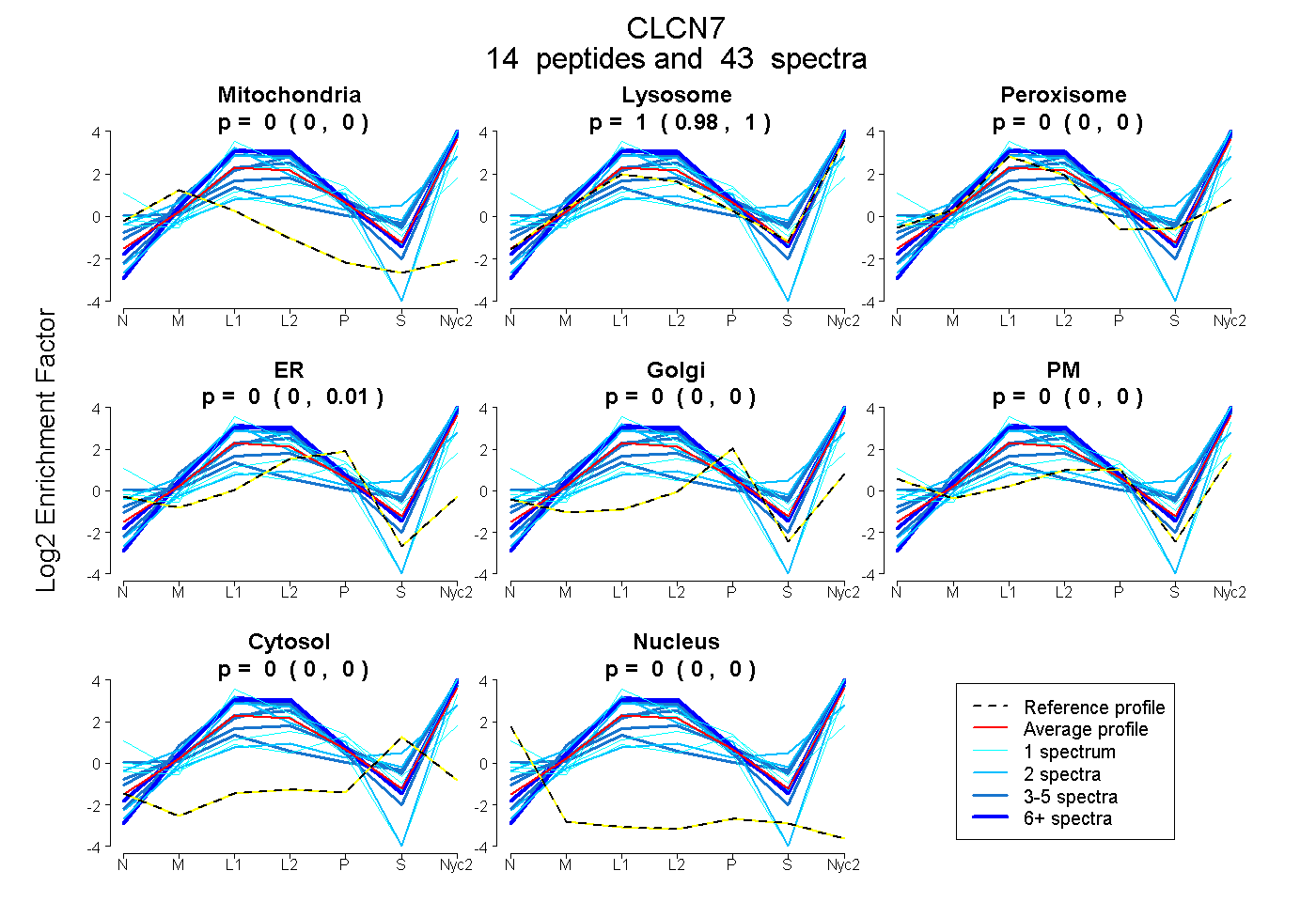
peptides
spectra
0.000 | 0.000
0.874 | 0.946
0.047 | 0.121
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
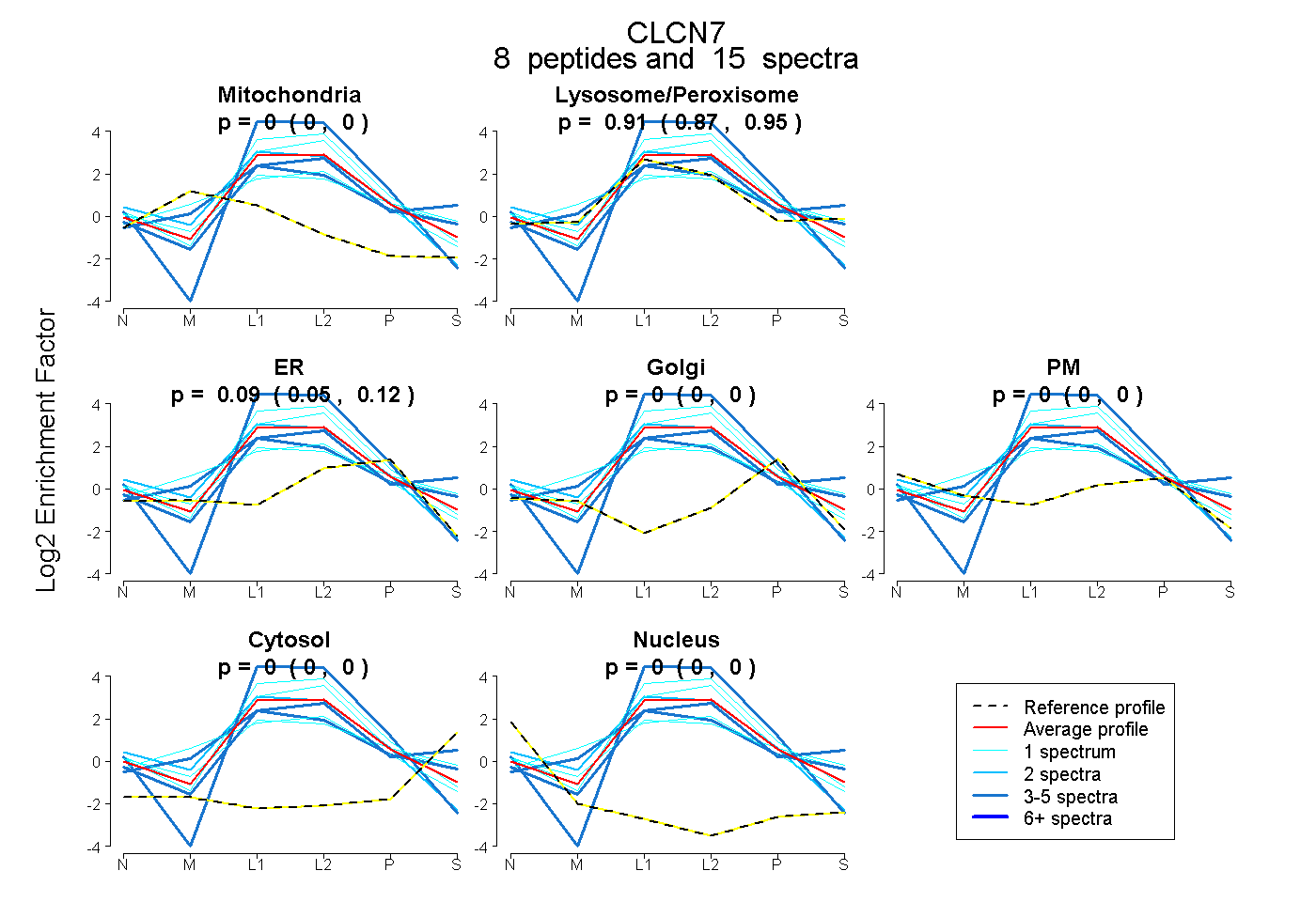
peptides
spectra
1.000 | 1.000
0.000 | 0.000