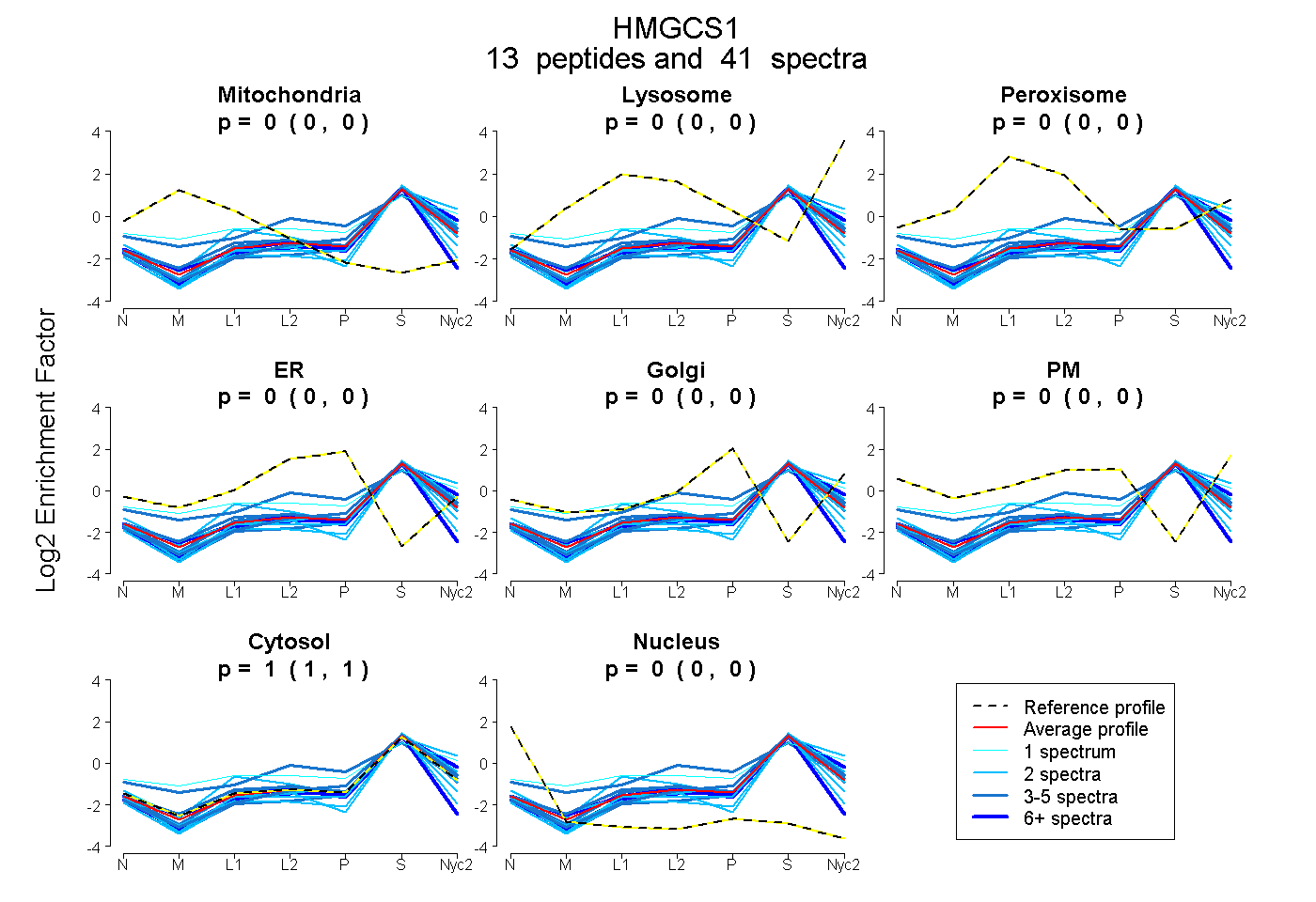
peptides
spectra
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
1.000 | 1.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
41 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
| 7 spectra, MFLNDFLNDQNR | 0.000 | 0.034 | 0.000 | 0.000 | 0.000 | 0.000 | 0.966 | 0.000 | ||
| 3 spectra, YTIGLGQAR | 0.000 | 0.042 | 0.000 | 0.000 | 0.000 | 0.000 | 0.958 | 0.000 | ||
| 2 spectra, MGFCTDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 3 spectra, CYSVYR | 0.000 | 0.000 | 0.117 | 0.171 | 0.000 | 0.000 | 0.711 | 0.000 | ||
| 3 spectra, LEDTYFDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.993 | 0.007 | ||
| 1 spectrum, VTQDATPGSALDK | 0.010 | 0.114 | 0.115 | 0.000 | 0.000 | 0.081 | 0.680 | 0.000 | ||
| 2 spectra, TCVAPDVFAENMK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.976 | 0.024 | ||
| 3 spectra, ITASLCDLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, NSIYSGLEAFGDVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 6 spectra, LSIQCYLSALDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.904 | 0.096 | ||
| 2 spectra, NSLSYDCIGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.904 | 0.096 | ||
| 5 spectra, YDGVDAGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, ASAELFNQK | 0.000 | 0.147 | 0.000 | 0.000 | 0.000 | 0.000 | 0.853 | 0.000 |
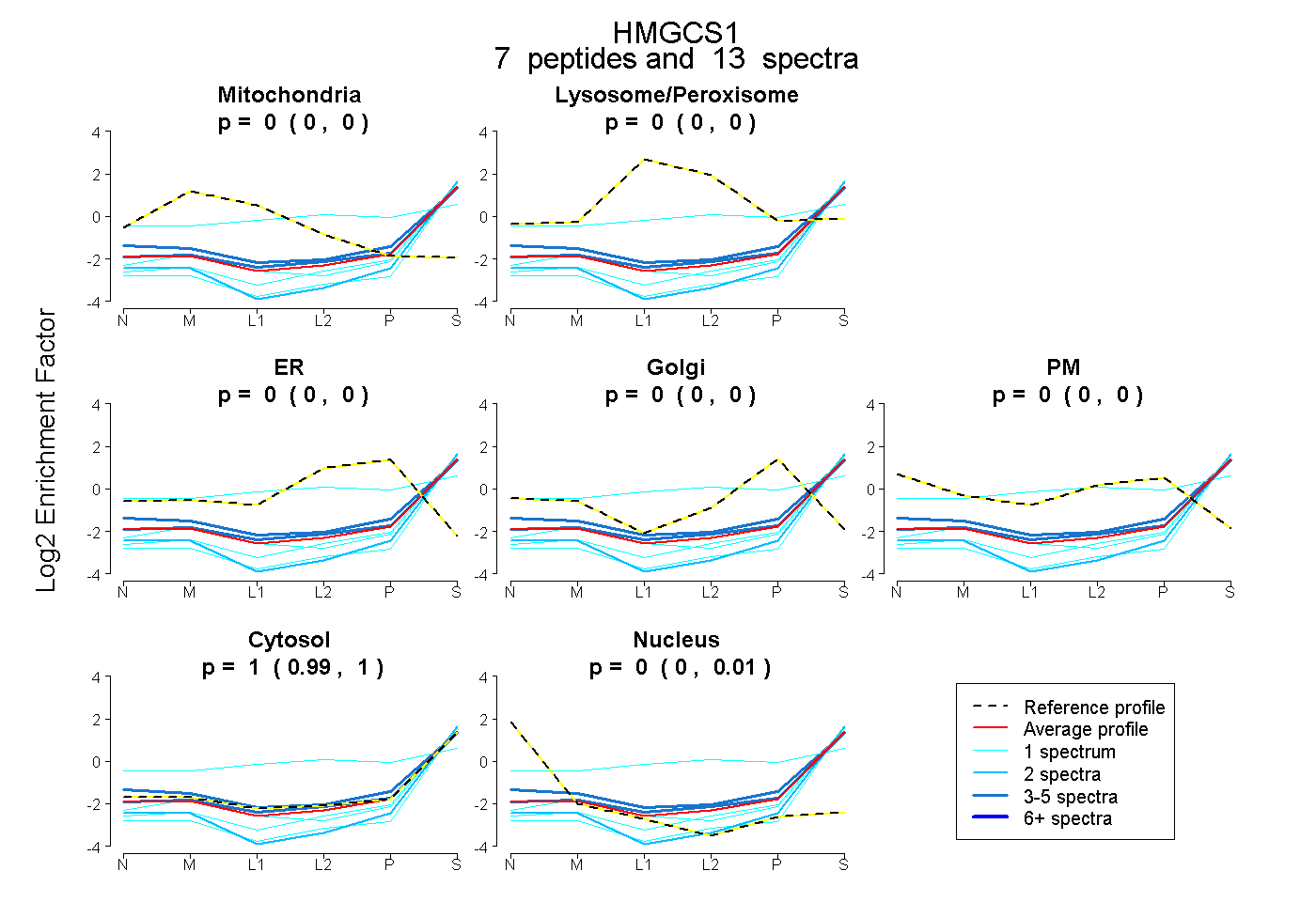
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
13 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
1.000 0.987 | 1.000 |
0.000 0.000 | 0.009 |
|||
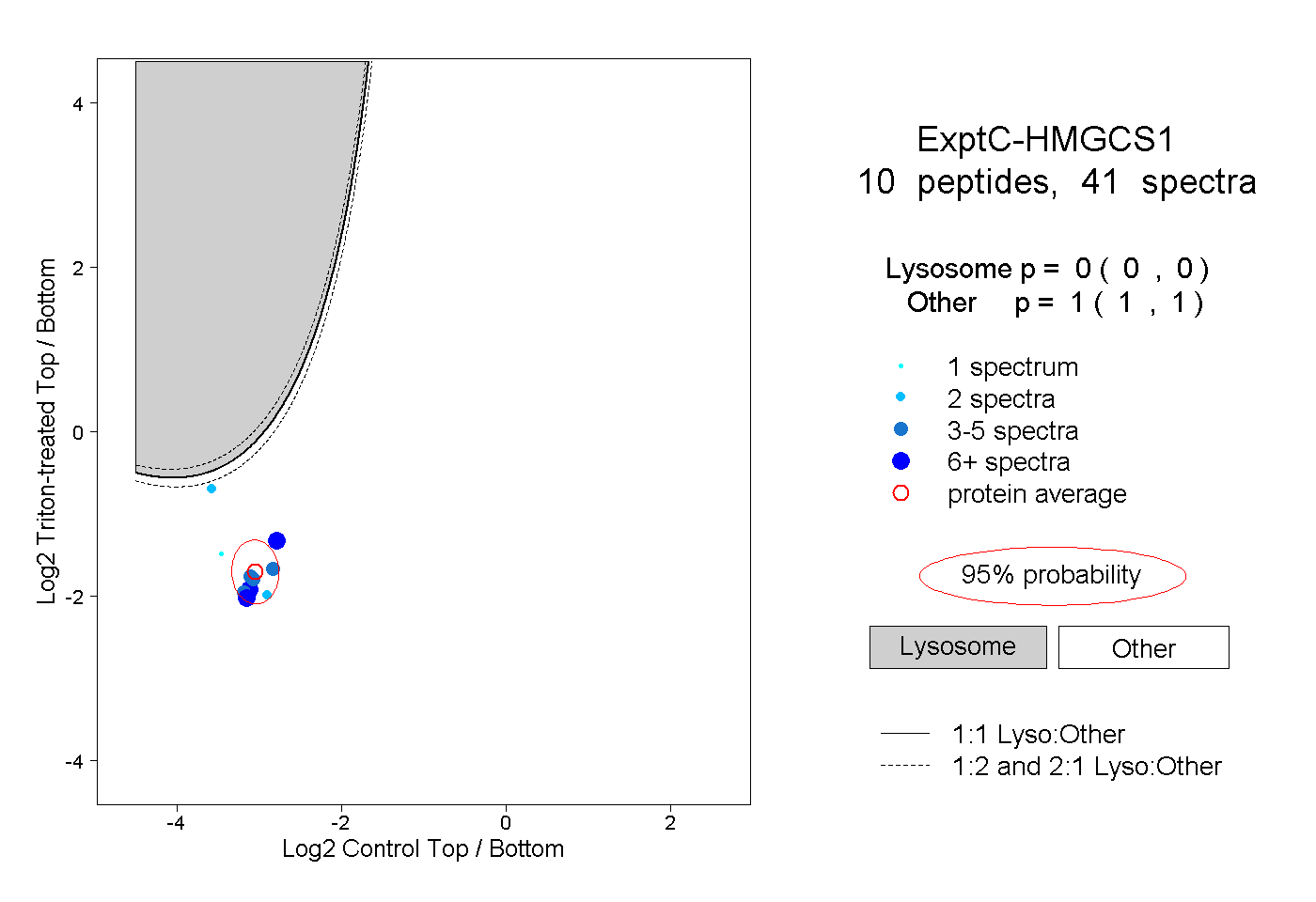
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
41 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
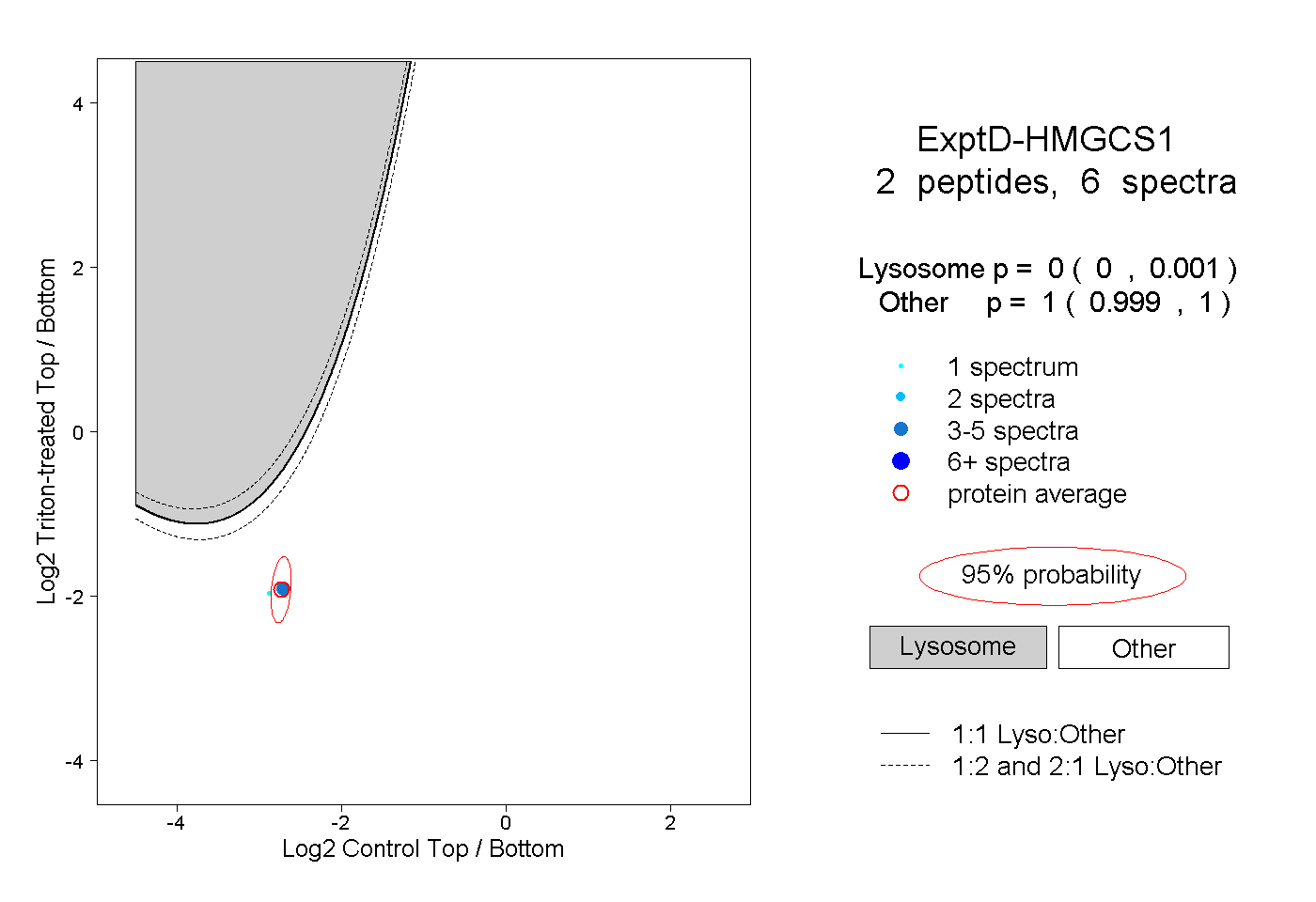
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
6 spectra |
 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |