peptides
spectra
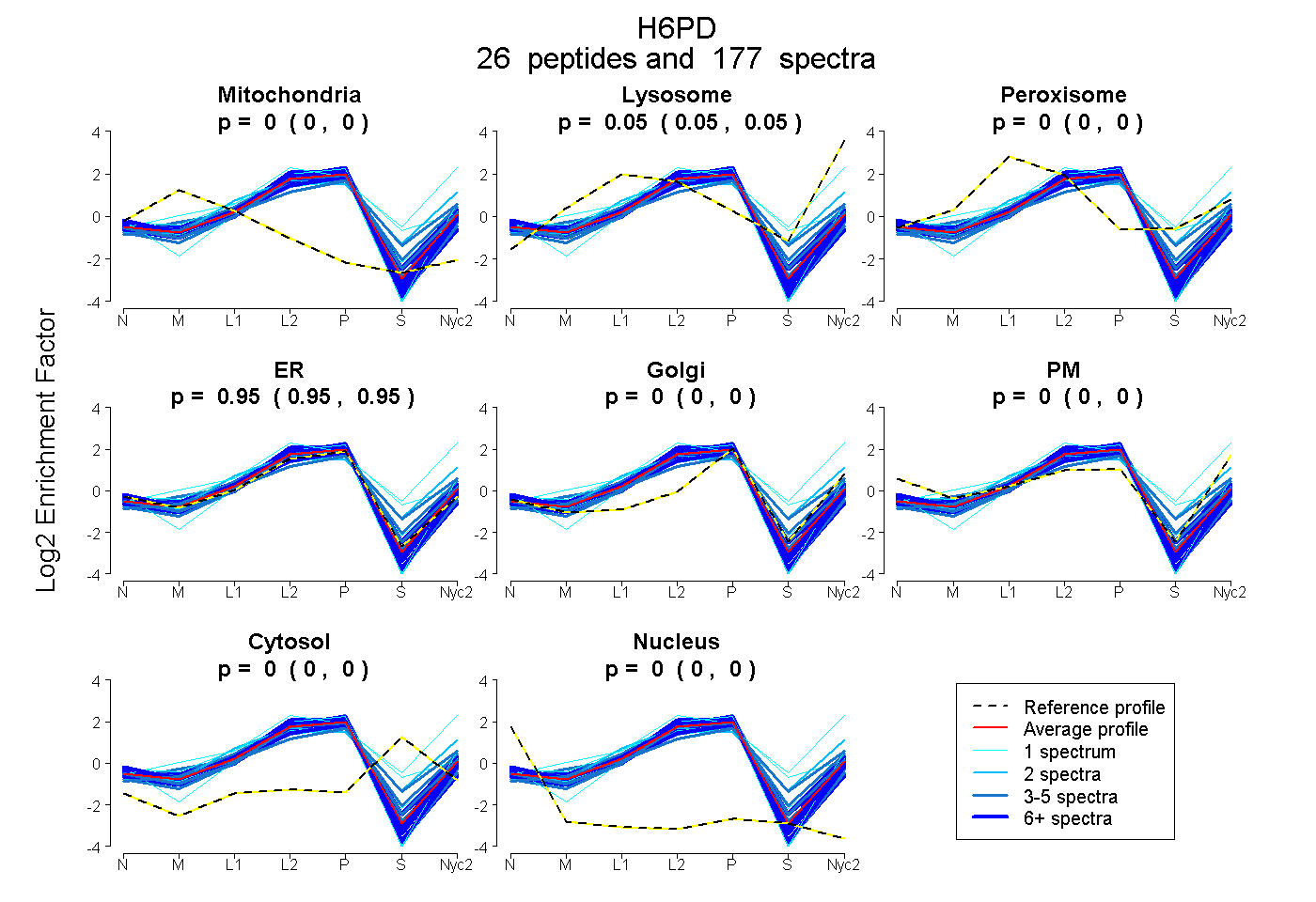
0.000 | 0.000
0.050 | 0.054
0.000 | 0.000
0.946 | 0.950
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
177 spectra |
 |
0.000 0.000 | 0.000 |
0.052 0.050 | 0.054 |
0.000 0.000 | 0.000 |
0.948 0.946 | 0.950 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 5 spectra, ASFYEEYGVIR | 0.061 | 0.040 | 0.000 | 0.899 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 16 spectra, AQFLQLSQYR | 0.000 | 0.027 | 0.000 | 0.973 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 22 spectra, MSLSLPLINR | 0.000 | 0.045 | 0.000 | 0.955 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 8 spectra, ALDGLWNR | 0.000 | 0.059 | 0.000 | 0.941 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, DIETQVQQDGLWEAGR | 0.000 | 0.452 | 0.000 | 0.043 | 0.305 | 0.103 | 0.097 | 0.000 | ||
| 5 spectra, VPYYNIHPMPVHLHQR | 0.000 | 0.218 | 0.000 | 0.557 | 0.106 | 0.000 | 0.119 | 0.000 | ||
| 1 spectrum, VELLLK | 0.000 | 0.142 | 0.000 | 0.858 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 4 spectra, SNAILGQYQAYSGQVR | 0.000 | 0.078 | 0.091 | 0.656 | 0.087 | 0.088 | 0.000 | 0.000 | ||
| 2 spectra, HWVPER | 0.000 | 0.068 | 0.000 | 0.932 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, DLVSPR | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 4 spectra, DLVPSR | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, SPLITAWPEELISK | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 5 spectra, WEGVPFILMSGK | 0.000 | 0.063 | 0.000 | 0.907 | 0.023 | 0.000 | 0.007 | 0.000 | ||
| 11 spectra, VDHYLGK | 0.000 | 0.000 | 0.045 | 0.894 | 0.060 | 0.000 | 0.002 | 0.000 | ||
| 12 spectra, LQAFQALR | 0.000 | 0.085 | 0.000 | 0.847 | 0.040 | 0.028 | 0.000 | 0.000 | ||
| 10 spectra, AYCTQGER | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, TVEDYQTLNK | 0.000 | 0.355 | 0.009 | 0.564 | 0.000 | 0.000 | 0.071 | 0.000 | ||
| 1 spectrum, NLFKPSLPAQSWK | 0.000 | 0.120 | 0.067 | 0.637 | 0.000 | 0.000 | 0.177 | 0.000 | ||
| 3 spectra, LANDIEAAAVQAVR | 0.000 | 0.034 | 0.000 | 0.952 | 0.000 | 0.014 | 0.000 | 0.000 | ||
| 6 spectra, VGHEPK | 0.000 | 0.000 | 0.000 | 0.931 | 0.000 | 0.069 | 0.000 | 0.000 | ||
| 32 spectra, VAVLVMGR | 0.000 | 0.016 | 0.000 | 0.984 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 6 spectra, ETVDAGGR | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 3 spectra, ALESLSCPK | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 9 spectra, QAVAQILPFR | 0.000 | 0.054 | 0.000 | 0.946 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, GLDGDQLVVLTESPFRPHQR | 0.000 | 0.057 | 0.120 | 0.823 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 5 spectra, EITTLVSR | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
100 spectra |
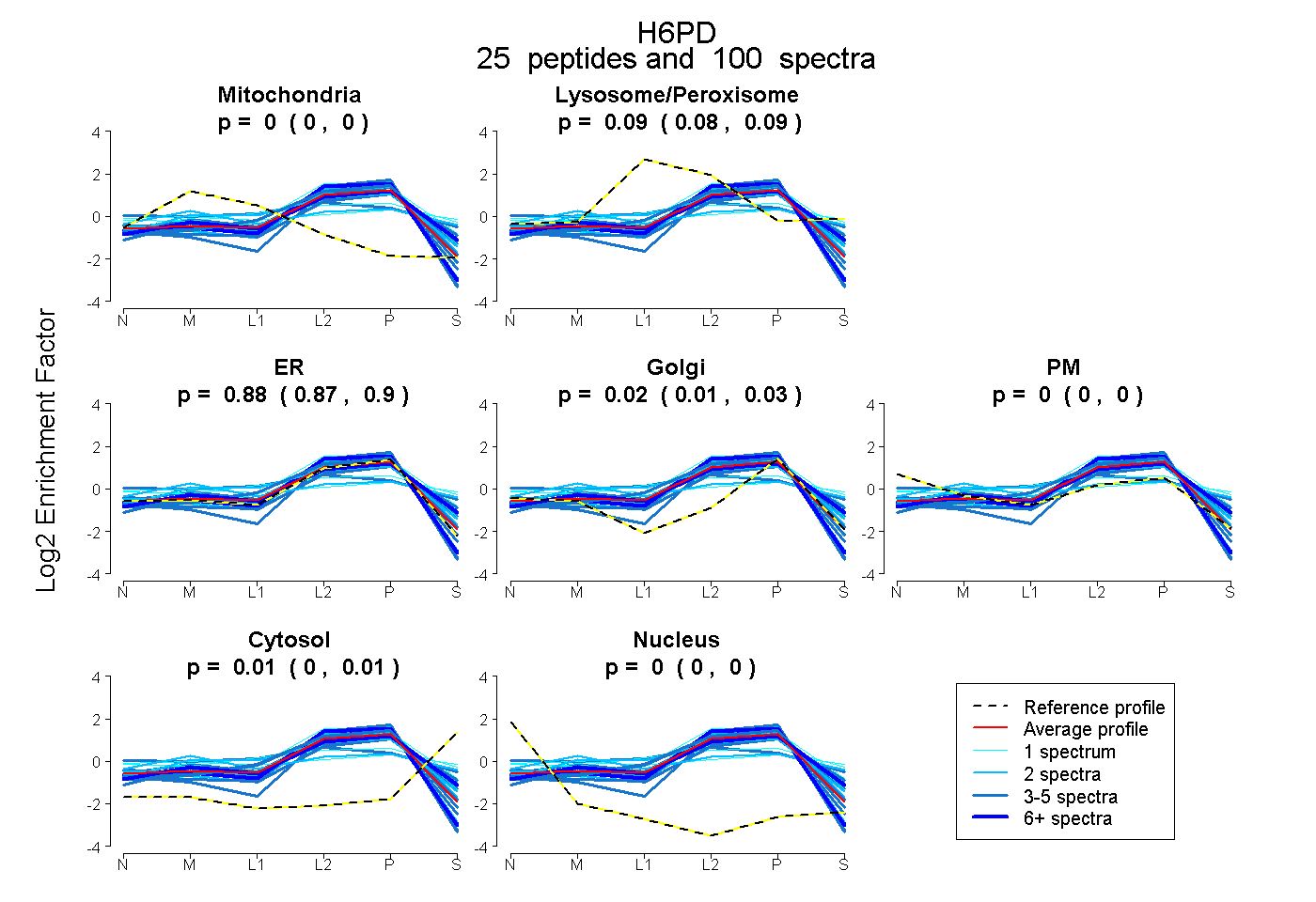 |
0.000 0.000 | 0.000 |
0.086 0.079 | 0.092 |
0.883 0.866 | 0.897 |
0.022 0.008 | 0.033 |
0.000 0.000 | 0.000 |
0.009 0.004 | 0.013 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
198 spectra |
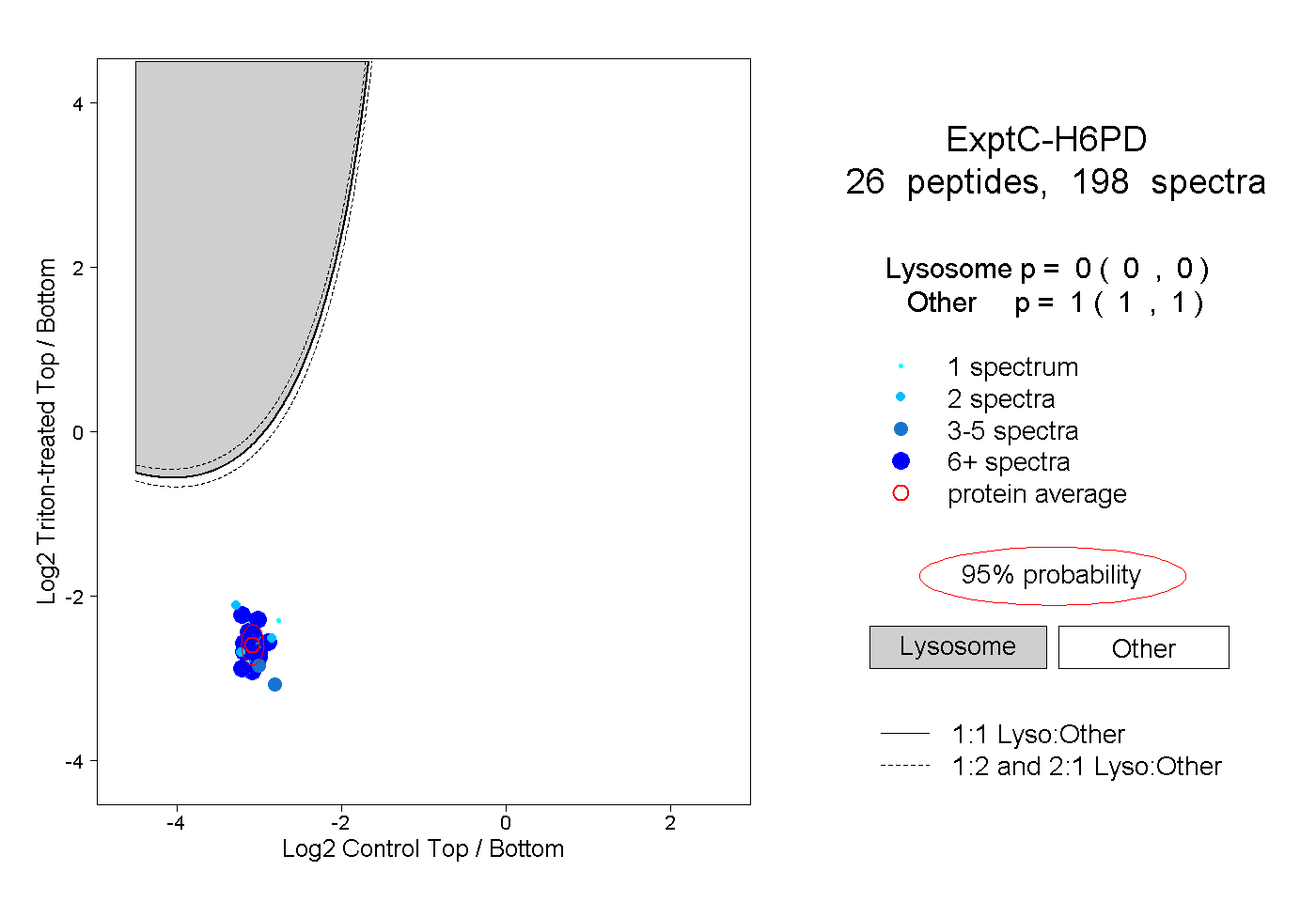 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
35 spectra |
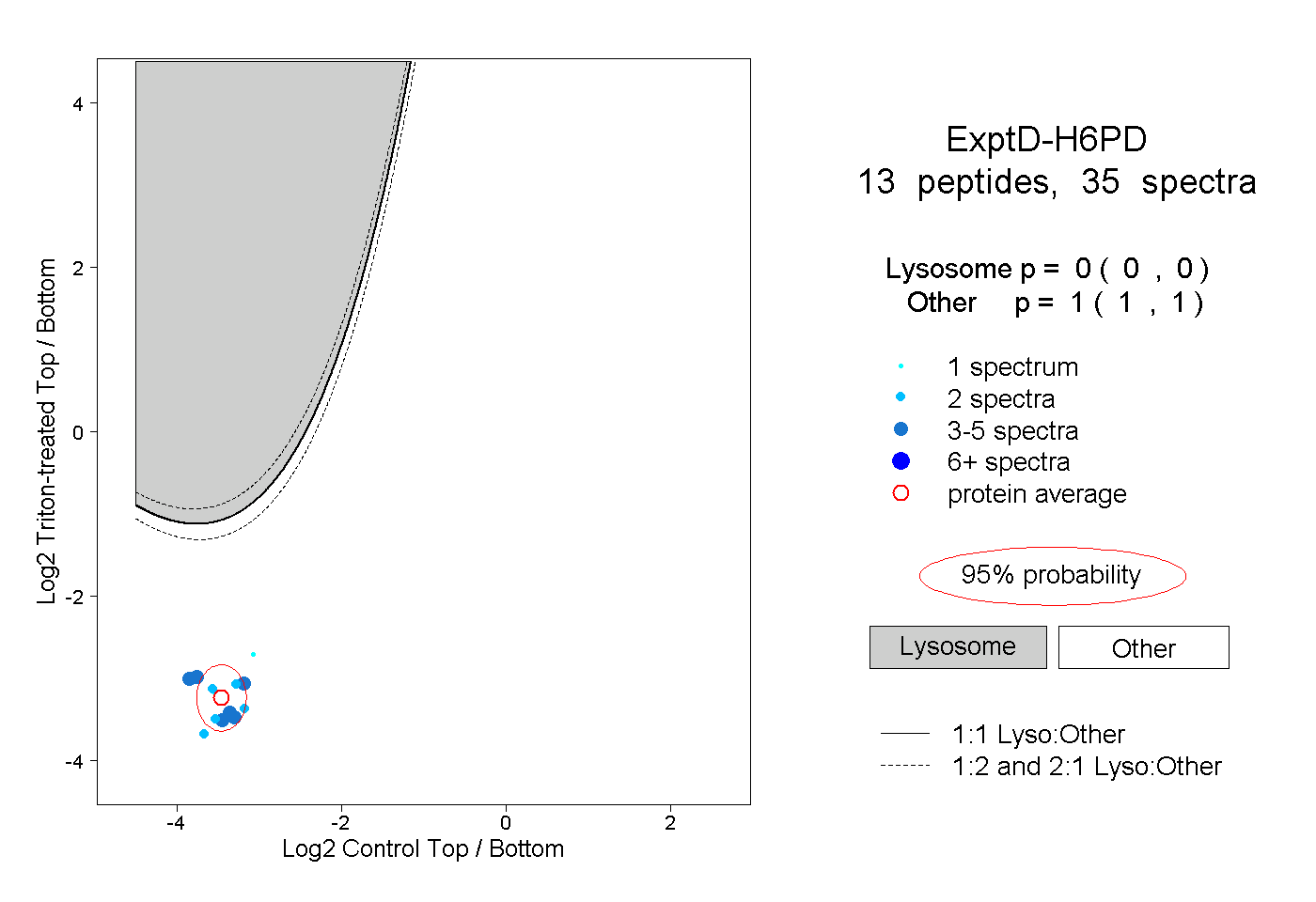 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |