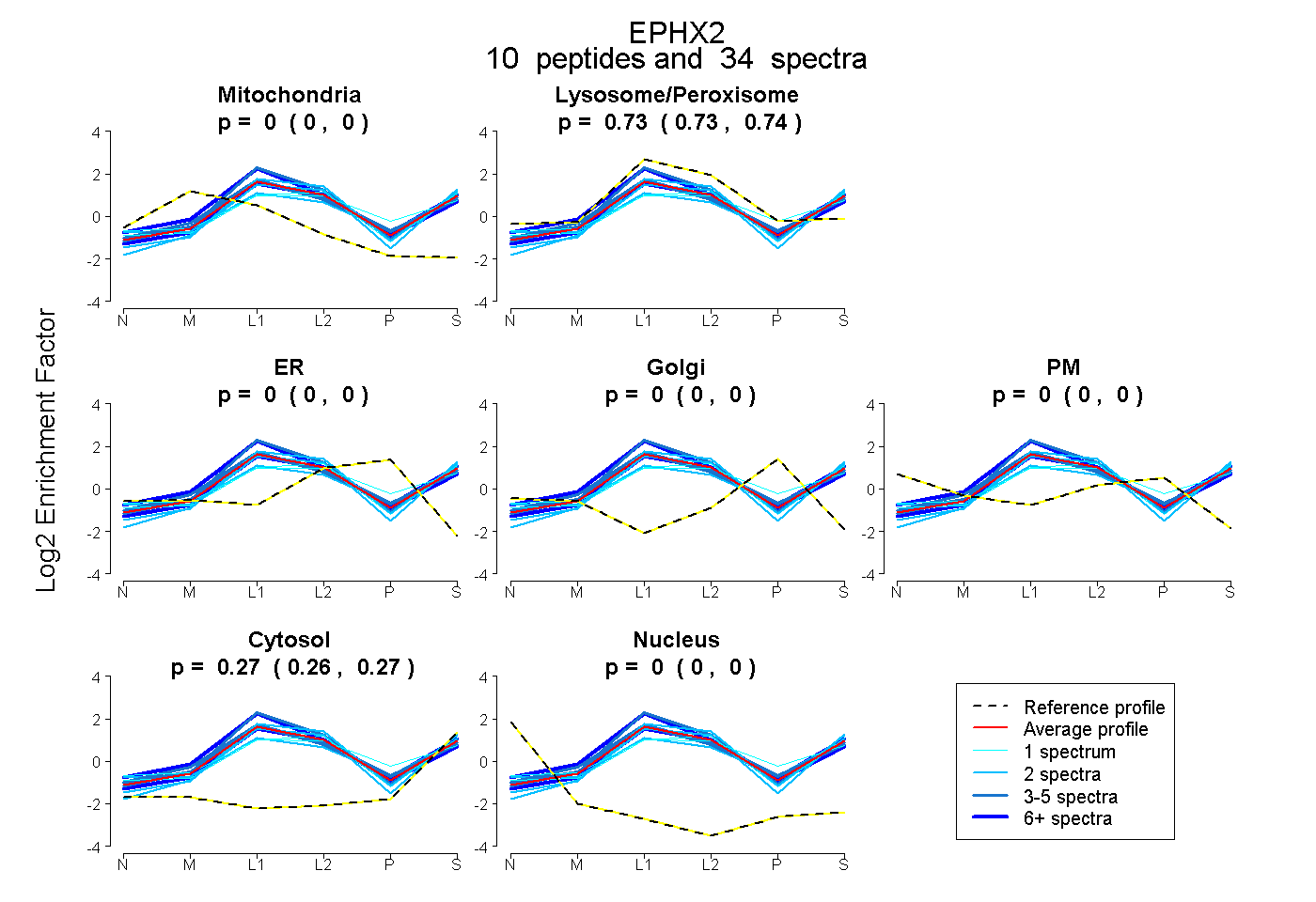
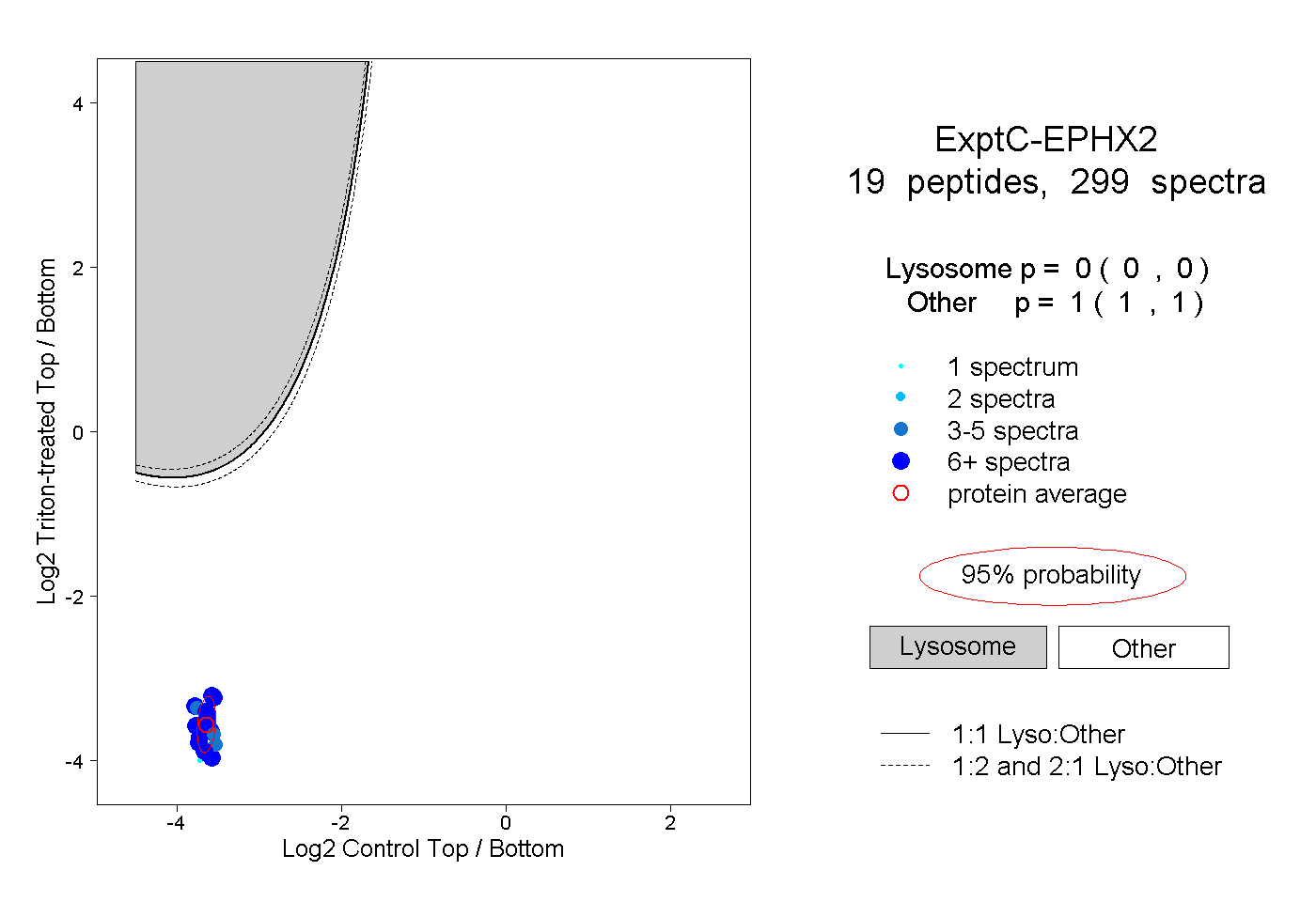
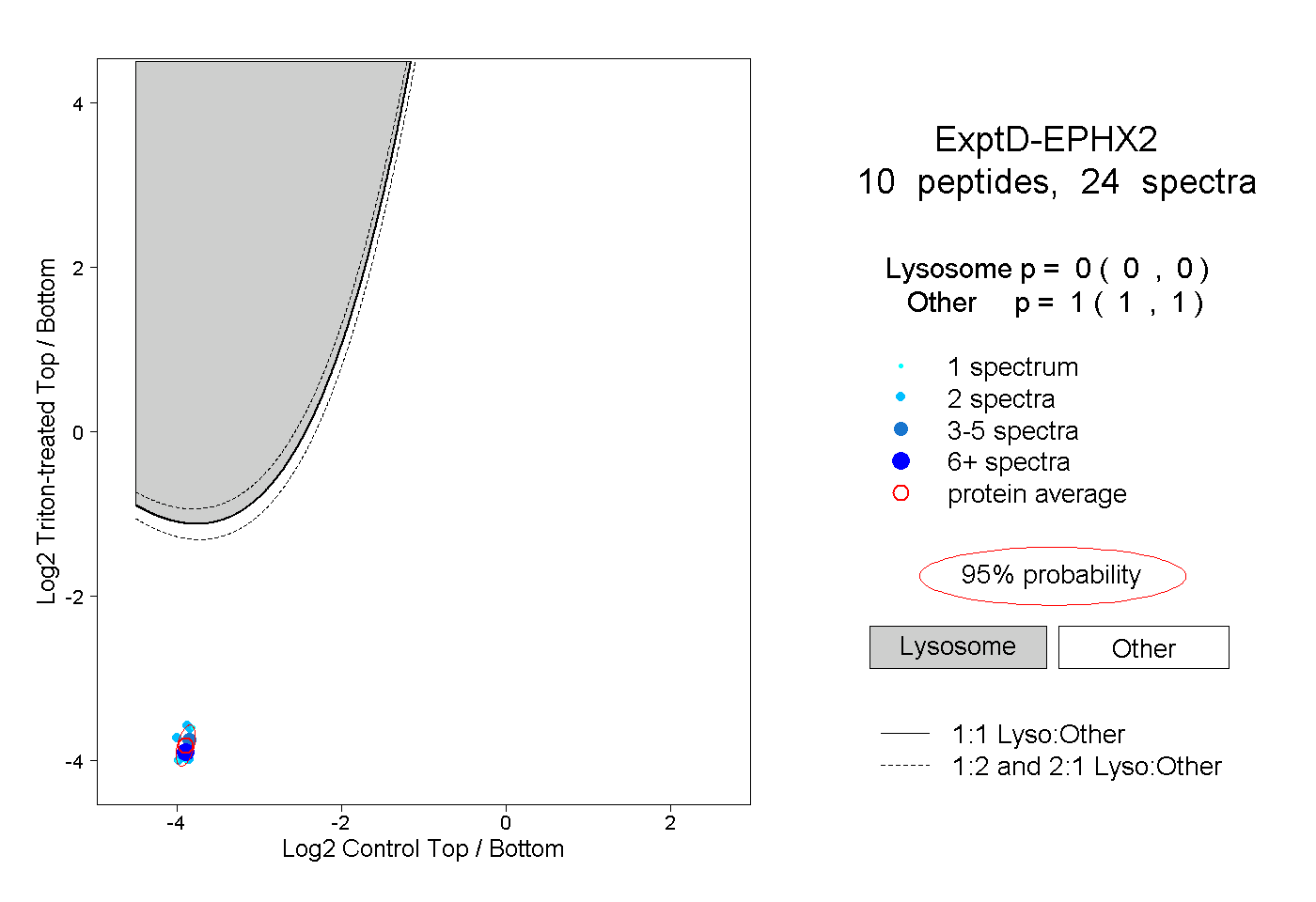
| 15 spectra, DMGMVTILVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, ITTEEEIEYYIQQFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 20 spectra, HTEEALALPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, ATEMGGILVGTPEDPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, AKPNEVVFLDDFGSNLKPAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 16 spectra, GPLNWYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 20 spectra, DFLLGAFQMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 37 spectra, SINRPMLQAAAALK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, DIVLRPEMSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 29 spectra, YQIPALAQAGFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 19 spectra, TEIQNPSVTSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 25 spectra, DTASALR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, ITFSQWVPLMDESCR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, TSDDMGLLTVNK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, ILVPALMVTAEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, FPEGPTEQLMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, NMENWIPFLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 23 spectra, VLAIDMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 47 spectra, FVLDTLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |