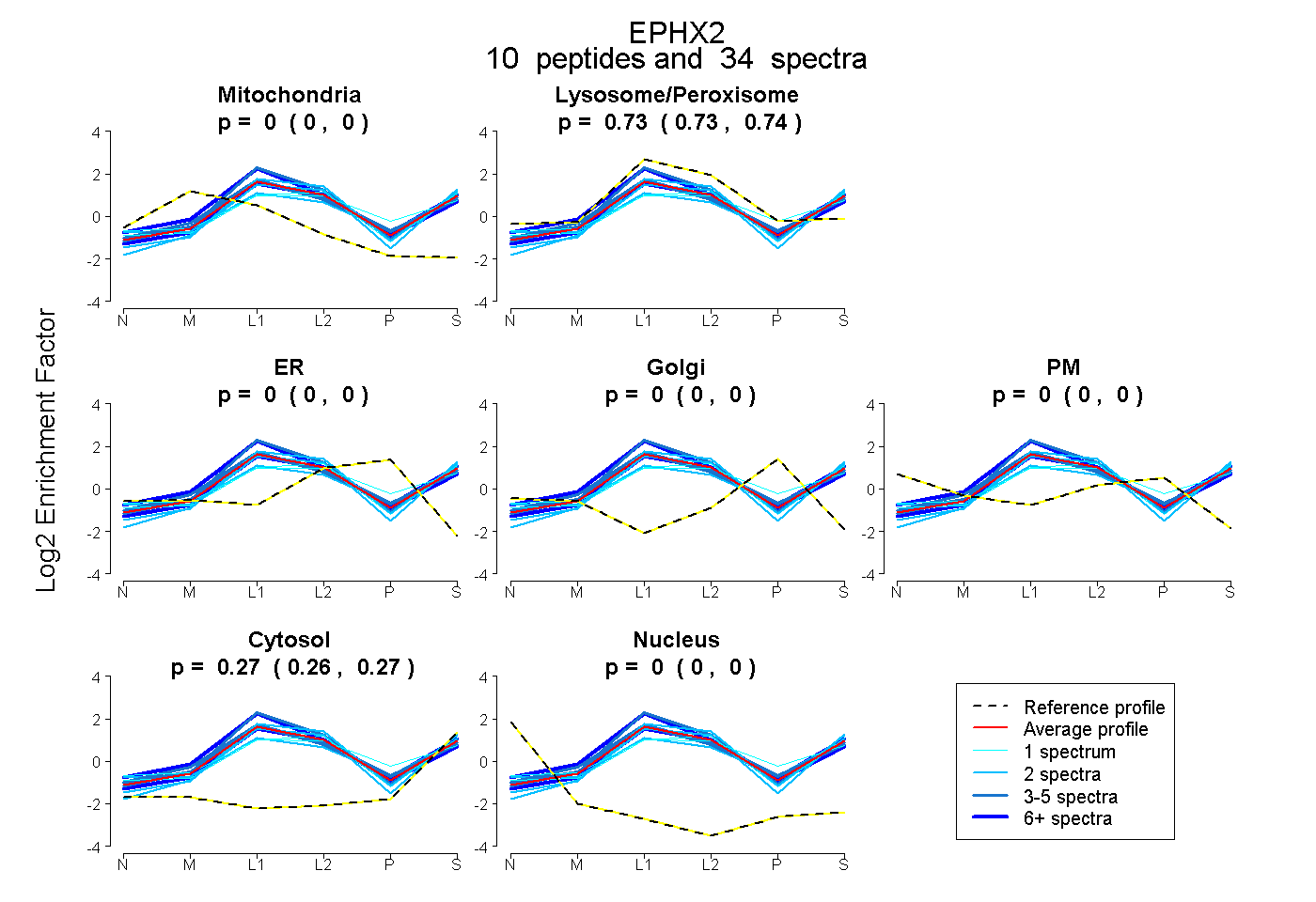
peptides
spectra

0.000 | 0.003
0.000 | 0.000
0.704 | 0.710
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.289 | 0.293
0.000 | 0.000
peptides
spectra
0.000 | 0.000
0.726 | 0.736
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.263 | 0.273
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
71 spectra |
 |
0.001 0.000 | 0.003 |
0.000 0.000 | 0.000 |
0.707 0.704 | 0.710 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.292 0.289 | 0.293 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
34 spectra |
 |
0.000 0.000 | 0.000 |
0.731 0.726 | 0.736 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.269 0.263 | 0.273 |
0.000 0.000 | 0.000 |
| 4 spectra, HTEEALALPR | 0.000 | 0.751 | 0.000 | 0.000 | 0.000 | 0.249 | 0.000 | |||
| 6 spectra, DTASALR | 0.007 | 0.816 | 0.000 | 0.000 | 0.000 | 0.177 | 0.000 | |||
| 2 spectra, ILVPALMVTAEK | 0.000 | 0.681 | 0.000 | 0.000 | 0.000 | 0.319 | 0.000 | |||
| 3 spectra, GPLNWYR | 0.000 | 0.732 | 0.000 | 0.000 | 0.000 | 0.268 | 0.000 | |||
| 9 spectra, DFLLGAFQMK | 0.000 | 0.710 | 0.000 | 0.000 | 0.000 | 0.290 | 0.000 | |||
| 2 spectra, FPEGPTEQLMK | 0.000 | 0.659 | 0.000 | 0.000 | 0.000 | 0.341 | 0.000 | |||
| 1 spectrum, VLAIDMK | 0.000 | 0.691 | 0.000 | 0.033 | 0.000 | 0.276 | 0.000 | |||
| 1 spectrum, SINRPMLQAAAALK | 0.000 | 0.665 | 0.000 | 0.000 | 0.000 | 0.335 | 0.000 | |||
| 4 spectra, FVLDTLK | 0.000 | 0.809 | 0.000 | 0.000 | 0.000 | 0.191 | 0.000 | |||
| 2 spectra, TEIQNPSVTSK | 0.000 | 0.740 | 0.000 | 0.000 | 0.000 | 0.260 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
299 spectra |
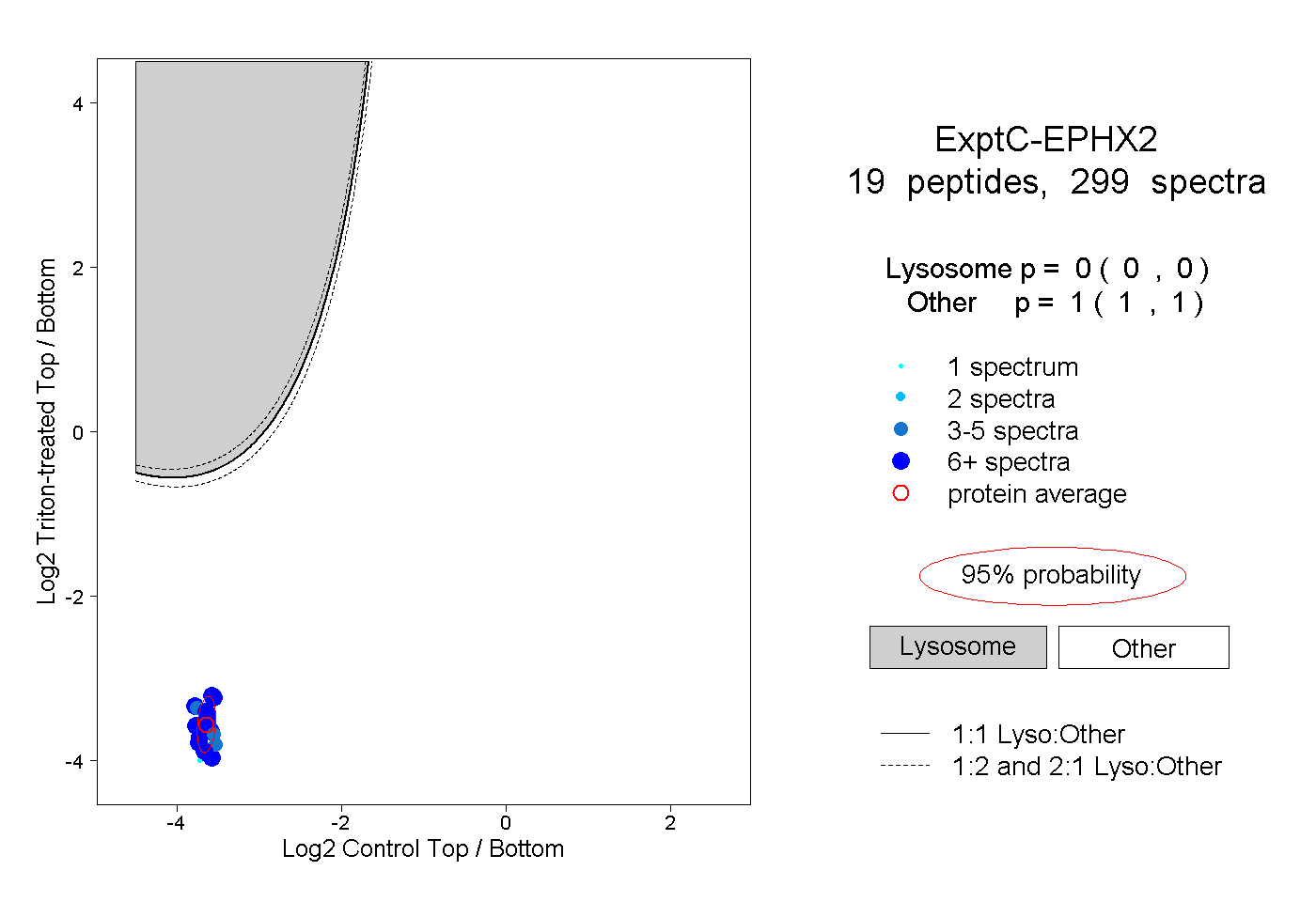 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
24 spectra |
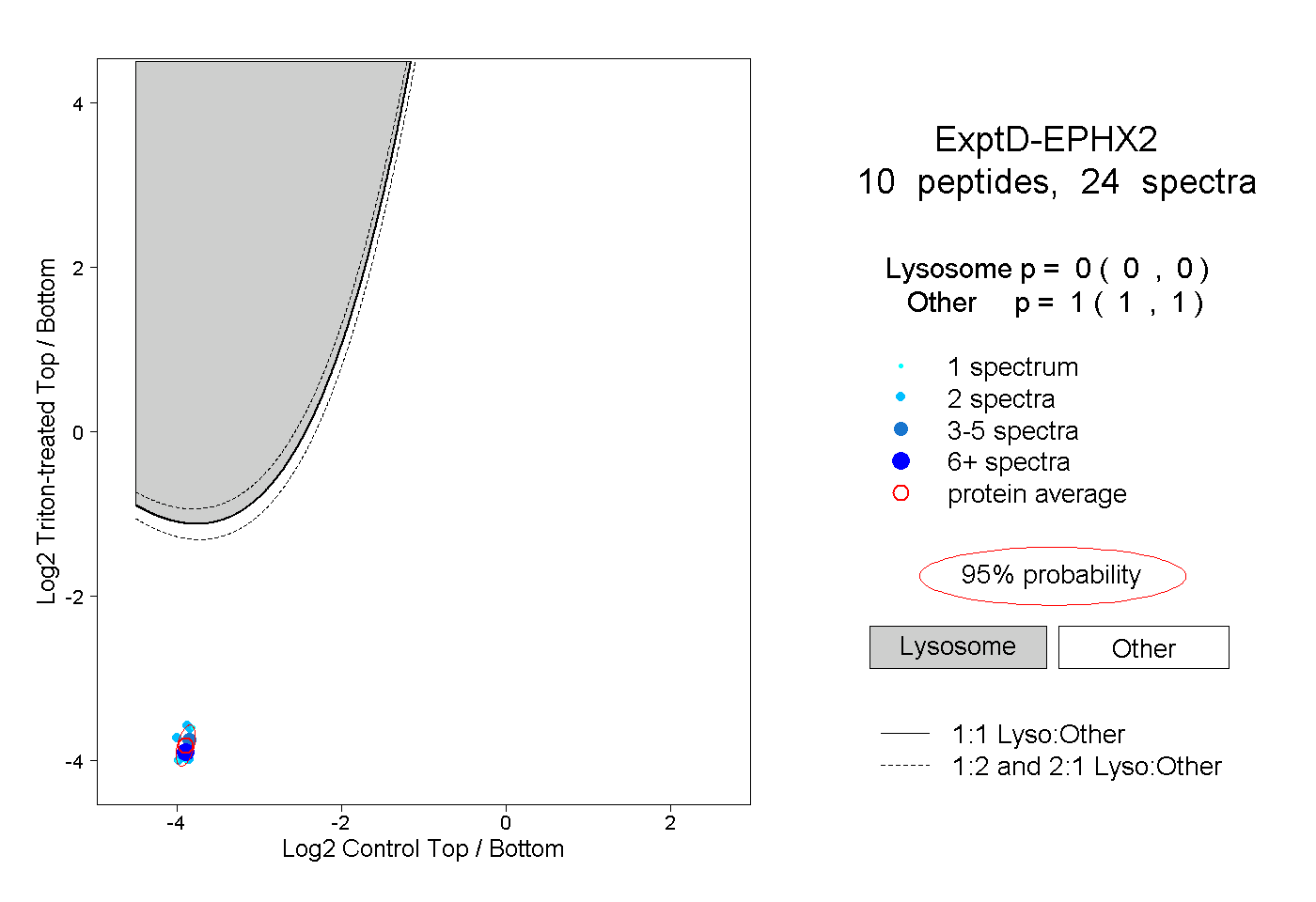 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |