peptides
spectra
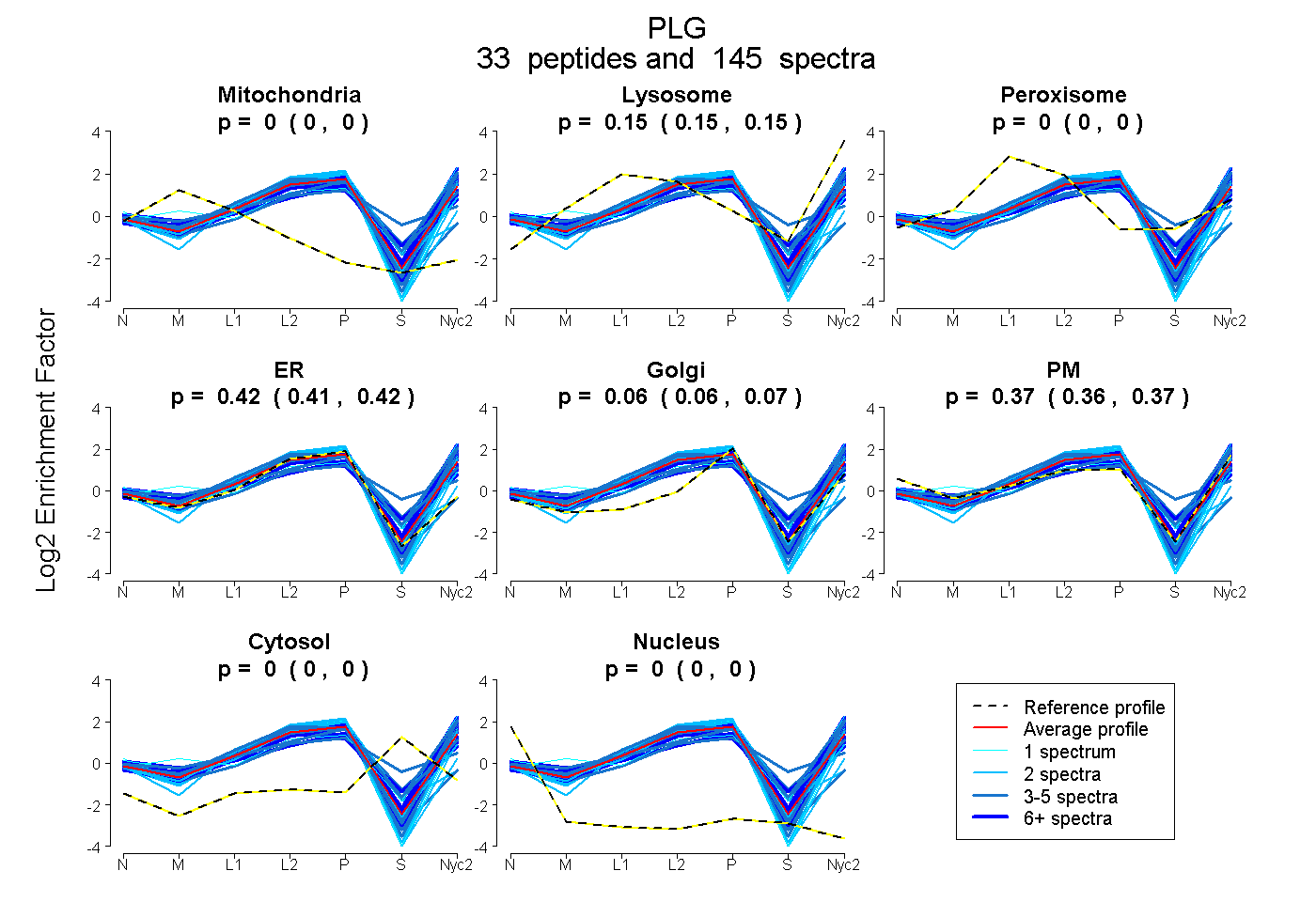
0.000 | 0.000
0.147 | 0.152
0.000 | 0.000
0.411 | 0.424
0.060 | 0.067
0.363 | 0.373
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
145 spectra |
 |
0.000 0.000 | 0.000 |
0.150 0.147 | 0.152 |
0.000 0.000 | 0.000 |
0.418 0.411 | 0.424 |
0.064 0.060 | 0.067 |
0.368 0.363 | 0.373 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 2 spectra, VYLSECK | 0.000 | 0.095 | 0.000 | 0.610 | 0.063 | 0.232 | 0.000 | 0.000 | ||
| 13 spectra, NLEENYCR | 0.000 | 0.109 | 0.000 | 0.369 | 0.023 | 0.499 | 0.000 | 0.000 | ||
| 1 spectrum, WEYCNLK | 0.000 | 0.293 | 0.000 | 0.000 | 0.240 | 0.467 | 0.000 | 0.000 | ||
| 2 spectra, GTSSTTNTGK | 0.000 | 0.057 | 0.000 | 0.348 | 0.000 | 0.595 | 0.000 | 0.000 | ||
| 6 spectra, NPDGDVNGPWCYTMNPR | 0.000 | 0.083 | 0.112 | 0.396 | 0.000 | 0.316 | 0.093 | 0.000 | ||
| 1 spectrum, VVGGCVANPHSWPWQISLR | 0.000 | 0.051 | 0.000 | 0.533 | 0.000 | 0.416 | 0.000 | 0.000 | ||
| 3 spectra, WSEQTPHR | 0.000 | 0.318 | 0.000 | 0.278 | 0.010 | 0.395 | 0.000 | 0.000 | ||
| 3 spectra, VILGAHEER | 0.000 | 0.146 | 0.000 | 0.362 | 0.050 | 0.442 | 0.000 | 0.000 | ||
| 1 spectrum, TSSLLR | 0.000 | 0.097 | 0.000 | 0.282 | 0.000 | 0.622 | 0.000 | 0.000 | ||
| 7 spectra, DVILFEK | 0.000 | 0.237 | 0.000 | 0.362 | 0.119 | 0.282 | 0.000 | 0.000 | ||
| 2 spectra, CEGETDFICR | 0.000 | 0.000 | 0.094 | 0.870 | 0.000 | 0.000 | 0.036 | 0.000 | ||
| 4 spectra, YVNWIER | 0.000 | 0.165 | 0.000 | 0.211 | 0.000 | 0.624 | 0.000 | 0.000 | ||
| 2 spectra, NPDGETAPWCYTTDSQLR | 0.000 | 0.247 | 0.000 | 0.500 | 0.129 | 0.123 | 0.001 | 0.000 | ||
| 3 spectra, WSDTSPHVPK | 0.000 | 0.133 | 0.120 | 0.211 | 0.372 | 0.164 | 0.000 | 0.000 | ||
| 5 spectra, LVLEPNDADIALLK | 0.000 | 0.229 | 0.000 | 0.264 | 0.172 | 0.336 | 0.000 | 0.000 | ||
| 5 spectra, CTTPPPPPGPTYQCLK | 0.000 | 0.195 | 0.000 | 0.423 | 0.002 | 0.282 | 0.098 | 0.000 | ||
| 9 spectra, TGVTCQK | 0.000 | 0.091 | 0.000 | 0.406 | 0.000 | 0.503 | 0.000 | 0.000 | ||
| 4 spectra, TPANFPDAGLEMNYCR | 0.000 | 0.066 | 0.086 | 0.329 | 0.045 | 0.217 | 0.258 | 0.000 | ||
| 3 spectra, SSRPEFYK | 0.000 | 0.148 | 0.000 | 0.273 | 0.076 | 0.503 | 0.000 | 0.000 | ||
| 6 spectra, AEYLNNR | 0.000 | 0.138 | 0.000 | 0.372 | 0.125 | 0.365 | 0.000 | 0.000 | ||
| 6 spectra, EAQLPVIENK | 0.000 | 0.167 | 0.000 | 0.286 | 0.231 | 0.316 | 0.000 | 0.000 | ||
| 7 spectra, TPENFPCK | 0.000 | 0.218 | 0.000 | 0.208 | 0.138 | 0.436 | 0.000 | 0.000 | ||
| 3 spectra, EQQCVIMAENSK | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 8 spectra, GTVSVTASGK | 0.009 | 0.161 | 0.000 | 0.222 | 0.301 | 0.306 | 0.000 | 0.000 | ||
| 2 spectra, WEYCDIPR | 0.000 | 0.070 | 0.000 | 0.499 | 0.000 | 0.431 | 0.000 | 0.000 | ||
| 15 spectra, IFTPQTNPR | 0.000 | 0.276 | 0.000 | 0.222 | 0.061 | 0.441 | 0.000 | 0.000 | ||
| 8 spectra, GPWCFTTDPSVR | 0.000 | 0.146 | 0.000 | 0.532 | 0.062 | 0.261 | 0.000 | 0.000 | ||
| 4 spectra, GTPGAGR | 0.000 | 0.105 | 0.000 | 0.330 | 0.000 | 0.564 | 0.000 | 0.000 | ||
| 2 spectra, QLAAGSIADCLAK | 0.000 | 0.000 | 0.000 | 0.553 | 0.000 | 0.447 | 0.000 | 0.000 | ||
| 1 spectrum, NPDGEPRPWCFTTDPNK | 0.000 | 0.106 | 0.000 | 0.292 | 0.027 | 0.575 | 0.000 | 0.000 | ||
| 3 spectra, ILGSDVQQIAVTK | 0.000 | 0.107 | 0.000 | 0.327 | 0.109 | 0.457 | 0.000 | 0.000 | ||
| 2 spectra, NPDNDQR | 0.000 | 0.075 | 0.000 | 0.398 | 0.000 | 0.526 | 0.000 | 0.000 | ||
| 2 spectra, TLCYITGWGETK | 0.000 | 0.000 | 0.000 | 0.891 | 0.000 | 0.109 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
53 spectra |
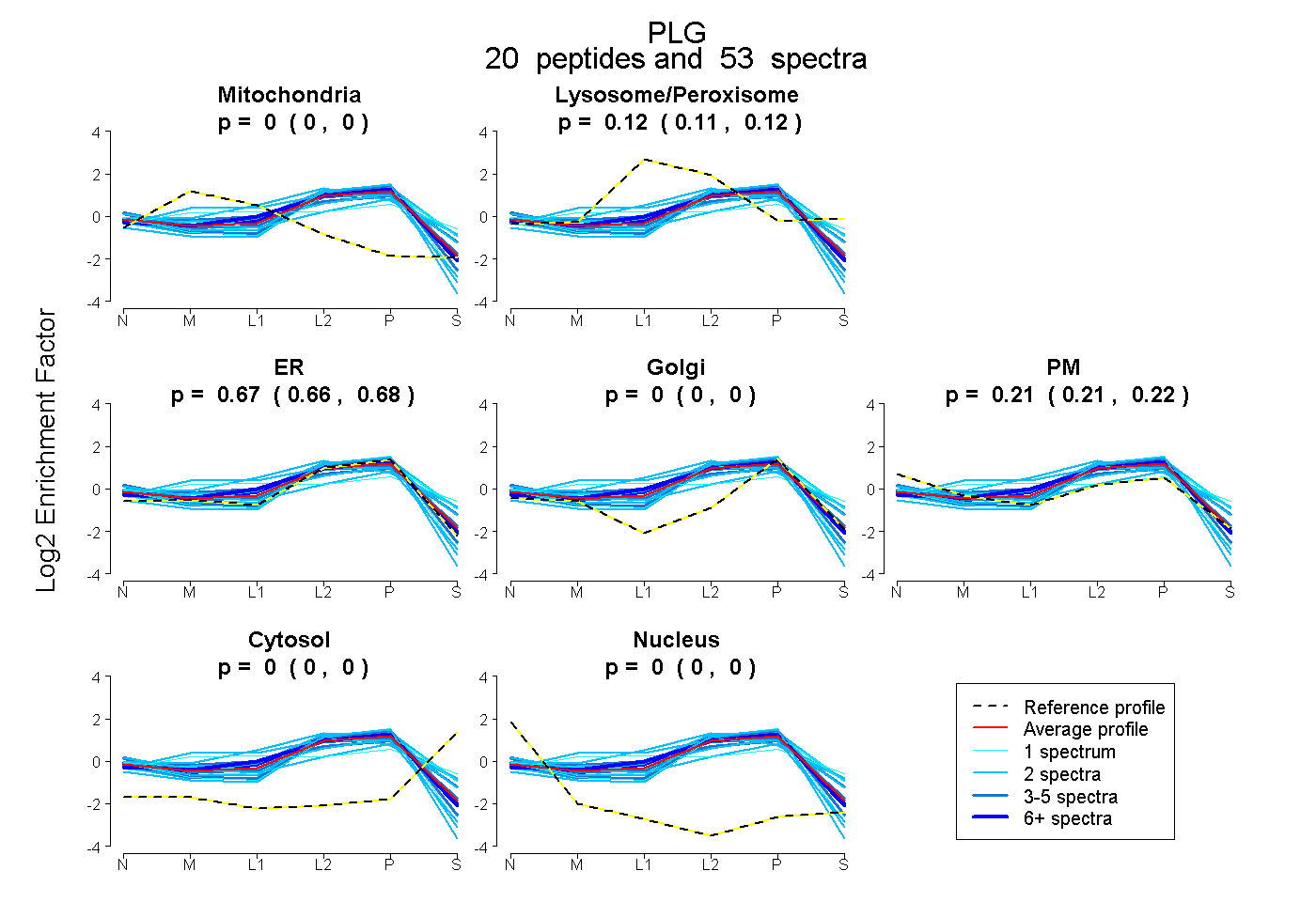 |
0.000 0.000 | 0.000 |
0.118 0.111 | 0.124 |
0.669 0.659 | 0.677 |
0.000 0.000 | 0.000 |
0.213 0.205 | 0.220 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
279 spectra |
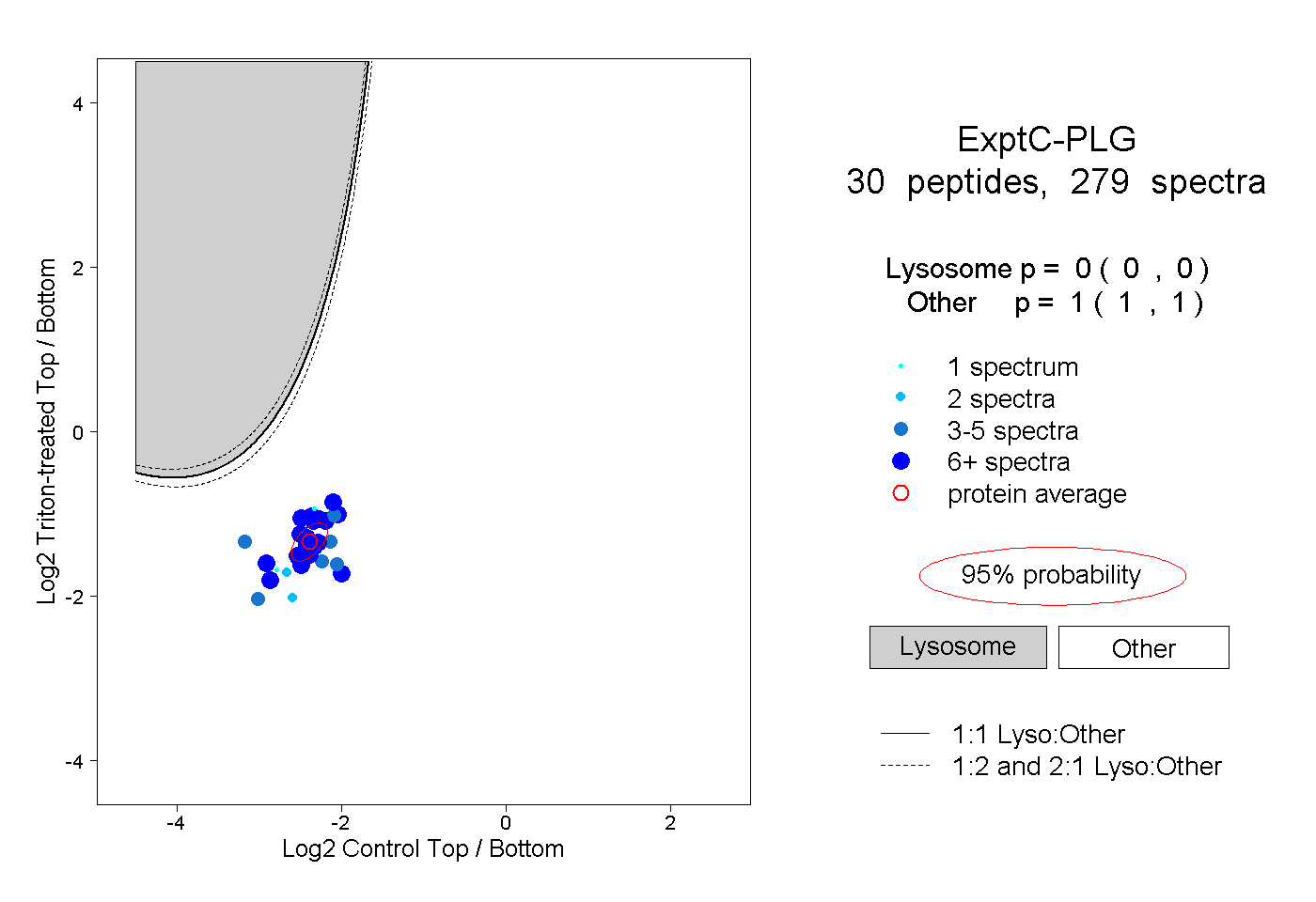 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
36 spectra |
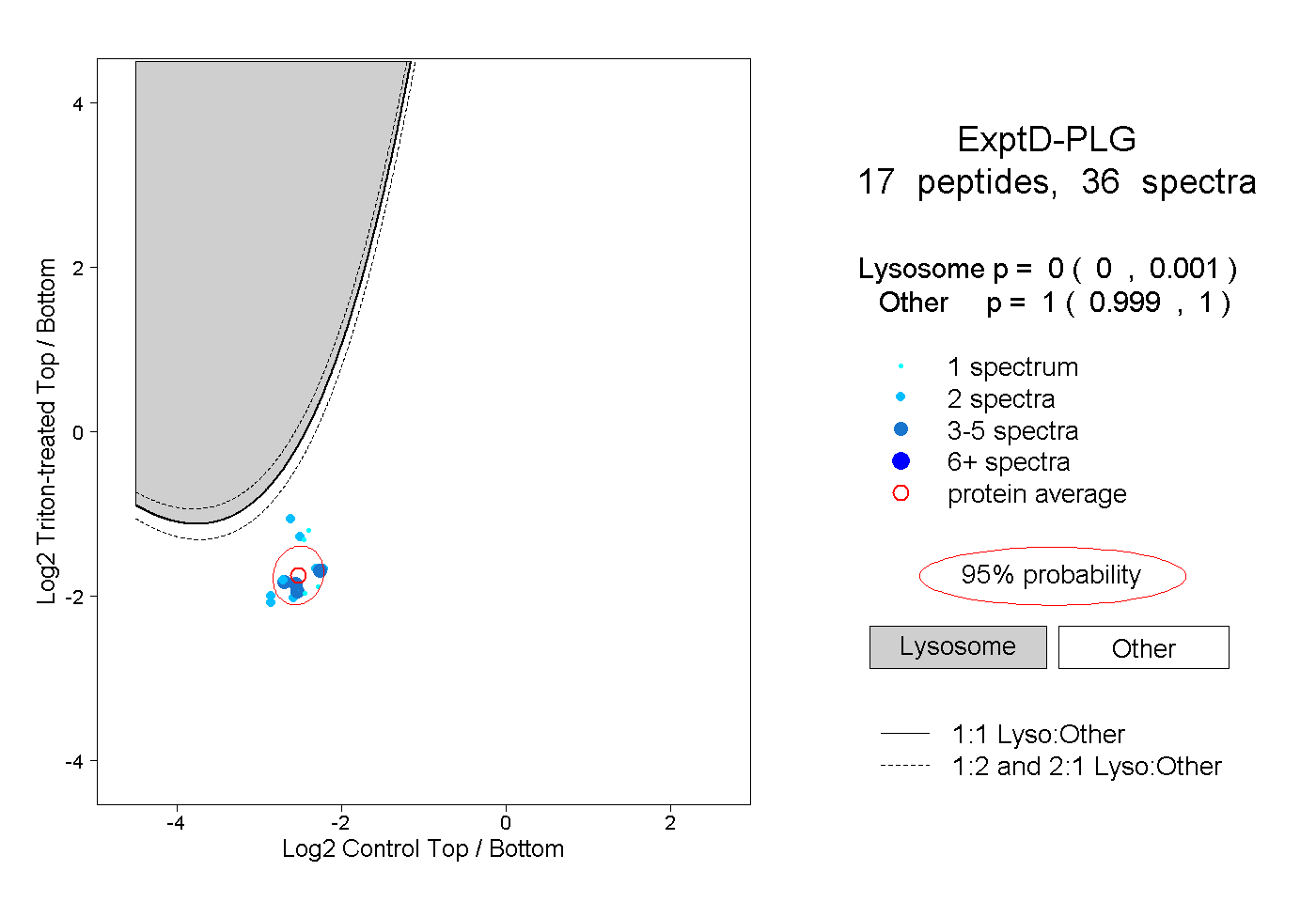 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |