peptides
spectra
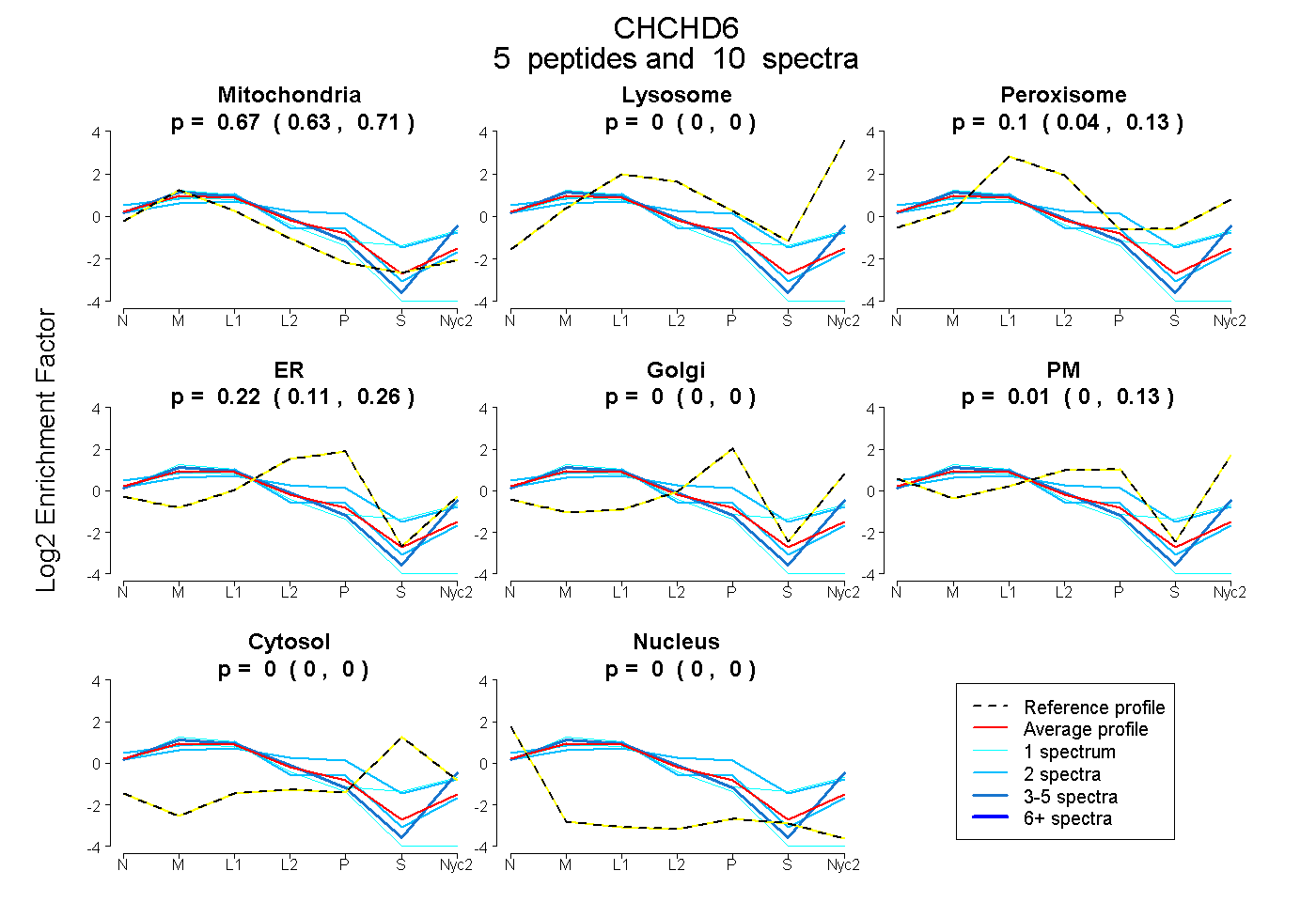
0.627 | 0.705
0.000 | 0.000
0.036 | 0.133
0.109 | 0.262
0.000 | 0.000
0.000 | 0.135
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
10 spectra |
 |
0.670 0.627 | 0.705 |
0.000 0.000 | 0.000 |
0.095 0.036 | 0.133 |
0.223 0.109 | 0.262 |
0.000 0.000 | 0.000 |
0.012 0.000 | 0.135 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 2 spectra, DHLHEVLLCSDLAK | 0.373 | 0.000 | 0.265 | 0.204 | 0.147 | 0.000 | 0.011 | 0.000 | ||
| 4 spectra, VSFEMDEEER | 0.649 | 0.053 | 0.000 | 0.000 | 0.000 | 0.298 | 0.000 | 0.000 | ||
| 1 spectrum, LSESVVNR | 0.529 | 0.000 | 0.278 | 0.000 | 0.000 | 0.128 | 0.065 | 0.000 | ||
| 1 spectrum, ATHEQQQSDR | 0.957 | 0.000 | 0.000 | 0.041 | 0.000 | 0.000 | 0.000 | 0.001 | ||
| 2 spectra, AYQHCVSTAR | 0.702 | 0.000 | 0.000 | 0.251 | 0.000 | 0.046 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
2 spectra |
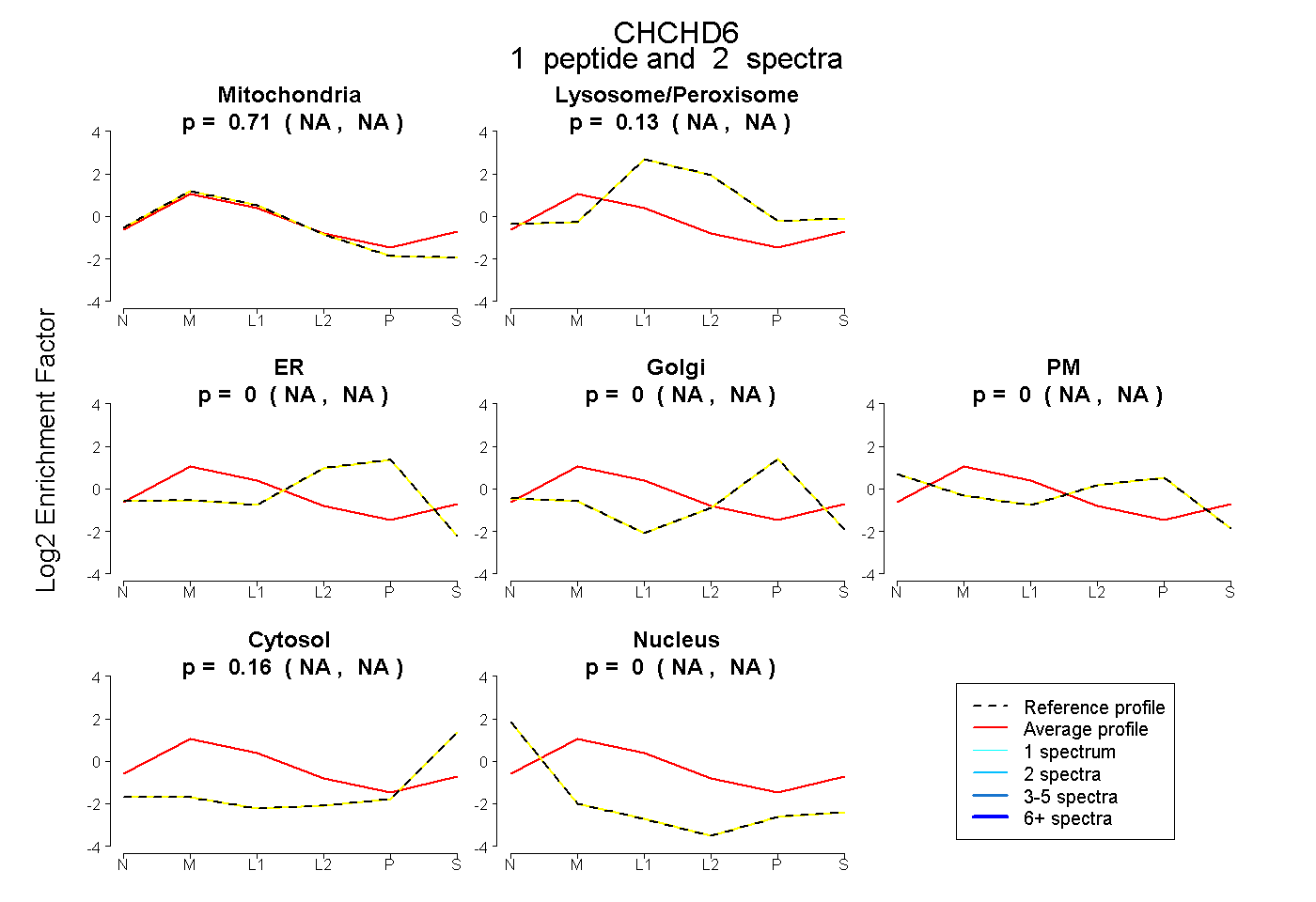 |
0.708 NA | NA |
0.130 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.162 NA | NA |
0.000 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
58 spectra |
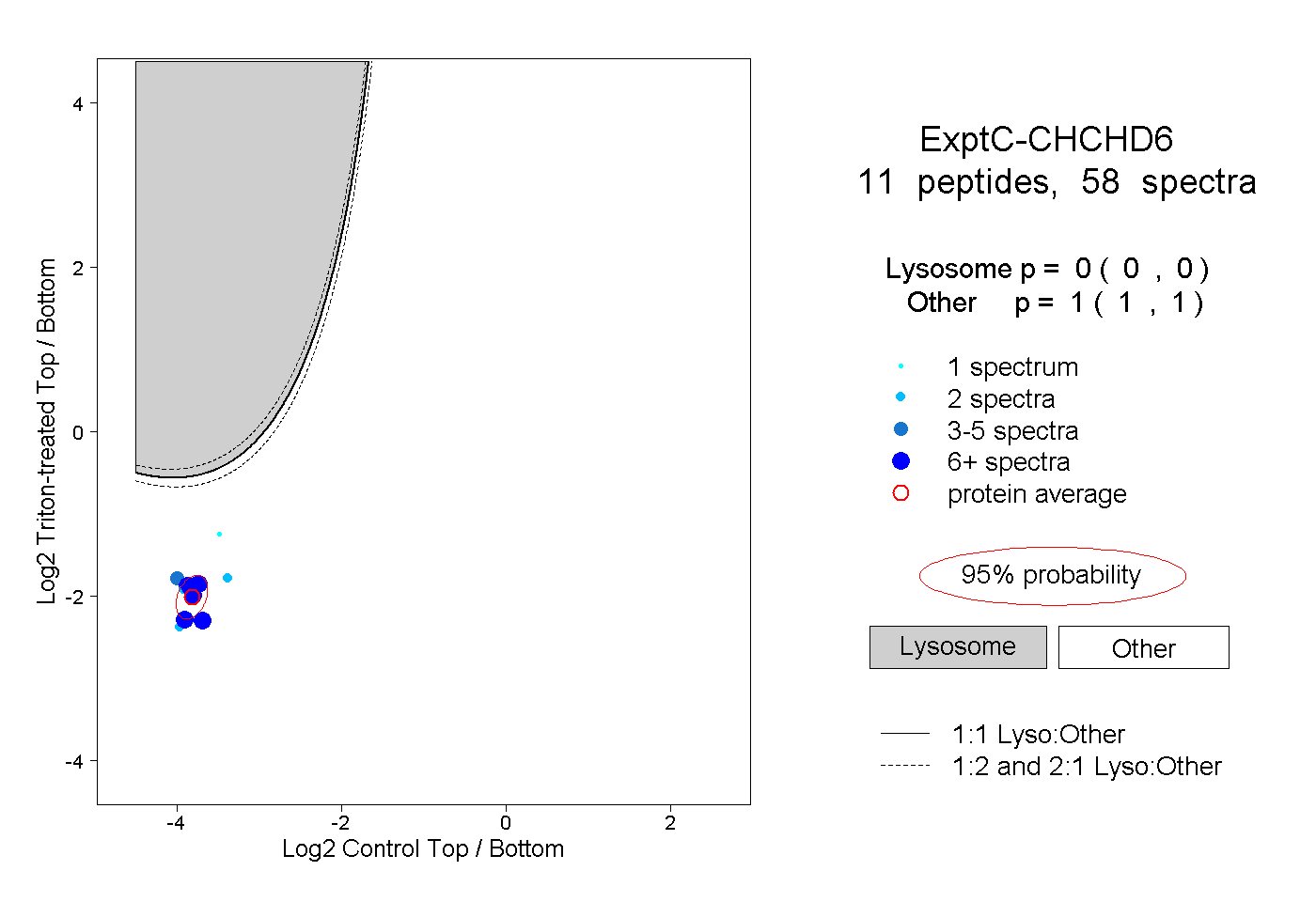 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
8 spectra |
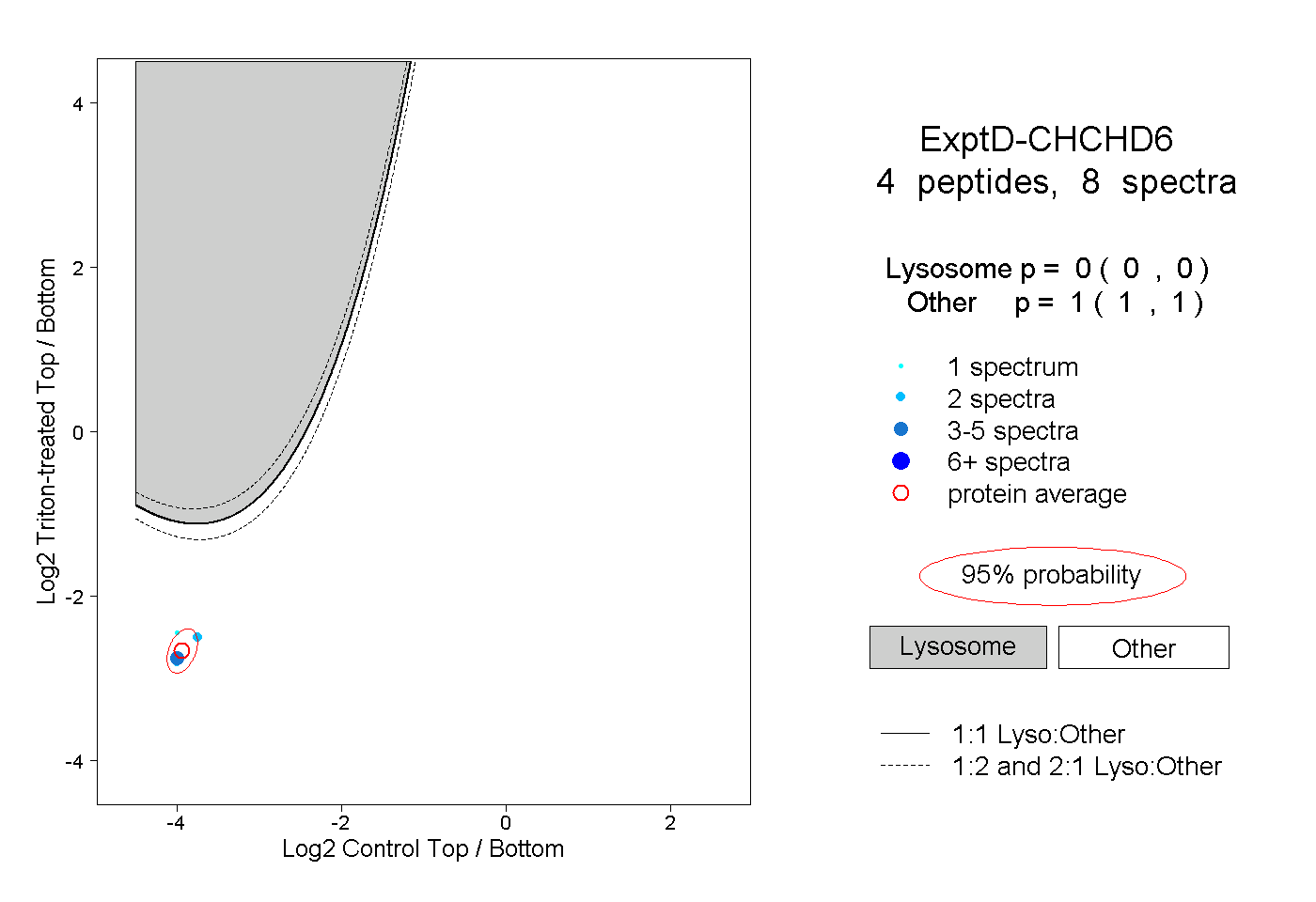 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |