peptides
spectra
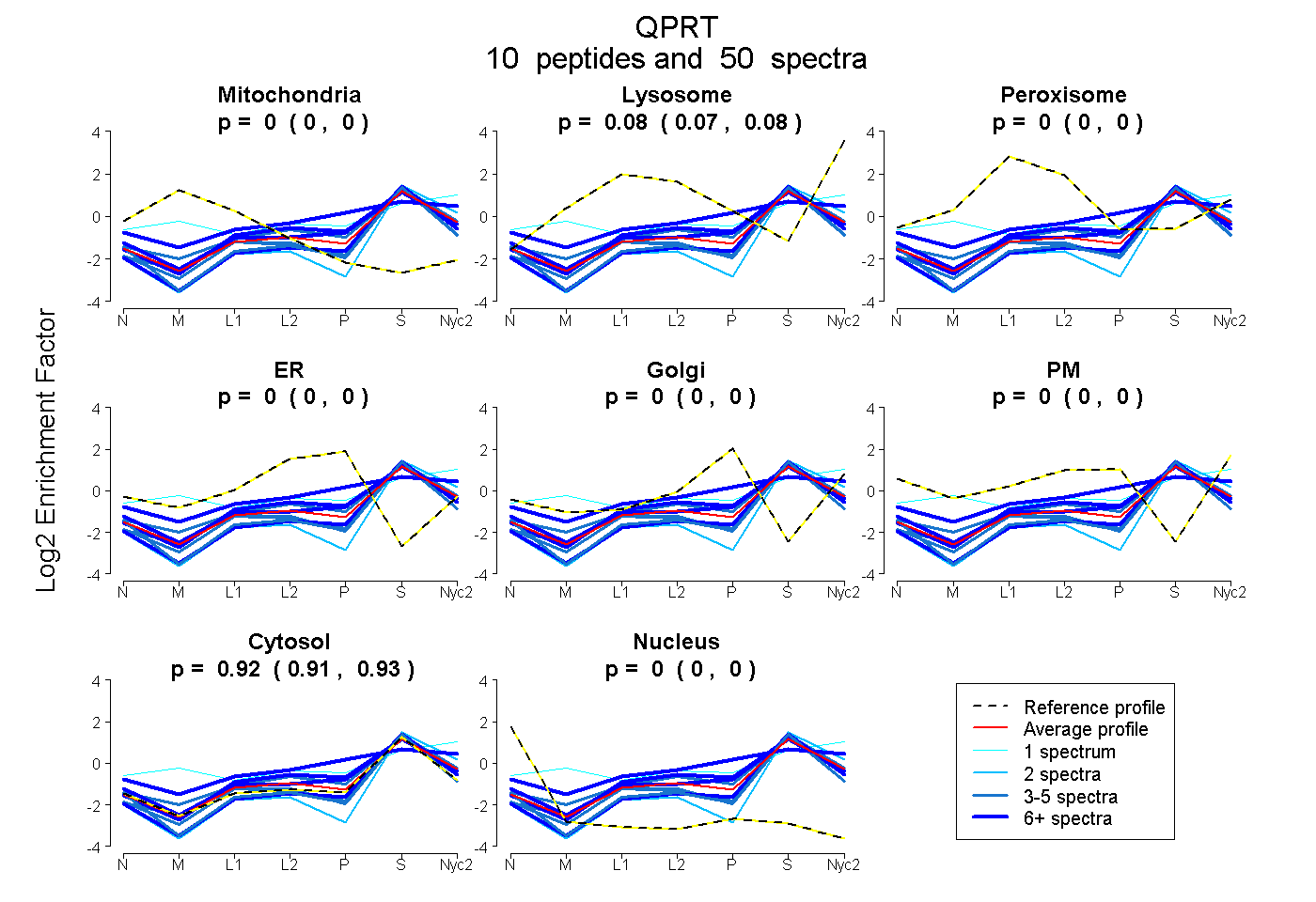
0.000 | 0.000
0.073 | 0.085
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.914 | 0.927
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
50 spectra |
 |
0.000 0.000 | 0.000 |
0.079 0.073 | 0.085 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.921 0.914 | 0.927 |
0.000 0.000 | 0.000 |
| 4 spectra, YDLGGLVMVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.980 | 0.020 | ||
| 8 spectra, YGLLVGGAECHR | 0.000 | 0.169 | 0.018 | 0.000 | 0.168 | 0.062 | 0.583 | 0.000 | ||
| 1 spectrum, CSGIASAAATAVEVATSTGWAGHVAGTR | 0.037 | 0.267 | 0.000 | 0.000 | 0.000 | 0.160 | 0.536 | 0.000 | ||
| 6 spectra, VALNTLAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 12 spectra, LYAEGDIPVPHAR | 0.000 | 0.068 | 0.000 | 0.000 | 0.059 | 0.000 | 0.873 | 0.000 | ||
| 6 spectra, VEVECSSLK | 0.000 | 0.090 | 0.000 | 0.051 | 0.000 | 0.000 | 0.859 | 0.000 | ||
| 3 spectra, DNHVVAAGSMEK | 0.000 | 0.049 | 0.000 | 0.000 | 0.000 | 0.000 | 0.951 | 0.000 | ||
| 4 spectra, LVPVVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 4 spectra, GPAHHLLLGER | 0.000 | 0.111 | 0.027 | 0.009 | 0.000 | 0.000 | 0.852 | 0.000 | ||
| 2 spectra, QAAGFPLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
13 spectra |
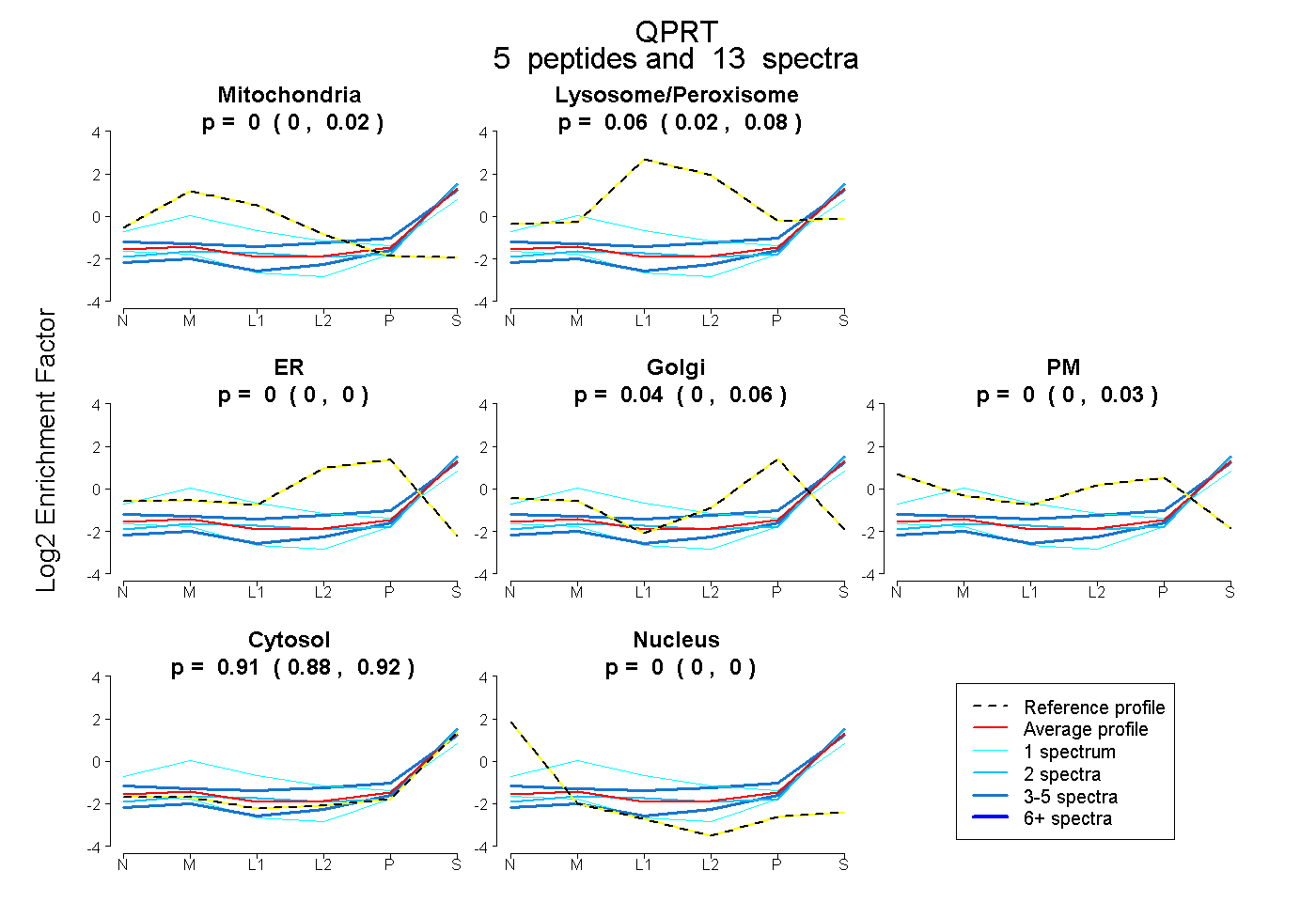 |
0.000 0.000 | 0.021 |
0.059 0.023 | 0.083 |
0.000 0.000 | 0.000 |
0.036 0.000 | 0.056 |
0.000 0.000 | 0.029 |
0.905 0.883 | 0.925 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
49 spectra |
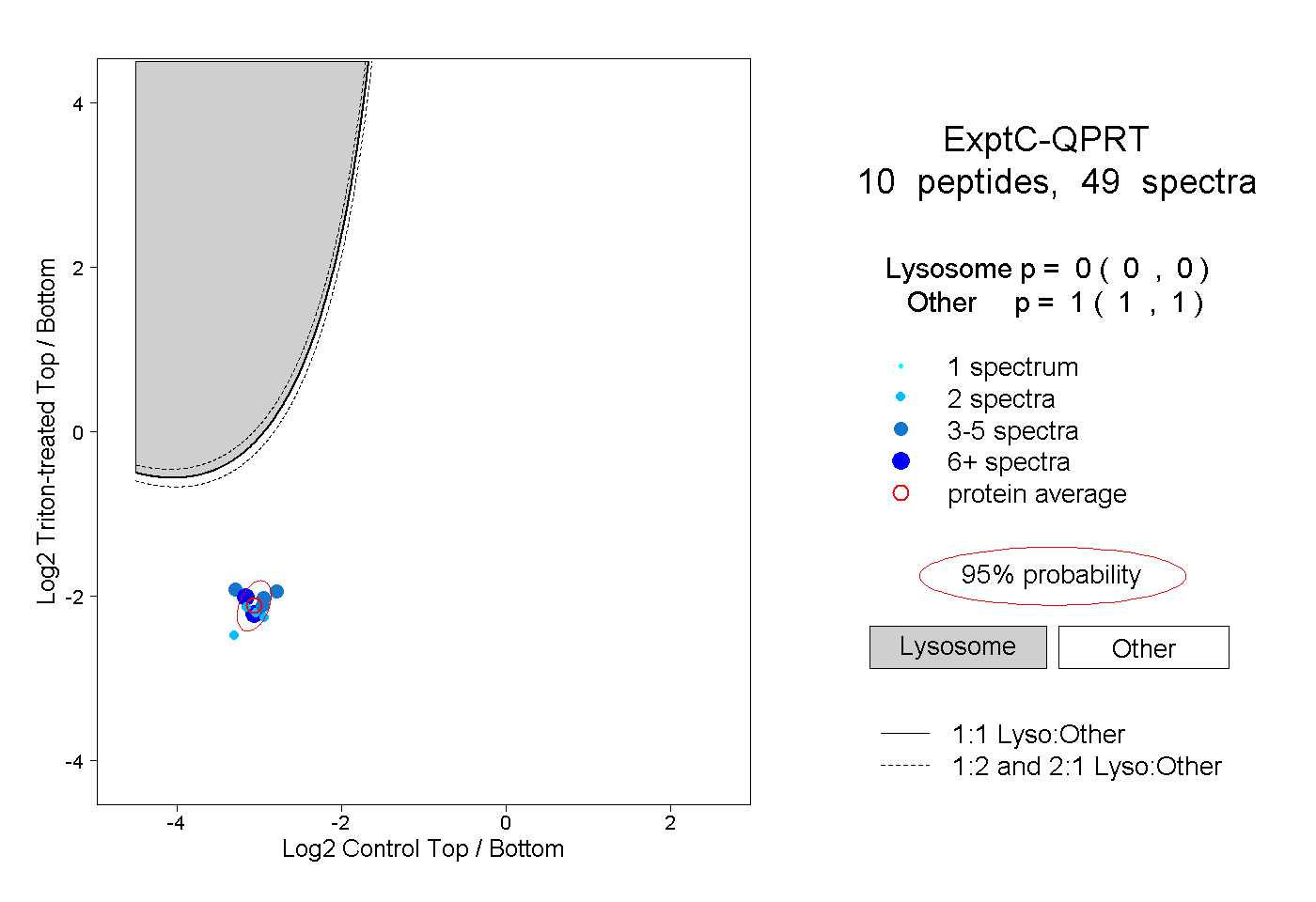 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
1 spectrum |
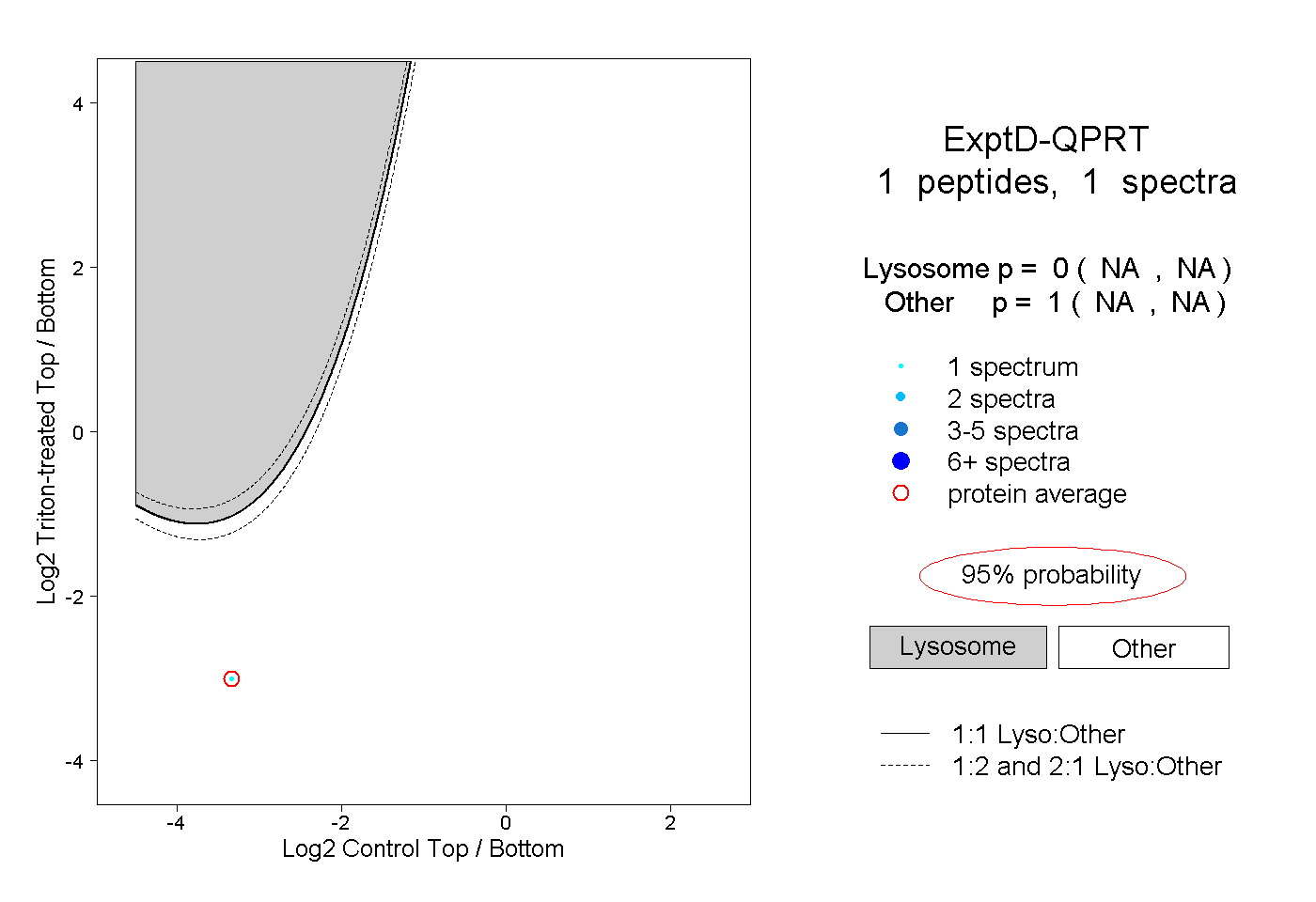 |
0.000 NA | NA |
1.000 NA | NA |