peptides
spectra
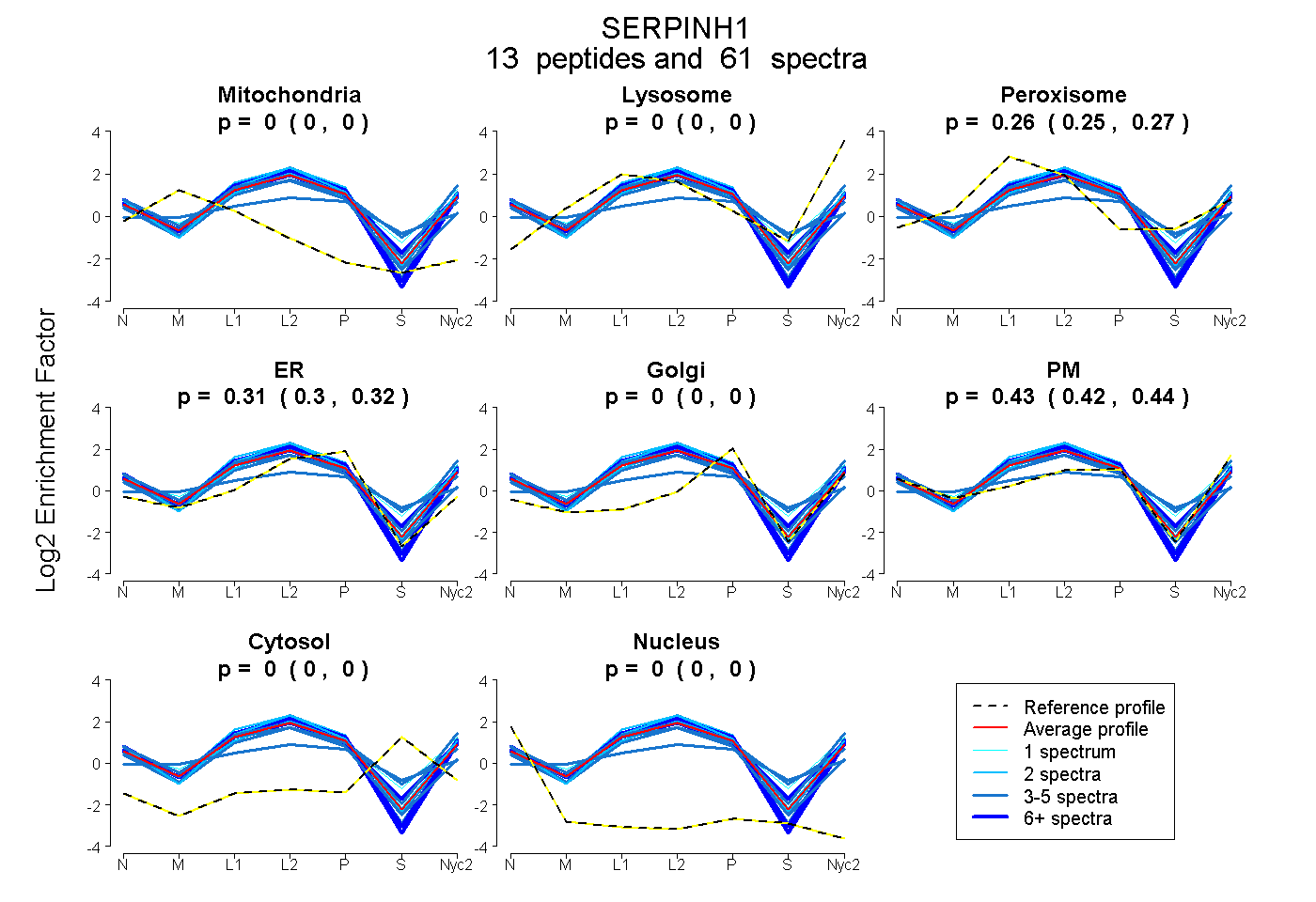
0.000 | 0.000
0.000 | 0.000
0.254 | 0.269
0.298 | 0.317
0.000 | 0.000
0.417 | 0.440
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
61 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.262 0.254 | 0.269 |
0.308 0.298 | 0.317 |
0.000 0.000 | 0.000 |
0.429 0.417 | 0.440 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 3 spectra, QHYNCEHSK | 0.000 | 0.000 | 0.284 | 0.434 | 0.000 | 0.256 | 0.000 | 0.026 | ||
| 9 spectra, ATTASQAK | 0.000 | 0.000 | 0.142 | 0.349 | 0.000 | 0.509 | 0.000 | 0.000 | ||
| 4 spectra, SYTVGVTMMHR | 0.043 | 0.000 | 0.334 | 0.231 | 0.127 | 0.123 | 0.142 | 0.000 | ||
| 5 spectra, GVVEVTHDLQK | 0.000 | 0.000 | 0.334 | 0.314 | 0.000 | 0.281 | 0.071 | 0.000 | ||
| 2 spectra, HLAGLGLTEAIDK | 0.000 | 0.000 | 0.231 | 0.332 | 0.000 | 0.437 | 0.000 | 0.000 | ||
| 6 spectra, LQLVEMPLAHK | 0.000 | 0.000 | 0.180 | 0.334 | 0.000 | 0.486 | 0.000 | 0.000 | ||
| 1 spectrum, DEEVHTGLGELLR | 0.000 | 0.000 | 0.360 | 0.119 | 0.000 | 0.521 | 0.000 | 0.000 | ||
| 4 spectra, STGLAFSLYQAMAK | 0.000 | 0.019 | 0.283 | 0.136 | 0.000 | 0.561 | 0.000 | 0.000 | ||
| 2 spectra, LYGPSSVSFADDFVR | 0.000 | 0.000 | 0.265 | 0.283 | 0.000 | 0.453 | 0.000 | 0.000 | ||
| 4 spectra, ATTLAER | 0.000 | 0.000 | 0.238 | 0.337 | 0.000 | 0.425 | 0.000 | 0.000 | ||
| 2 spectra, AVLSAEK | 0.000 | 0.000 | 0.202 | 0.354 | 0.000 | 0.443 | 0.000 | 0.000 | ||
| 4 spectra, DNQSGSLLFIGR | 0.000 | 0.000 | 0.193 | 0.237 | 0.000 | 0.570 | 0.000 | 0.000 | ||
| 15 spectra, GFMVTR | 0.000 | 0.000 | 0.326 | 0.255 | 0.000 | 0.419 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
13 spectra |
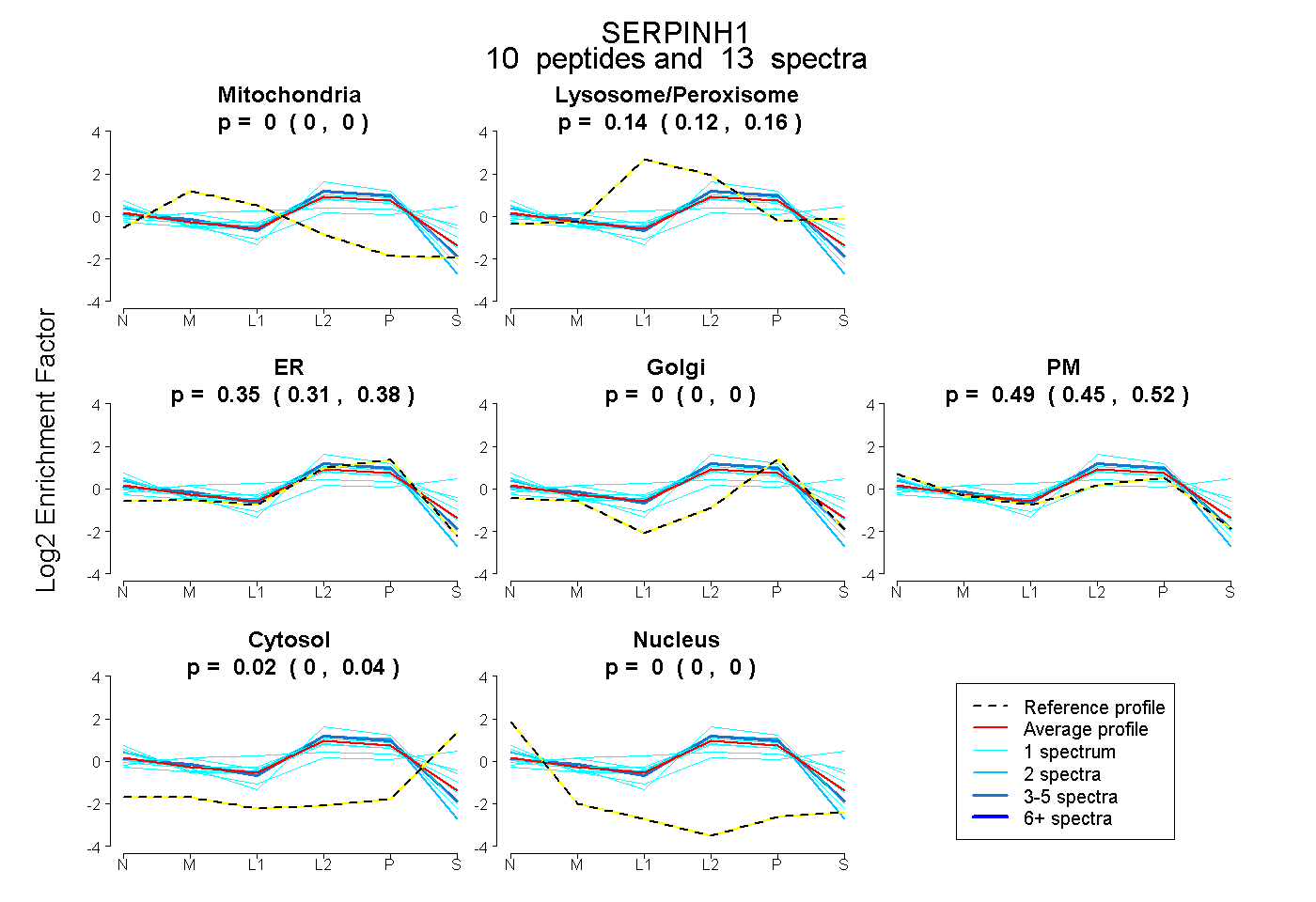 |
0.000 0.000 | 0.000 |
0.140 0.119 | 0.159 |
0.351 0.313 | 0.384 |
0.000 0.000 | 0.000 |
0.488 0.446 | 0.520 |
0.020 0.002 | 0.036 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
140 spectra |
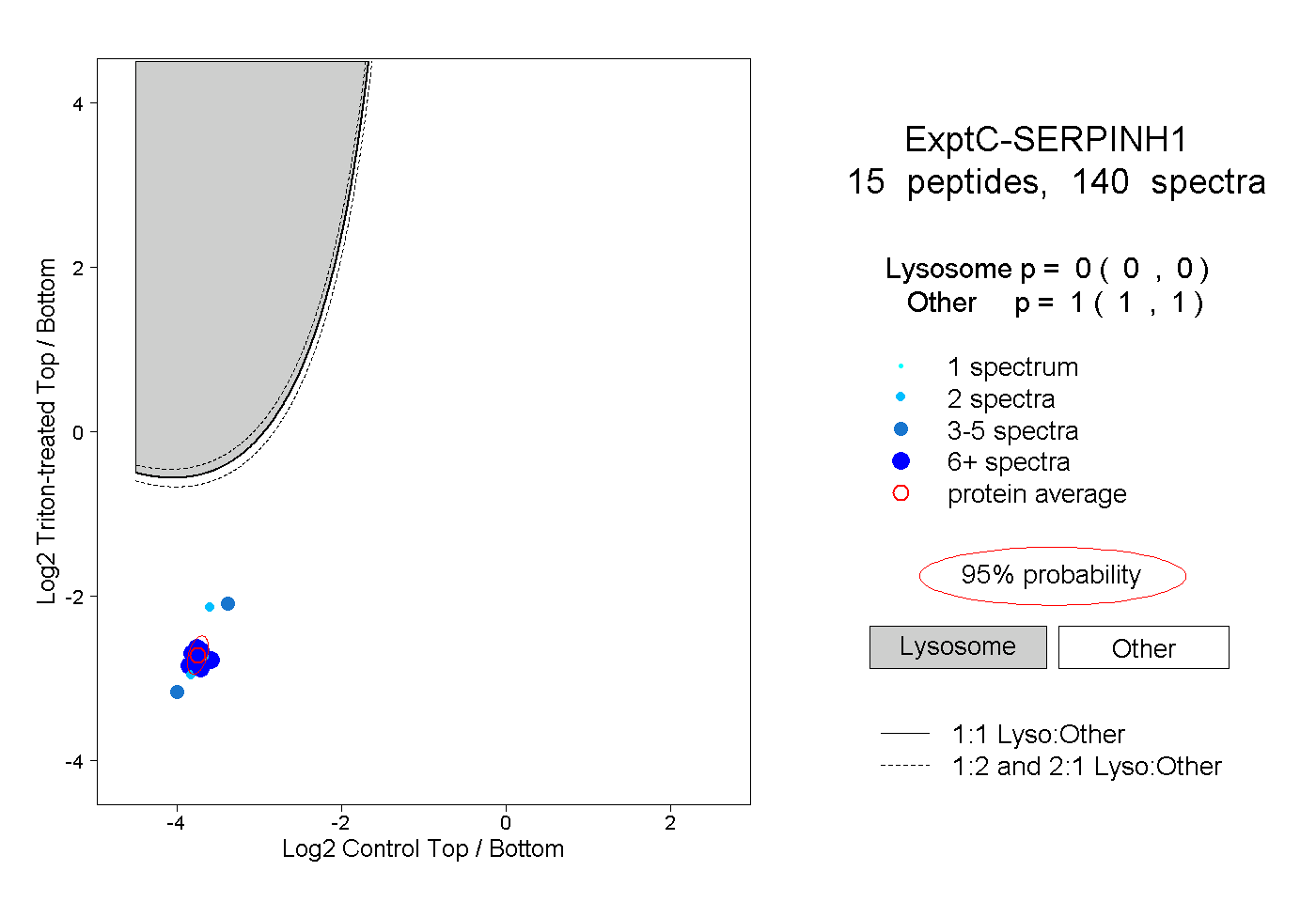 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
8 spectra |
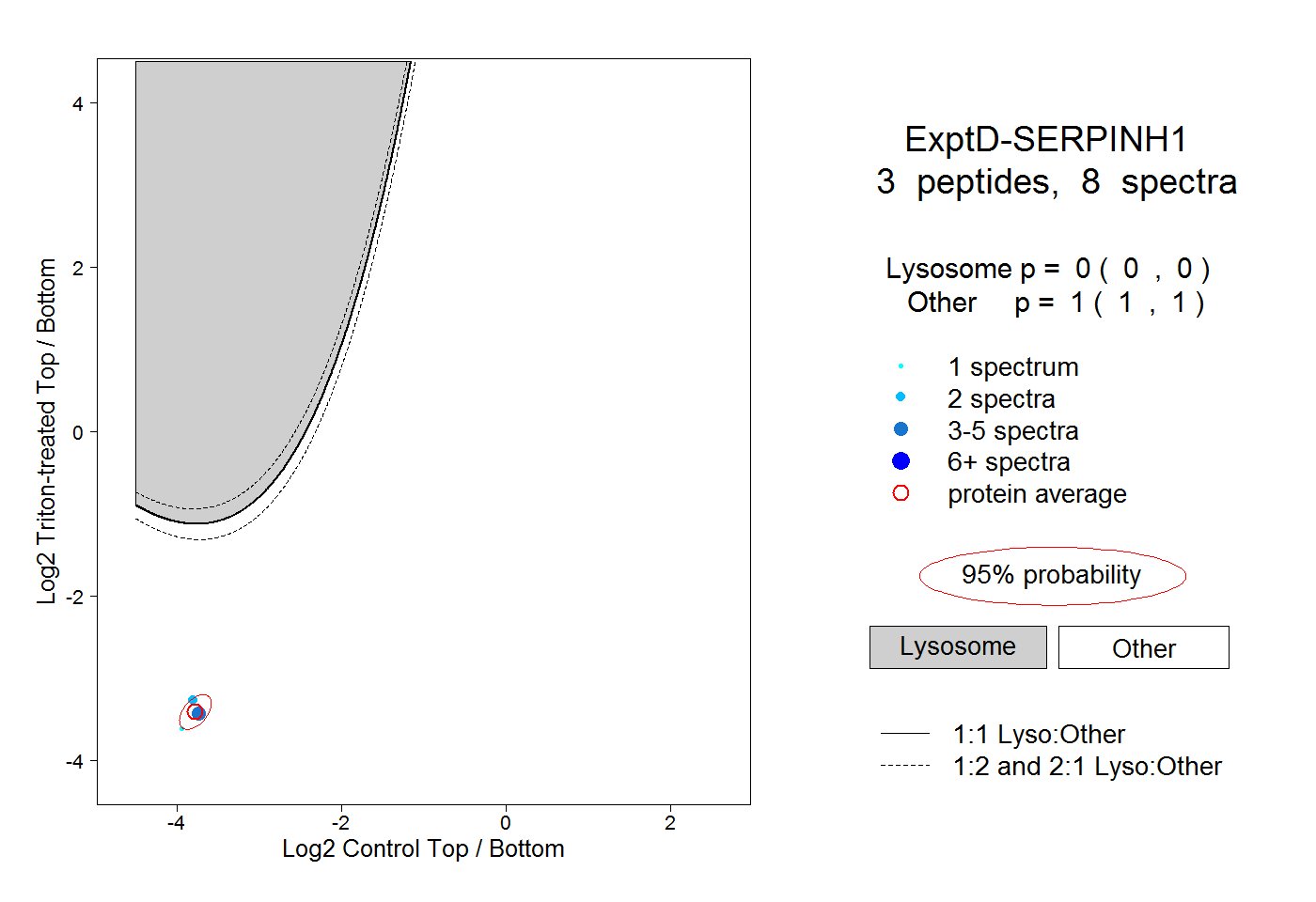 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |