peptides
spectra
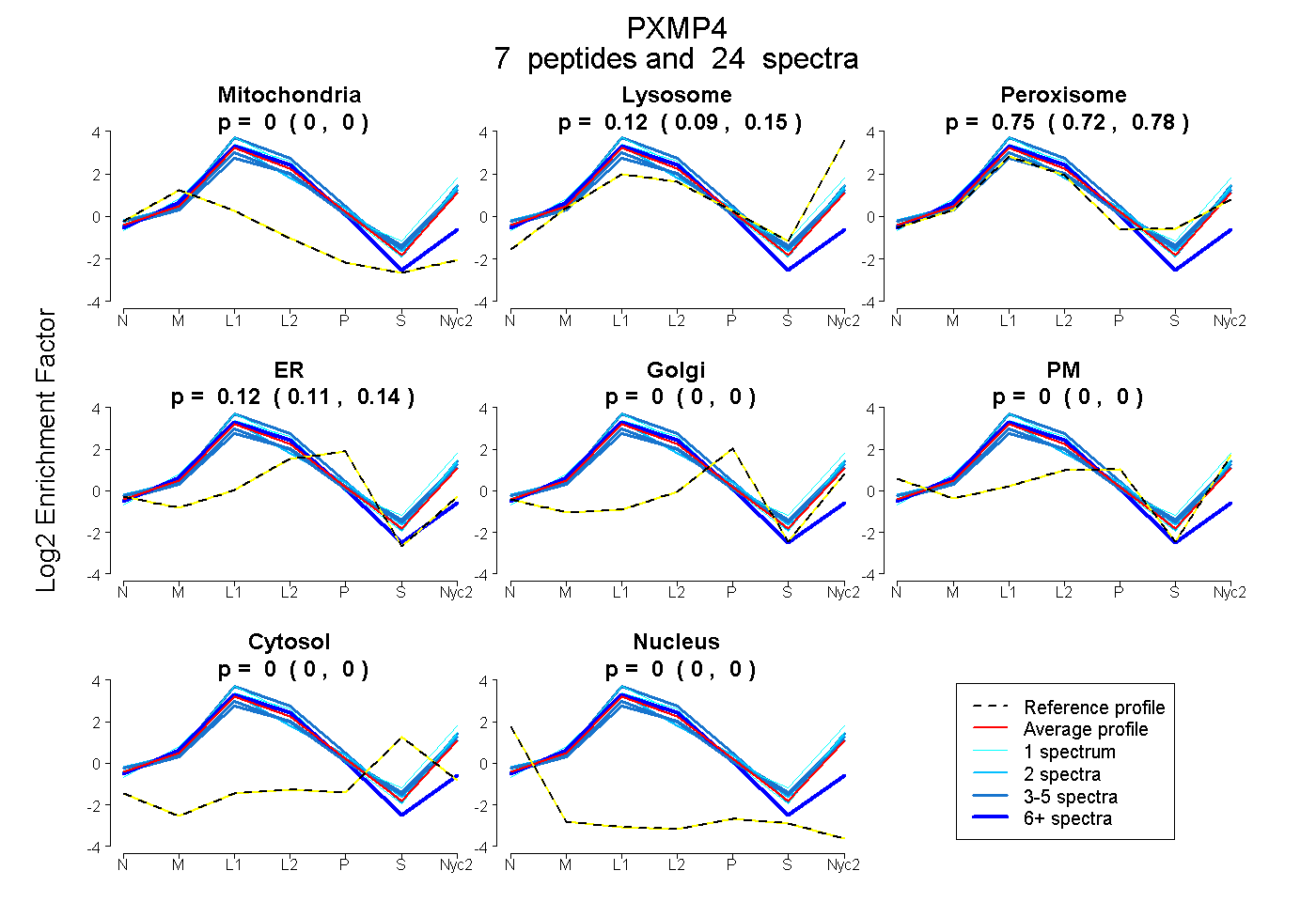
0.000 | 0.000
0.088 | 0.155
0.720 | 0.781
0.106 | 0.136
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
24 spectra |
 |
0.000 0.000 | 0.000 |
0.124 0.088 | 0.155 |
0.754 0.720 | 0.781 |
0.122 0.106 | 0.136 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 5 spectra, ALLQAVNK | 0.000 | 0.170 | 0.677 | 0.113 | 0.000 | 0.041 | 0.000 | 0.000 | ||
| 1 spectrum, NGAVYGVK | 0.000 | 0.249 | 0.714 | 0.036 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 6 spectra, VLFALCR | 0.067 | 0.000 | 0.709 | 0.224 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 5 spectra, YHAALAVIK | 0.000 | 0.059 | 0.787 | 0.044 | 0.000 | 0.110 | 0.000 | 0.000 | ||
| 1 spectrum, SGSLQEK | 0.000 | 0.246 | 0.754 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, ATYTHSR | 0.000 | 0.130 | 0.729 | 0.016 | 0.000 | 0.125 | 0.000 | 0.000 | ||
| 4 spectra, AAPPQLR | 0.000 | 0.220 | 0.721 | 0.058 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
23 spectra |
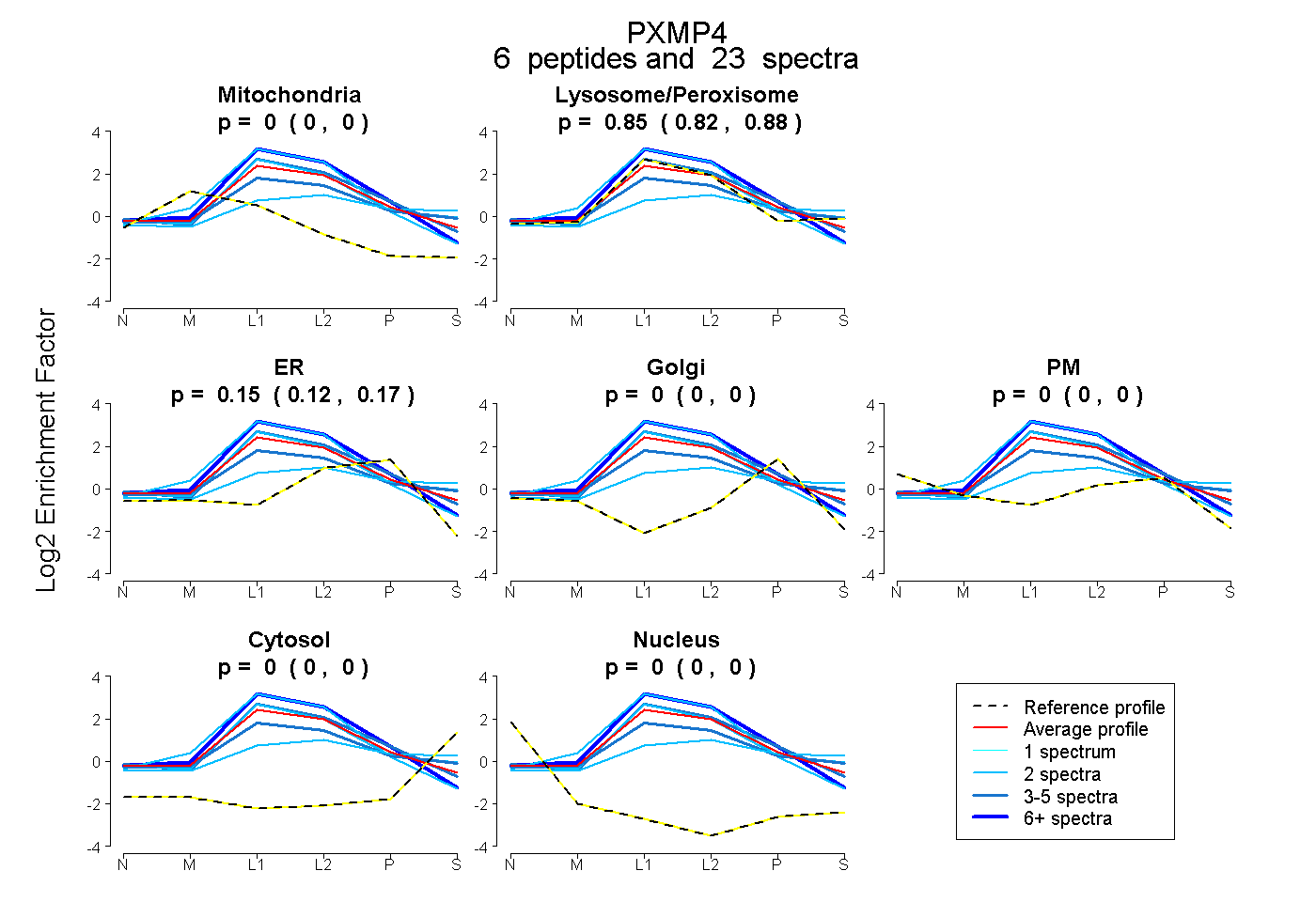 |
0.000 0.000 | 0.000 |
0.851 0.822 | 0.877 |
0.149 0.118 | 0.173 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
254 spectra |
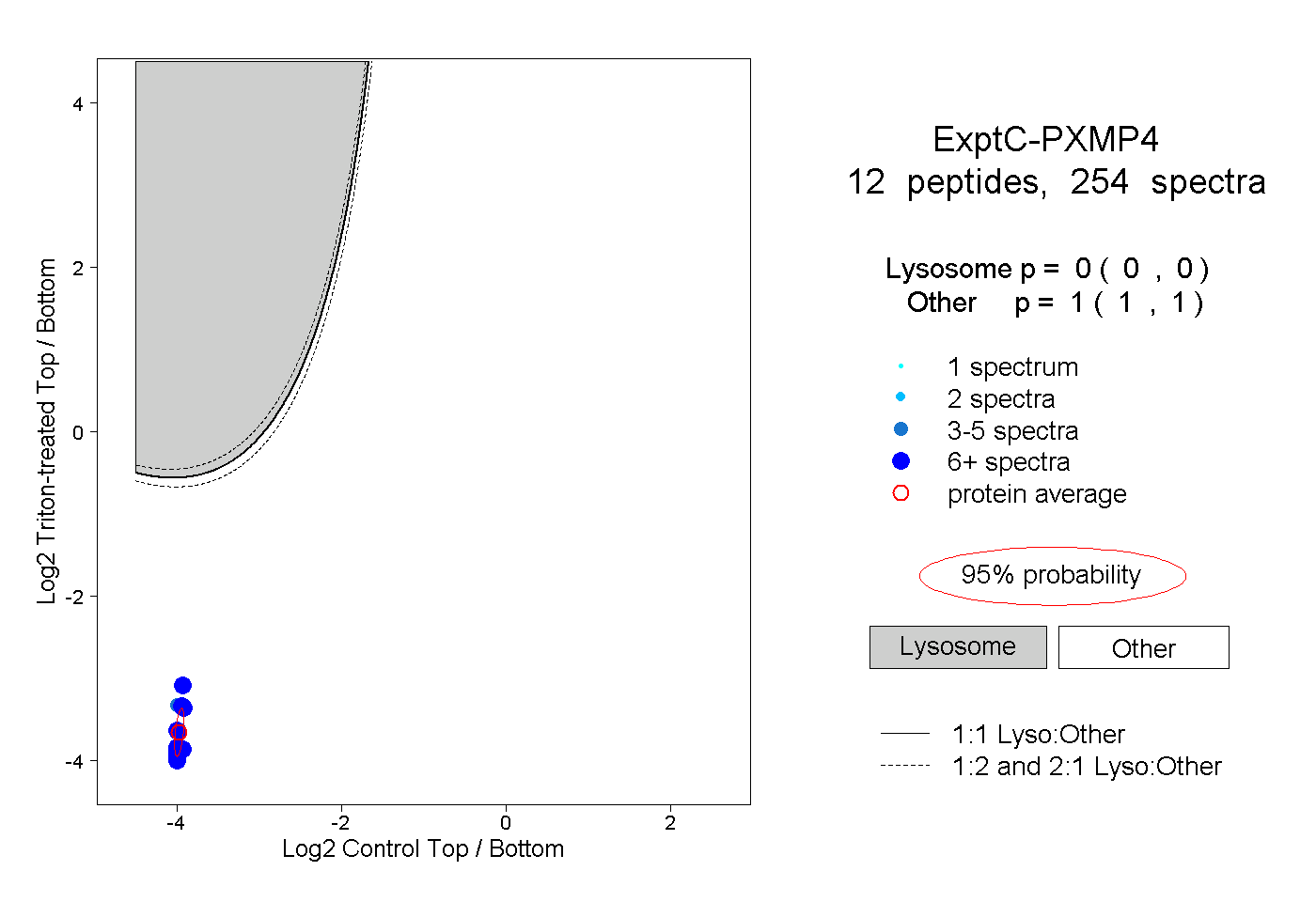 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
14 spectra |
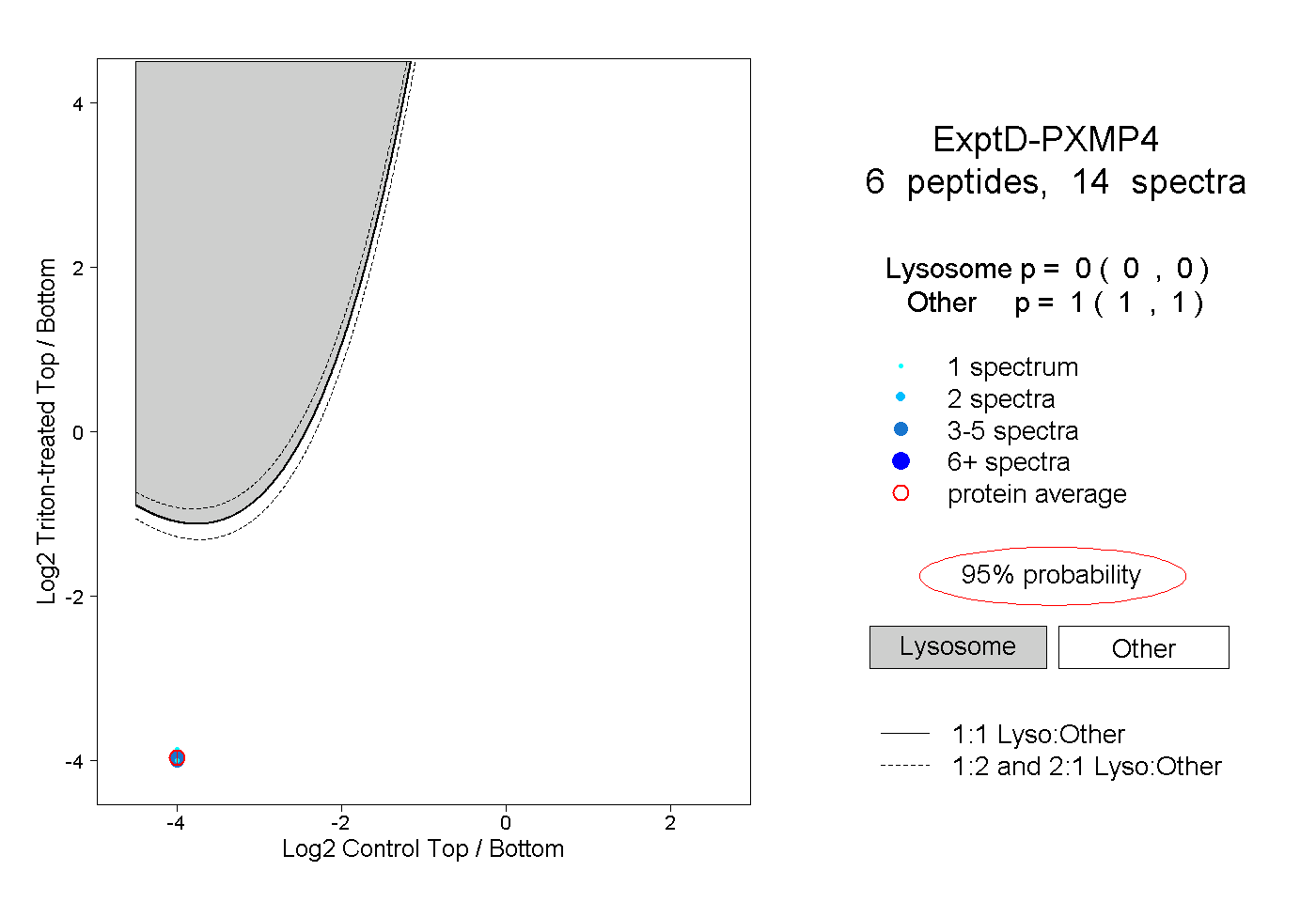 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |