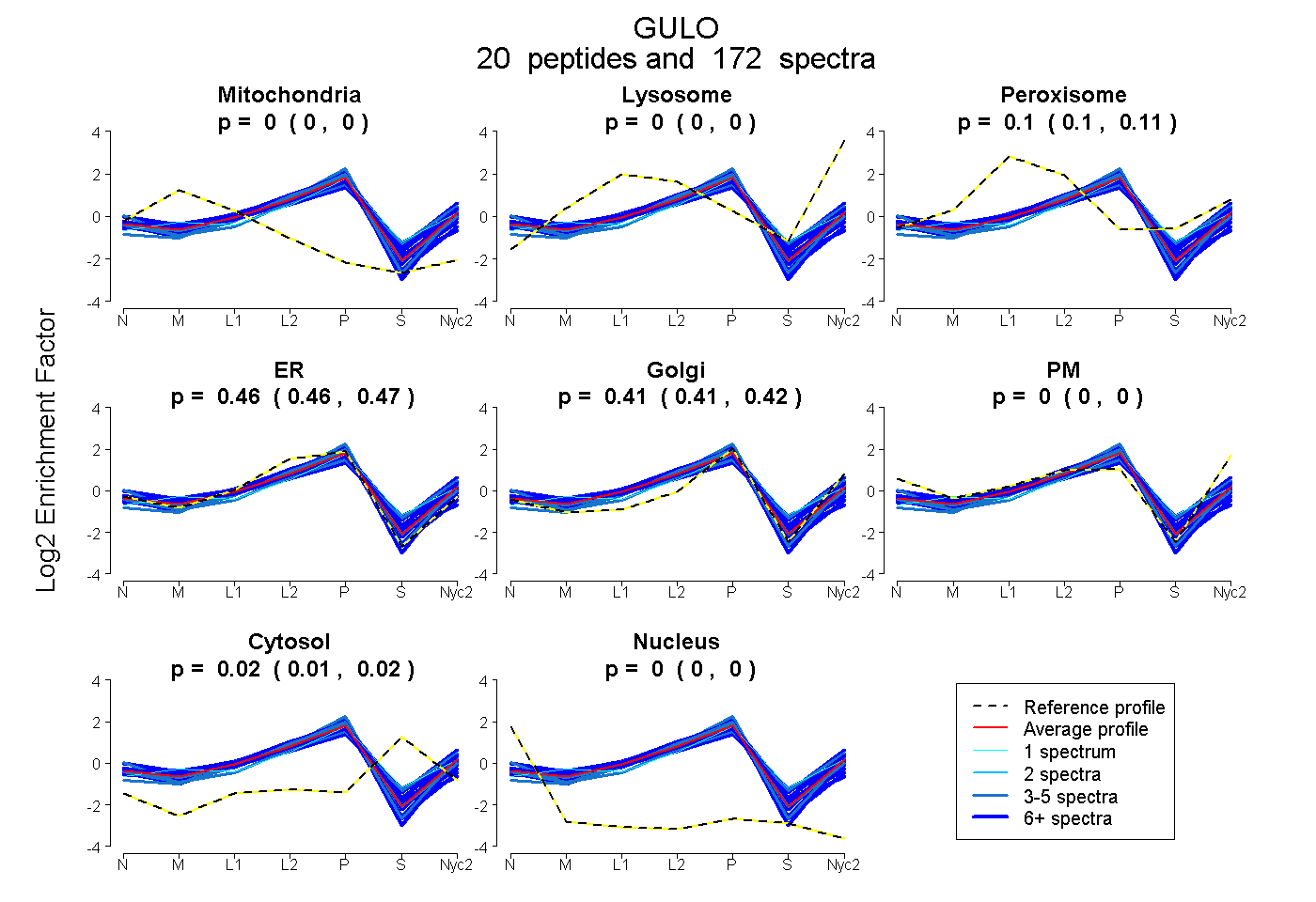
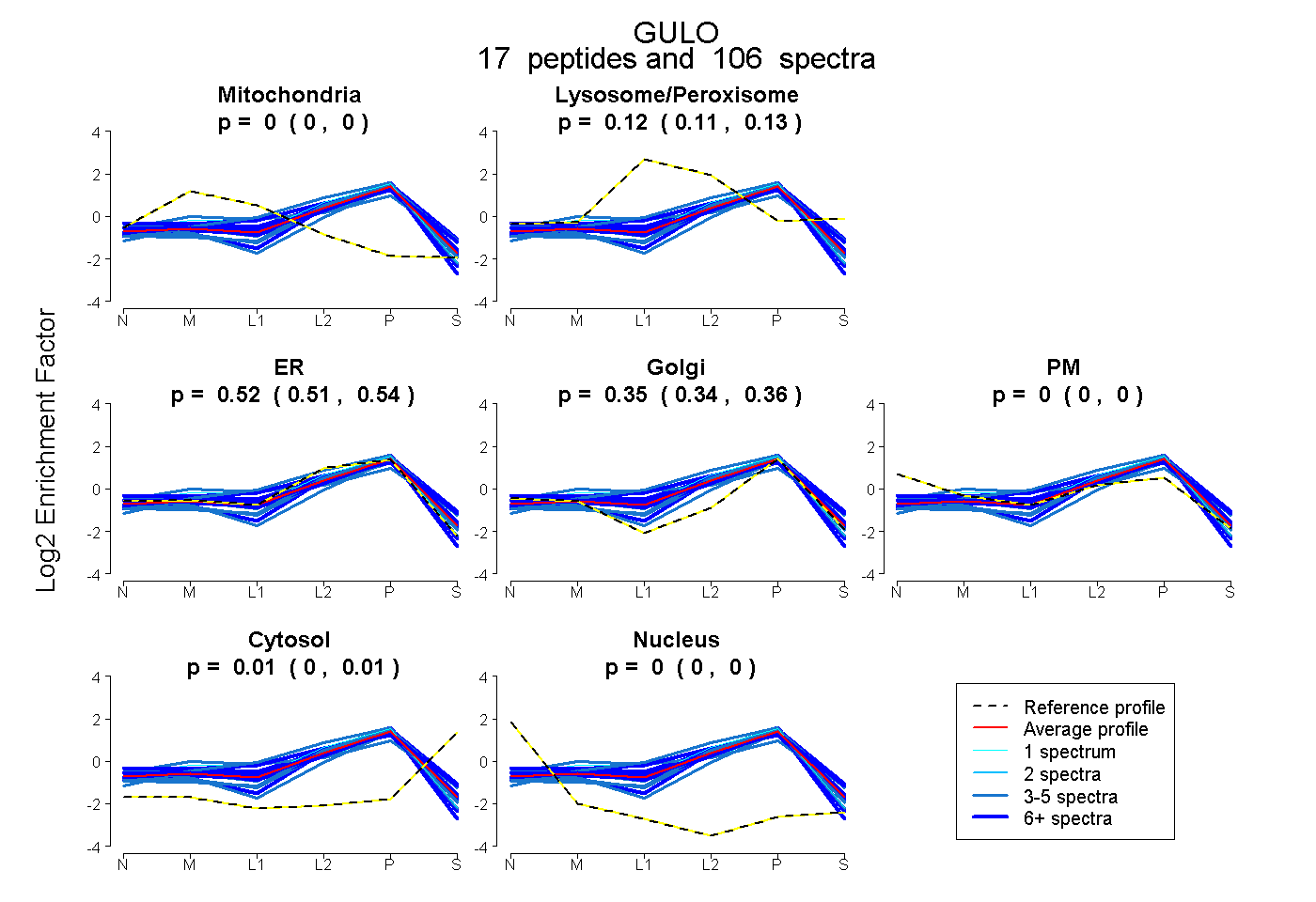
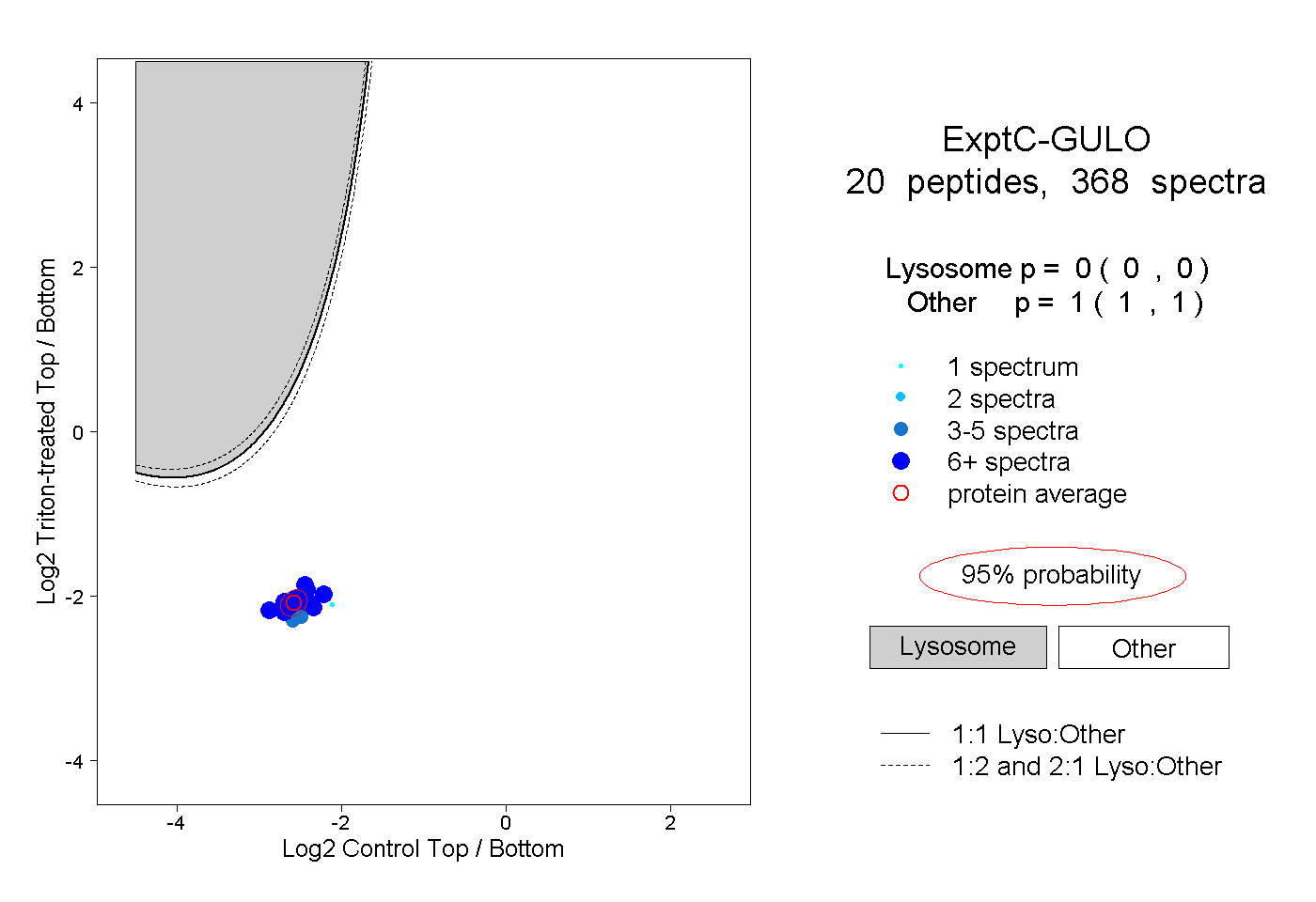
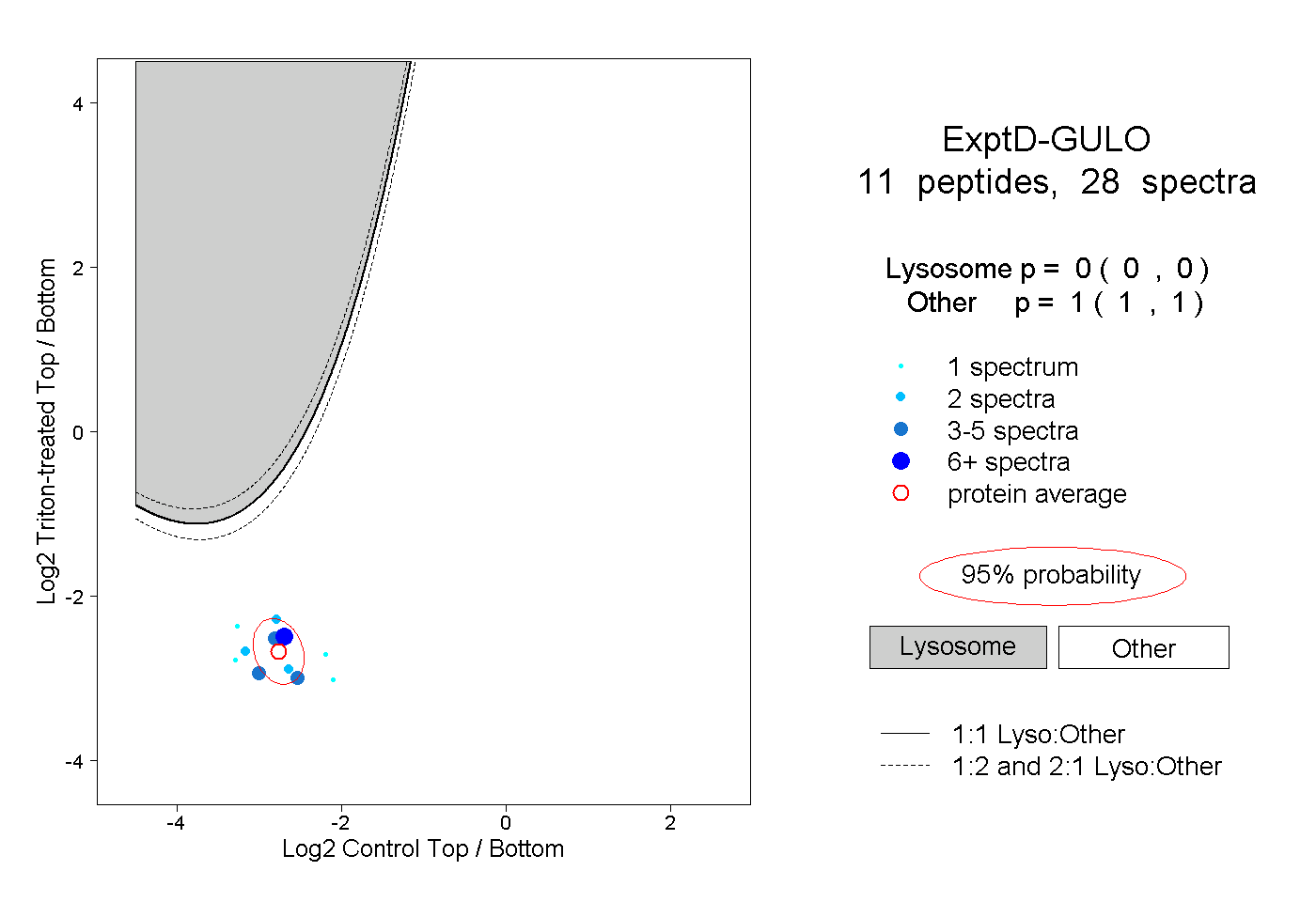
| 20 spectra, GVQFQNWAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, VVGGGHSPSDIACTDGFMIHMGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 91 spectra, AMLEAHPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, ESSNLSHK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 11 spectra, QHVQDWAIPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, FLWFPHTENVSIIYQDHTNK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 17 spectra, GDDILLSPCFQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 16 spectra, VLQVDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, IFTYECR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 24 spectra, VHGYK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 25 spectra, VVAHYPVEVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, LDPTGMFLNSYLEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, LDYWLAYETIMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 35 spectra, EVLDNLDSHLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 16 spectra, FGGRPHWAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 16 spectra, EVLALAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, EALLELK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 19 spectra, DFEEMYPTFHK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 17 spectra, DSCYMNIIMYRPYGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 28 spectra, NADVFQAAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |