peptides
spectra
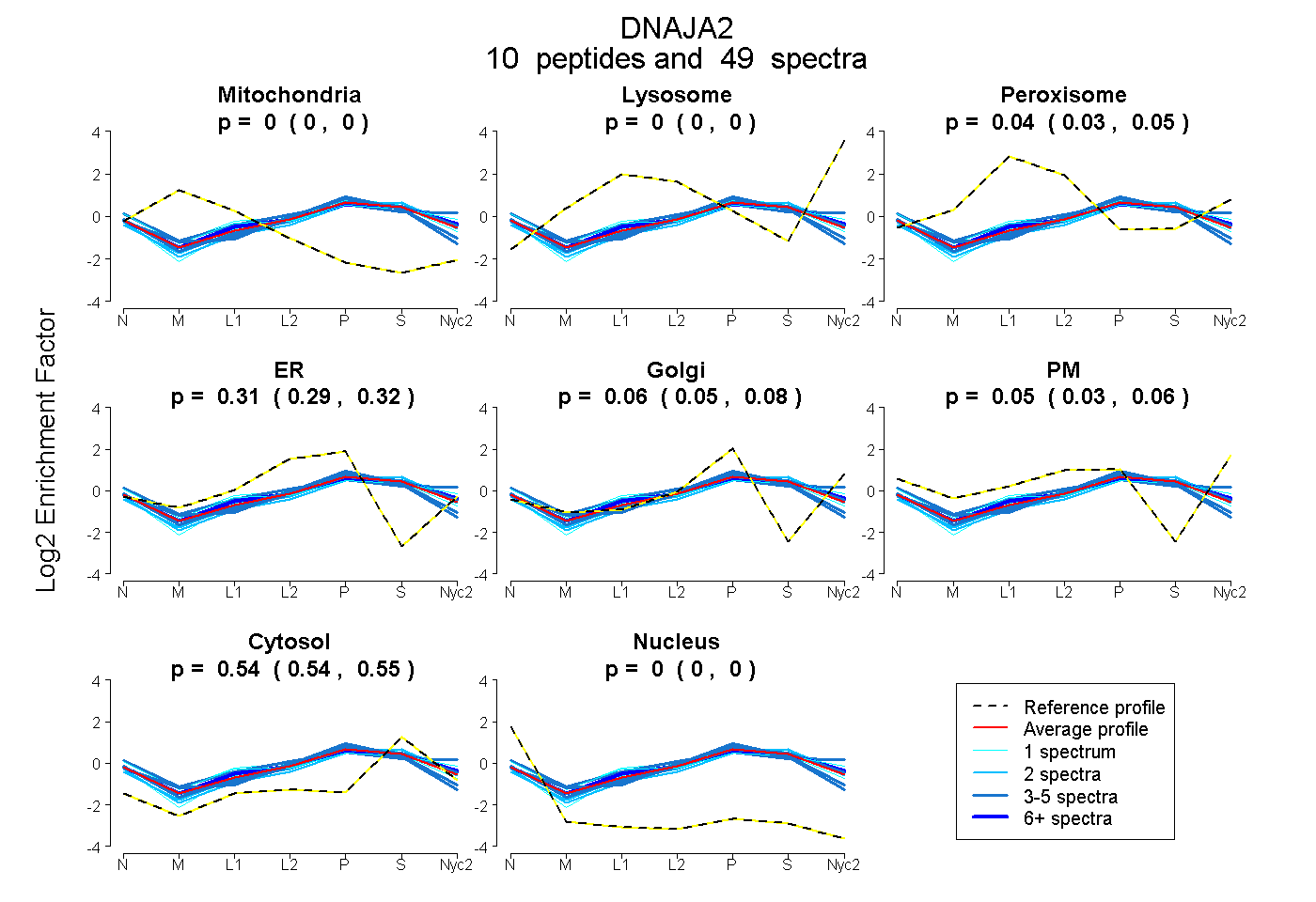
0.000 | 0.000
0.000 | 0.000
0.032 | 0.048
0.289 | 0.321
0.046 | 0.075
0.035 | 0.061
0.538 | 0.547
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
49 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.041 0.032 | 0.048 |
0.306 0.289 | 0.321 |
0.062 0.046 | 0.075 |
0.049 0.035 | 0.061 |
0.543 0.538 | 0.547 |
0.000 0.000 | 0.000 |
| 5 spectra, IIEVHVDK | 0.000 | 0.000 | 0.000 | 0.265 | 0.068 | 0.103 | 0.564 | 0.000 | ||
| 1 spectrum, EISFAYEVLSNPEK | 0.000 | 0.000 | 0.027 | 0.258 | 0.150 | 0.012 | 0.553 | 0.000 | ||
| 4 spectra, VIEPGCVR | 0.000 | 0.000 | 0.000 | 0.452 | 0.000 | 0.000 | 0.548 | 0.000 | ||
| 3 spectra, EHEVFQR | 0.000 | 0.000 | 0.070 | 0.078 | 0.007 | 0.382 | 0.464 | 0.000 | ||
| 1 spectrum, LYDILGVPPGASENELK | 0.000 | 0.000 | 0.111 | 0.076 | 0.100 | 0.222 | 0.492 | 0.000 | ||
| 26 spectra, GEGMPQYR | 0.000 | 0.000 | 0.092 | 0.212 | 0.109 | 0.064 | 0.523 | 0.000 | ||
| 4 spectra, NVLCSACSGQGGK | 0.000 | 0.000 | 0.000 | 0.452 | 0.000 | 0.000 | 0.546 | 0.002 | ||
| 1 spectrum, DGNDLHMTYK | 0.000 | 0.000 | 0.121 | 0.378 | 0.000 | 0.000 | 0.501 | 0.000 | ||
| 2 spectra, GDLYIK | 0.000 | 0.000 | 0.000 | 0.257 | 0.087 | 0.022 | 0.634 | 0.000 | ||
| 2 spectra, FDVQFPENNWINPDK | 0.000 | 0.000 | 0.060 | 0.200 | 0.163 | 0.000 | 0.577 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
8 spectra |
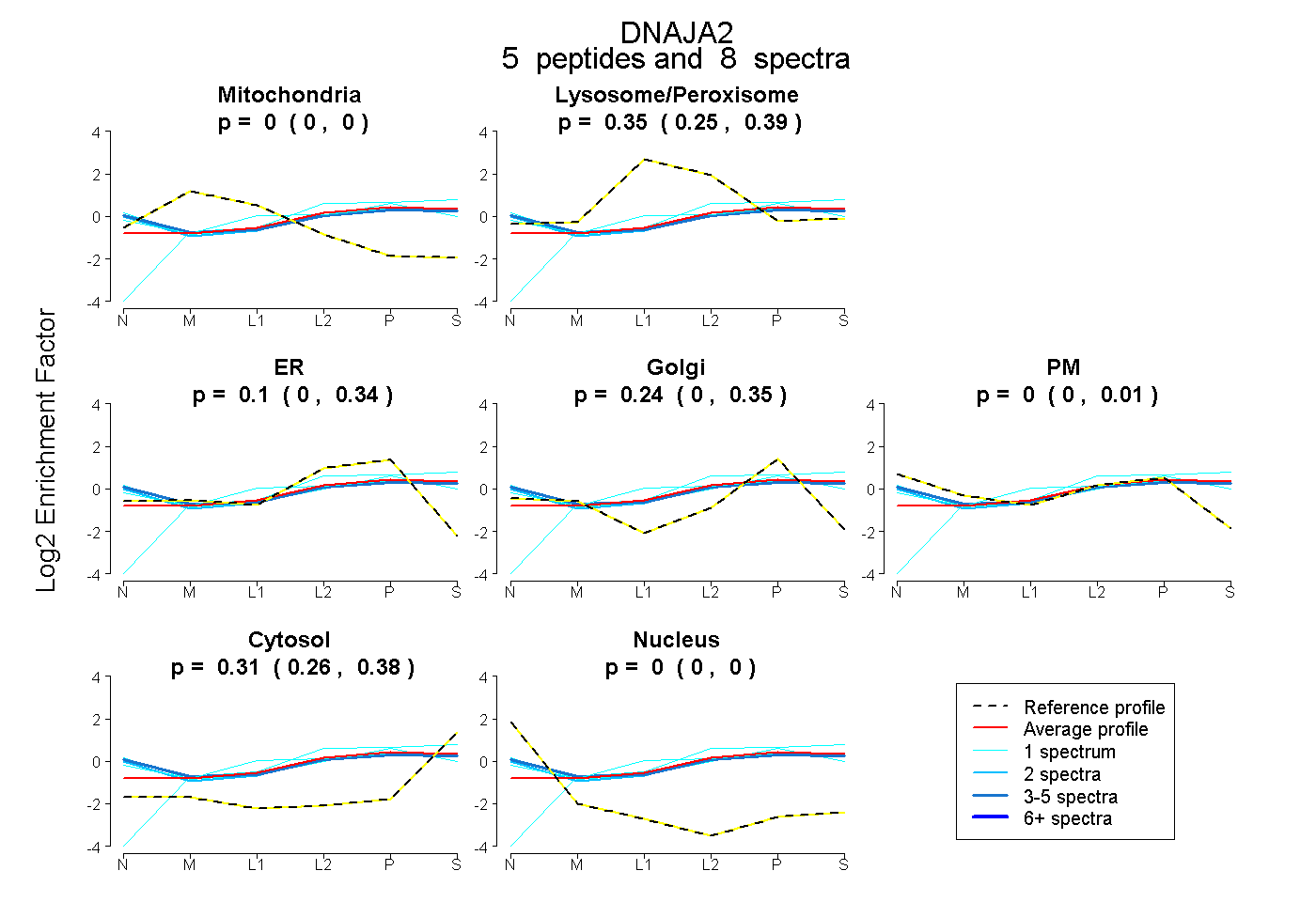 |
0.000 0.000 | 0.000 |
0.350 0.253 | 0.391 |
0.098 0.000 | 0.339 |
0.243 0.000 | 0.347 |
0.000 0.000 | 0.005 |
0.309 0.257 | 0.385 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
56 spectra |
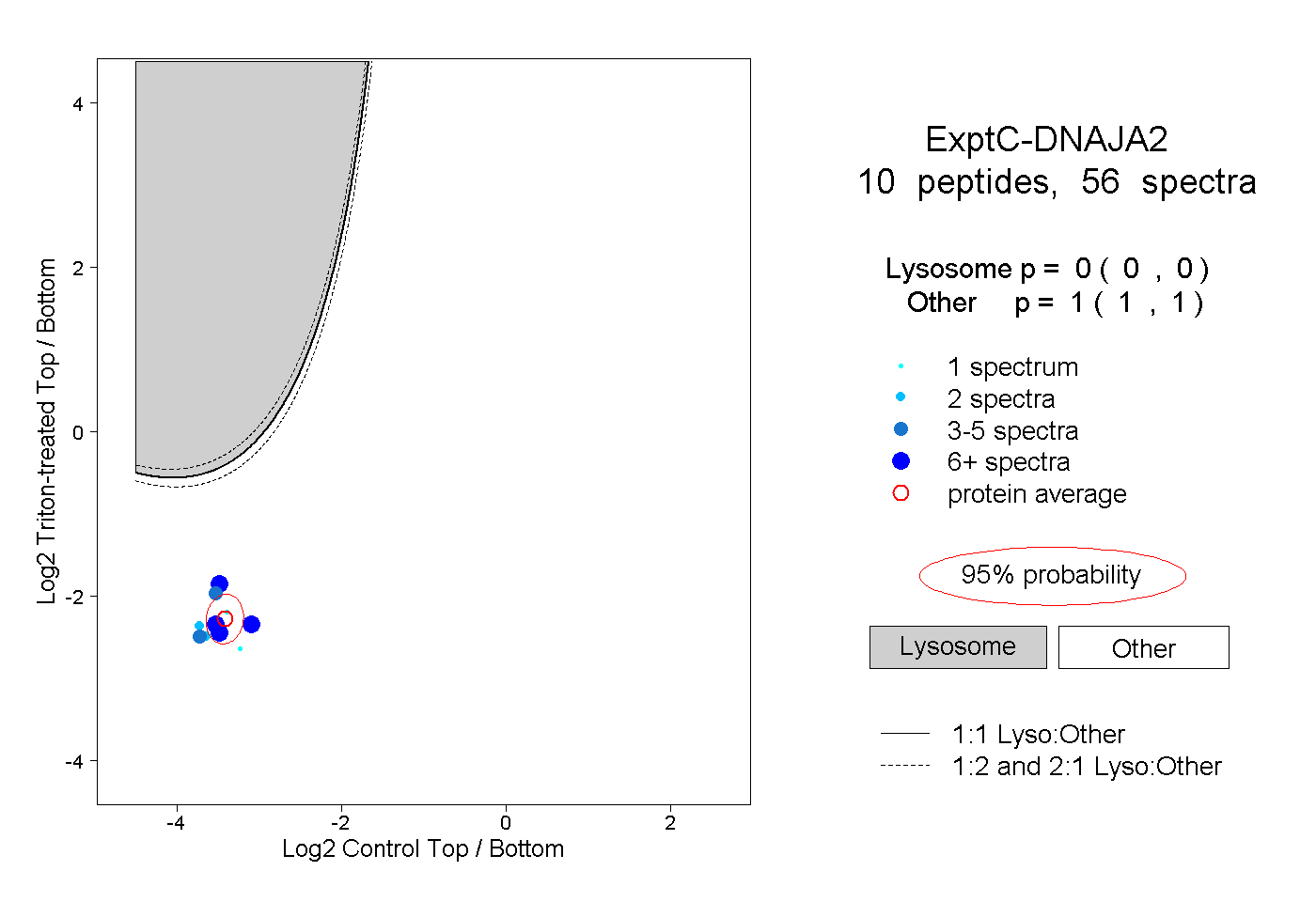 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
5 spectra |
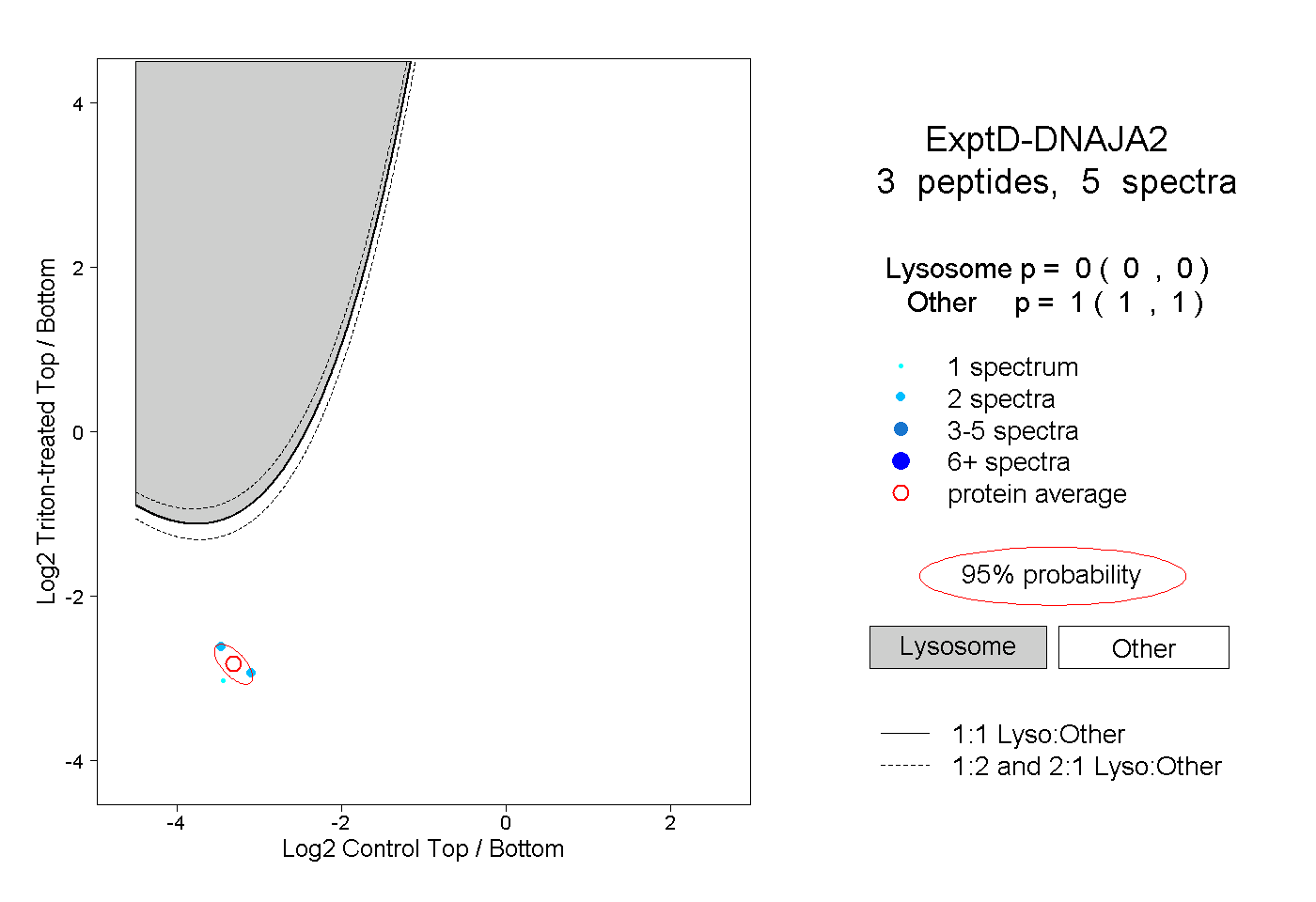 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |