peptides
spectra
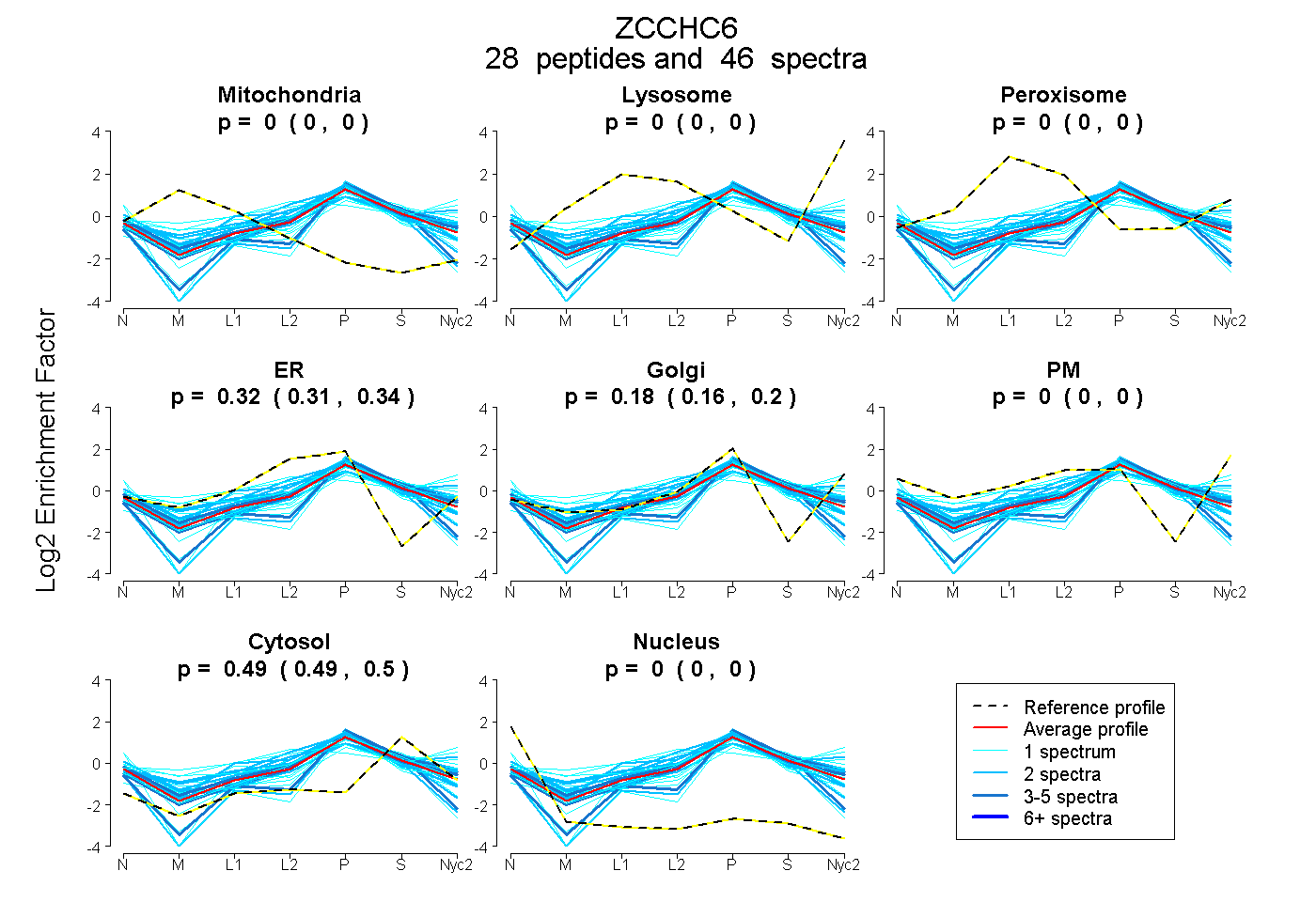
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.305 | 0.337
0.164 | 0.199
0.000 | 0.000
0.491 | 0.498
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
46 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.322 0.305 | 0.337 |
0.183 0.164 | 0.199 |
0.000 0.000 | 0.000 |
0.495 0.491 | 0.498 |
0.000 0.000 | 0.000 |
| 2 spectra, ELLGLQQAEER | 0.000 | 0.000 | 0.000 | 0.508 | 0.027 | 0.000 | 0.464 | 0.000 | ||
| 1 spectrum, ADVNER | 0.000 | 0.000 | 0.000 | 0.000 | 0.362 | 0.083 | 0.494 | 0.060 | ||
| 1 spectrum, YFALPHK | 0.000 | 0.000 | 0.000 | 0.325 | 0.155 | 0.000 | 0.520 | 0.000 | ||
| 2 spectra, TIEELAR | 0.000 | 0.000 | 0.000 | 0.416 | 0.109 | 0.000 | 0.476 | 0.000 | ||
| 1 spectrum, NILPITTAK | 0.000 | 0.000 | 0.000 | 0.369 | 0.241 | 0.000 | 0.390 | 0.000 | ||
| 1 spectrum, EHVISIR | 0.000 | 0.000 | 0.000 | 0.148 | 0.347 | 0.000 | 0.505 | 0.000 | ||
| 1 spectrum, ESFQESEDTYR | 0.000 | 0.000 | 0.000 | 0.000 | 0.296 | 0.000 | 0.592 | 0.112 | ||
| 1 spectrum, YLCYTMK | 0.020 | 0.000 | 0.060 | 0.371 | 0.203 | 0.000 | 0.346 | 0.000 | ||
| 1 spectrum, LSLFGSSK | 0.000 | 0.000 | 0.000 | 0.091 | 0.481 | 0.000 | 0.428 | 0.000 | ||
| 1 spectrum, GIIDDDDFR | 0.000 | 0.000 | 0.000 | 0.000 | 0.435 | 0.000 | 0.565 | 0.000 | ||
| 2 spectra, IAIEDPYSVK | 0.000 | 0.000 | 0.033 | 0.102 | 0.357 | 0.000 | 0.508 | 0.000 | ||
| 2 spectra, QNLESFIK | 0.000 | 0.000 | 0.153 | 0.202 | 0.243 | 0.000 | 0.401 | 0.000 | ||
| 1 spectrum, FYTEEFDFK | 0.000 | 0.000 | 0.053 | 0.406 | 0.000 | 0.000 | 0.540 | 0.000 | ||
| 1 spectrum, LYGSSCSR | 0.000 | 0.000 | 0.311 | 0.000 | 0.153 | 0.240 | 0.297 | 0.000 | ||
| 1 spectrum, AAPCTAAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.444 | 0.036 | 0.521 | 0.000 | ||
| 4 spectra, IGHFMK | 0.000 | 0.000 | 0.000 | 0.413 | 0.000 | 0.000 | 0.540 | 0.047 | ||
| 2 spectra, VPVVVCR | 0.000 | 0.000 | 0.000 | 0.548 | 0.000 | 0.000 | 0.436 | 0.016 | ||
| 1 spectrum, TLNNQPVFEYILHCLR | 0.000 | 0.033 | 0.214 | 0.000 | 0.216 | 0.262 | 0.274 | 0.000 | ||
| 1 spectrum, LGNFSLK | 0.000 | 0.000 | 0.000 | 0.258 | 0.254 | 0.000 | 0.489 | 0.000 | ||
| 2 spectra, LPDCSLR | 0.000 | 0.000 | 0.000 | 0.377 | 0.219 | 0.000 | 0.404 | 0.000 | ||
| 3 spectra, VVQEFGLHNENLDQR | 0.000 | 0.000 | 0.000 | 0.348 | 0.195 | 0.000 | 0.457 | 0.000 | ||
| 2 spectra, QSGLLCK | 0.000 | 0.000 | 0.068 | 0.500 | 0.072 | 0.000 | 0.360 | 0.000 | ||
| 4 spectra, MSPGNYGNTPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.421 | 0.000 | 0.579 | 0.000 | ||
| 2 spectra, EFKPGPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.352 | 0.000 | 0.608 | 0.040 | ||
| 2 spectra, MCDIGDASR | 0.000 | 0.000 | 0.007 | 0.177 | 0.018 | 0.372 | 0.425 | 0.000 | ||
| 2 spectra, DFSPTIVEDQAR | 0.000 | 0.000 | 0.000 | 0.436 | 0.000 | 0.000 | 0.527 | 0.038 | ||
| 1 spectrum, CFICGR | 0.000 | 0.000 | 0.000 | 0.464 | 0.140 | 0.000 | 0.391 | 0.006 | ||
| 1 spectrum, LCDALIDSIPFAHK | 0.000 | 0.000 | 0.000 | 0.429 | 0.000 | 0.000 | 0.452 | 0.119 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
13 spectra |
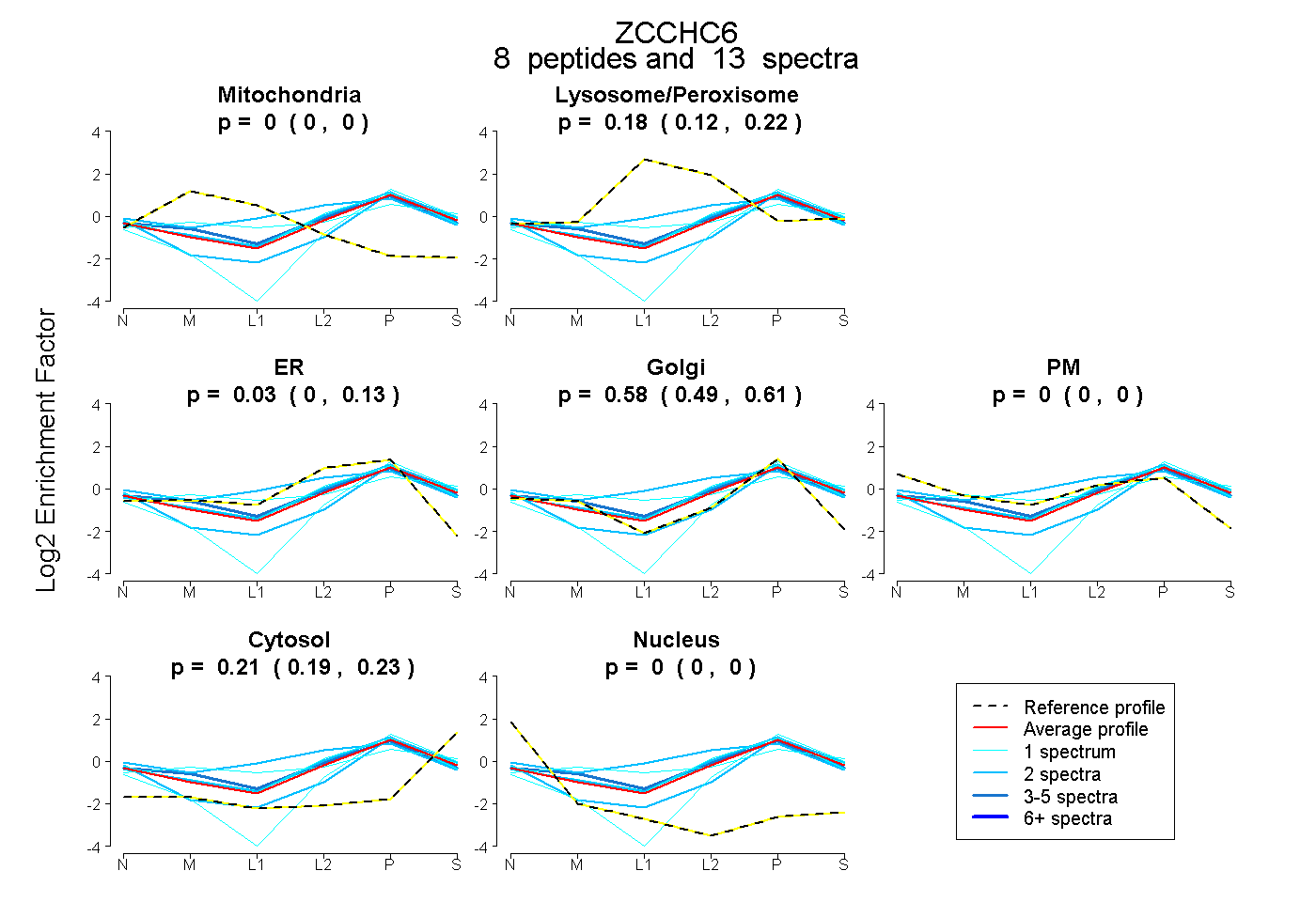 |
0.000 0.000 | 0.000 |
0.181 0.118 | 0.216 |
0.028 0.000 | 0.128 |
0.584 0.487 | 0.614 |
0.000 0.000 | 0.000 |
0.206 0.187 | 0.232 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
39 spectra |
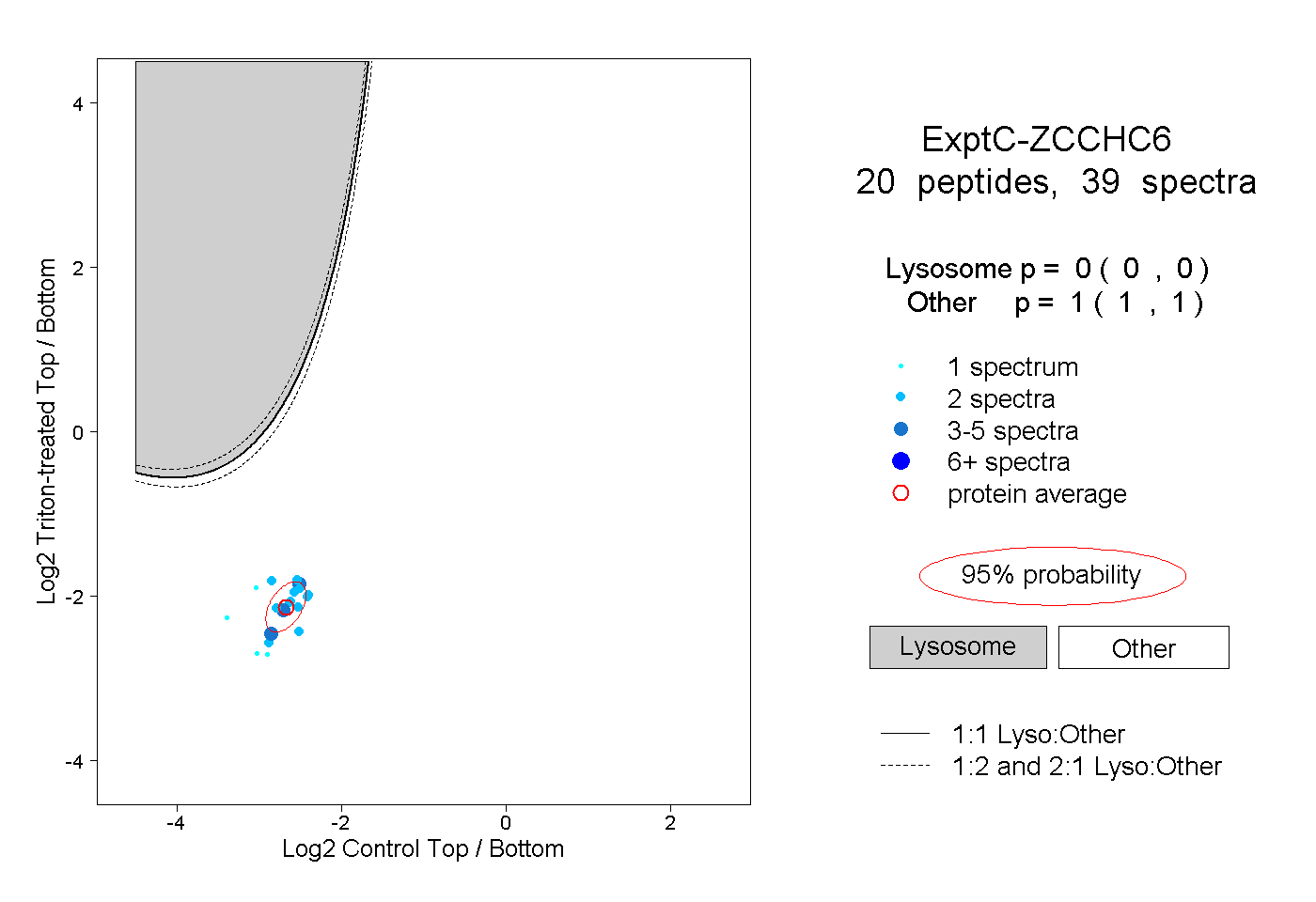 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
3 spectra |
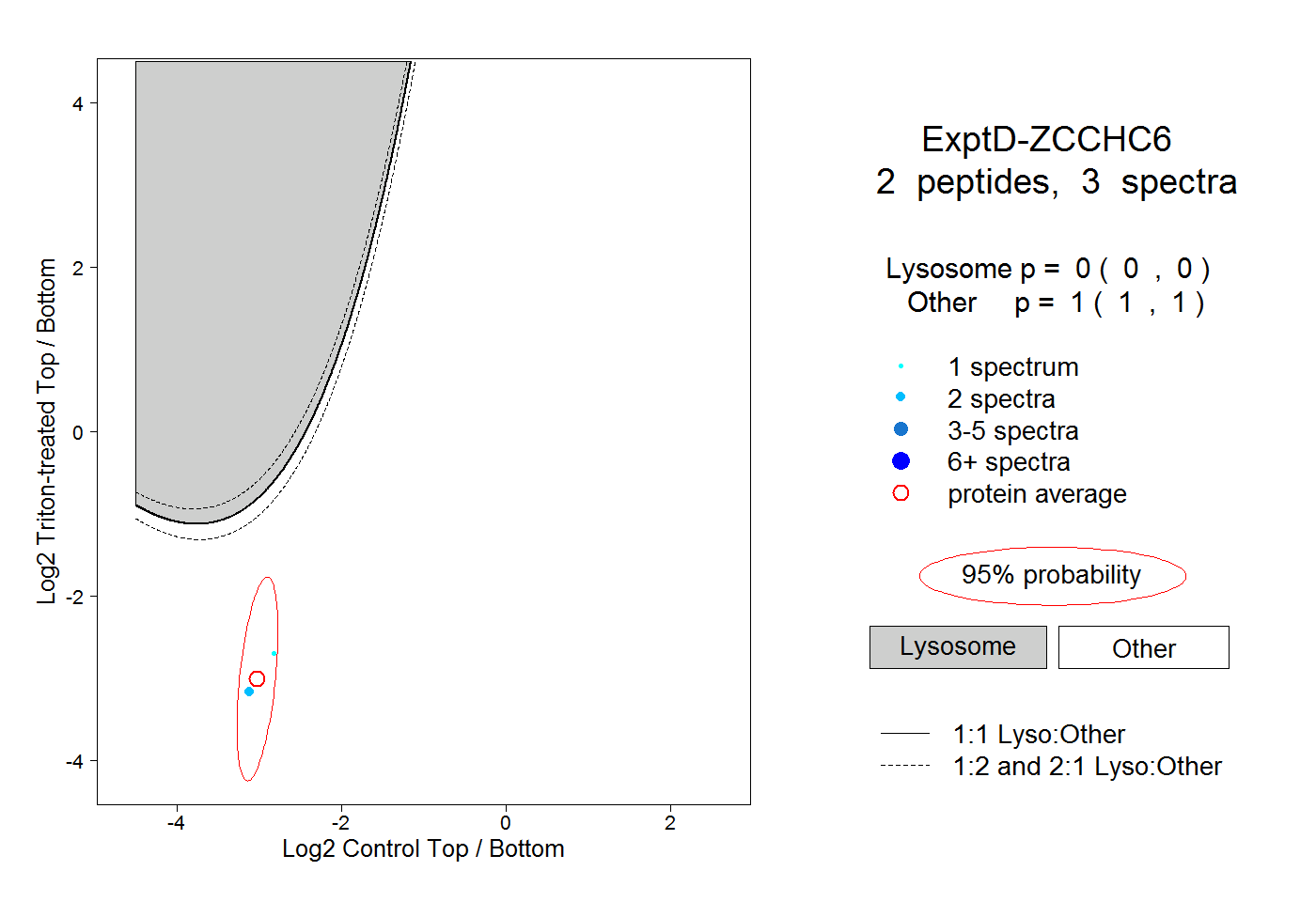 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |