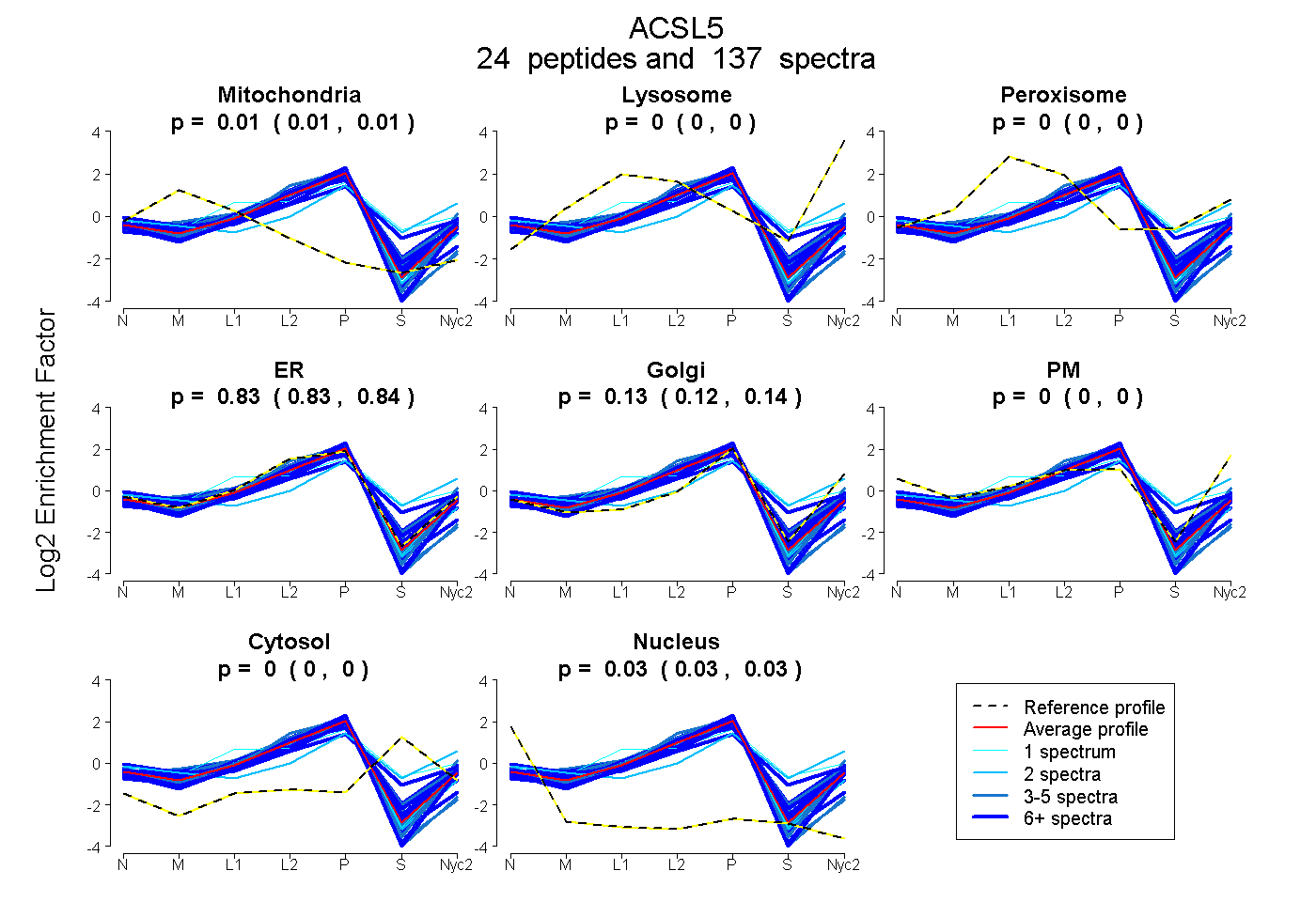
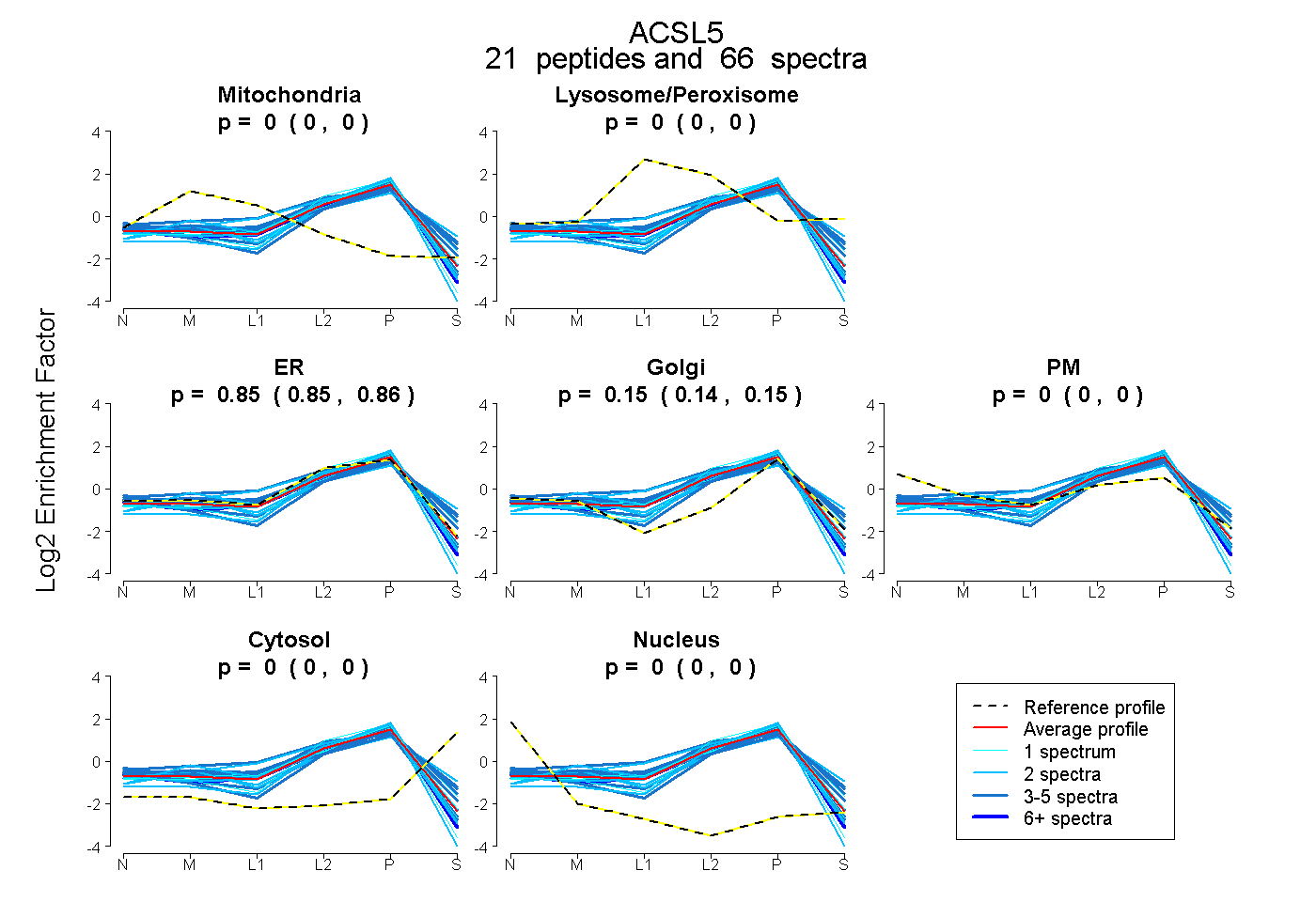
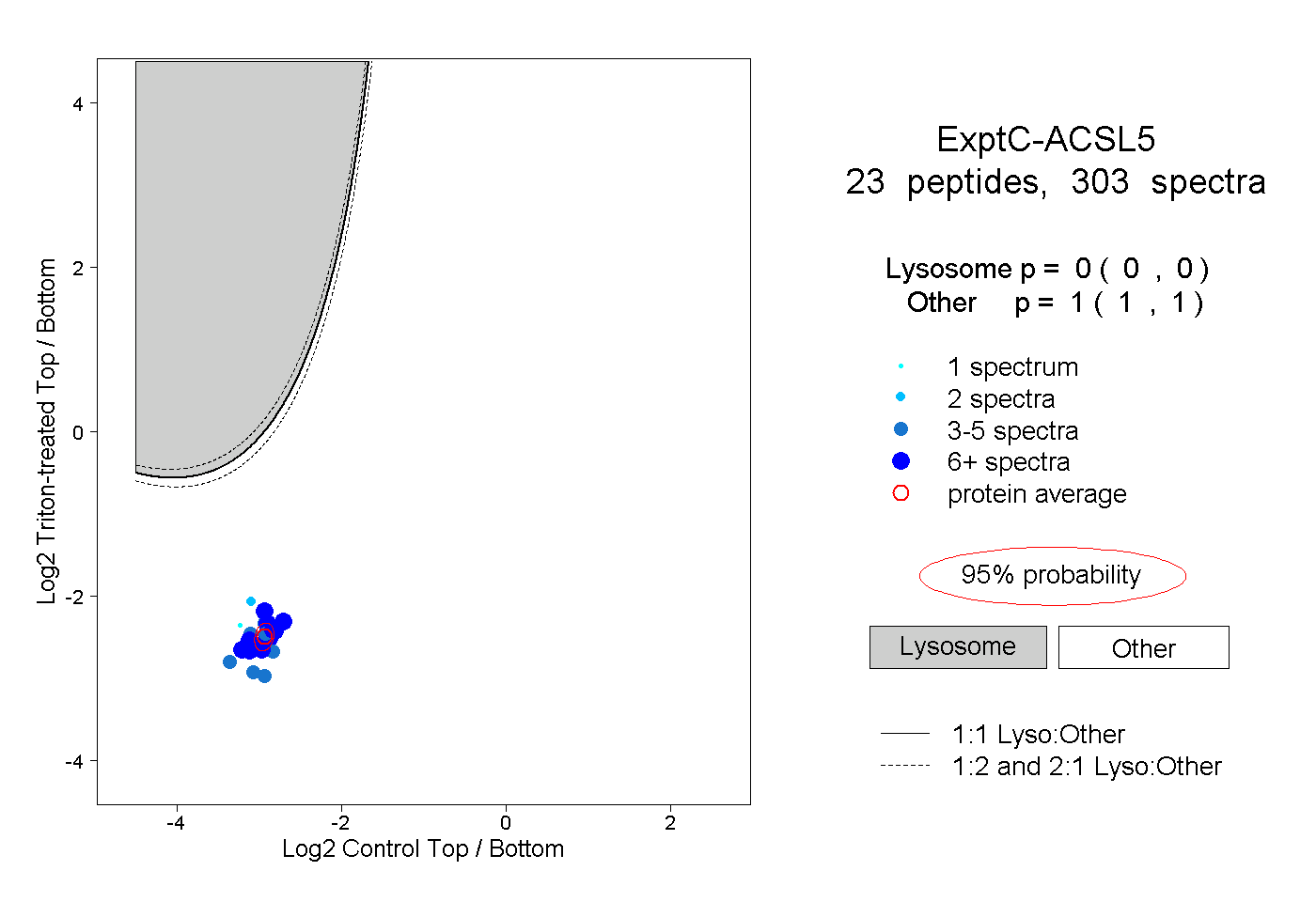
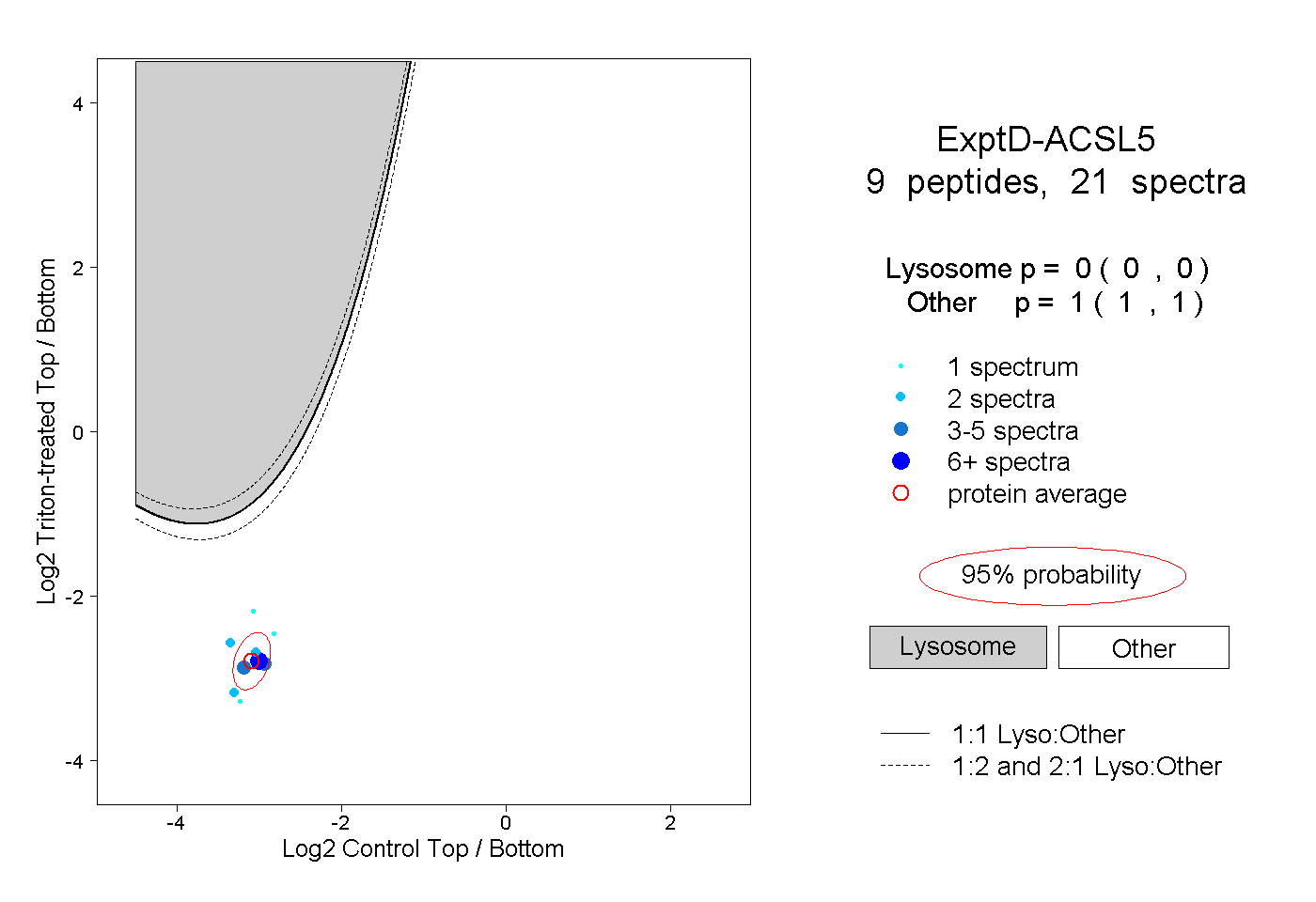
| 8 spectra, TQEVLDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LMITGAAPISTPVLTFFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, GSFEELCQNQCVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 15 spectra, SFEQVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 11 spectra, TLYEVFQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 13 spectra, DLTPGLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, LLPDDMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 33 spectra, GNNVFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 13 spectra, AILEDLQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 21 spectra, ALKPTVFPTVPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, TVILMDPFDDDLMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, AEYLGSCLLHK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, DGWLHTGDIGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, GAMLTHQNIVSNMAAFLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, ATMLIENVEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, NNDLILYYFSDAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, FFQTQIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, NSLWDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 41 spectra, VQNEAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, ADISVVICDTPQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, GLAVSDNGPCLGYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 65 spectra, KPNQPYK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 19 spectra, IENVYSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |