peptides
spectra
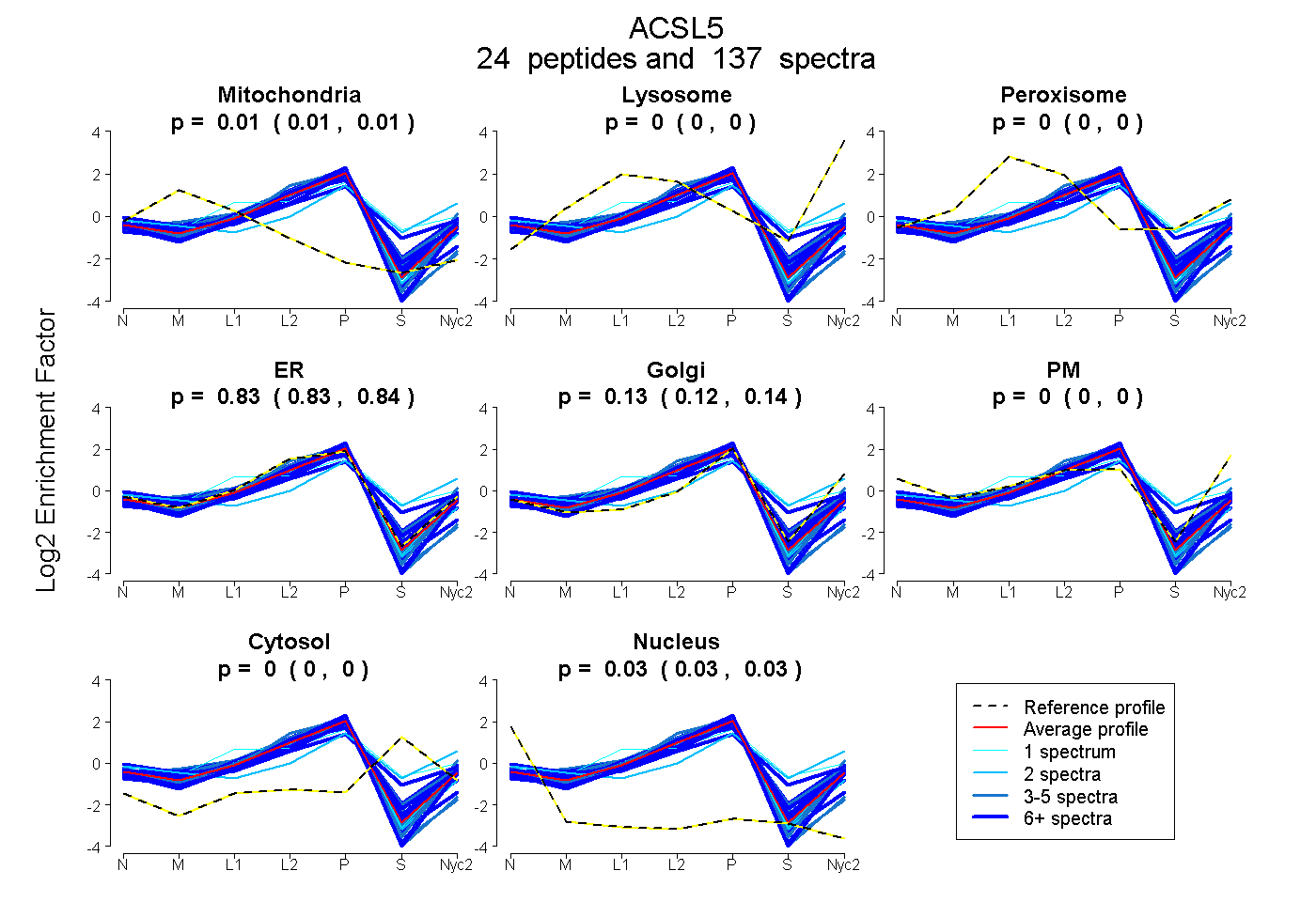
0.007 | 0.011
0.000 | 0.000
0.000 | 0.000
0.827 | 0.840
0.122 | 0.135
0.000 | 0.000
0.000 | 0.000
0.025 | 0.029
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
137 spectra |
 |
0.009 0.007 | 0.011 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.834 0.827 | 0.840 |
0.129 0.122 | 0.135 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.027 0.025 | 0.029 |
| 5 spectra, TQEVLDK | 0.000 | 0.000 | 0.000 | 0.840 | 0.158 | 0.000 | 0.000 | 0.002 | ||
| 7 spectra, SFEQVK | 0.072 | 0.000 | 0.000 | 0.614 | 0.278 | 0.000 | 0.036 | 0.000 | ||
| 4 spectra, TLYEVFQR | 0.000 | 0.000 | 0.000 | 0.908 | 0.085 | 0.000 | 0.000 | 0.006 | ||
| 5 spectra, DLTPGLK | 0.024 | 0.000 | 0.073 | 0.624 | 0.279 | 0.000 | 0.000 | 0.000 | ||
| 8 spectra, LLPDDMK | 0.000 | 0.000 | 0.078 | 0.661 | 0.191 | 0.000 | 0.069 | 0.000 | ||
| 7 spectra, GNNVFK | 0.000 | 0.000 | 0.000 | 0.977 | 0.001 | 0.000 | 0.000 | 0.023 | ||
| 9 spectra, AILEDLQK | 0.000 | 0.000 | 0.000 | 0.901 | 0.000 | 0.000 | 0.000 | 0.099 | ||
| 16 spectra, ALKPTVFPTVPR | 0.000 | 0.000 | 0.000 | 0.880 | 0.106 | 0.000 | 0.000 | 0.014 | ||
| 10 spectra, TVILMDPFDDDLMK | 0.000 | 0.000 | 0.000 | 0.783 | 0.176 | 0.000 | 0.040 | 0.000 | ||
| 4 spectra, AEYLGSCLLHK | 0.126 | 0.000 | 0.000 | 0.865 | 0.000 | 0.000 | 0.000 | 0.009 | ||
| 4 spectra, DGWLHTGDIGR | 0.000 | 0.000 | 0.000 | 0.953 | 0.016 | 0.000 | 0.000 | 0.031 | ||
| 9 spectra, SLYESIEE | 0.012 | 0.000 | 0.100 | 0.431 | 0.241 | 0.028 | 0.188 | 0.000 | ||
| 6 spectra, GAMLTHQNIVSNMAAFLK | 0.000 | 0.000 | 0.000 | 0.826 | 0.174 | 0.000 | 0.000 | 0.000 | ||
| 6 spectra, ATMLIENVEK | 0.071 | 0.000 | 0.000 | 0.778 | 0.151 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, SRPILQVFVHGESLR | 0.000 | 0.000 | 0.103 | 0.000 | 0.588 | 0.111 | 0.197 | 0.000 | ||
| 4 spectra, NNDLILYYFSDAK | 0.000 | 0.000 | 0.000 | 0.849 | 0.139 | 0.012 | 0.000 | 0.000 | ||
| 9 spectra, FFQTQIK | 0.000 | 0.000 | 0.000 | 0.822 | 0.100 | 0.000 | 0.022 | 0.056 | ||
| 4 spectra, NSLWDK | 0.016 | 0.000 | 0.003 | 0.732 | 0.182 | 0.000 | 0.067 | 0.000 | ||
| 8 spectra, VQNEAK | 0.000 | 0.000 | 0.000 | 0.840 | 0.129 | 0.000 | 0.000 | 0.030 | ||
| 3 spectra, ADISVVICDTPQK | 0.000 | 0.000 | 0.000 | 0.925 | 0.000 | 0.000 | 0.000 | 0.075 | ||
| 2 spectra, GLAVSDNGPCLGYR | 0.000 | 0.000 | 0.000 | 0.929 | 0.013 | 0.000 | 0.000 | 0.058 | ||
| 1 spectrum, KPNQPYK | 0.000 | 0.000 | 0.000 | 0.877 | 0.106 | 0.000 | 0.000 | 0.017 | ||
| 3 spectra, CGIEMLSLHDAENLGK | 0.065 | 0.000 | 0.000 | 0.912 | 0.023 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, IENVYSR | 0.000 | 0.000 | 0.295 | 0.316 | 0.246 | 0.000 | 0.142 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
66 spectra |
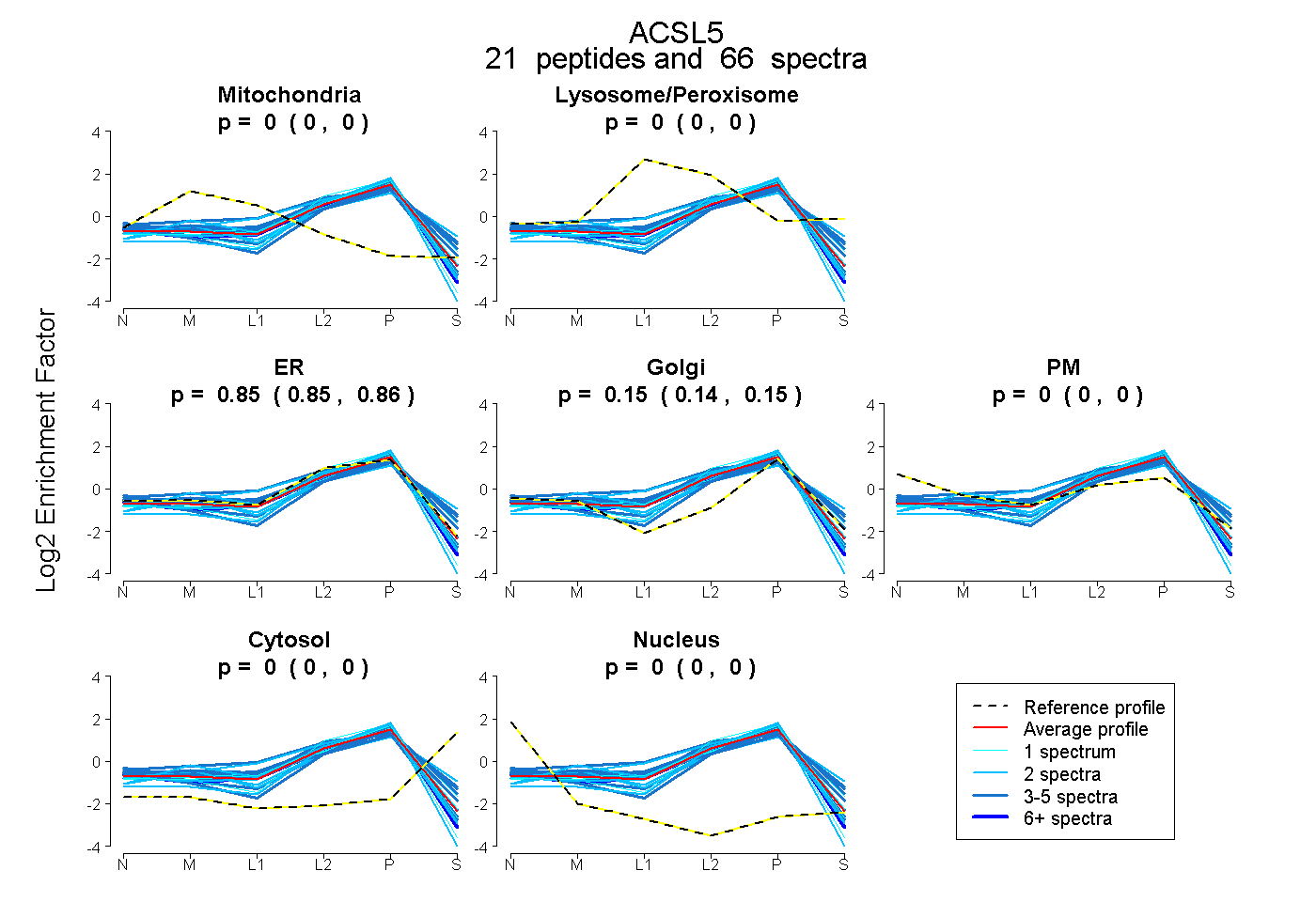 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.854 0.847 | 0.860 |
0.146 0.139 | 0.152 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
303 spectra |
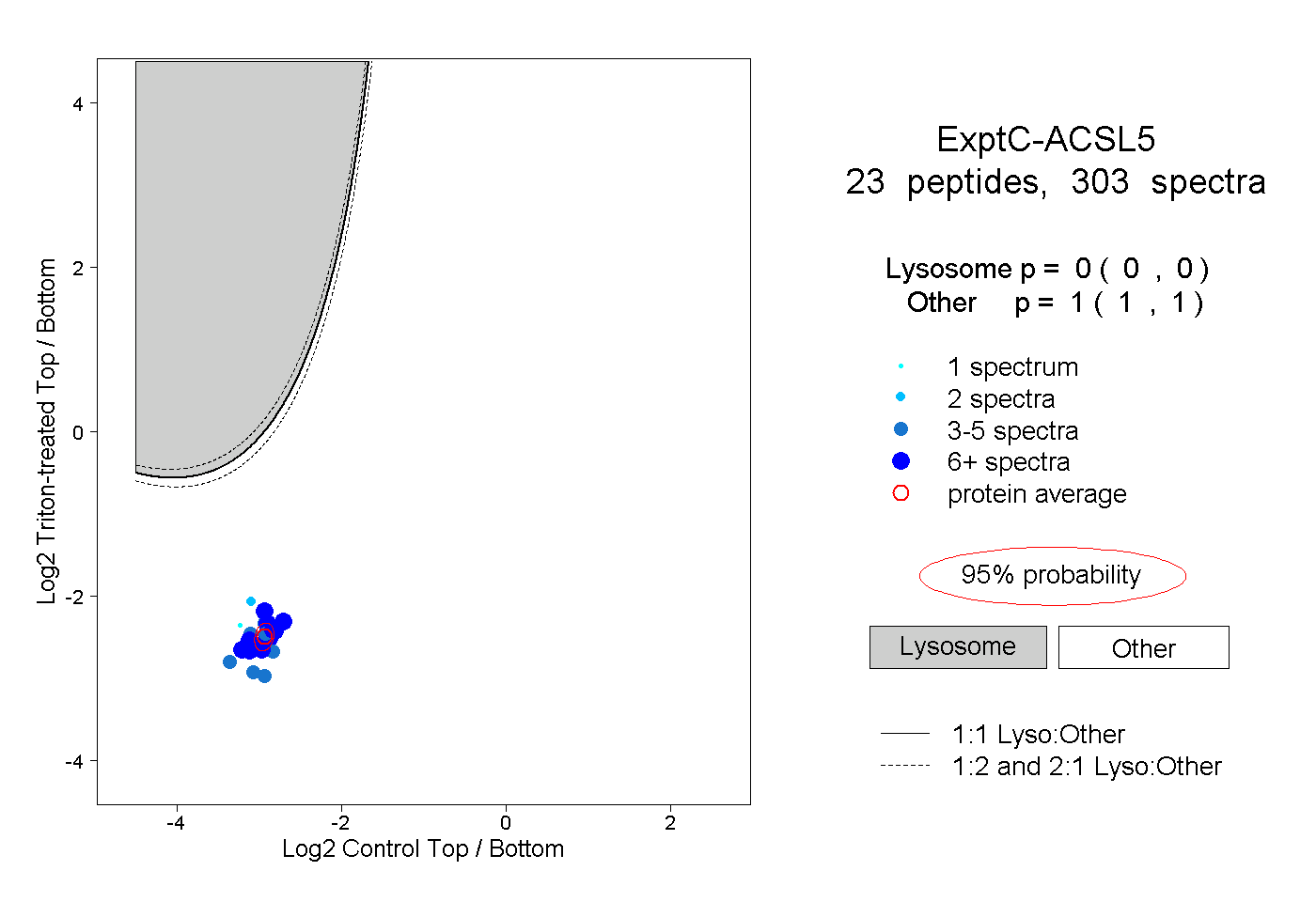 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
21 spectra |
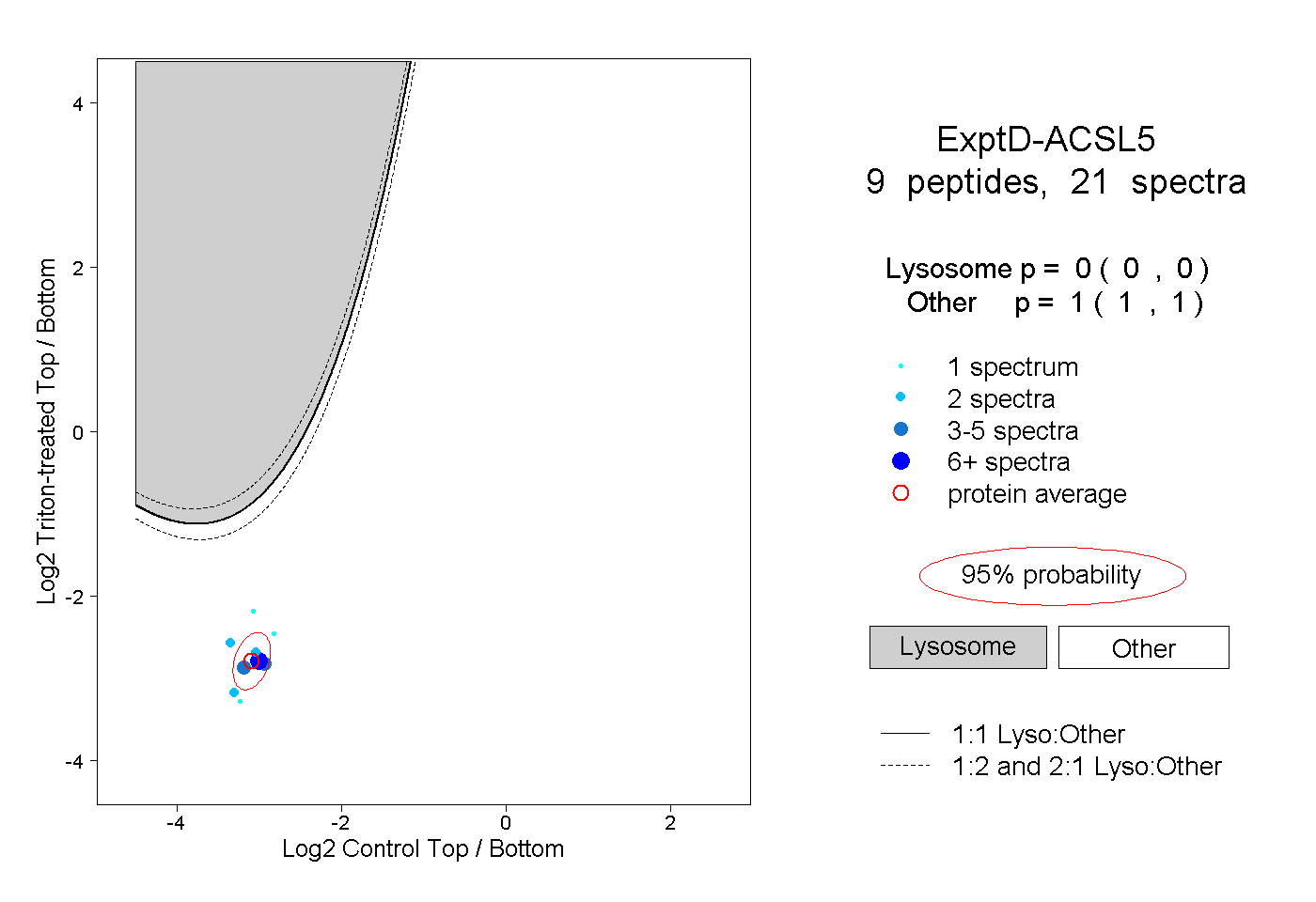 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |