peptides
spectra
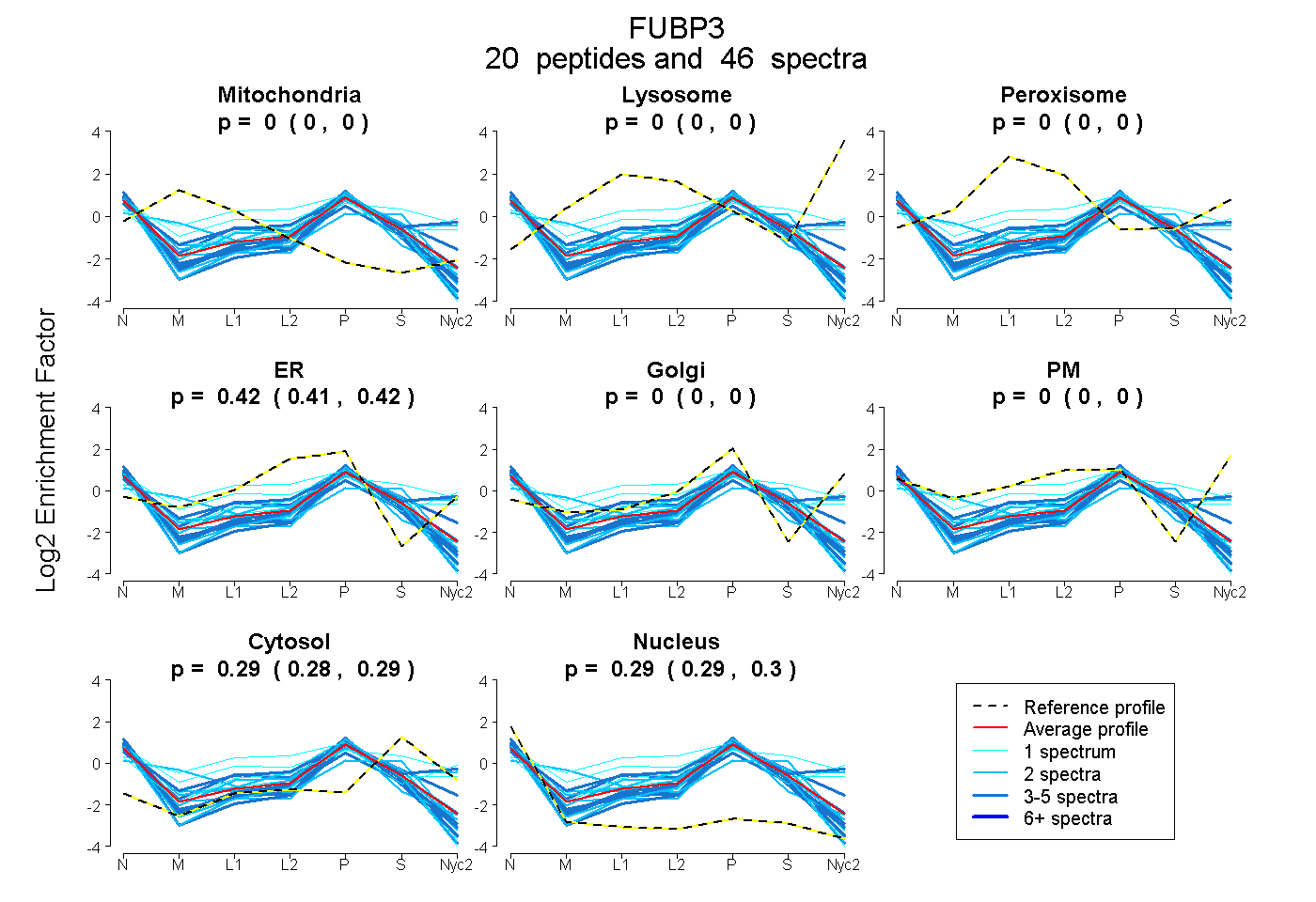
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.411 | 0.420
0.000 | 0.000
0.000 | 0.000
0.284 | 0.295
0.288 | 0.300
peptides
spectra
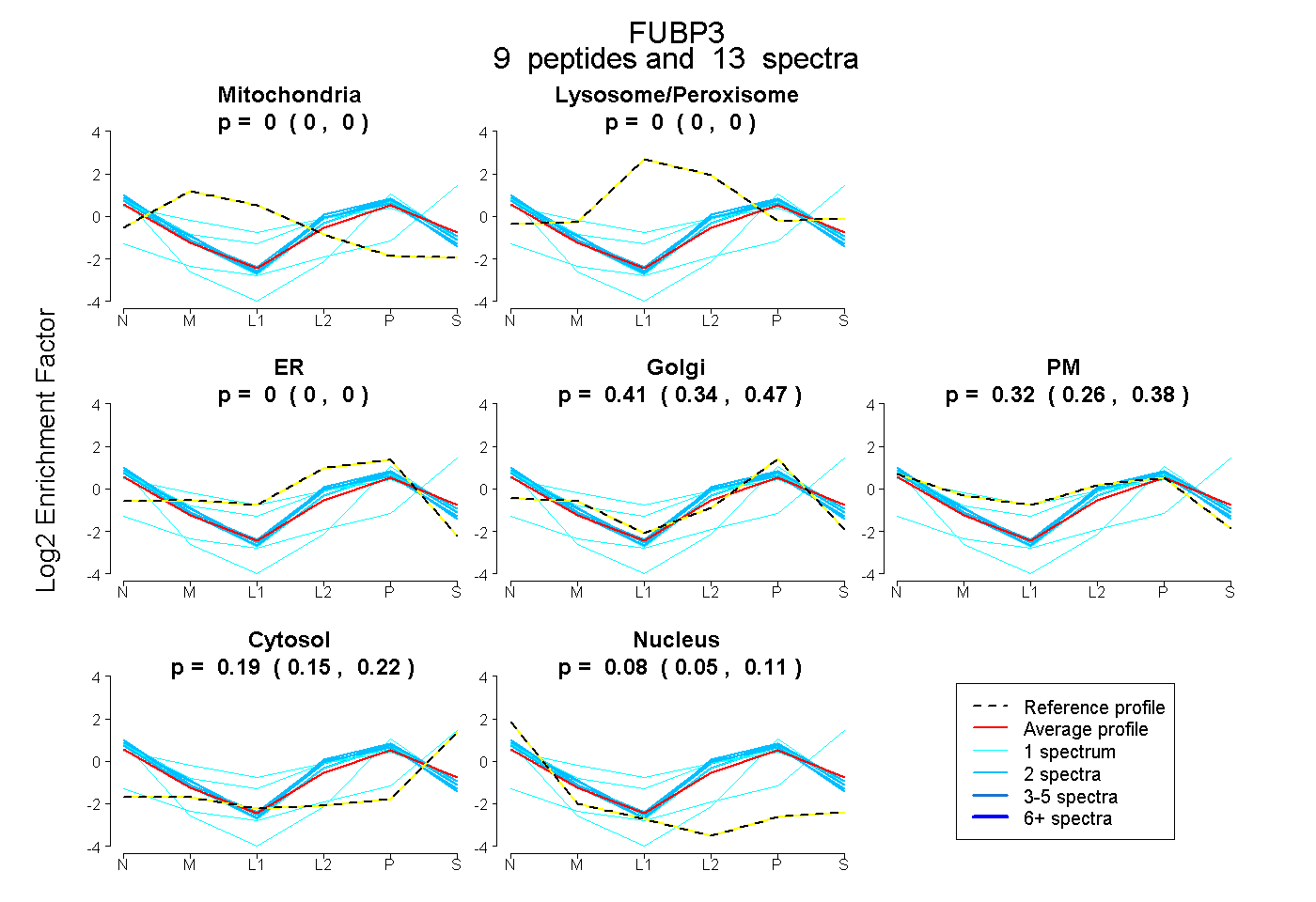
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.343 | 0.467
0.255 | 0.376
0.153 | 0.216
0.051 | 0.106
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
46 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.416 0.411 | 0.420 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.290 0.284 | 0.295 |
0.294 0.288 | 0.300 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
13 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.413 0.343 | 0.467 |
0.317 0.255 | 0.376 |
0.189 0.153 | 0.216 |
0.080 0.051 | 0.106 |
| 1 spectrum, ITGDPFK | 0.000 | 0.000 | 0.000 | 0.033 | 0.814 | 0.153 | 0.000 | |||
| 2 spectra, MVGFIIGR | 0.000 | 0.000 | 0.000 | 0.459 | 0.396 | 0.118 | 0.027 | |||
| 1 spectrum, AEDFVDALHR | 0.000 | 0.000 | 0.000 | 0.588 | 0.000 | 0.075 | 0.337 | |||
| 1 spectrum, IINELILTAQER | 0.000 | 0.000 | 0.000 | 0.062 | 0.000 | 0.933 | 0.006 | |||
| 2 spectra, EMVLELIR | 0.000 | 0.000 | 0.000 | 0.470 | 0.395 | 0.082 | 0.052 | |||
| 1 spectrum, IQFKPDDGISPER | 0.000 | 0.099 | 0.000 | 0.017 | 0.727 | 0.157 | 0.000 | |||
| 2 spectra, LLGQIVDR | 0.000 | 0.000 | 0.000 | 0.354 | 0.502 | 0.042 | 0.103 | |||
| 2 spectra, EILGGLTGTR | 0.000 | 0.000 | 0.000 | 0.558 | 0.307 | 0.006 | 0.130 | |||
| 1 spectrum, GAPQQIEVAR | 0.000 | 0.000 | 0.000 | 0.490 | 0.305 | 0.109 | 0.097 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
18 spectra |
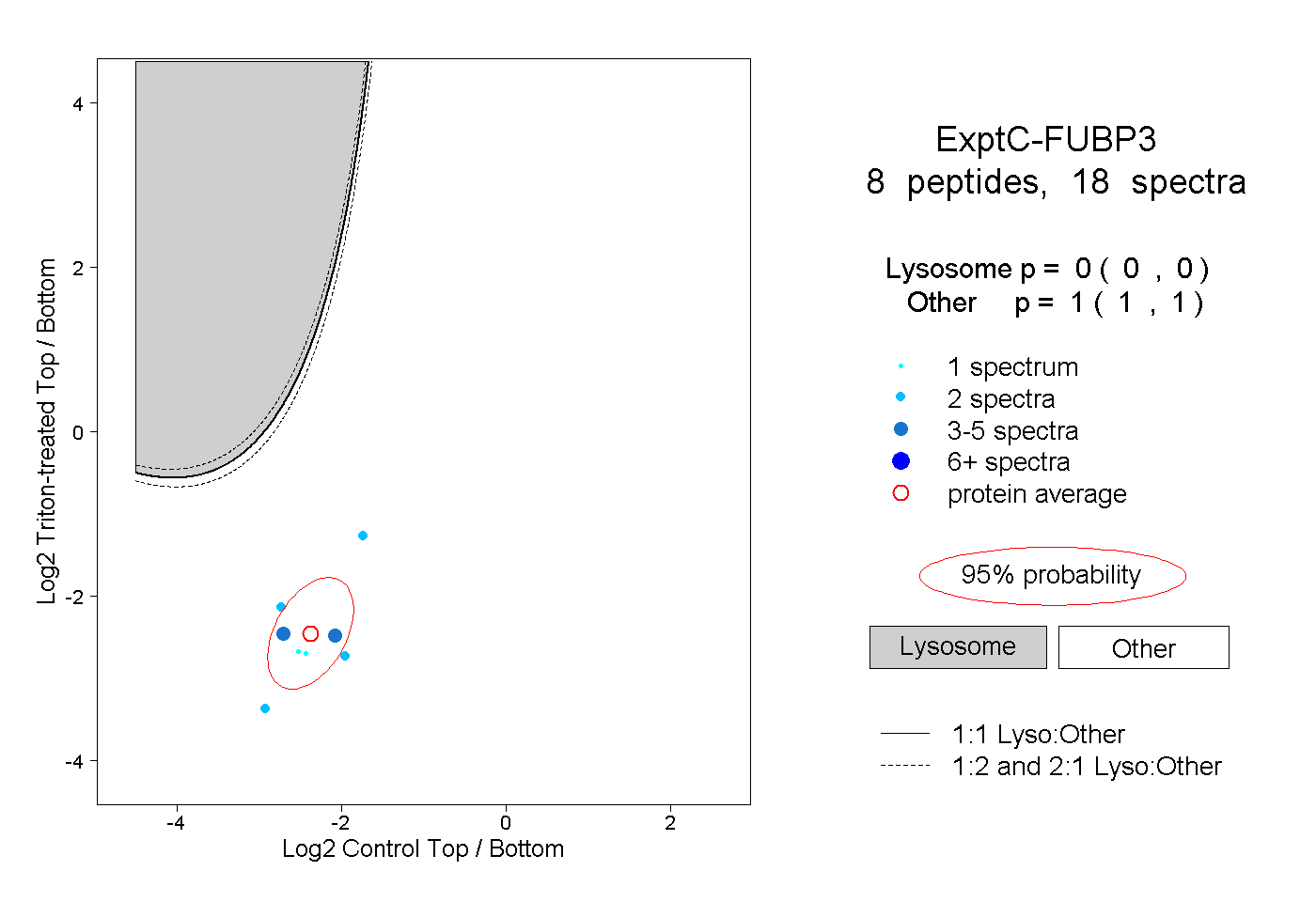 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
3 spectra |
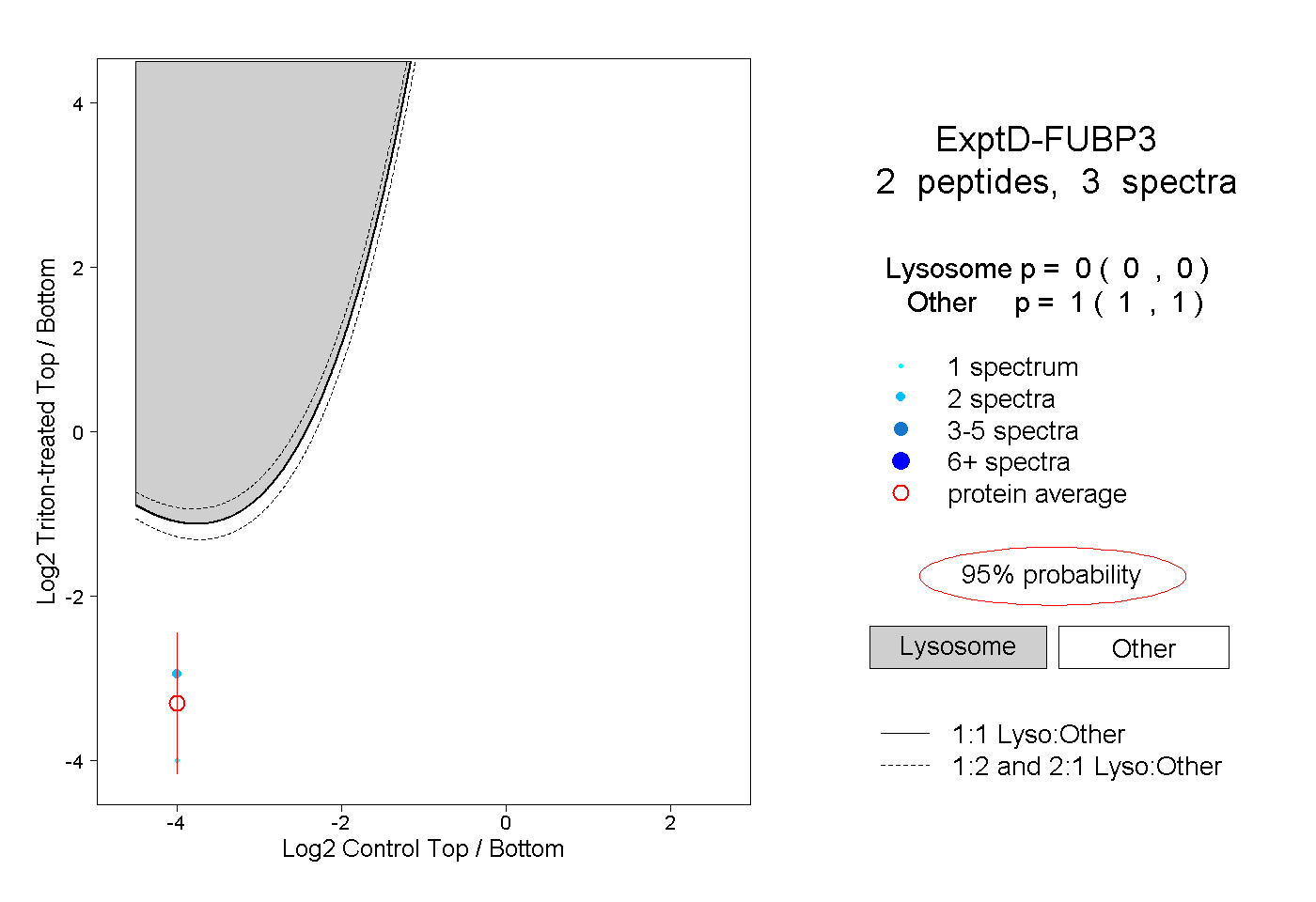 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |