peptides
spectra
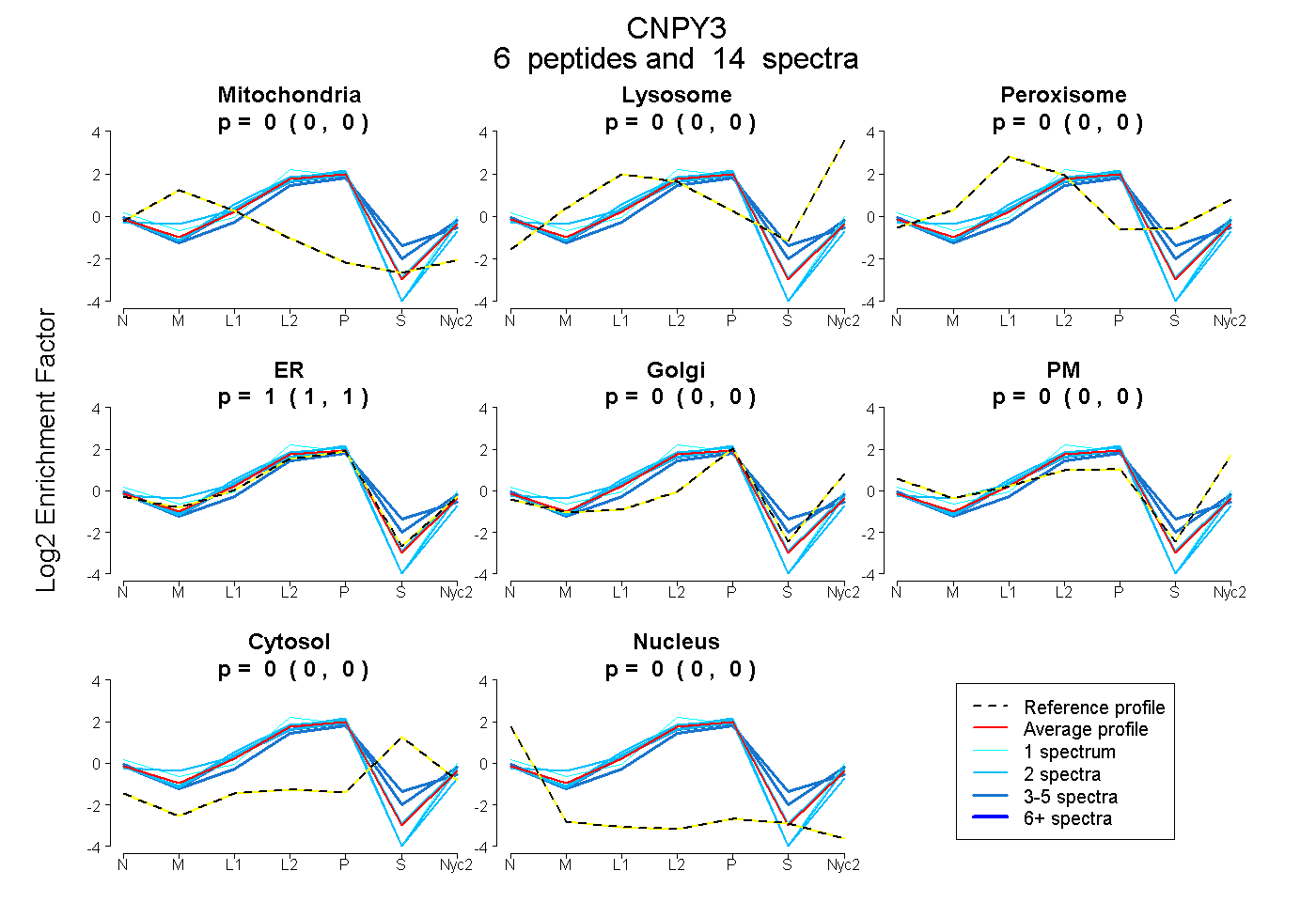
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
1.000 | 1.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
14 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 2 spectra, LLDYSLHK | 0.000 | 0.000 | 0.014 | 0.986 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, SAFEETGK | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, NHQEEDLTQFLCANHVLK | 0.000 | 0.000 | 0.000 | 0.947 | 0.000 | 0.053 | 0.000 | 0.000 | ||
| 4 spectra, EVIDTGYGILDR | 0.000 | 0.000 | 0.063 | 0.897 | 0.000 | 0.000 | 0.041 | 0.000 | ||
| 2 spectra, YVAVELK | 0.048 | 0.000 | 0.000 | 0.952 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 3 spectra, DTSCLAER | 0.000 | 0.000 | 0.000 | 0.831 | 0.000 | 0.000 | 0.169 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
3 spectra |
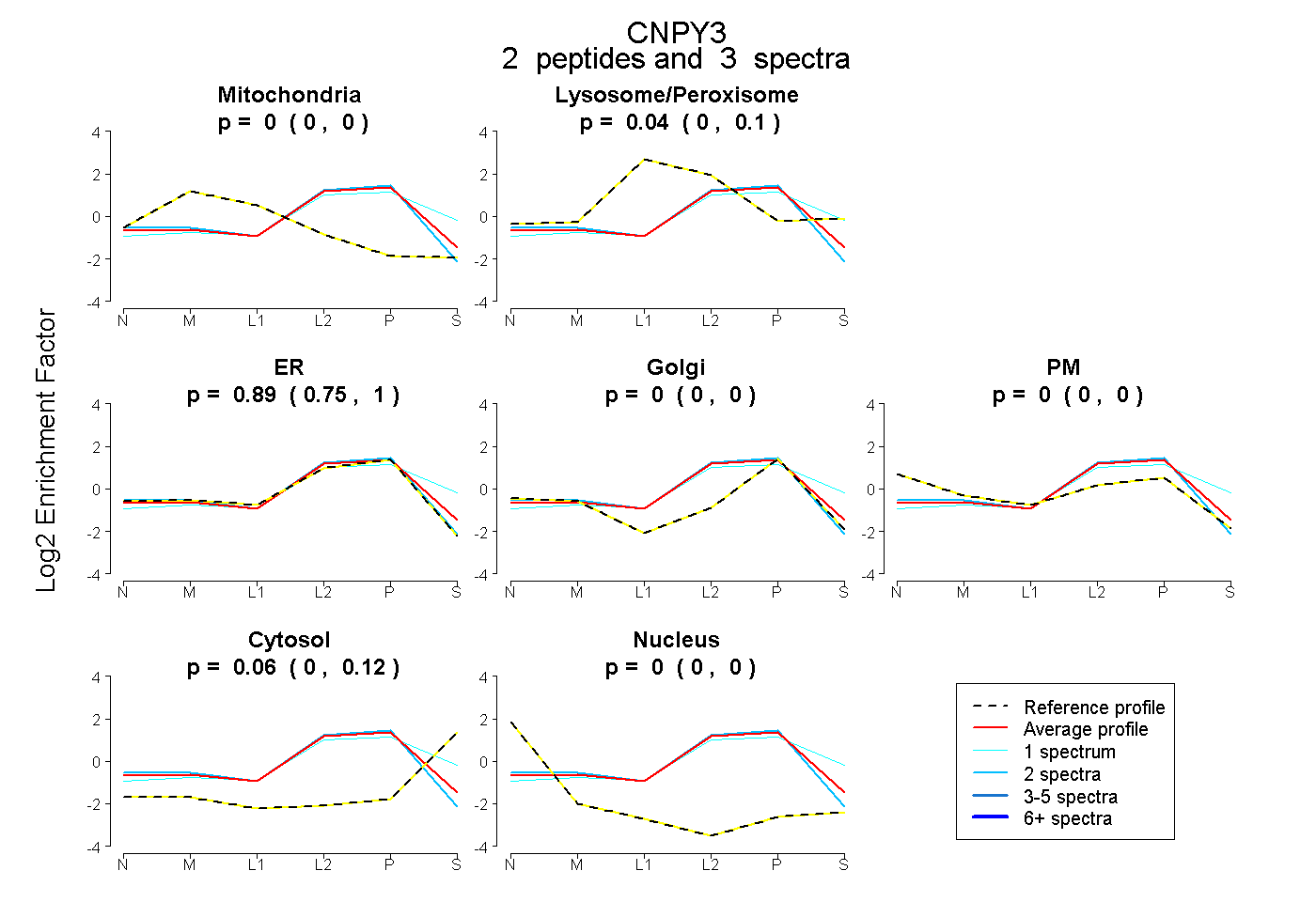 |
0.000 0.000 | 0.000 |
0.043 0.000 | 0.098 |
0.894 0.751 | 0.999 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.063 0.000 | 0.122 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
26 spectra |
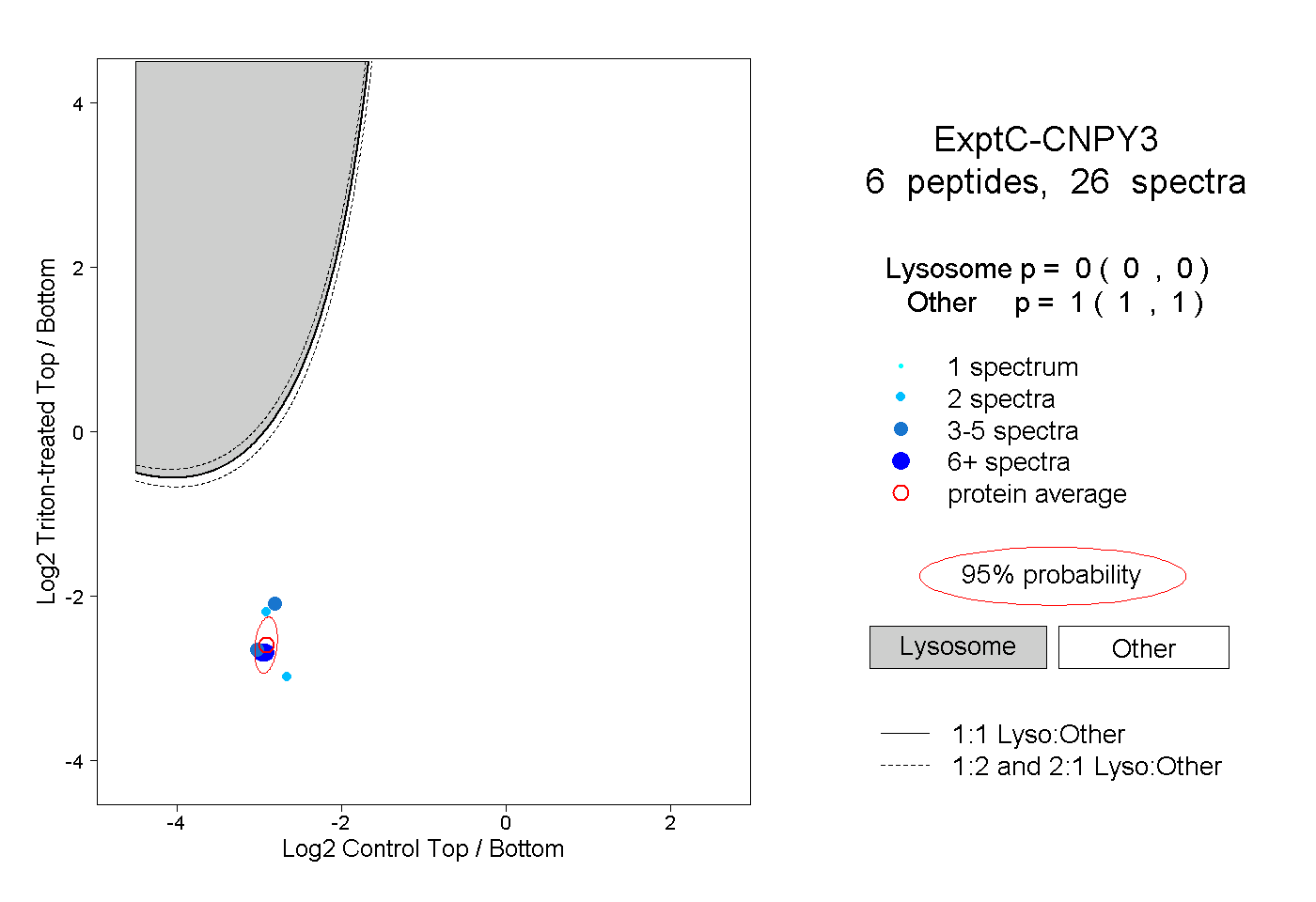 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
6 spectra |
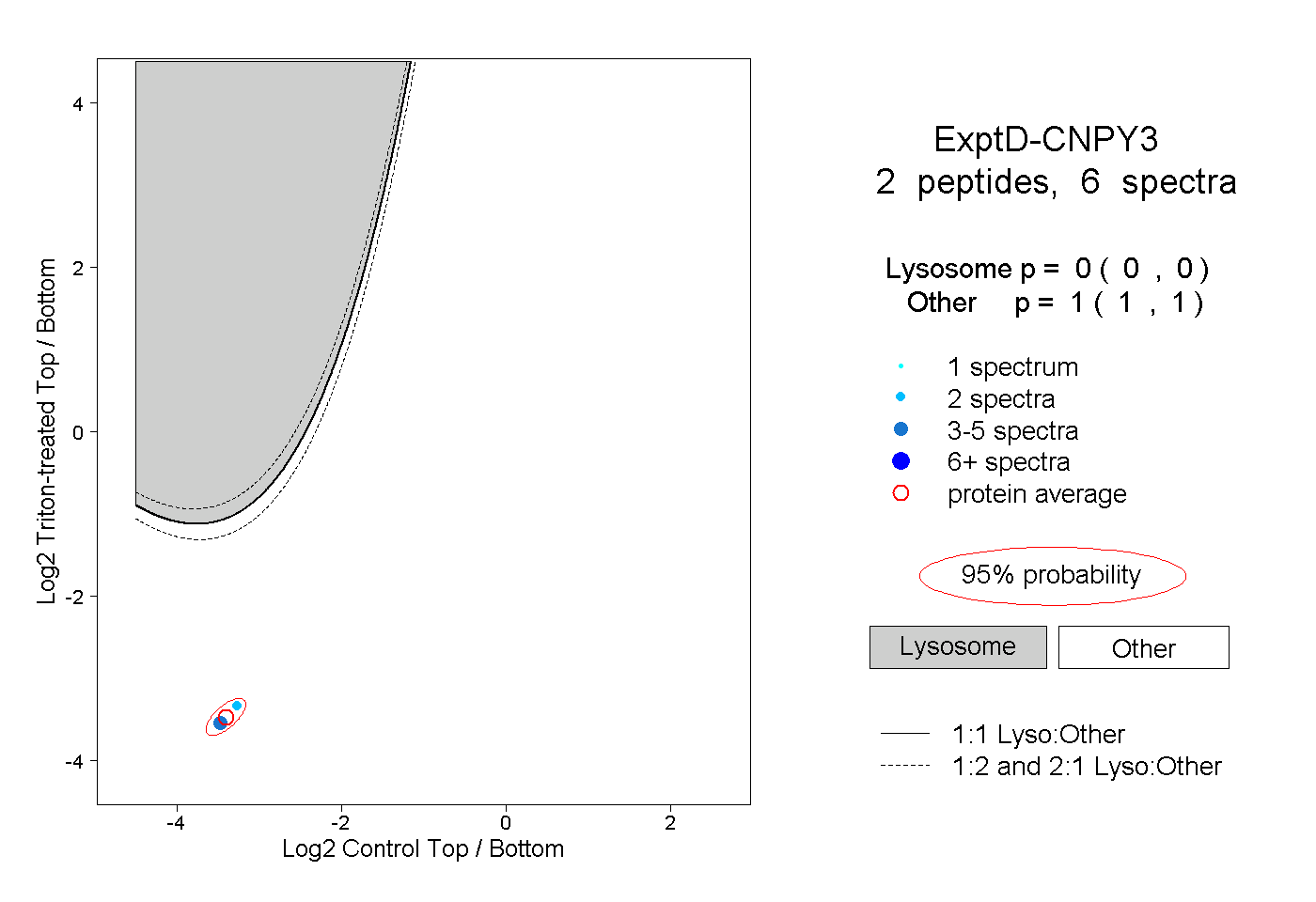 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |