peptides
spectra
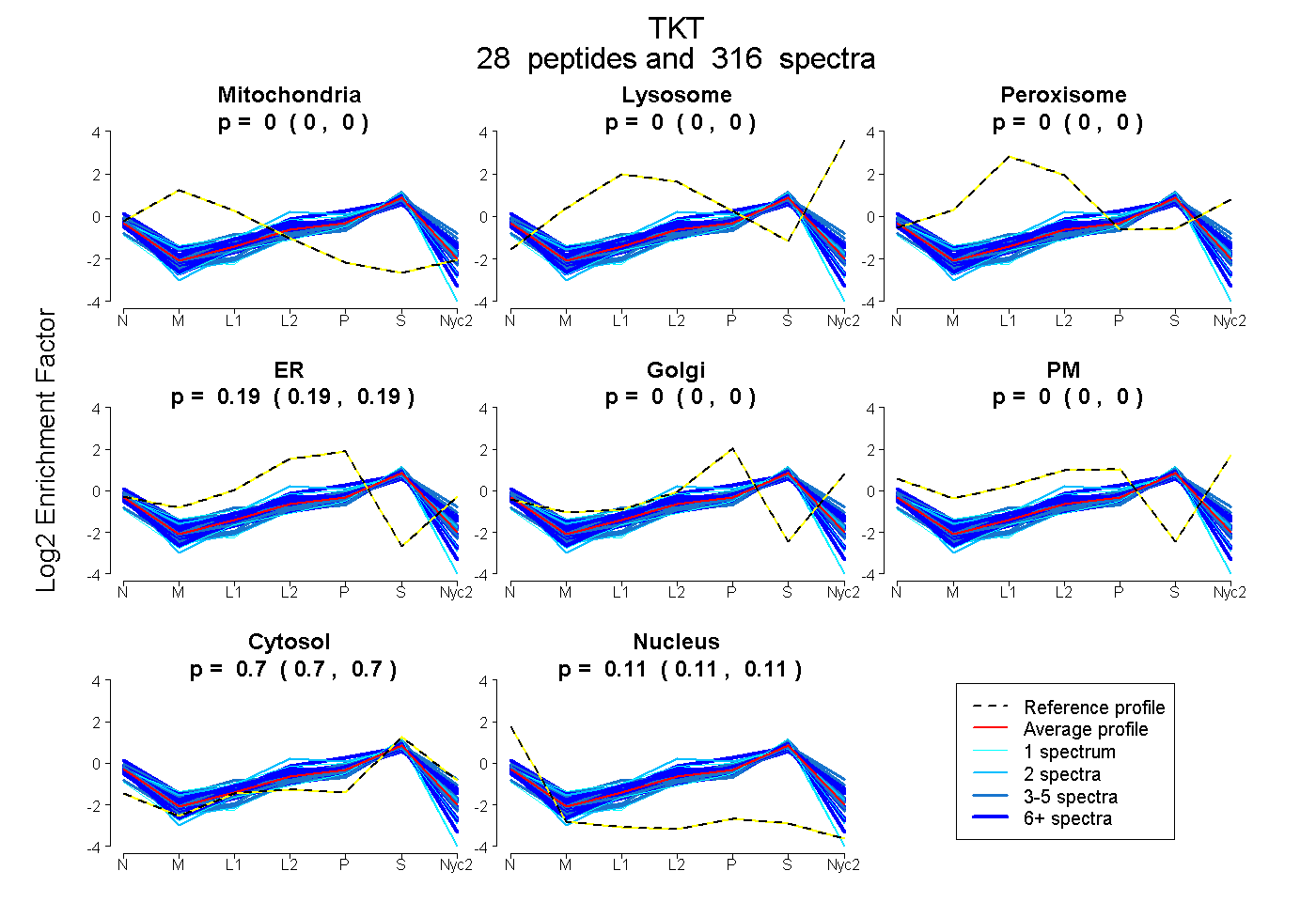
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.188 | 0.190
0.000 | 0.000
0.000 | 0.000
0.703 | 0.705
0.106 | 0.108
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
316 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.189 0.188 | 0.190 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.704 0.703 | 0.705 |
0.107 0.106 | 0.108 |
| 1 spectrum, TSRPENAIIYSNNEDFQVGQAK | 0.073 | 0.000 | 0.000 | 0.261 | 0.000 | 0.000 | 0.604 | 0.063 | ||
| 5 spectra, LDNLVAIFDINR | 0.005 | 0.000 | 0.085 | 0.201 | 0.000 | 0.000 | 0.614 | 0.095 | ||
| 2 spectra, CEAFGWHAIIVDGHSVEELCK | 0.000 | 0.000 | 0.000 | 0.097 | 0.000 | 0.000 | 0.644 | 0.259 | ||
| 14 spectra, MPTPPNYK | 0.000 | 0.000 | 0.000 | 0.144 | 0.000 | 0.000 | 0.739 | 0.117 | ||
| 40 spectra, LAVSQVPR | 0.000 | 0.000 | 0.000 | 0.149 | 0.000 | 0.000 | 0.753 | 0.097 | ||
| 19 spectra, AVELAANTK | 0.000 | 0.000 | 0.000 | 0.245 | 0.000 | 0.000 | 0.696 | 0.059 | ||
| 1 spectrum, VLDPFTIKPLDK | 0.000 | 0.000 | 0.000 | 0.018 | 0.000 | 0.000 | 0.757 | 0.225 | ||
| 6 spectra, GLVTK | 0.000 | 0.000 | 0.000 | 0.103 | 0.000 | 0.000 | 0.785 | 0.112 | ||
| 18 spectra, LILDCAR | 0.000 | 0.000 | 0.000 | 0.121 | 0.000 | 0.000 | 0.717 | 0.161 | ||
| 11 spectra, GITGIEDK | 0.000 | 0.000 | 0.000 | 0.266 | 0.000 | 0.000 | 0.637 | 0.096 | ||
| 39 spectra, GICFIR | 0.000 | 0.000 | 0.000 | 0.086 | 0.000 | 0.000 | 0.709 | 0.205 | ||
| 1 spectrum, FIECYIAEQNMVSIAVGCATR | 0.000 | 0.000 | 0.000 | 0.139 | 0.000 | 0.000 | 0.604 | 0.257 | ||
| 9 spectra, SVPMSTVFYPSDGVATEK | 0.000 | 0.000 | 0.016 | 0.239 | 0.000 | 0.000 | 0.693 | 0.052 | ||
| 5 spectra, EAWHGKPLPK | 0.000 | 0.000 | 0.000 | 0.209 | 0.000 | 0.006 | 0.750 | 0.036 | ||
| 5 spectra, AFGQAK | 0.000 | 0.000 | 0.000 | 0.159 | 0.000 | 0.000 | 0.688 | 0.153 | ||
| 4 spectra, NMAEQIIQEIYSQVQSK | 0.000 | 0.000 | 0.012 | 0.094 | 0.000 | 0.113 | 0.747 | 0.035 | ||
| 2 spectra, AYGLALAK | 0.000 | 0.000 | 0.000 | 0.080 | 0.000 | 0.000 | 0.718 | 0.203 | ||
| 29 spectra, HQPTAIIAK | 0.000 | 0.000 | 0.046 | 0.196 | 0.000 | 0.036 | 0.611 | 0.112 | ||
| 3 spectra, LGQSDPAPLQHQVDVYQK | 0.000 | 0.000 | 0.000 | 0.181 | 0.000 | 0.000 | 0.718 | 0.101 | ||
| 2 spectra, SGKPAELLK | 0.000 | 0.000 | 0.001 | 0.342 | 0.000 | 0.000 | 0.631 | 0.025 | ||
| 4 spectra, MFGIDK | 0.000 | 0.000 | 0.000 | 0.069 | 0.000 | 0.000 | 0.830 | 0.101 | ||
| 5 spectra, DAIVQAVK | 0.000 | 0.000 | 0.000 | 0.105 | 0.000 | 0.000 | 0.784 | 0.111 | ||
| 4 spectra, TVPFCSTFAAFFTR | 0.000 | 0.000 | 0.000 | 0.168 | 0.000 | 0.000 | 0.678 | 0.154 | ||
| 16 spectra, NSTFSELFK | 0.006 | 0.000 | 0.021 | 0.254 | 0.000 | 0.000 | 0.663 | 0.056 | ||
| 14 spectra, IIALDGDTK | 0.000 | 0.000 | 0.000 | 0.181 | 0.000 | 0.000 | 0.715 | 0.103 | ||
| 15 spectra, ISSDLDGHPVPK | 0.000 | 0.000 | 0.000 | 0.215 | 0.000 | 0.000 | 0.674 | 0.111 | ||
| 5 spectra, LGHASDR | 0.000 | 0.000 | 0.049 | 0.247 | 0.000 | 0.000 | 0.654 | 0.050 | ||
| 37 spectra, AFDQIR | 0.037 | 0.000 | 0.001 | 0.191 | 0.000 | 0.000 | 0.681 | 0.091 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
98 spectra |
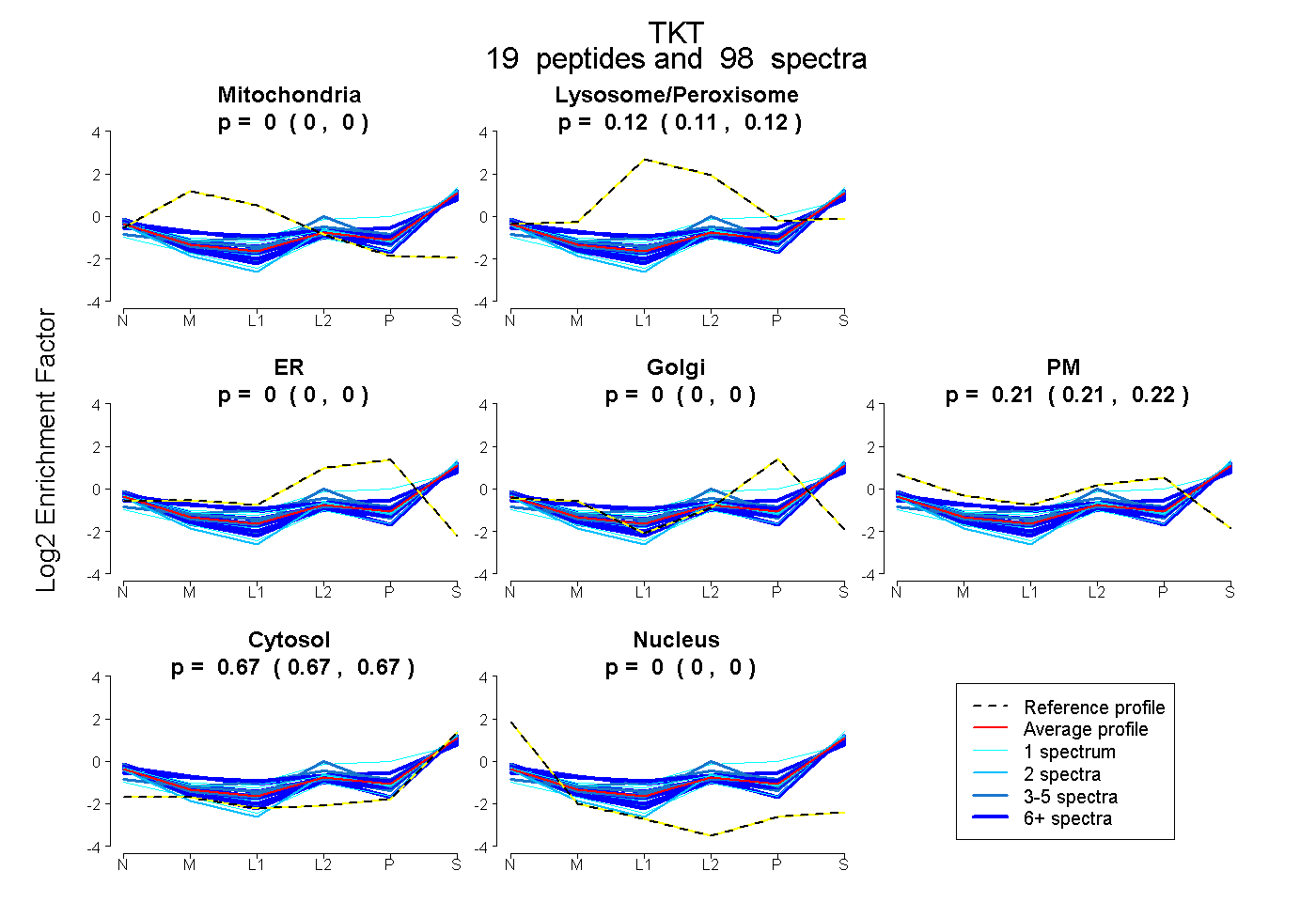 |
0.000 0.000 | 0.000 |
0.117 0.113 | 0.121 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.213 0.209 | 0.216 |
0.670 0.667 | 0.672 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
446 spectra |
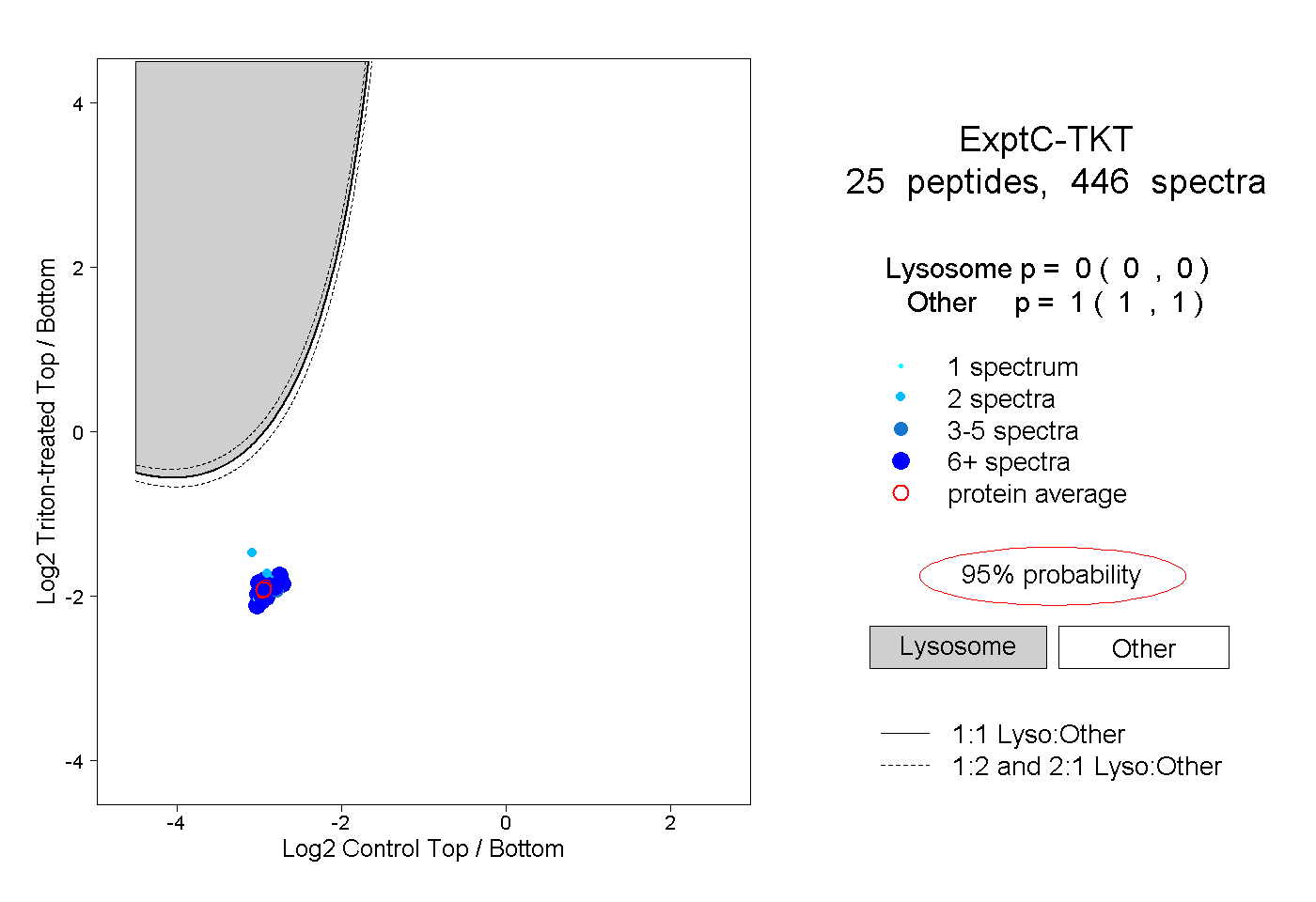 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
45 spectra |
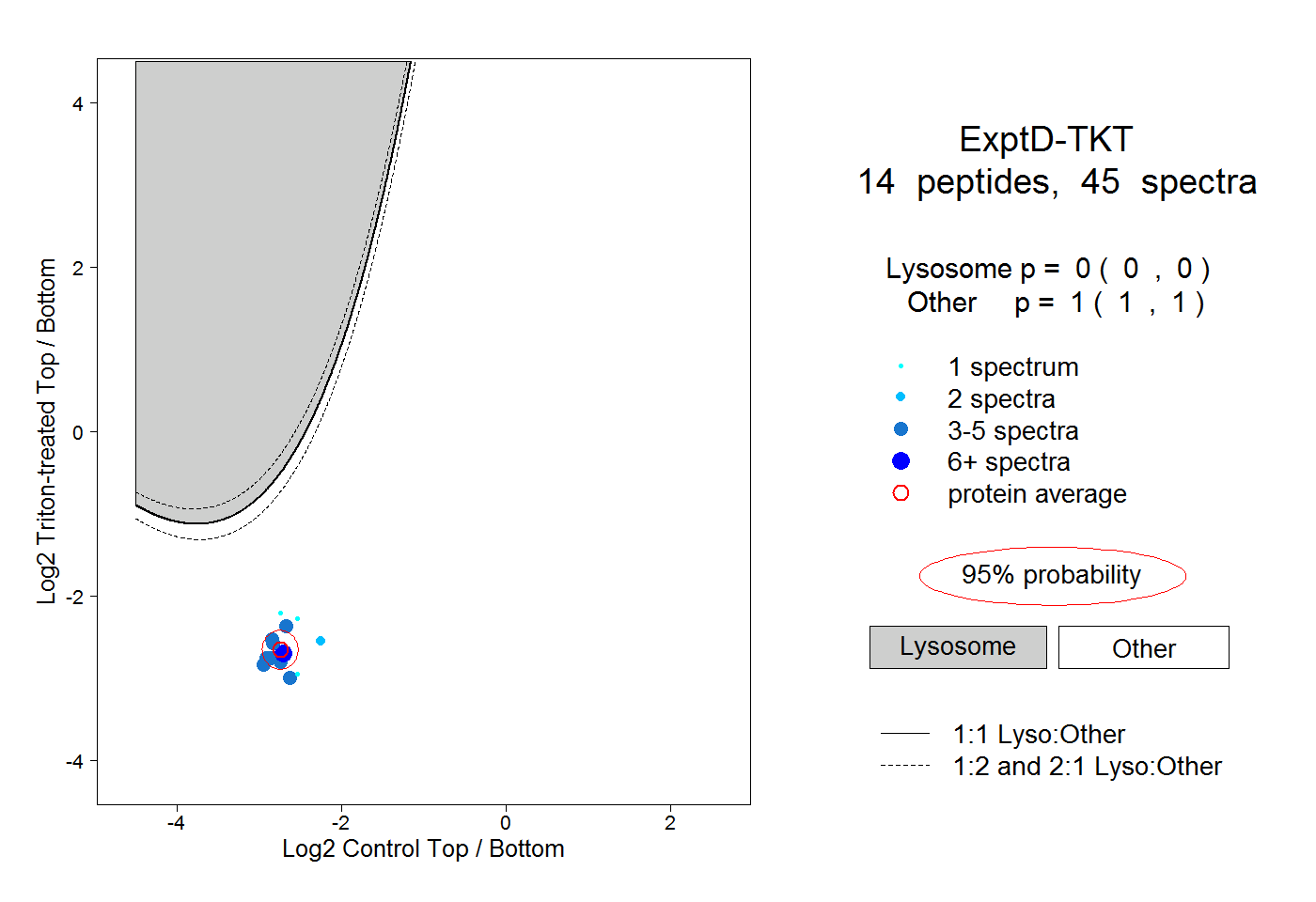 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |