peptides
spectra
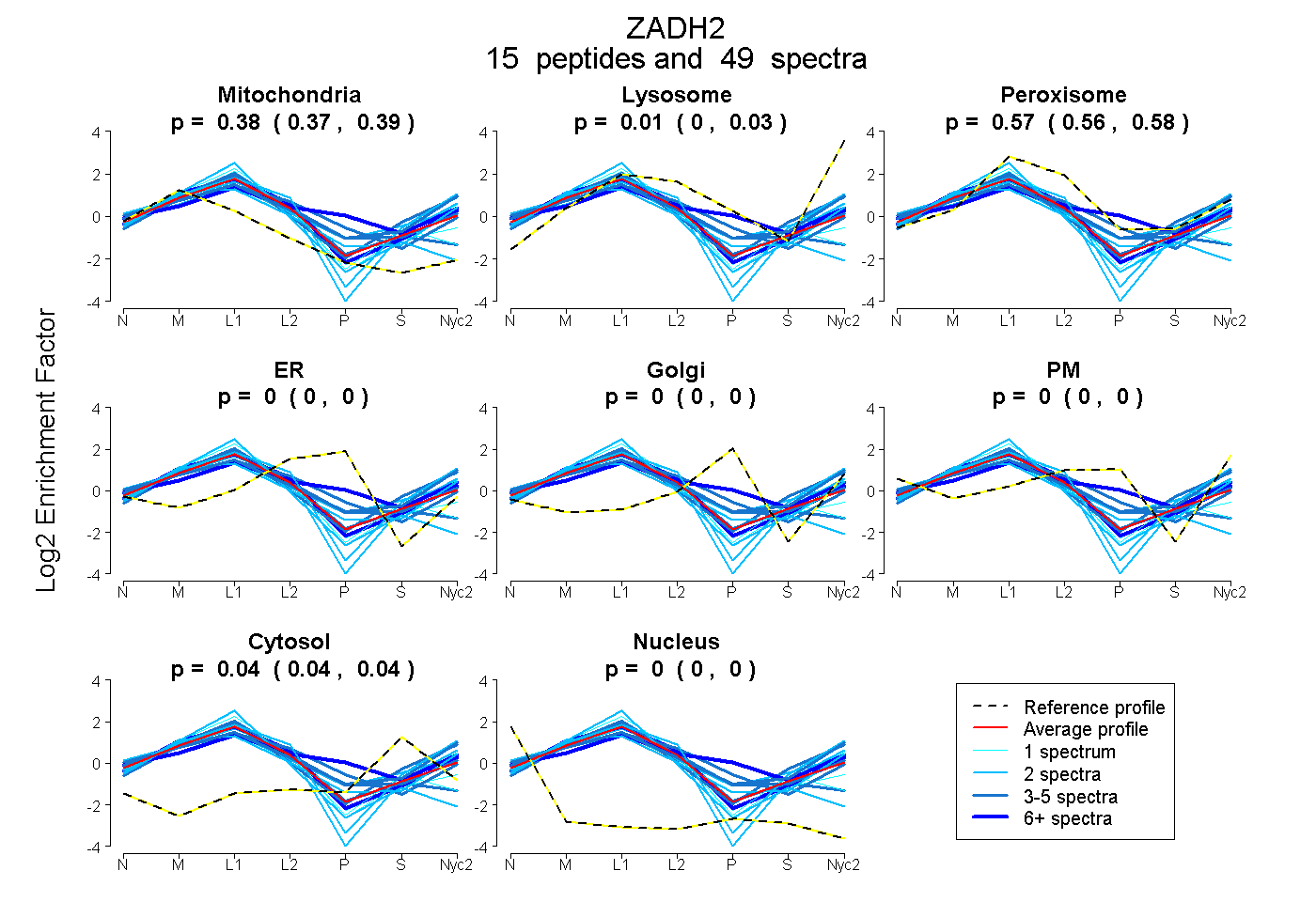
0.374 | 0.386
0.000 | 0.026
0.555 | 0.579
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.035 | 0.043
0.000 | 0.000
peptides
spectra
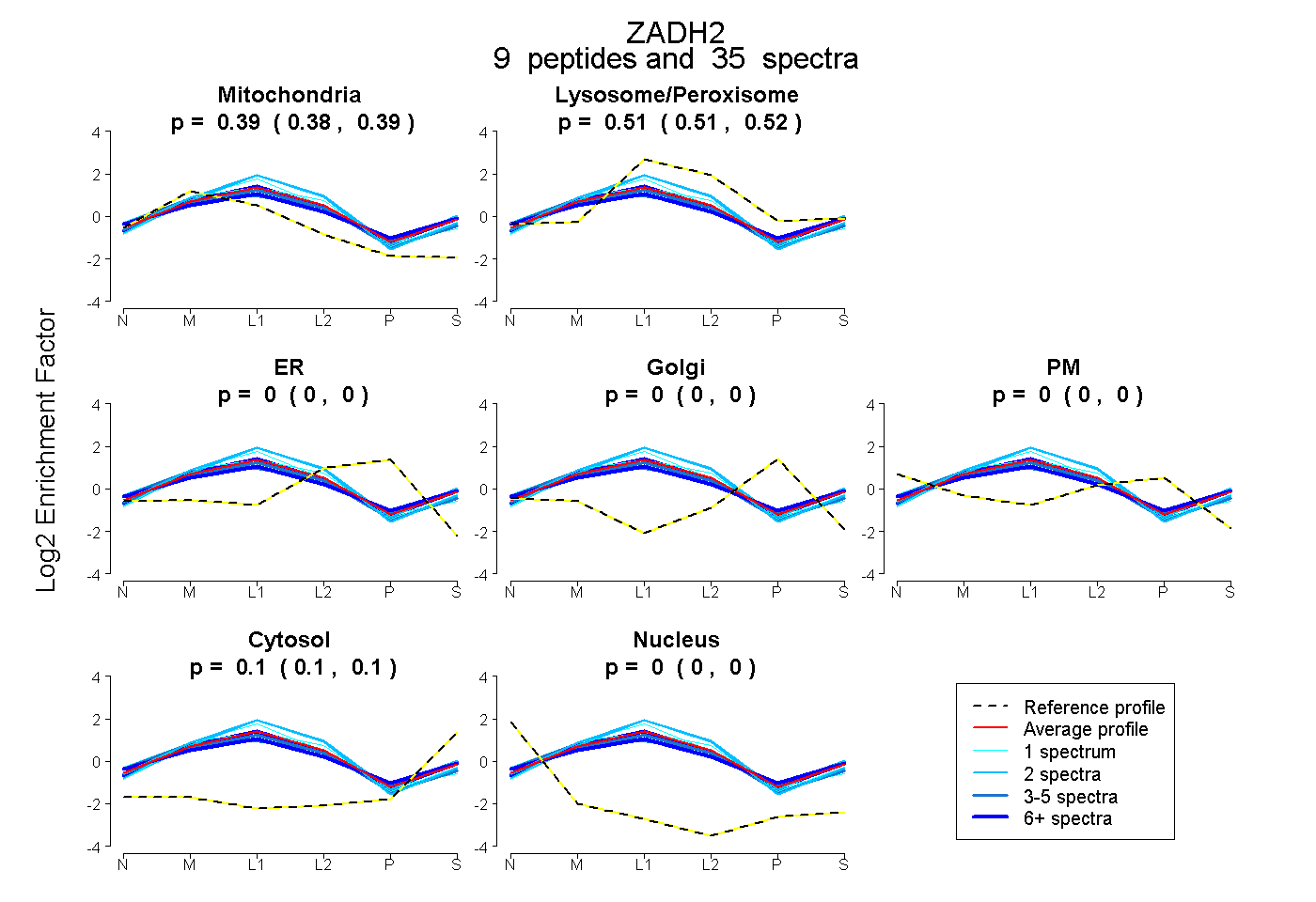
0.382 | 0.393
0.506 | 0.517
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.095 | 0.104
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
49 spectra |
 |
0.380 0.374 | 0.386 |
0.011 0.000 | 0.026 |
0.570 0.555 | 0.579 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.039 0.035 | 0.043 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
35 spectra |
 |
0.388 0.382 | 0.393 |
0.512 0.506 | 0.517 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.100 0.095 | 0.104 |
0.000 0.000 | 0.000 |
| 5 spectra, HFLDFQGSAIPR | 0.355 | 0.502 | 0.000 | 0.000 | 0.000 | 0.143 | 0.000 | |||
| 1 spectrum, AGALPAK | 0.500 | 0.500 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, TEPVETVLK | 0.431 | 0.569 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 11 spectra, SVGCDRPINYR | 0.370 | 0.470 | 0.000 | 0.000 | 0.000 | 0.160 | 0.000 | |||
| 8 spectra, GDLVCEVDLGHLAPEGR | 0.391 | 0.499 | 0.000 | 0.000 | 0.000 | 0.111 | 0.000 | |||
| 1 spectrum, ELGELSEGK | 0.354 | 0.495 | 0.000 | 0.000 | 0.000 | 0.151 | 0.000 | |||
| 2 spectra, LSPNFHEAVTLR | 0.318 | 0.629 | 0.000 | 0.000 | 0.000 | 0.054 | 0.000 | |||
| 1 spectrum, LVVELPHPVSSK | 0.436 | 0.493 | 0.000 | 0.000 | 0.000 | 0.071 | 0.000 | |||
| 4 spectra, FVGINASDINYSAGR | 0.496 | 0.410 | 0.000 | 0.000 | 0.000 | 0.094 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
237 spectra |
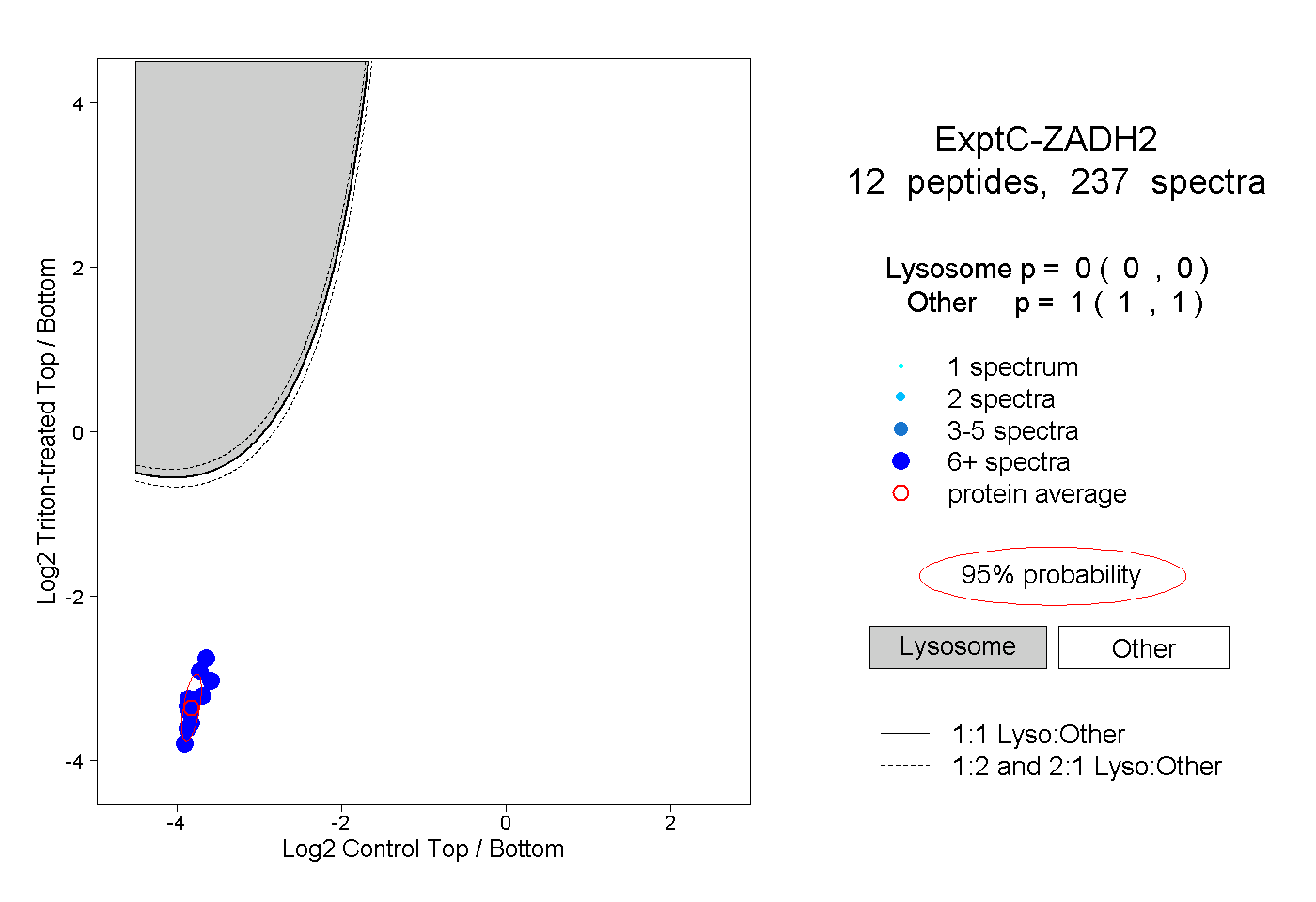 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
20 spectra |
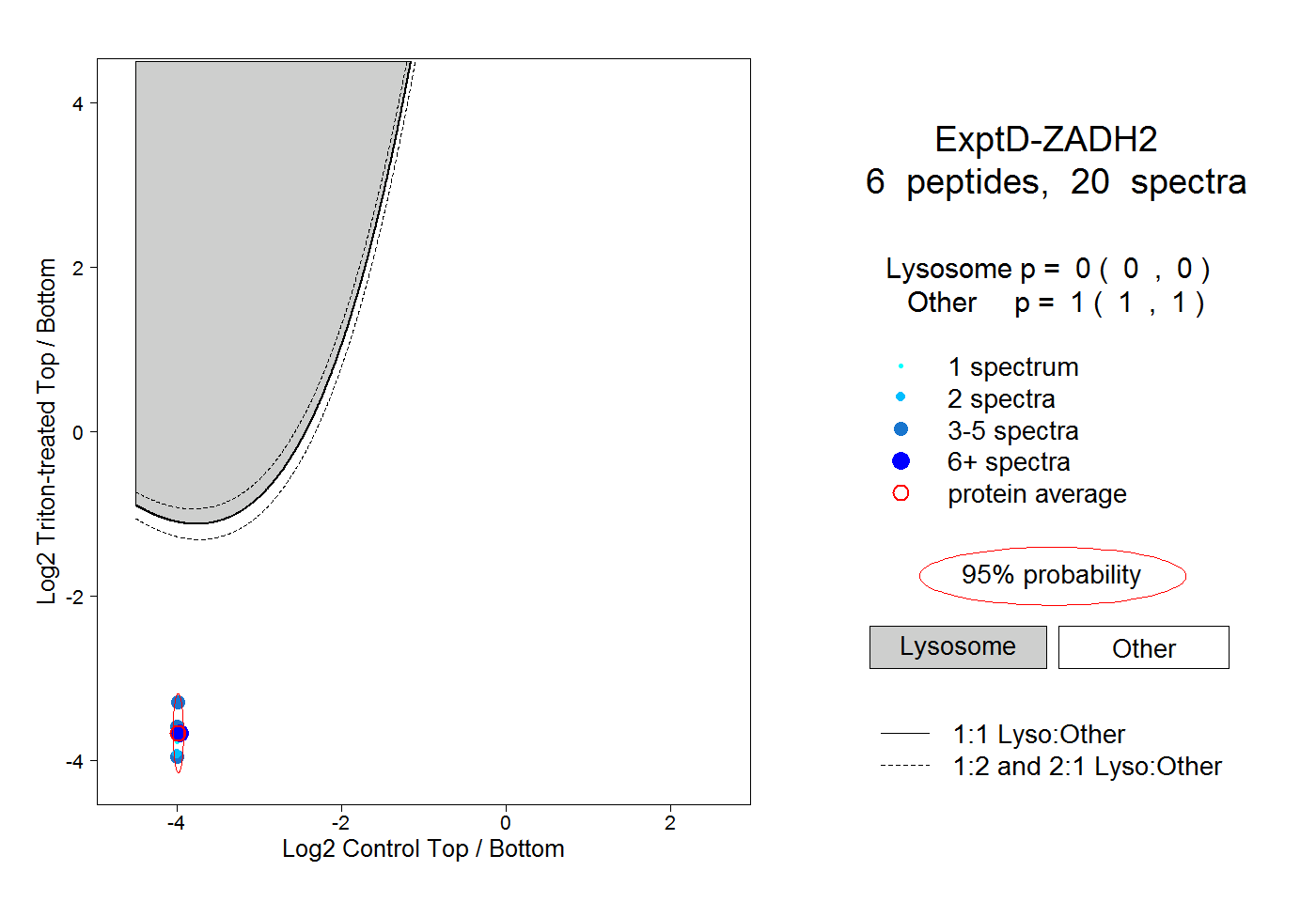 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |