peptides
spectra
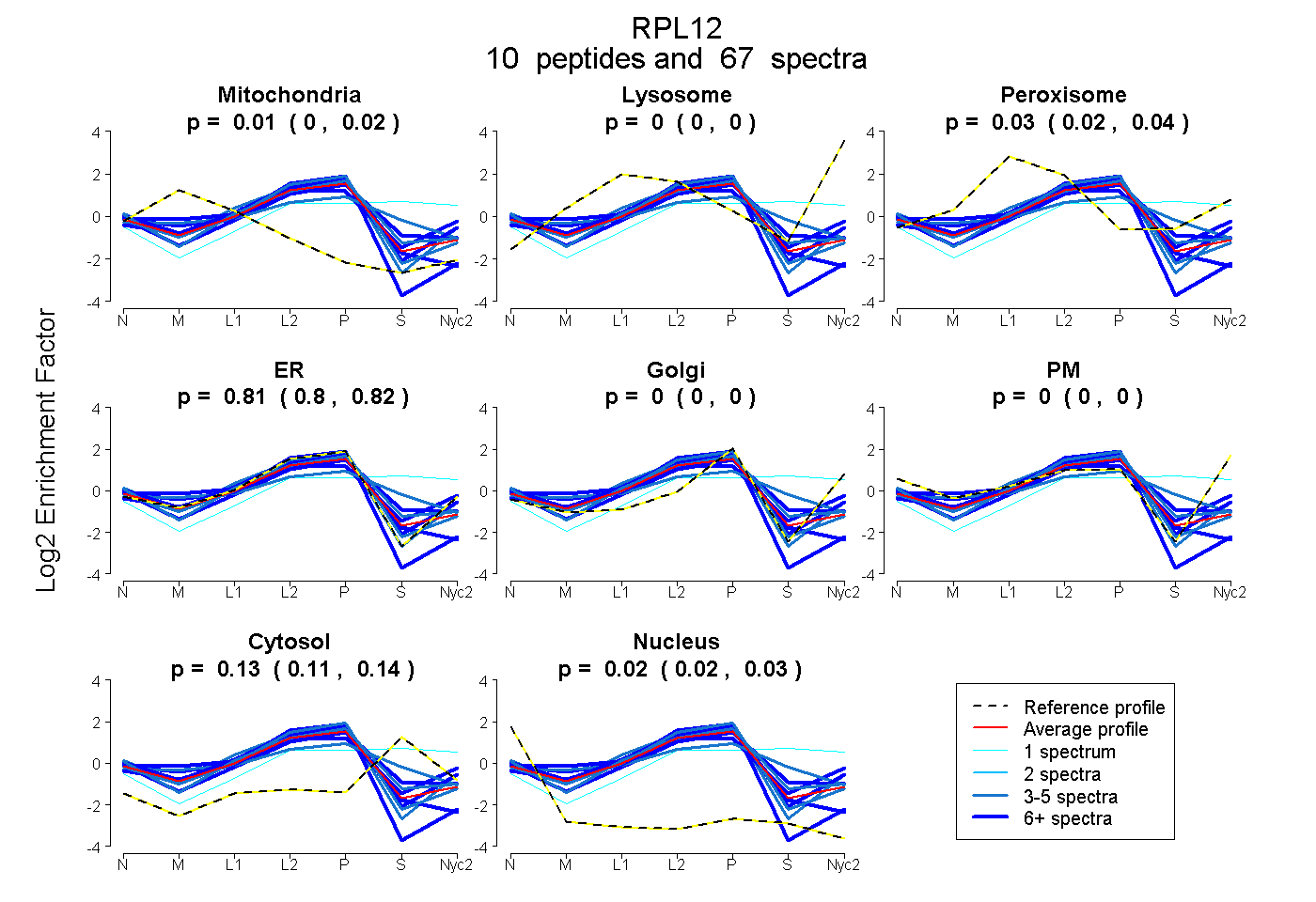
0.000 | 0.023
0.000 | 0.000
0.016 | 0.035
0.800 | 0.819
0.000 | 0.000
0.000 | 0.000
0.112 | 0.136
0.016 | 0.031
peptides
spectra
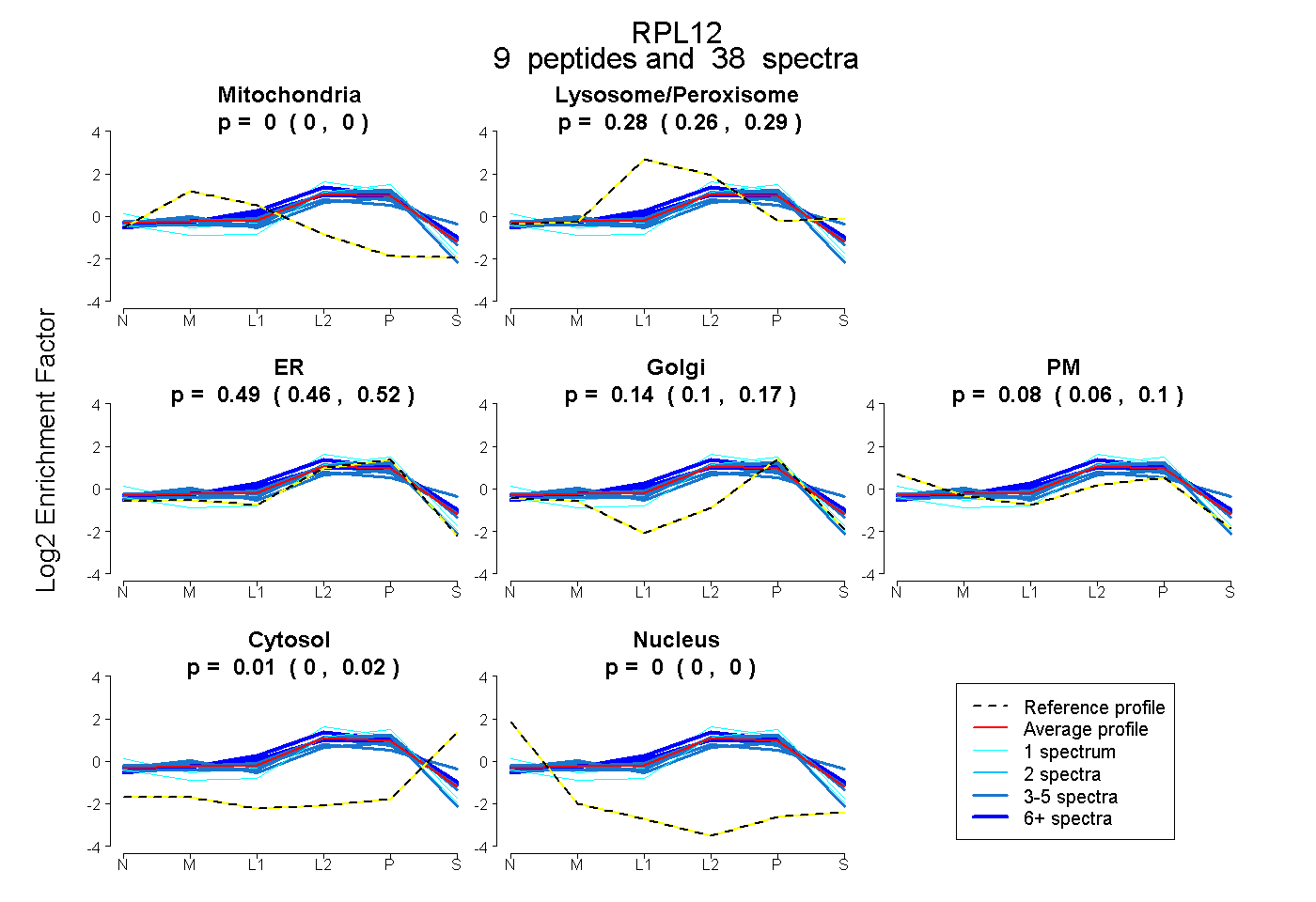
0.000 | 0.000
0.261 | 0.295
0.458 | 0.518
0.103 | 0.172
0.057 | 0.097
0.002 | 0.020
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
67 spectra |
 |
0.013 0.000 | 0.023 |
0.000 0.000 | 0.000 |
0.026 0.016 | 0.035 |
0.811 0.800 | 0.819 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.126 0.112 | 0.136 |
0.024 0.016 | 0.031 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
38 spectra |
 |
0.000 0.000 | 0.000 |
0.279 0.261 | 0.295 |
0.489 0.458 | 0.518 |
0.142 0.103 | 0.172 |
0.078 0.057 | 0.097 |
0.012 0.002 | 0.020 |
0.000 0.000 | 0.000 |
| 3 spectra, QAQIEVVPSASALIIK | 0.009 | 0.278 | 0.229 | 0.369 | 0.109 | 0.006 | 0.000 | |||
| 5 spectra, ITIQNR | 0.003 | 0.140 | 0.743 | 0.000 | 0.114 | 0.000 | 0.000 | |||
| 1 spectrum, ATGDWK | 0.000 | 0.147 | 0.733 | 0.000 | 0.120 | 0.000 | 0.000 | |||
| 9 spectra, HNGNITFDEIVNIAR | 0.000 | 0.375 | 0.384 | 0.238 | 0.000 | 0.003 | 0.000 | |||
| 1 spectrum, VGDDIAK | 0.000 | 0.029 | 0.947 | 0.000 | 0.000 | 0.024 | 0.000 | |||
| 7 spectra, HPHDIIDDINSSAVECPAS | 0.000 | 0.385 | 0.514 | 0.100 | 0.002 | 0.000 | 0.000 | |||
| 3 spectra, CTGGEVGATSALAPK | 0.000 | 0.216 | 0.493 | 0.000 | 0.220 | 0.071 | 0.000 | |||
| 5 spectra, EILGTAQSVGCNVDGR | 0.000 | 0.402 | 0.112 | 0.252 | 0.123 | 0.111 | 0.000 | |||
| 4 spectra, IGPLGLSPK | 0.000 | 0.191 | 0.709 | 0.081 | 0.000 | 0.019 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
122 spectra |
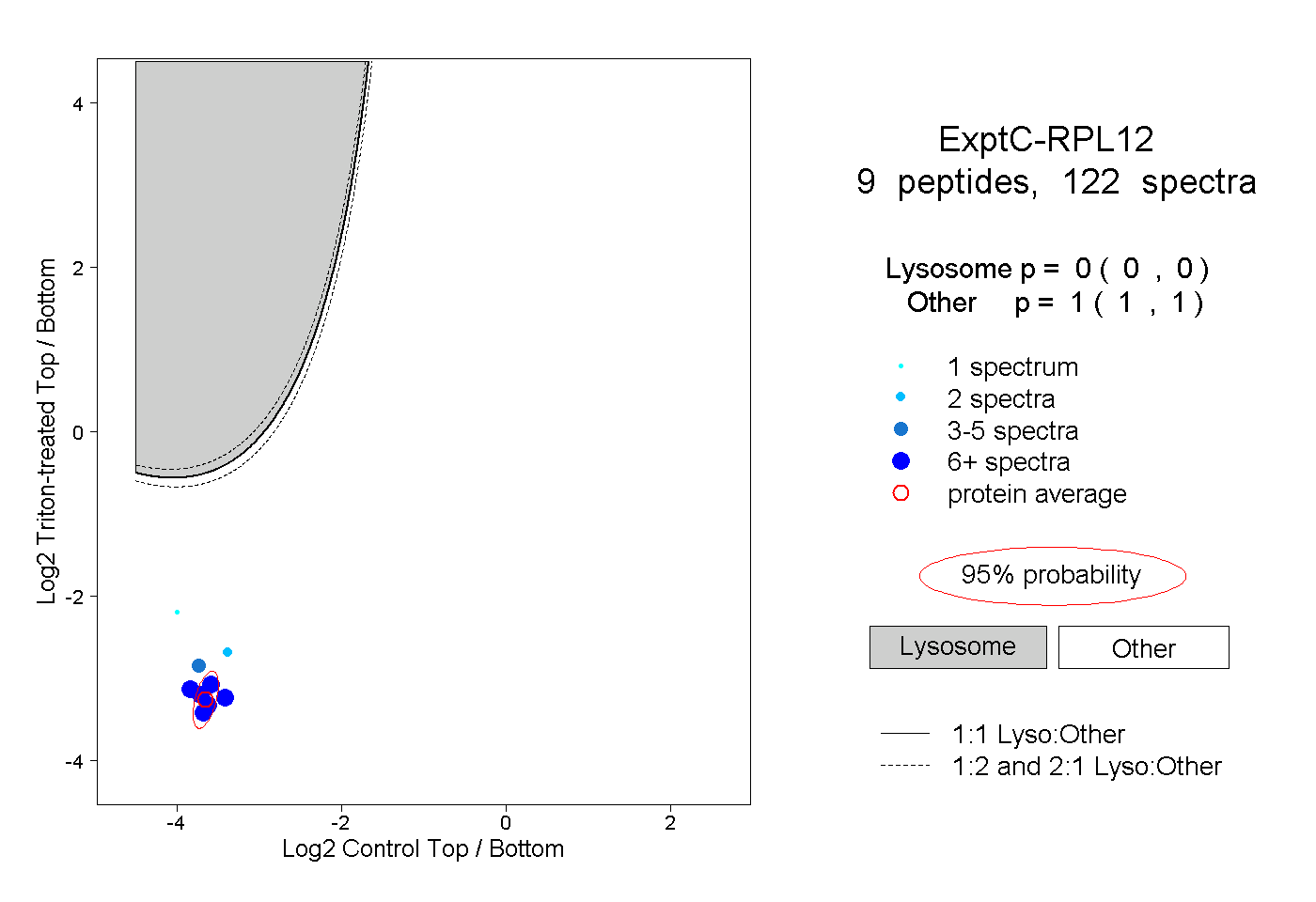 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
15 spectra |
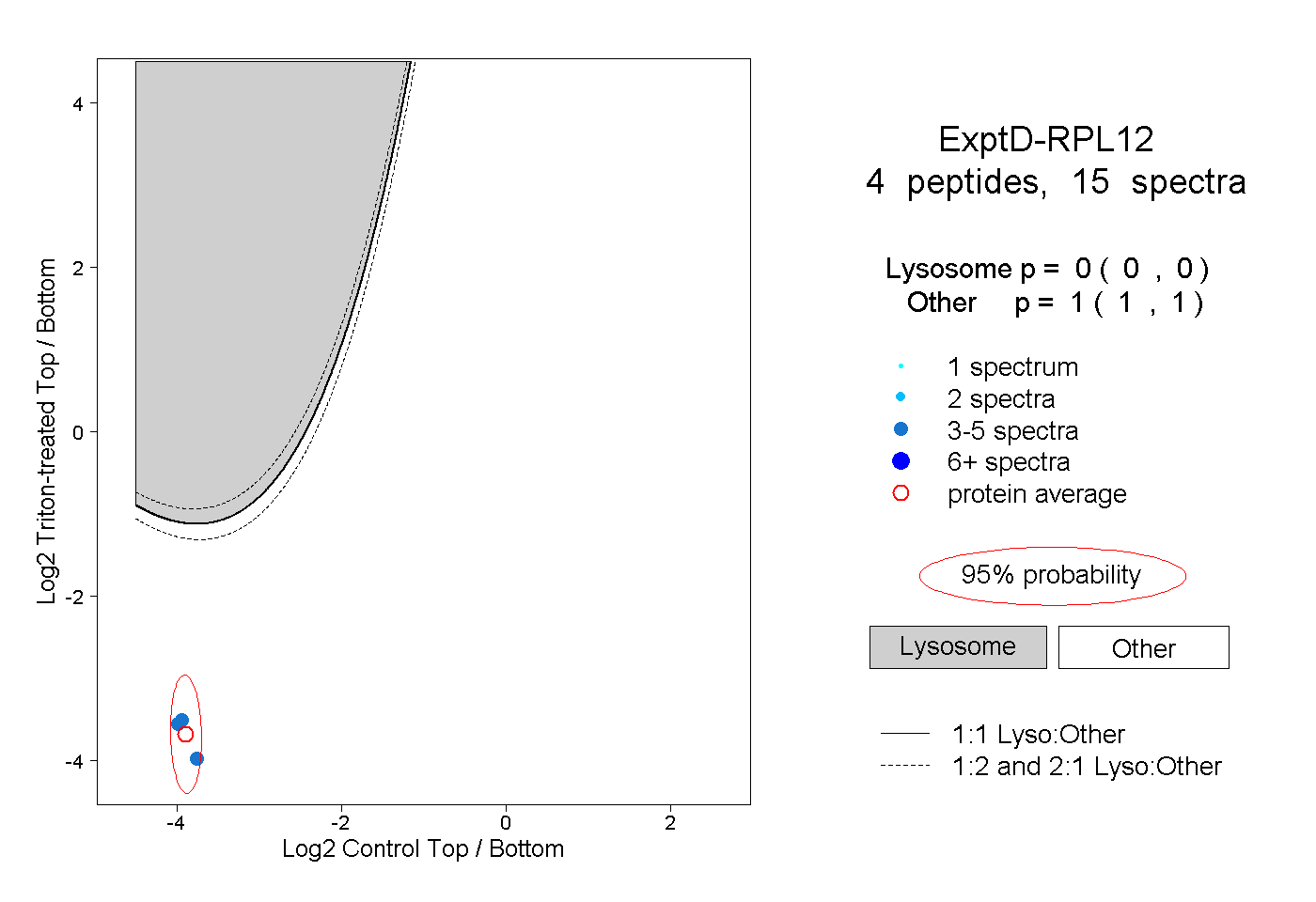 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |