peptides
spectra
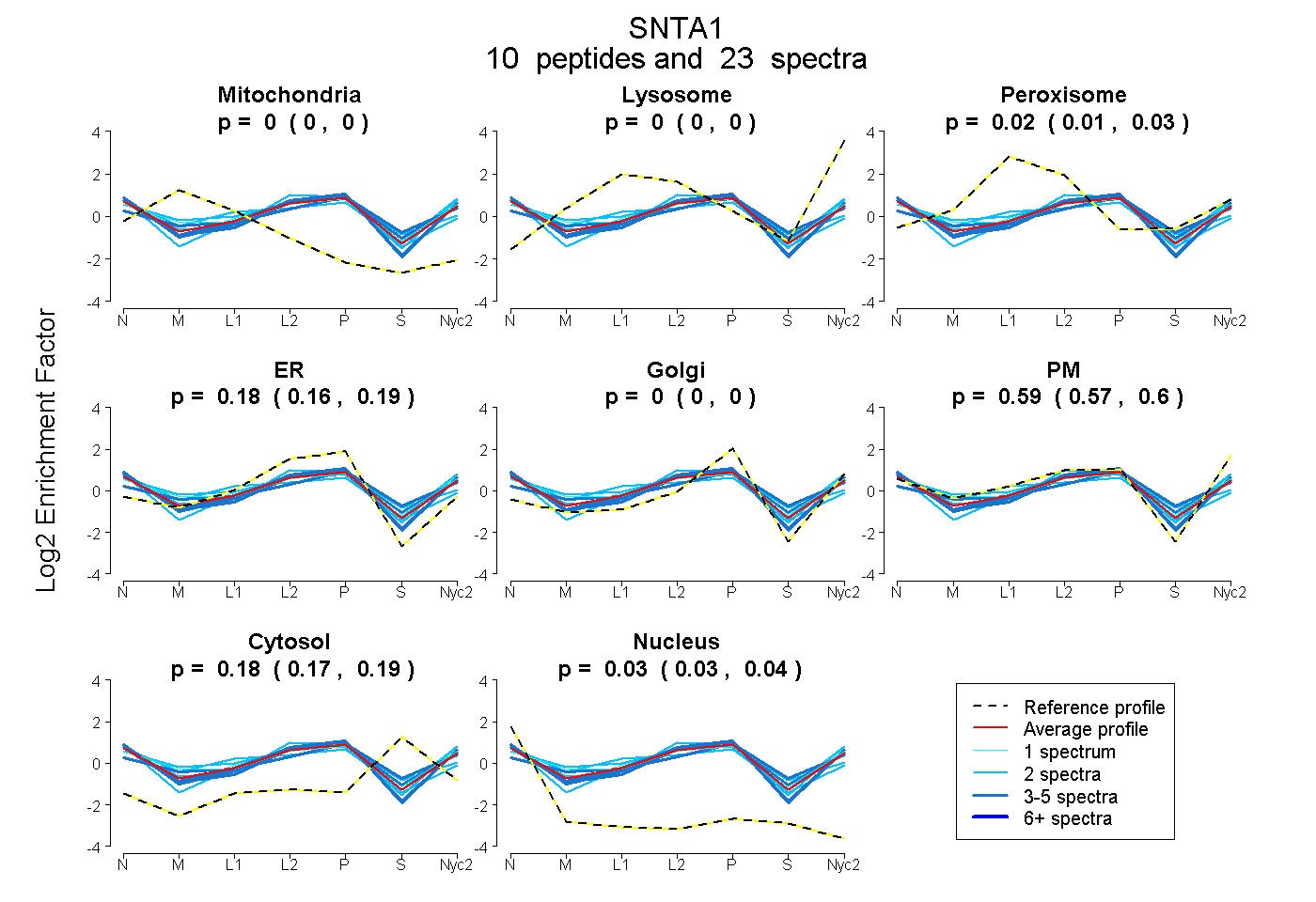
0.000 | 0.000
0.000 | 0.000
0.013 | 0.029
0.161 | 0.186
0.000 | 0.000
0.573 | 0.604
0.168 | 0.189
0.027 | 0.040
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
23 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.022 0.013 | 0.029 |
0.175 0.161 | 0.186 |
0.000 0.000 | 0.000 |
0.589 0.573 | 0.604 |
0.180 0.168 | 0.189 |
0.034 0.027 | 0.040 |
| 3 spectra, TAPLIATR | 0.000 | 0.000 | 0.000 | 0.148 | 0.000 | 0.592 | 0.234 | 0.026 | ||
| 2 spectra, EVVLEVK | 0.000 | 0.000 | 0.027 | 0.283 | 0.000 | 0.388 | 0.262 | 0.040 | ||
| 1 spectrum, GSVPYDAELSFALR | 0.000 | 0.000 | 0.019 | 0.113 | 0.000 | 0.635 | 0.233 | 0.000 | ||
| 3 spectra, LVHSGPSK | 0.003 | 0.000 | 0.105 | 0.091 | 0.160 | 0.393 | 0.248 | 0.000 | ||
| 1 spectrum, TMVFIIHSFLSAK | 0.041 | 0.000 | 0.019 | 0.107 | 0.000 | 0.633 | 0.200 | 0.000 | ||
| 3 spectra, QPSSPGPQPR | 0.000 | 0.000 | 0.000 | 0.190 | 0.000 | 0.656 | 0.085 | 0.070 | ||
| 2 spectra, ELLLYCSLPQTR | 0.000 | 0.000 | 0.130 | 0.000 | 0.000 | 0.683 | 0.137 | 0.050 | ||
| 4 spectra, SGAGSGAGGER | 0.000 | 0.000 | 0.000 | 0.213 | 0.000 | 0.636 | 0.070 | 0.081 | ||
| 2 spectra, CTPTDPEPR | 0.000 | 0.000 | 0.048 | 0.405 | 0.000 | 0.346 | 0.126 | 0.075 | ||
| 2 spectra, GFTLWAAEPGATR | 0.063 | 0.000 | 0.034 | 0.068 | 0.000 | 0.710 | 0.125 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
2 spectra |
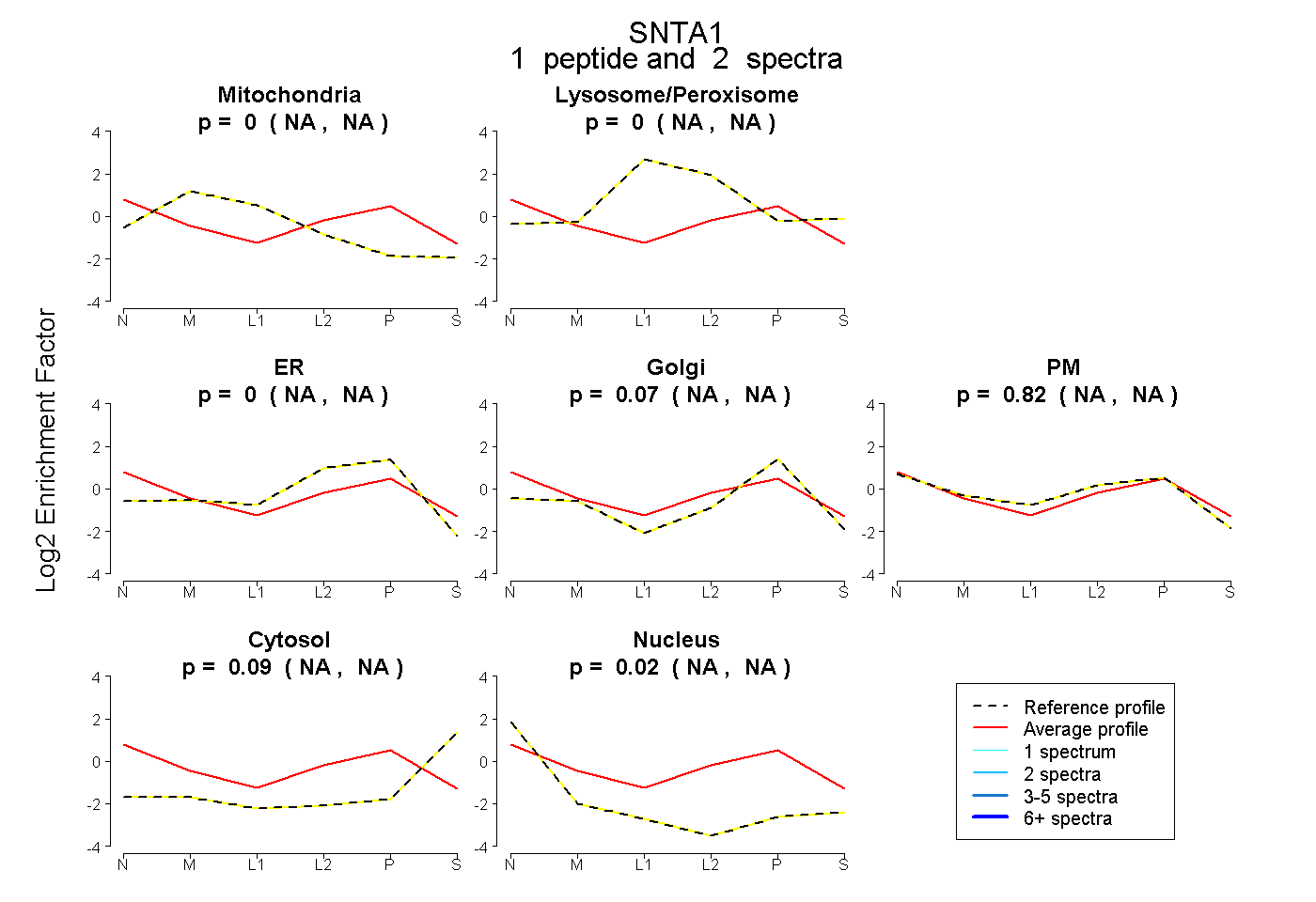 |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.069 NA | NA |
0.818 NA | NA |
0.091 NA | NA |
0.022 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
32 spectra |
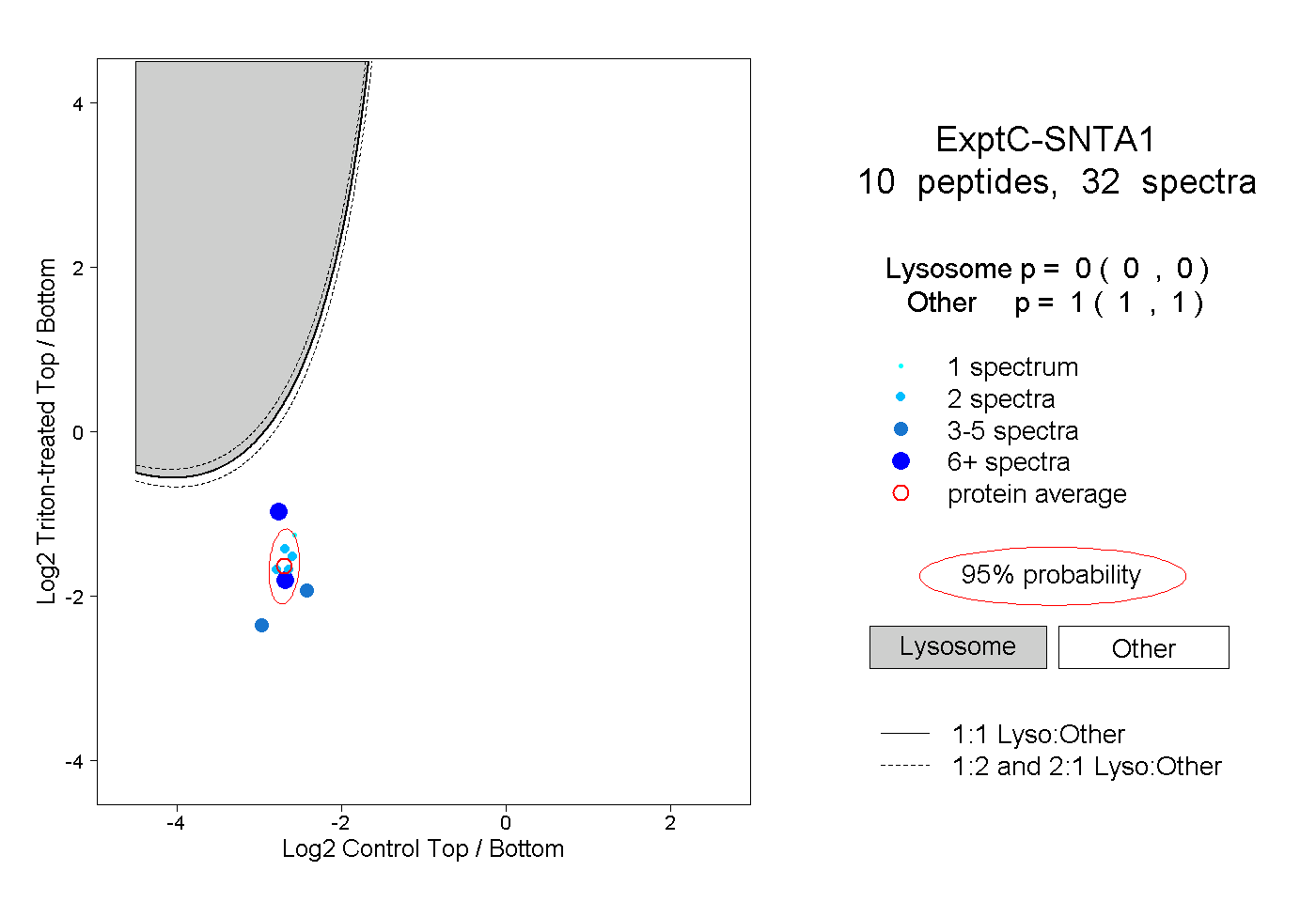 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
3 spectra |
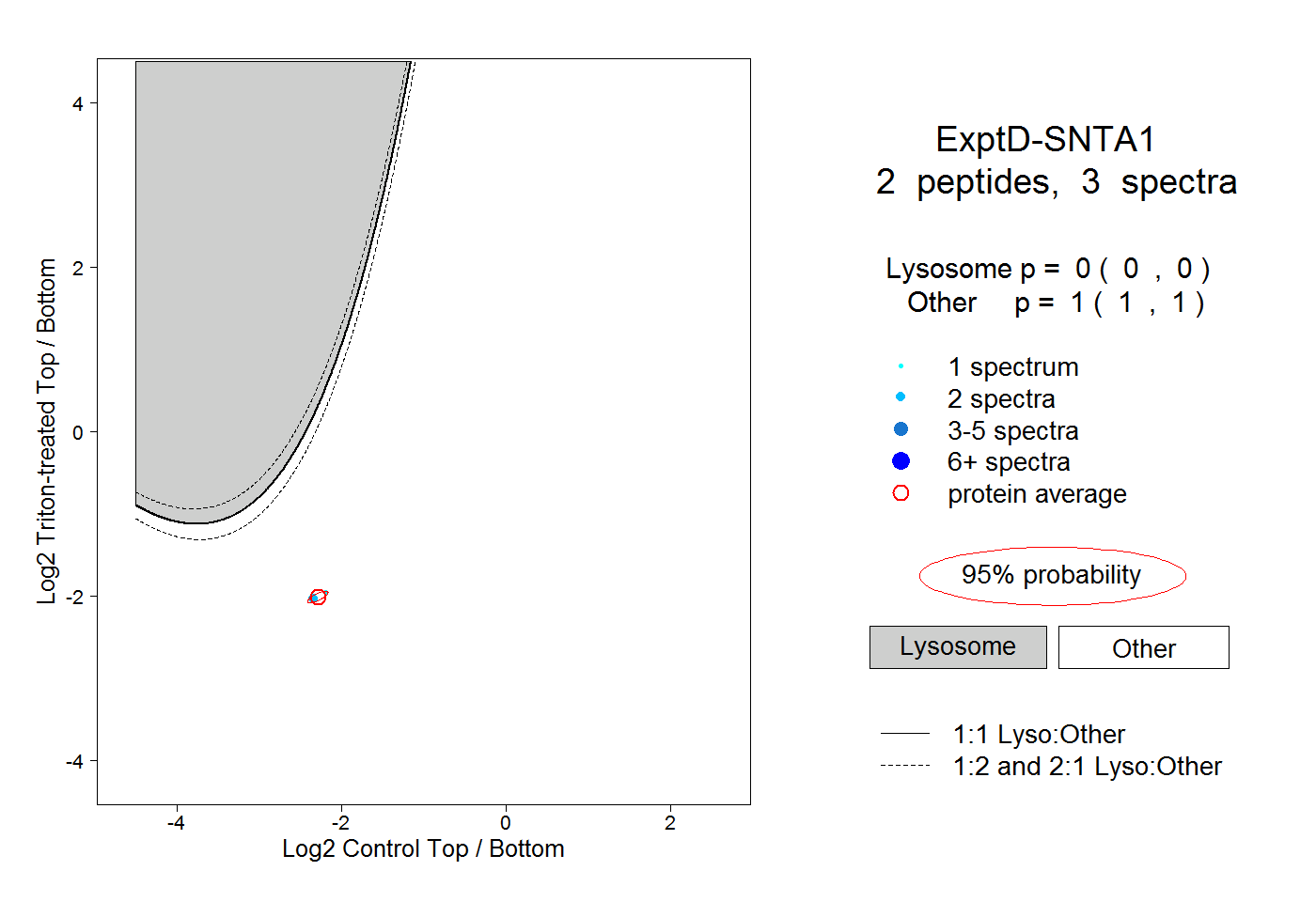 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |