peptides
spectra
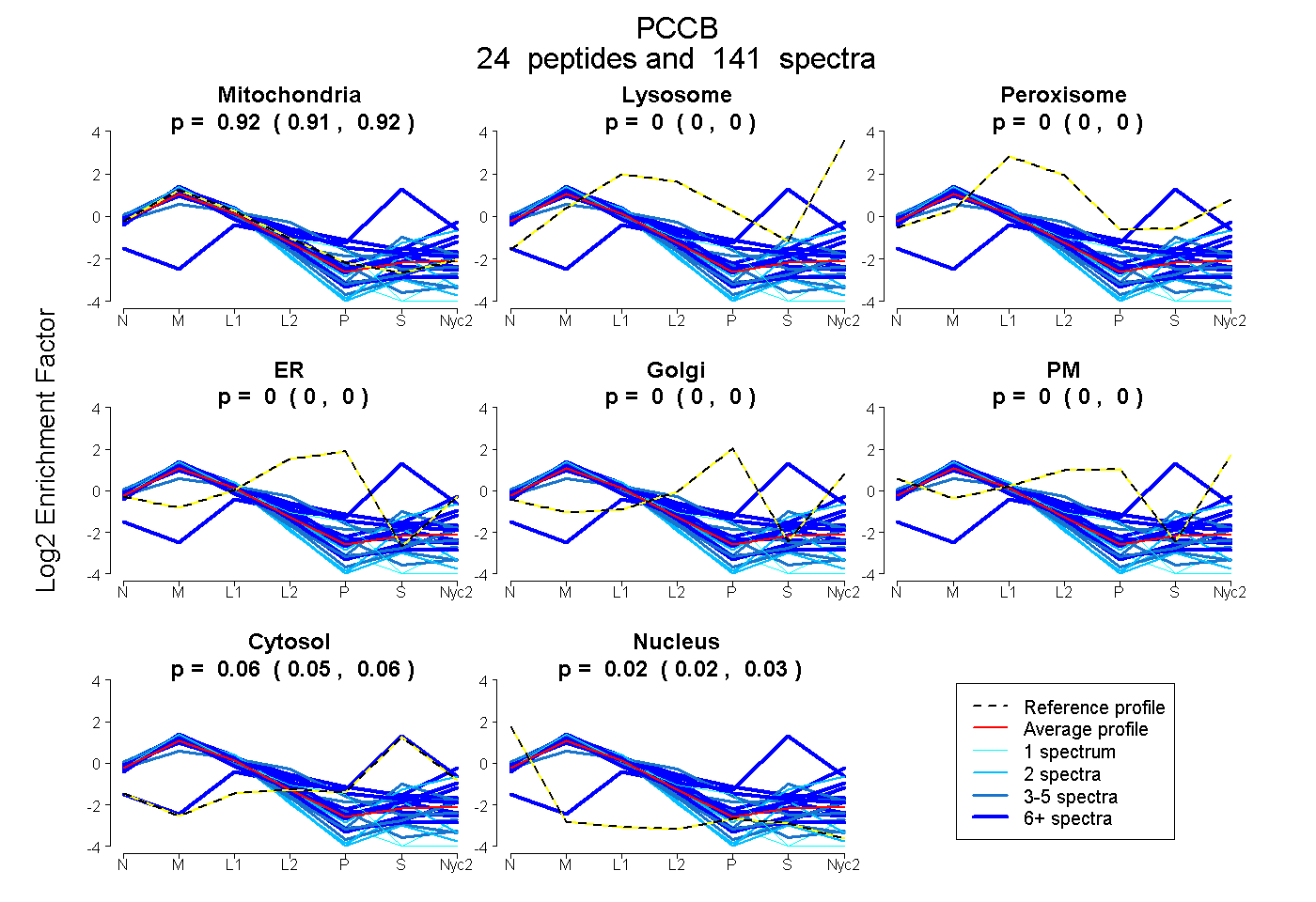
0.914 | 0.923
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.053 | 0.063
0.019 | 0.026
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
141 spectra |
 |
0.919 0.914 | 0.923 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.059 0.053 | 0.063 |
0.023 0.019 | 0.026 |
| 4 spectra, GHQDVEAAQAEYVEK | 0.836 | 0.000 | 0.000 | 0.141 | 0.000 | 0.000 | 0.000 | 0.023 | ||
| 1 spectrum, DTSYLFITGPEVVK | 0.939 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.061 | ||
| 2 spectra, HLLGDTNYAWPTAEIAVMGAK | 0.753 | 0.106 | 0.000 | 0.000 | 0.000 | 0.000 | 0.141 | 0.000 | ||
| 2 spectra, ICCDLEVLASK | 0.875 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.125 | ||
| 23 spectra, FANPFPAAVR | 0.939 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.061 | ||
| 1 spectrum, TVGIVGNQPNVASGCLDINSSVK | 0.917 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.083 | ||
| 2 spectra, IQEGVESLAGYADIFLR | 0.853 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.147 | ||
| 3 spectra, FPGDSVVTGR | 0.879 | 0.011 | 0.000 | 0.000 | 0.000 | 0.000 | 0.110 | 0.000 | ||
| 3 spectra, ECHDPSDR | 0.952 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.048 | ||
| 9 spectra, AFDNDVDALCNLR | 0.910 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.073 | 0.017 | ||
| 16 spectra, HAALLGGGQR | 0.849 | 0.079 | 0.000 | 0.000 | 0.000 | 0.000 | 0.061 | 0.012 | ||
| 5 spectra, ITVITR | 0.944 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.056 | ||
| 13 spectra, AYNMLDIIHAVIDER | 0.945 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.014 | 0.042 | ||
| 7 spectra, CADFGMAAEK | 0.585 | 0.159 | 0.000 | 0.000 | 0.000 | 0.164 | 0.092 | 0.000 | ||
| 6 spectra, EFFEIMPNYAK | 0.817 | 0.000 | 0.053 | 0.000 | 0.000 | 0.000 | 0.130 | 0.000 | ||
| 8 spectra, NIVIGFAR | 0.822 | 0.070 | 0.000 | 0.000 | 0.000 | 0.000 | 0.109 | 0.000 | ||
| 3 spectra, EFFNFLPLSNQDPAPIR | 0.909 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.091 | ||
| 3 spectra, GAVEIIFK | 0.890 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.110 | ||
| 3 spectra, HANVPL | 0.756 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.244 | 0.000 | ||
| 6 spectra, THTTVSGVAHR | 0.769 | 0.000 | 0.054 | 0.075 | 0.000 | 0.000 | 0.103 | 0.000 | ||
| 7 spectra, ISLLLDPGSFVESDMFVEHR | 0.954 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.046 | ||
| 2 spectra, AYGGAYDVMSSK | 0.935 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.065 | ||
| 6 spectra, AAAIR | 0.000 | 0.000 | 0.134 | 0.000 | 0.000 | 0.000 | 0.866 | 0.000 | ||
| 6 spectra, GFVDDIIQPSSTR | 0.984 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.016 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
71 spectra |
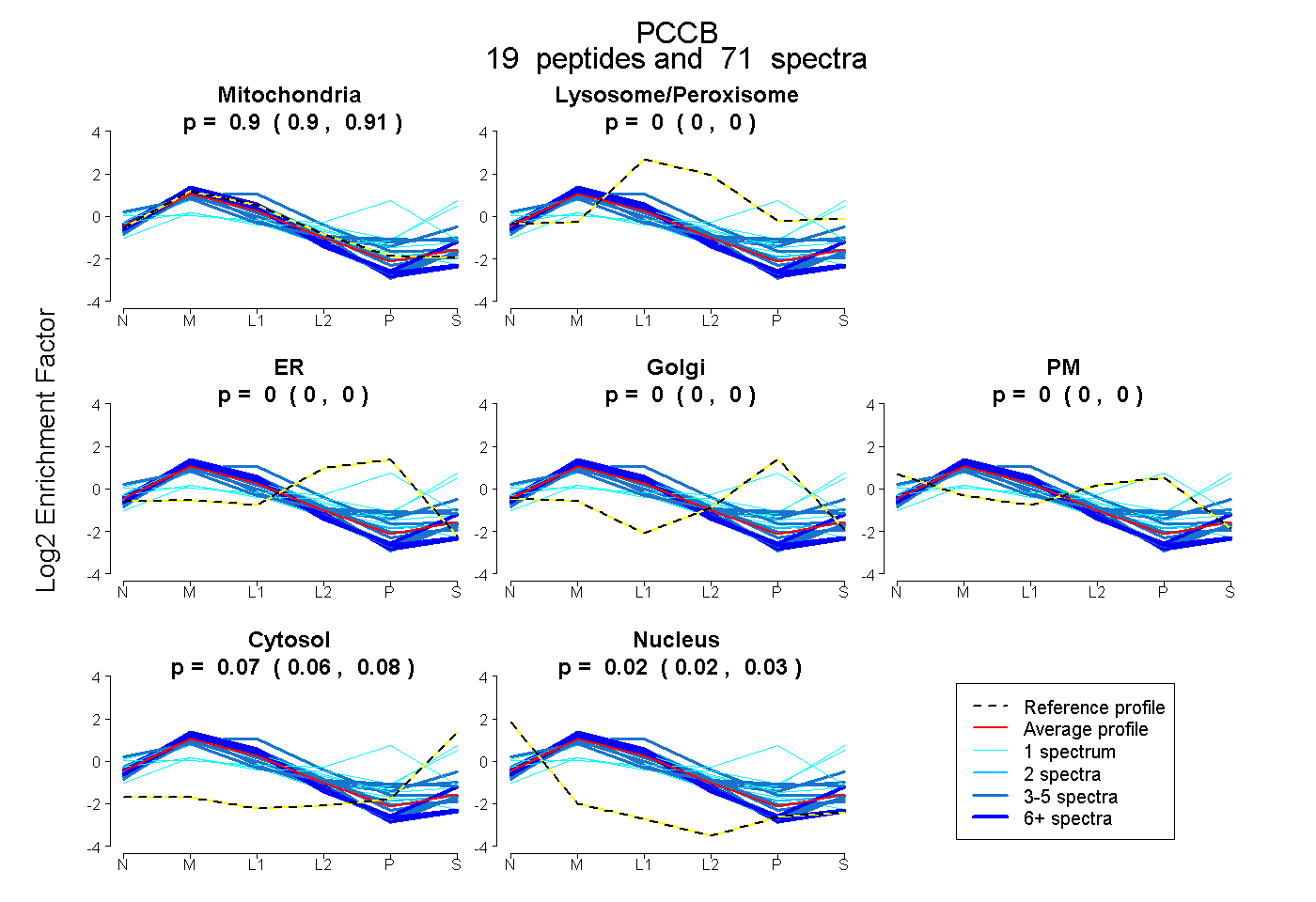 |
0.905 0.901 | 0.908 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.071 0.065 | 0.076 |
0.024 0.019 | 0.028 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
369 spectra |
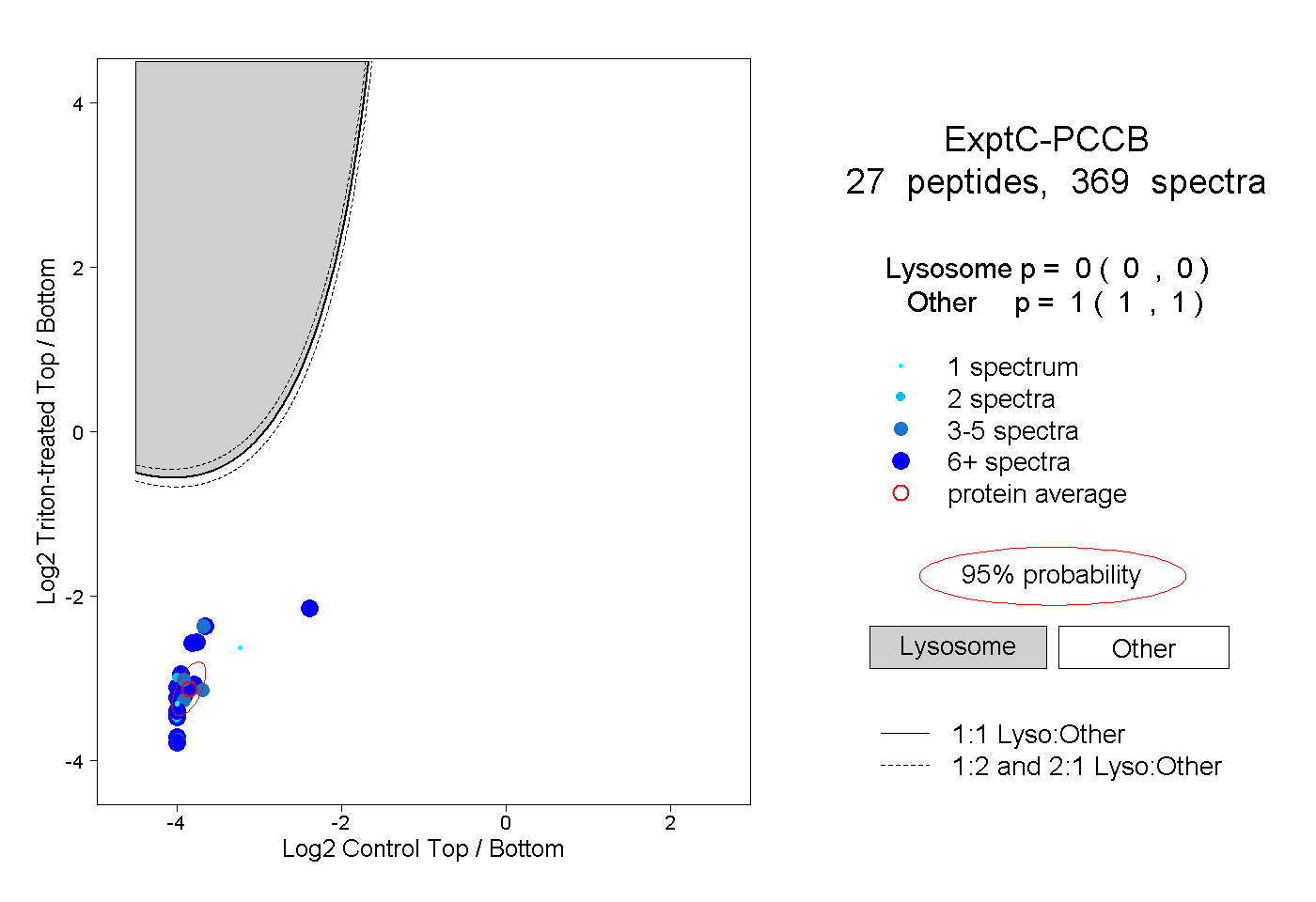 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
32 spectra |
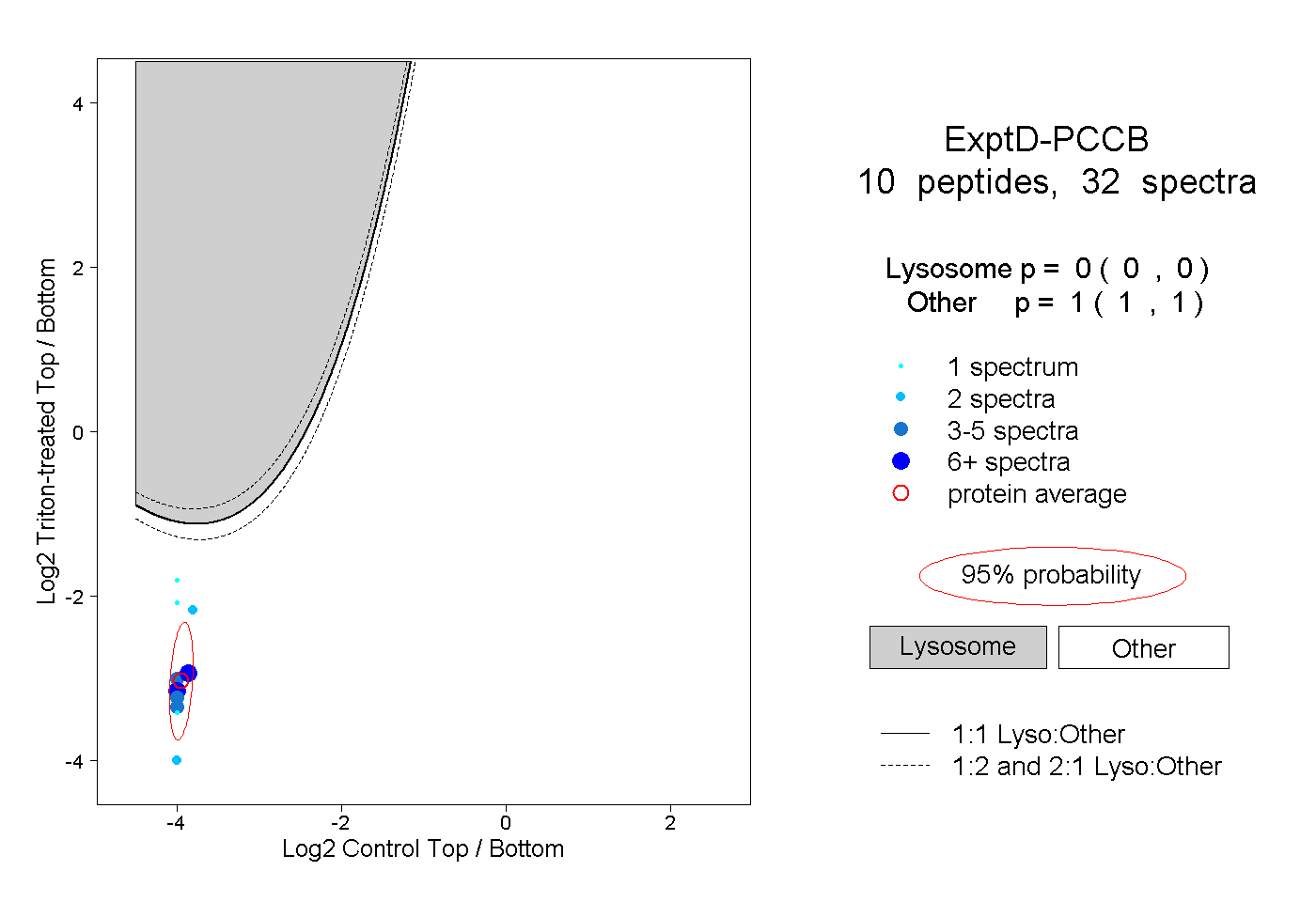 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |