peptides
spectra
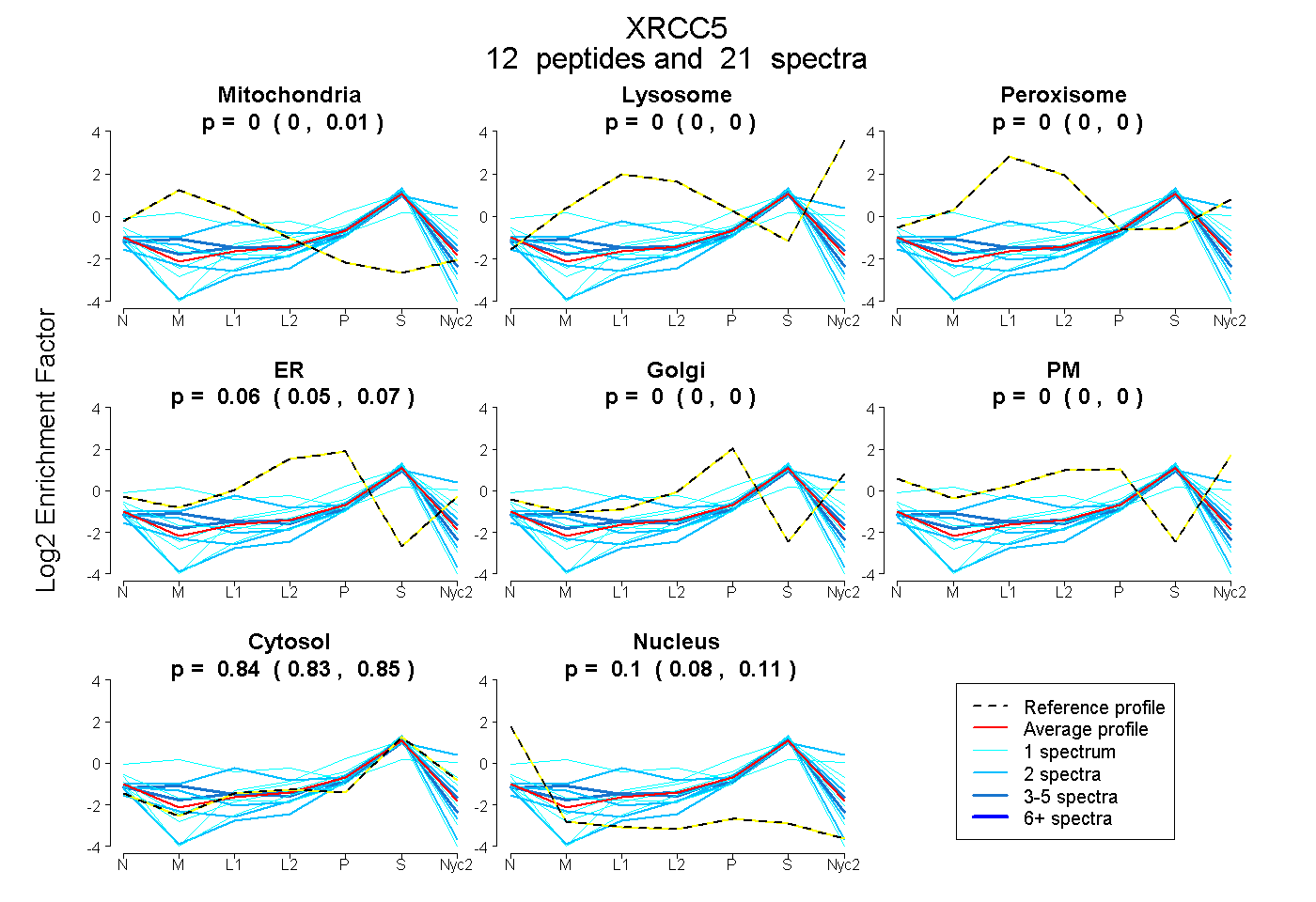
0.000 | 0.007
0.000 | 0.000
0.000 | 0.000
0.047 | 0.068
0.000 | 0.000
0.000 | 0.000
0.831 | 0.852
0.084 | 0.110
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
21 spectra |
 |
0.000 0.000 | 0.007 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.058 0.047 | 0.068 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.842 0.831 | 0.852 |
0.099 0.084 | 0.110 |
| 4 spectra, FFMGHQVLK | 0.204 | 0.000 | 0.000 | 0.000 | 0.002 | 0.000 | 0.794 | 0.000 | ||
| 1 spectrum, GLTEQQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.065 | 0.000 | 0.910 | 0.025 | ||
| 1 spectrum, ANPQVGVAFPFIK | 0.209 | 0.050 | 0.145 | 0.000 | 0.000 | 0.193 | 0.403 | 0.000 | ||
| 1 spectrum, ALHLQER | 0.000 | 0.000 | 0.000 | 0.054 | 0.000 | 0.000 | 0.740 | 0.207 | ||
| 2 spectra, FNSFLEGLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.775 | 0.225 | ||
| 3 spectra, LYQCLLHR | 0.081 | 0.000 | 0.000 | 0.012 | 0.000 | 0.000 | 0.825 | 0.081 | ||
| 1 spectrum, EEAIQFSEEQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.171 | 0.000 | 0.829 | 0.000 | ||
| 2 spectra, QYMFSSLK | 0.029 | 0.235 | 0.075 | 0.000 | 0.000 | 0.000 | 0.660 | 0.000 | ||
| 1 spectrum, VGSVNPVENFR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.794 | 0.206 | ||
| 2 spectra, VMTMFVQR | 0.071 | 0.000 | 0.000 | 0.000 | 0.054 | 0.000 | 0.821 | 0.054 | ||
| 1 spectrum, YGSDIIPFSK | 0.070 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.776 | 0.154 | ||
| 2 spectra, EGIHMVTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.776 | 0.224 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
1 spectrum |
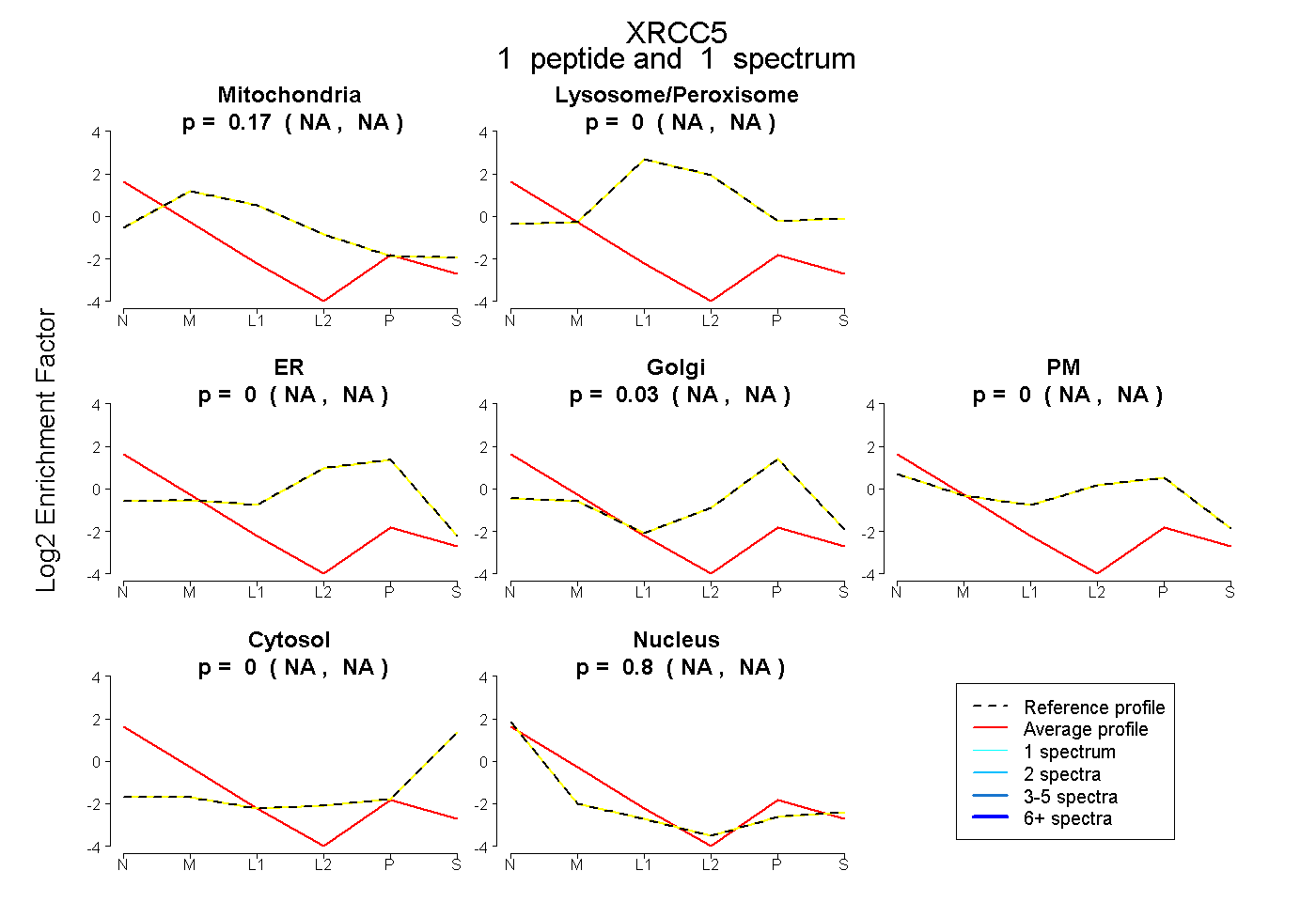 |
0.171 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.034 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.795 NA | NA |