peptides
spectra
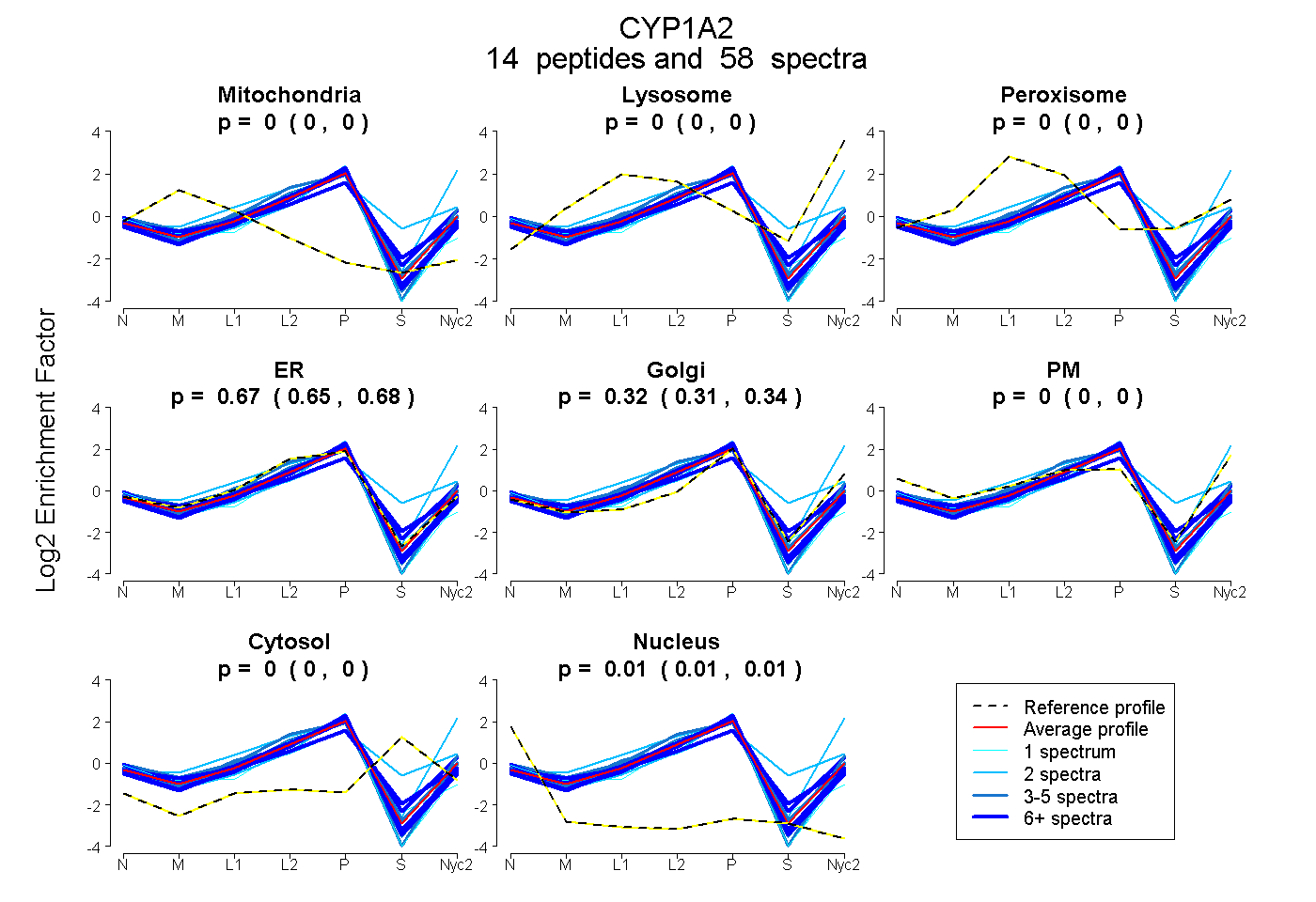
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.653 | 0.676
0.309 | 0.336
0.000 | 0.000
0.000 | 0.000
0.008 | 0.014
peptides
spectra
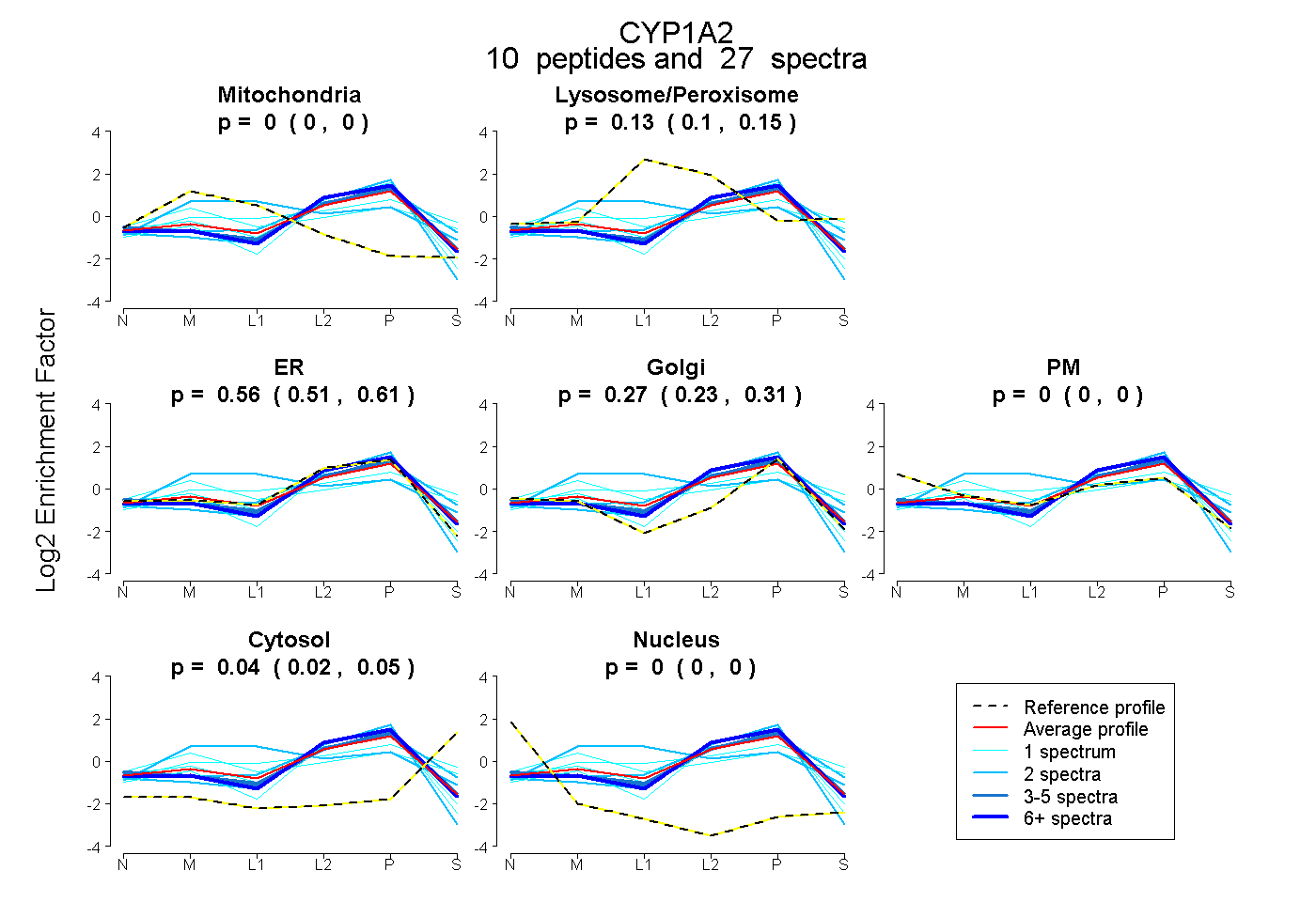
0.000 | 0.000
0.099 | 0.147
0.509 | 0.607
0.228 | 0.308
0.000 | 0.000
0.023 | 0.055
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
58 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.666 0.653 | 0.676 |
0.323 0.309 | 0.336 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.011 0.008 | 0.014 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
27 spectra |
 |
0.000 0.000 | 0.000 |
0.126 0.099 | 0.147 |
0.562 0.509 | 0.607 |
0.272 0.228 | 0.308 |
0.000 0.000 | 0.000 |
0.040 0.023 | 0.055 |
0.000 0.000 | 0.000 |
| 5 spectra, NSIQDITGALFK | 0.000 | 0.019 | 0.743 | 0.157 | 0.000 | 0.081 | 0.000 | |||
| 1 spectrum, IGSTPVVVLSGLNTIK | 0.029 | 0.012 | 0.779 | 0.180 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, FLTNDNTAIDK | 0.138 | 0.298 | 0.000 | 0.477 | 0.000 | 0.087 | 0.000 | |||
| 2 spectra, IHEELDTVIGR | 0.270 | 0.382 | 0.036 | 0.312 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, DPFVFRPER | 0.000 | 0.000 | 0.836 | 0.164 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, TVQEHYQDFNK | 0.000 | 0.056 | 0.654 | 0.233 | 0.000 | 0.058 | 0.000 | |||
| 8 spectra, VMLFGLGK | 0.000 | 0.000 | 0.844 | 0.094 | 0.000 | 0.062 | 0.000 | |||
| 1 spectrum, DTSLNGFHIPK | 0.000 | 0.435 | 0.000 | 0.457 | 0.000 | 0.108 | 0.000 | |||
| 2 spectra, EANHLISK | 0.000 | 0.222 | 0.442 | 0.236 | 0.000 | 0.100 | 0.000 | |||
| 1 spectrum, VDLTPSYGLTMKPR | 0.000 | 0.000 | 0.699 | 0.301 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
152 spectra |
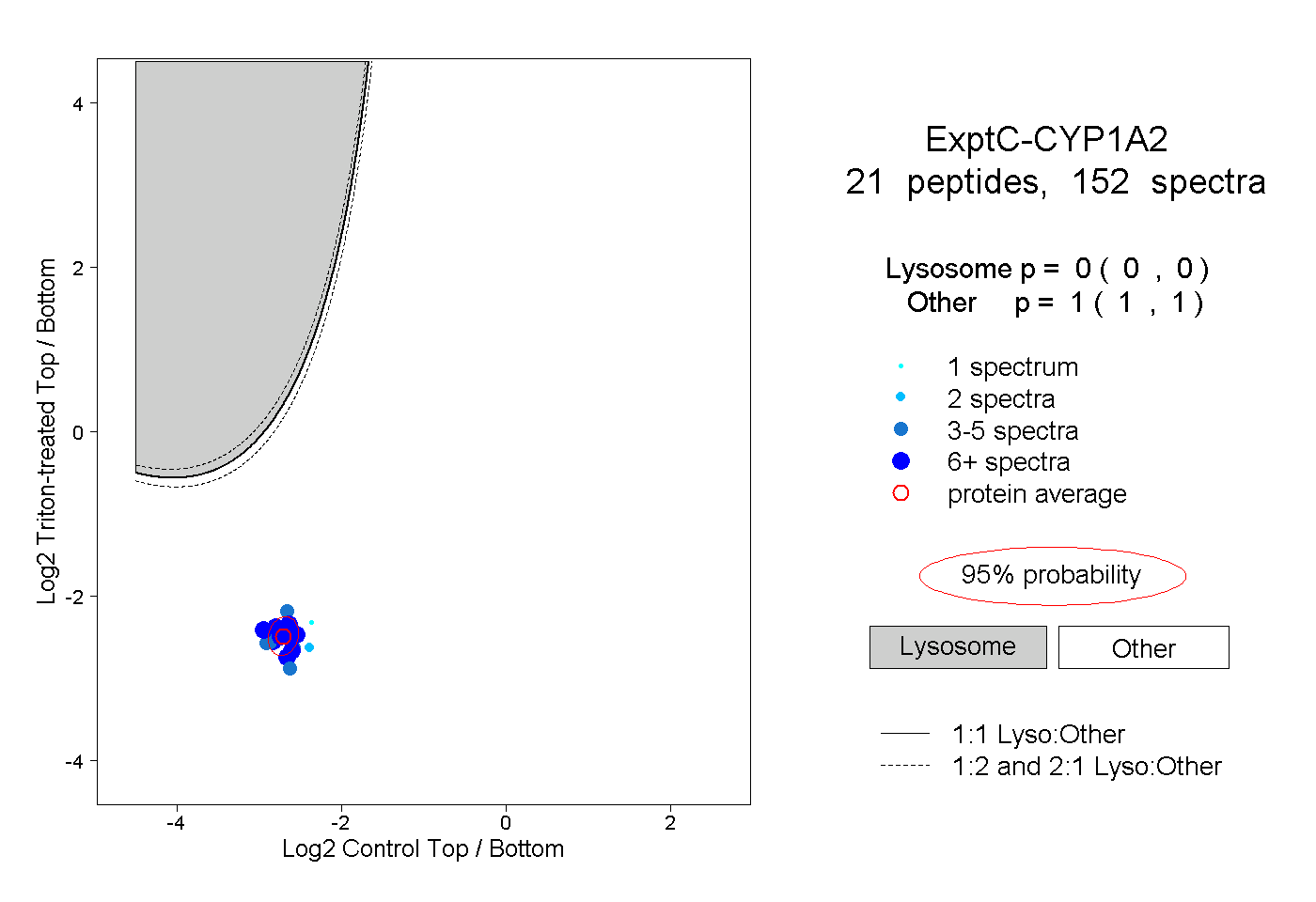 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
7 spectra |
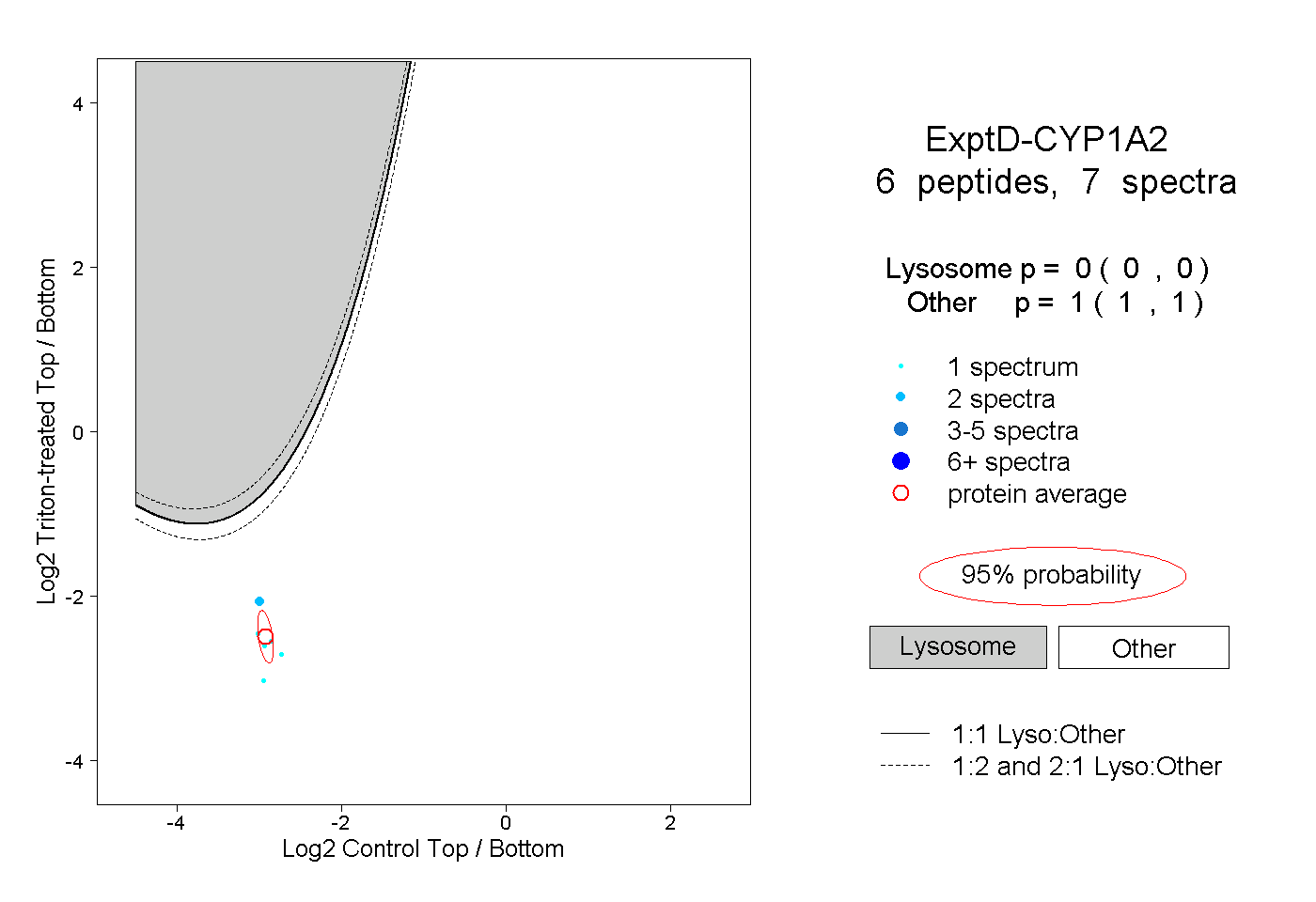 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |