peptides
spectra
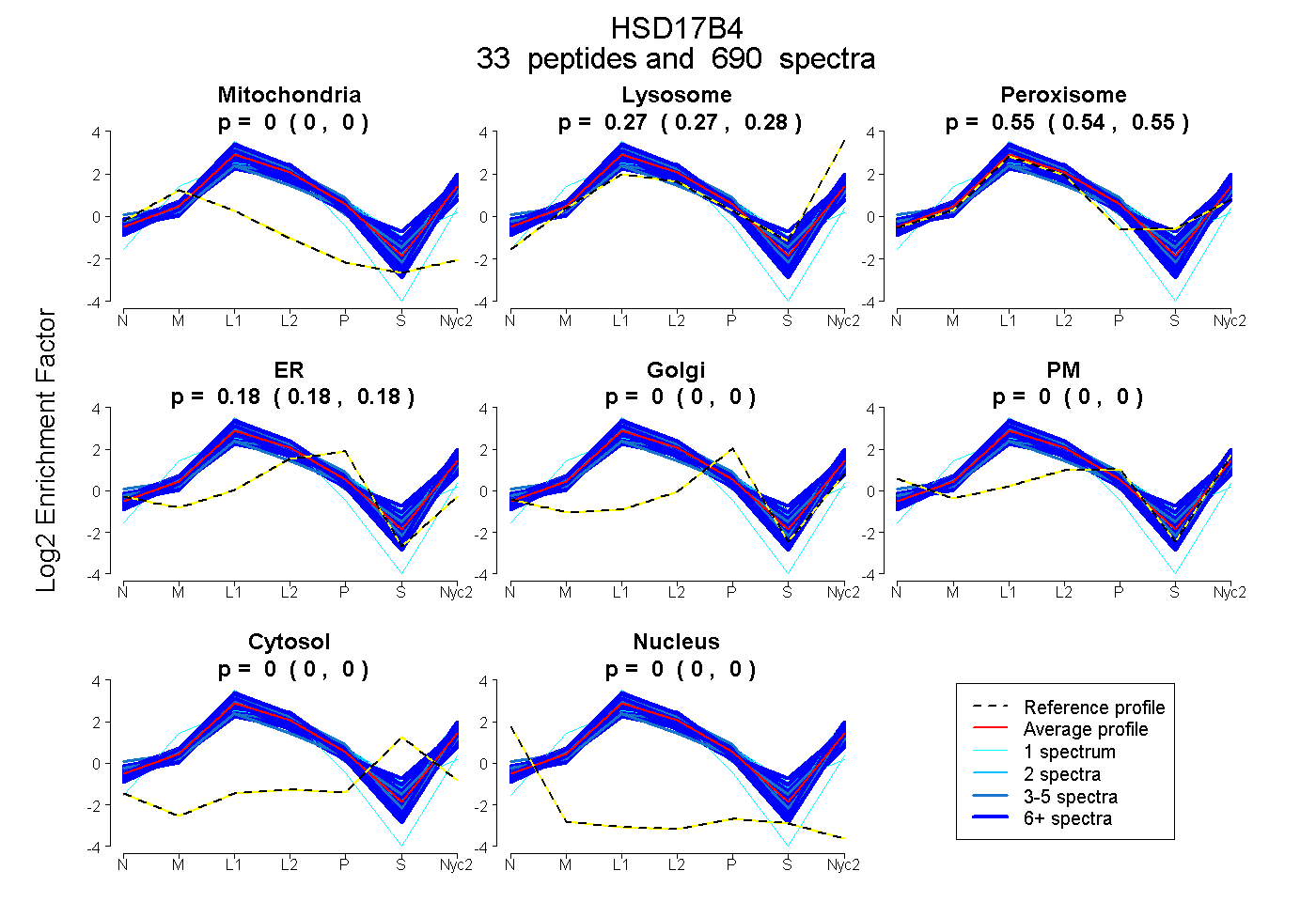
0.000 | 0.000
0.274 | 0.276
0.544 | 0.547
0.178 | 0.181
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
690 spectra |
 |
0.000 0.000 | 0.000 |
0.275 0.274 | 0.276 |
0.545 0.544 | 0.547 |
0.180 0.178 | 0.181 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 27 spectra, TALDTFGR | 0.000 | 0.368 | 0.580 | 0.052 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 16 spectra, LQMILK | 0.000 | 0.119 | 0.591 | 0.150 | 0.000 | 0.140 | 0.000 | 0.000 | ||
| 18 spectra, CEAVIADILDK | 0.000 | 0.100 | 0.603 | 0.297 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 38 spectra, NQPMTPEAVR | 0.000 | 0.436 | 0.424 | 0.140 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 33 spectra, IHFQTK | 0.000 | 0.201 | 0.524 | 0.189 | 0.000 | 0.087 | 0.000 | 0.000 | ||
| 20 spectra, TLGAIVR | 0.000 | 0.318 | 0.633 | 0.049 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 33 spectra, AAWDHMK | 0.000 | 0.261 | 0.544 | 0.166 | 0.000 | 0.030 | 0.000 | 0.000 | ||
| 2 spectra, GSADTTITISDEDFMEVVLGK | 0.000 | 0.124 | 0.777 | 0.099 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 15 spectra, NNIHCNTIAPNAGSR | 0.000 | 0.258 | 0.459 | 0.217 | 0.000 | 0.066 | 0.000 | 0.000 | ||
| 2 spectra, GSSAADK | 0.000 | 0.363 | 0.490 | 0.105 | 0.000 | 0.042 | 0.000 | 0.000 | ||
| 14 spectra, AVANYDSVEAGEK | 0.000 | 0.188 | 0.597 | 0.104 | 0.000 | 0.111 | 0.000 | 0.000 | ||
| 1 spectrum, NGNVAAK | 0.270 | 0.297 | 0.262 | 0.171 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 59 spectra, DTTSLNQAALYR | 0.000 | 0.409 | 0.443 | 0.148 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 51 spectra, AAVAVPSRPPDAVLR | 0.000 | 0.308 | 0.520 | 0.172 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 33 spectra, HVLQQFADNDVSR | 0.000 | 0.189 | 0.520 | 0.124 | 0.000 | 0.167 | 0.000 | 0.000 | ||
| 48 spectra, VVLVTGAGGGLGR | 0.000 | 0.432 | 0.454 | 0.114 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, ELICYNQFSVFVVGSGGFGGK | 0.000 | 0.000 | 0.822 | 0.178 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 24 spectra, GALVVVNDLGGDFK | 0.000 | 0.240 | 0.575 | 0.185 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 5 spectra, VNAVFEWHITK | 0.000 | 0.190 | 0.610 | 0.200 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 3 spectra, FAKPVYPGQTLQTEMWK | 0.000 | 0.023 | 0.661 | 0.000 | 0.000 | 0.316 | 0.000 | 0.000 | ||
| 45 spectra, ISDEDWDIIQR | 0.000 | 0.319 | 0.577 | 0.104 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 8 spectra, WTIDLK | 0.000 | 0.286 | 0.465 | 0.249 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 4 spectra, NGSGEVYQGPAK | 0.000 | 0.303 | 0.416 | 0.281 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 20 spectra, GNIMLSQK | 0.000 | 0.156 | 0.638 | 0.206 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 31 spectra, IDVVVNNAGILR | 0.000 | 0.453 | 0.437 | 0.110 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 43 spectra, GSFQVTR | 0.000 | 0.432 | 0.508 | 0.060 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 35 spectra, AYALAFAER | 0.000 | 0.300 | 0.561 | 0.139 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 37 spectra, LNPQNAFFSGR | 0.000 | 0.170 | 0.626 | 0.205 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 5 spectra, VLHGEQYLELYKPLPR | 0.000 | 0.274 | 0.510 | 0.217 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 8 spectra, SIQESTGGIIEVLHK | 0.000 | 0.128 | 0.689 | 0.183 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, LTGALVR | 0.000 | 0.293 | 0.546 | 0.036 | 0.000 | 0.125 | 0.000 | 0.000 | ||
| 6 spectra, GSGIVIVMDVYSYSGK | 0.065 | 0.206 | 0.450 | 0.047 | 0.000 | 0.233 | 0.000 | 0.000 | ||
| 3 spectra, SLMSGGLAEVPGLSINFAK | 0.000 | 0.096 | 0.594 | 0.054 | 0.000 | 0.255 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
466 spectra |
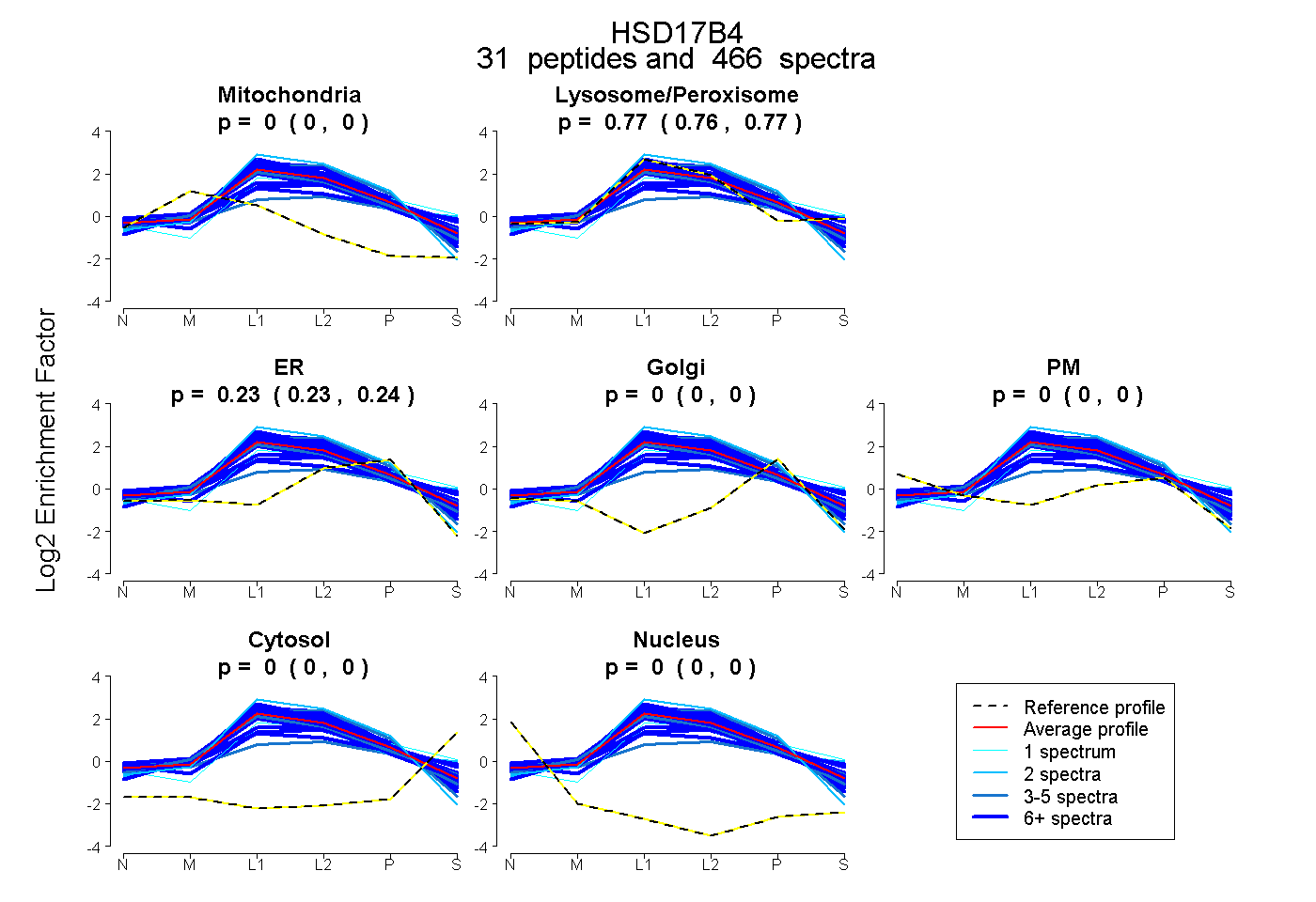 |
0.000 0.000 | 0.000 |
0.765 0.764 | 0.766 |
0.235 0.234 | 0.236 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
2870 spectra |
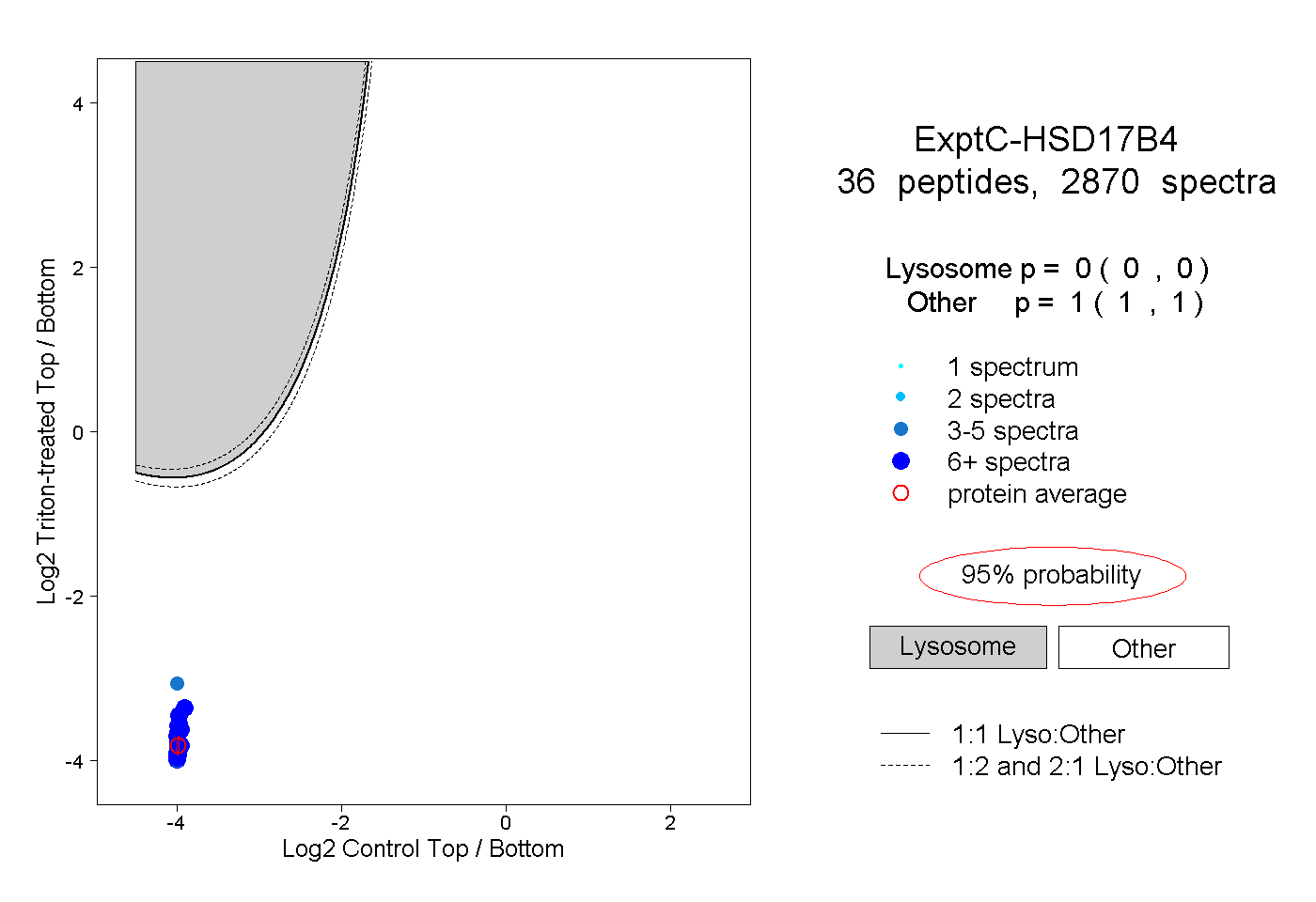 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
245 spectra |
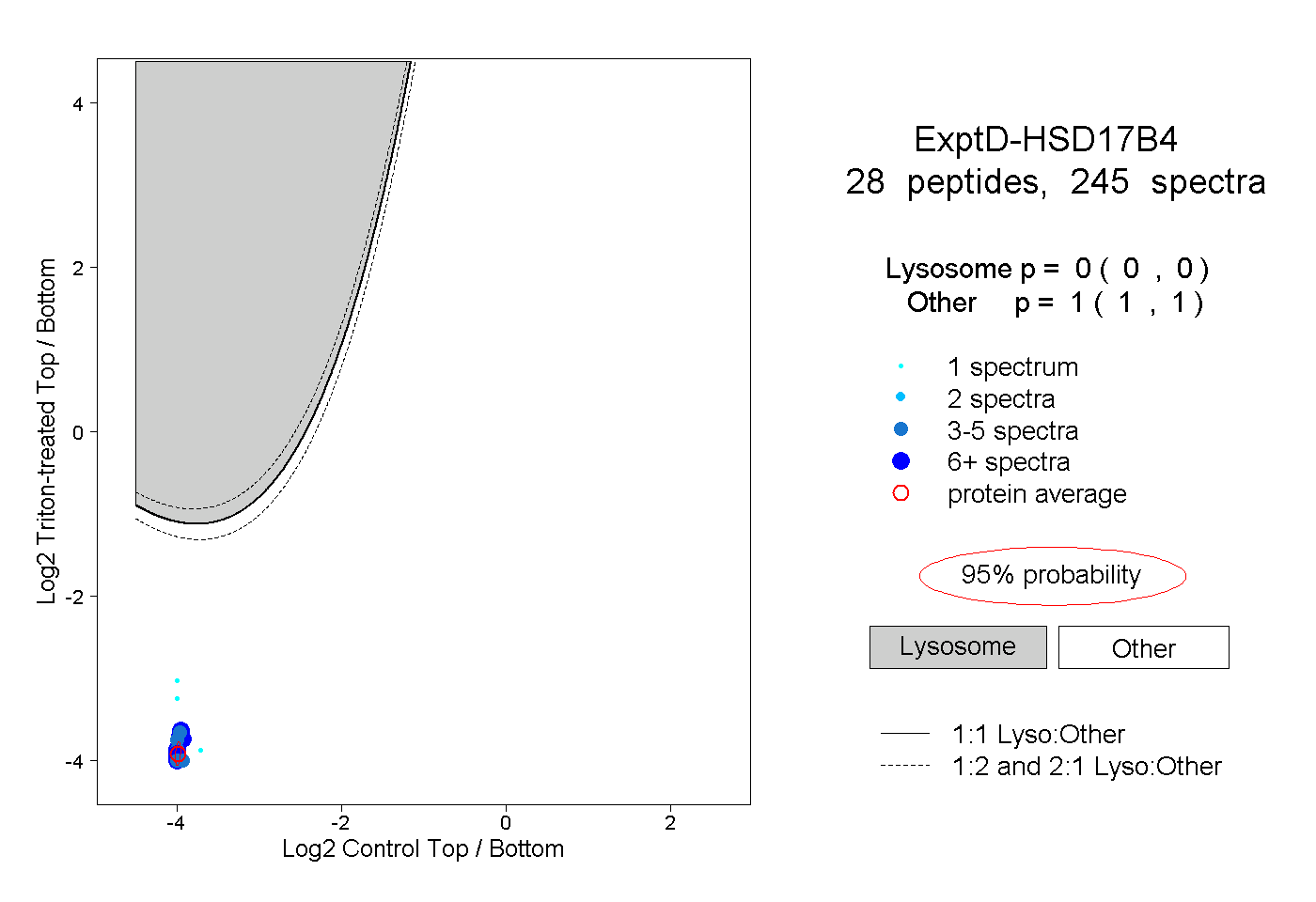 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |