peptides
spectra

0.000 | 0.000
0.032 | 0.048
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.951 | 0.966
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
38 spectra |
 |
0.000 0.000 | 0.000 |
0.041 0.032 | 0.048 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.959 0.951 | 0.966 |
0.000 0.000 | 0.000 |
| 2 spectra, TLQQQTFK | 0.000 | 0.300 | 0.000 | 0.000 | 0.036 | 0.000 | 0.664 | 0.000 | ||
| 3 spectra, AVEYLLMGIPGDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.982 | 0.018 | ||
| 1 spectrum, ILSDDTALK | 0.140 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.860 | 0.000 | ||
| 8 spectra, NQPQFQQMR | 0.000 | 0.014 | 0.000 | 0.000 | 0.000 | 0.000 | 0.986 | 0.000 | ||
| 12 spectra, ASFNNPDR | 0.125 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.875 | 0.000 | ||
| 1 spectrum, MQVTLK | 0.000 | 0.019 | 0.000 | 0.000 | 0.156 | 0.082 | 0.742 | 0.000 | ||
| 5 spectra, IDIDPEETVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.977 | 0.023 | ||
| 1 spectrum, DAFPVAGQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.940 | 0.060 | ||
| 2 spectra, LIYAGK | 0.000 | 0.077 | 0.000 | 0.000 | 0.000 | 0.000 | 0.923 | 0.000 | ||
| 3 spectra, EQVIAALR | 0.000 | 0.110 | 0.000 | 0.000 | 0.000 | 0.000 | 0.890 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
7 spectra |
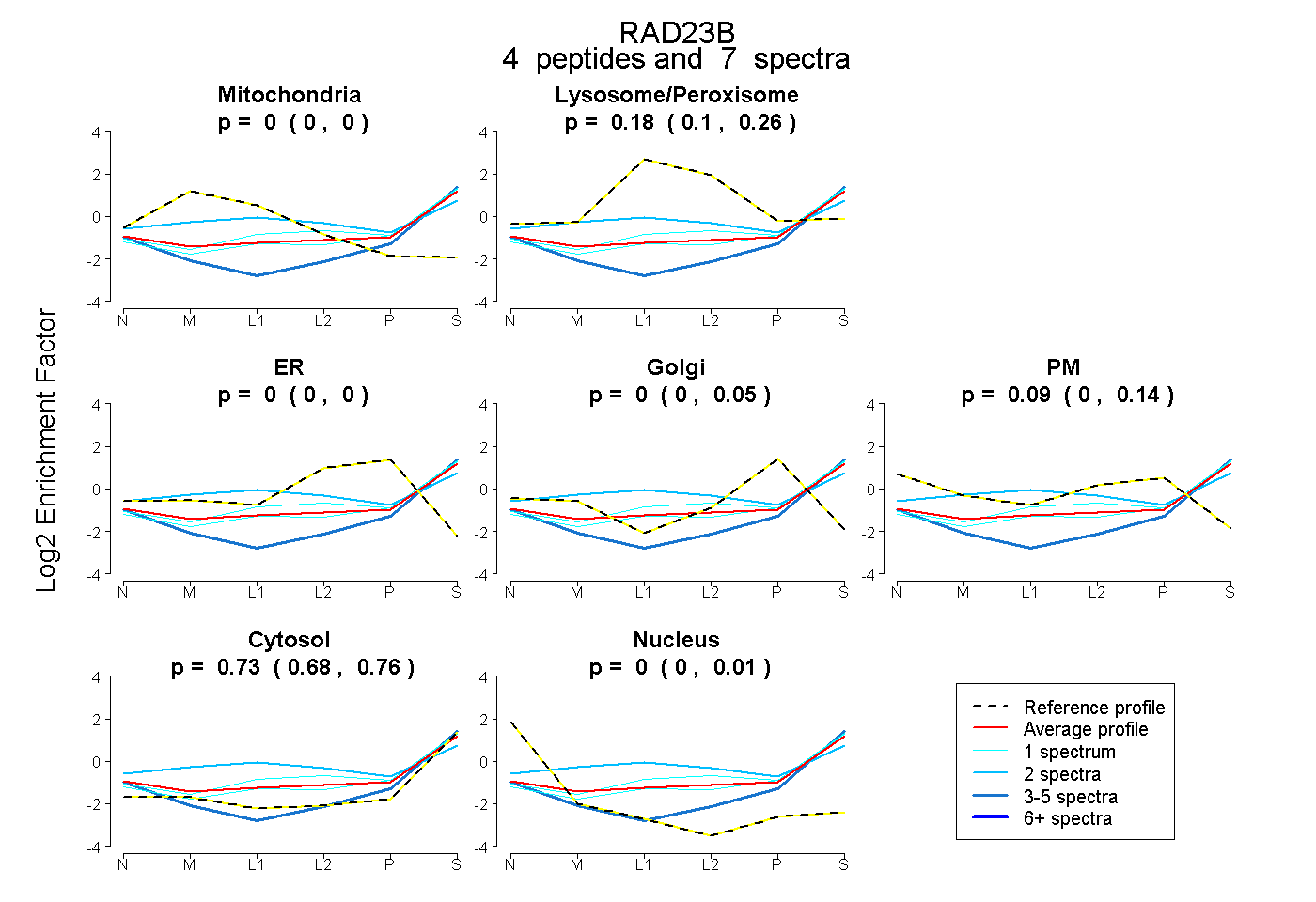 |
0.000 0.000 | 0.000 |
0.181 0.103 | 0.258 |
0.000 0.000 | 0.001 |
0.000 0.000 | 0.048 |
0.092 0.000 | 0.137 |
0.727 0.684 | 0.756 |
0.000 0.000 | 0.011 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
55 spectra |
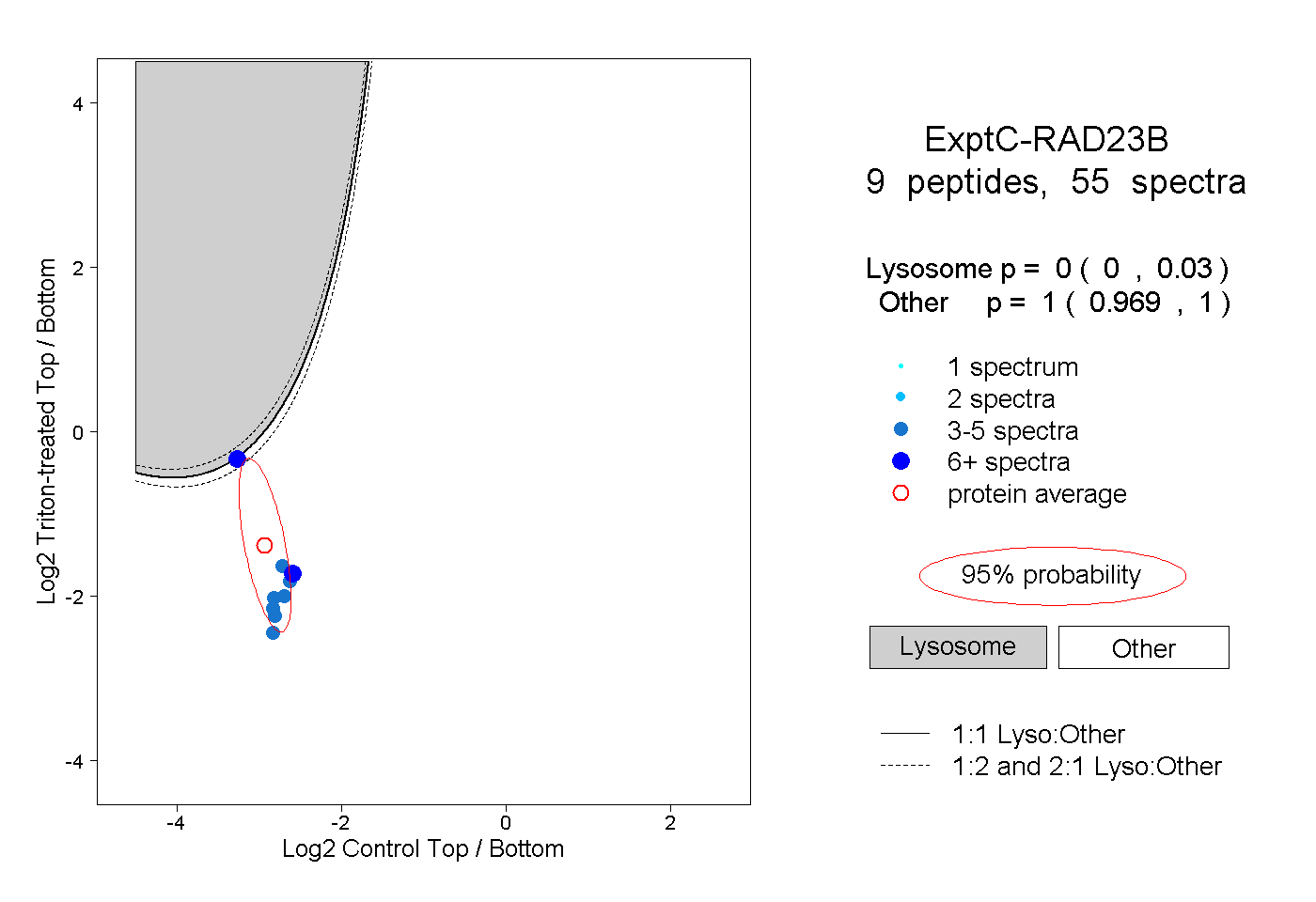 |
0.000 0.000 | 0.030 |
1.000 0.969 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
1 spectrum |
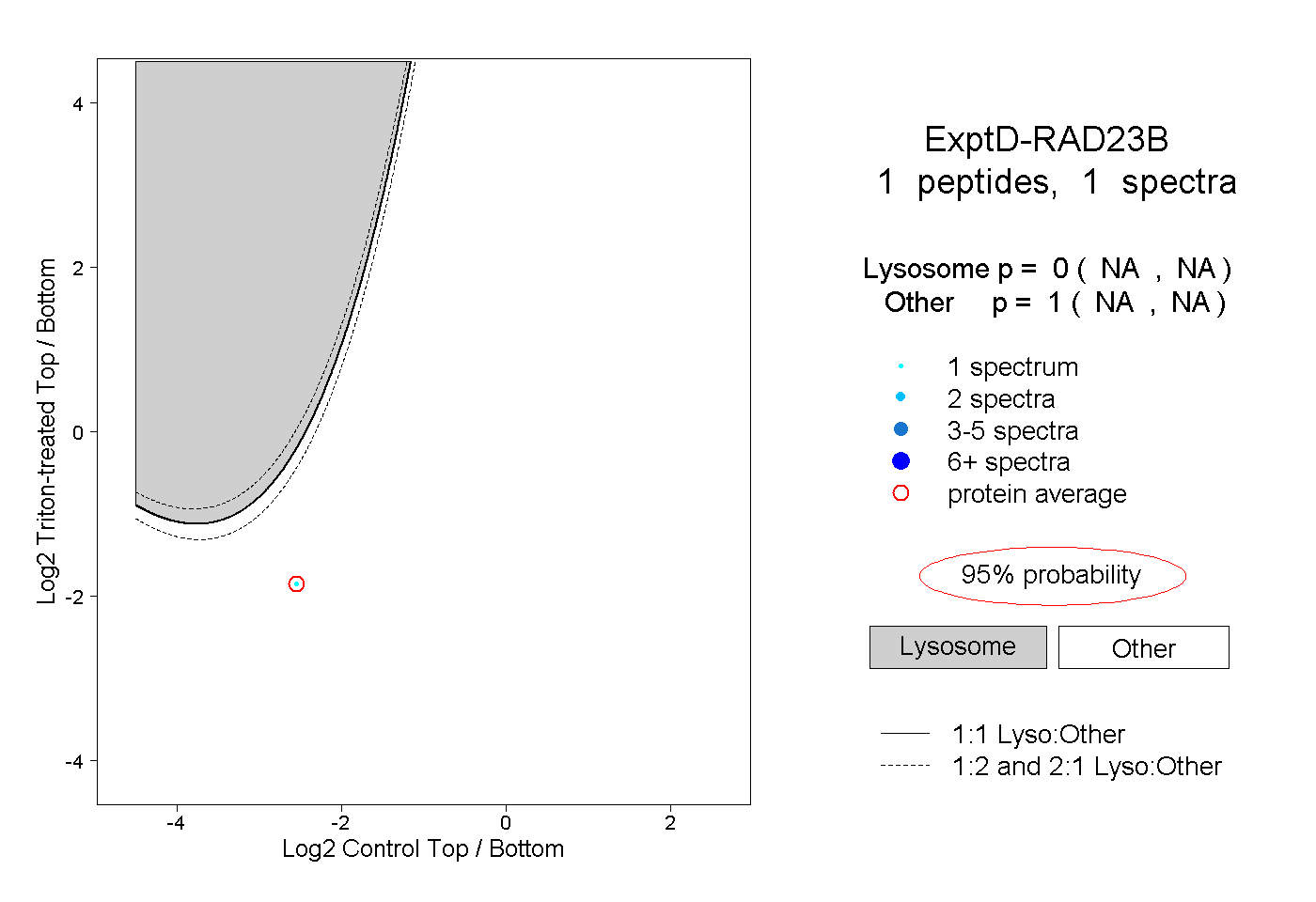 |
0.000 NA | NA |
1.000 NA | NA |