peptides
spectra
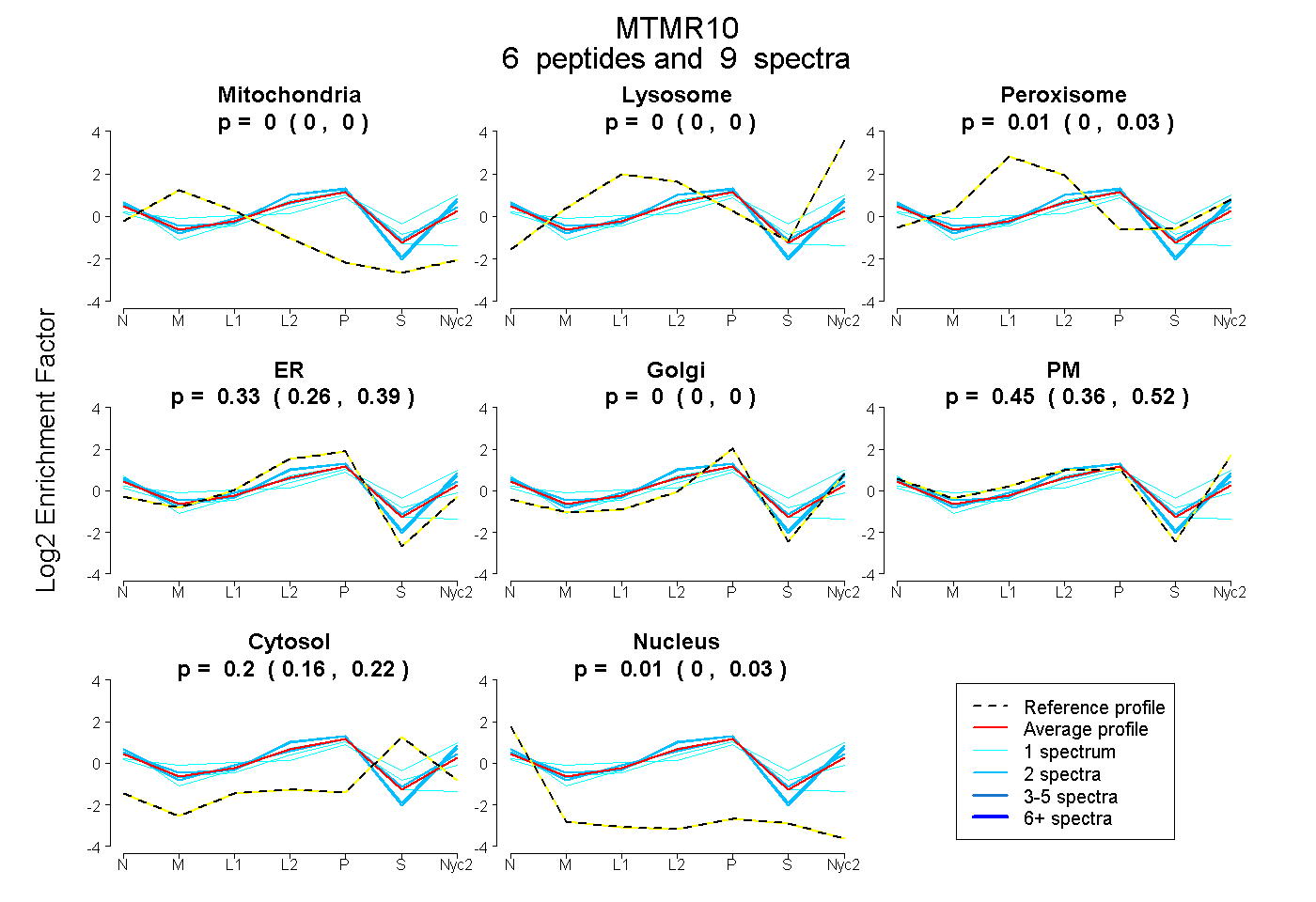
0.000 | 0.000
0.000 | 0.000
0.000 | 0.033
0.259 | 0.389
0.000 | 0.000
0.357 | 0.520
0.161 | 0.217
0.000 | 0.030
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
9 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.010 0.000 | 0.033 |
0.332 0.259 | 0.389 |
0.000 0.000 | 0.000 |
0.453 0.357 | 0.520 |
0.197 0.161 | 0.217 |
0.009 0.000 | 0.030 |
| 1 spectrum, LICSNFK | 0.000 | 0.000 | 0.062 | 0.670 | 0.000 | 0.000 | 0.125 | 0.143 | ||
| 2 spectra, TPLFETYSDWDR | 0.000 | 0.000 | 0.009 | 0.262 | 0.000 | 0.515 | 0.214 | 0.000 | ||
| 2 spectra, LSVVLQEEEGR | 0.000 | 0.000 | 0.000 | 0.302 | 0.005 | 0.607 | 0.047 | 0.039 | ||
| 2 spectra, WLEYVR | 0.000 | 0.000 | 0.000 | 0.264 | 0.034 | 0.623 | 0.074 | 0.005 | ||
| 1 spectrum, LSVLADEVDK | 0.000 | 0.049 | 0.028 | 0.000 | 0.126 | 0.512 | 0.286 | 0.000 | ||
| 1 spectrum, QSTEFAISK | 0.114 | 0.000 | 0.212 | 0.084 | 0.349 | 0.089 | 0.152 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
1 spectrum |
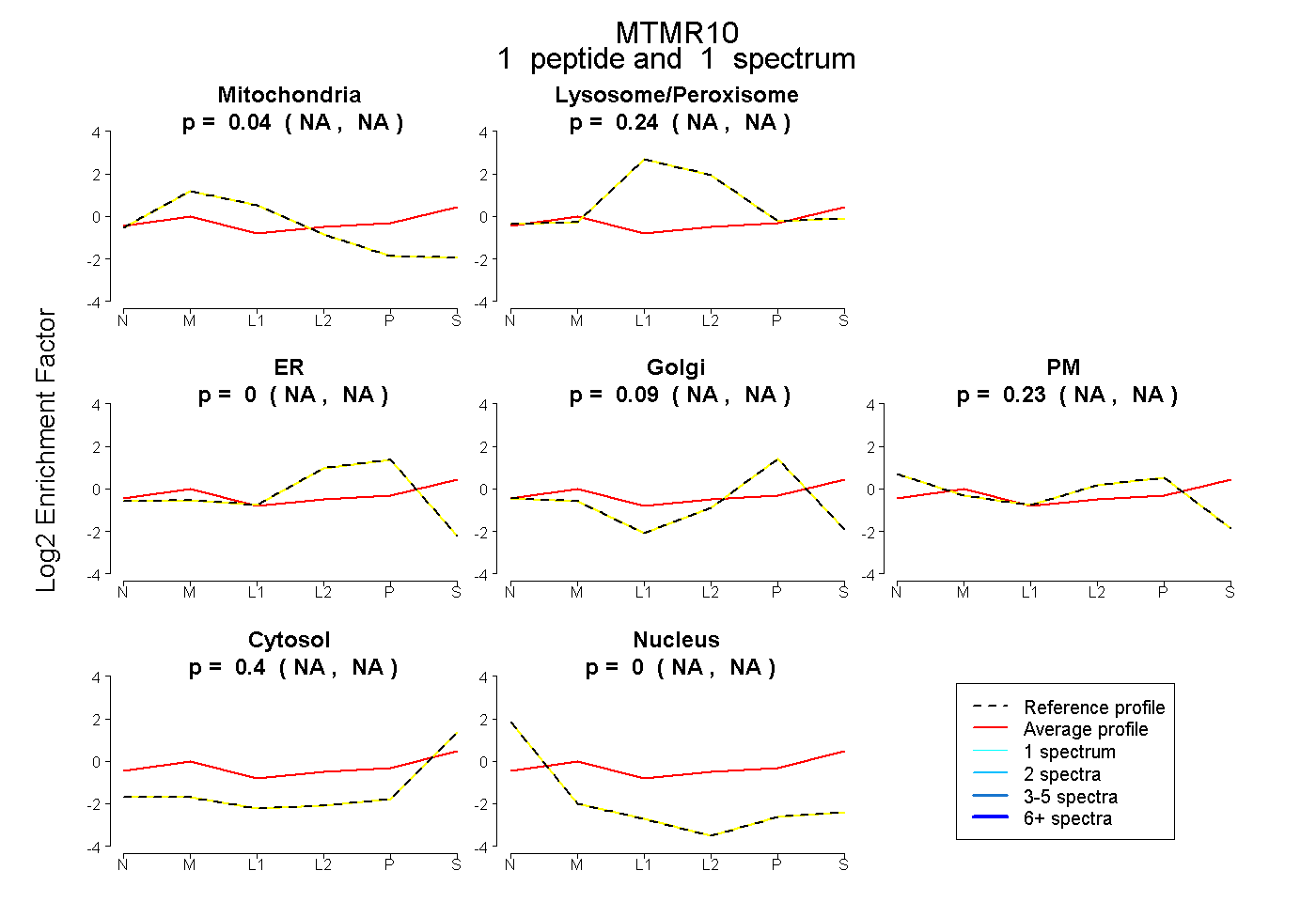 |
0.042 NA | NA |
0.236 NA | NA |
0.000 NA | NA |
0.092 NA | NA |
0.225 NA | NA |
0.404 NA | NA |
0.000 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
6 spectra |
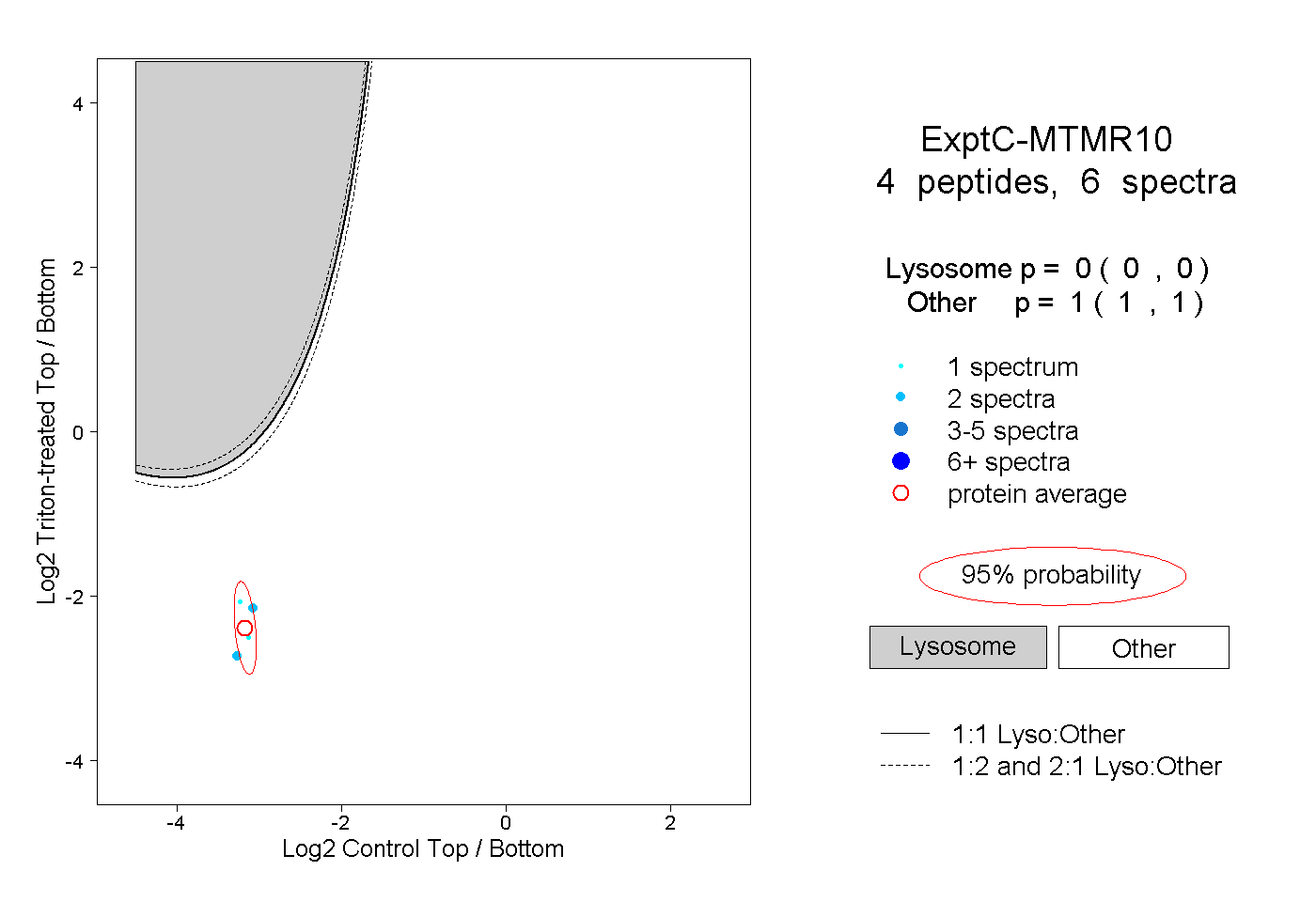 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |