peptides
spectra
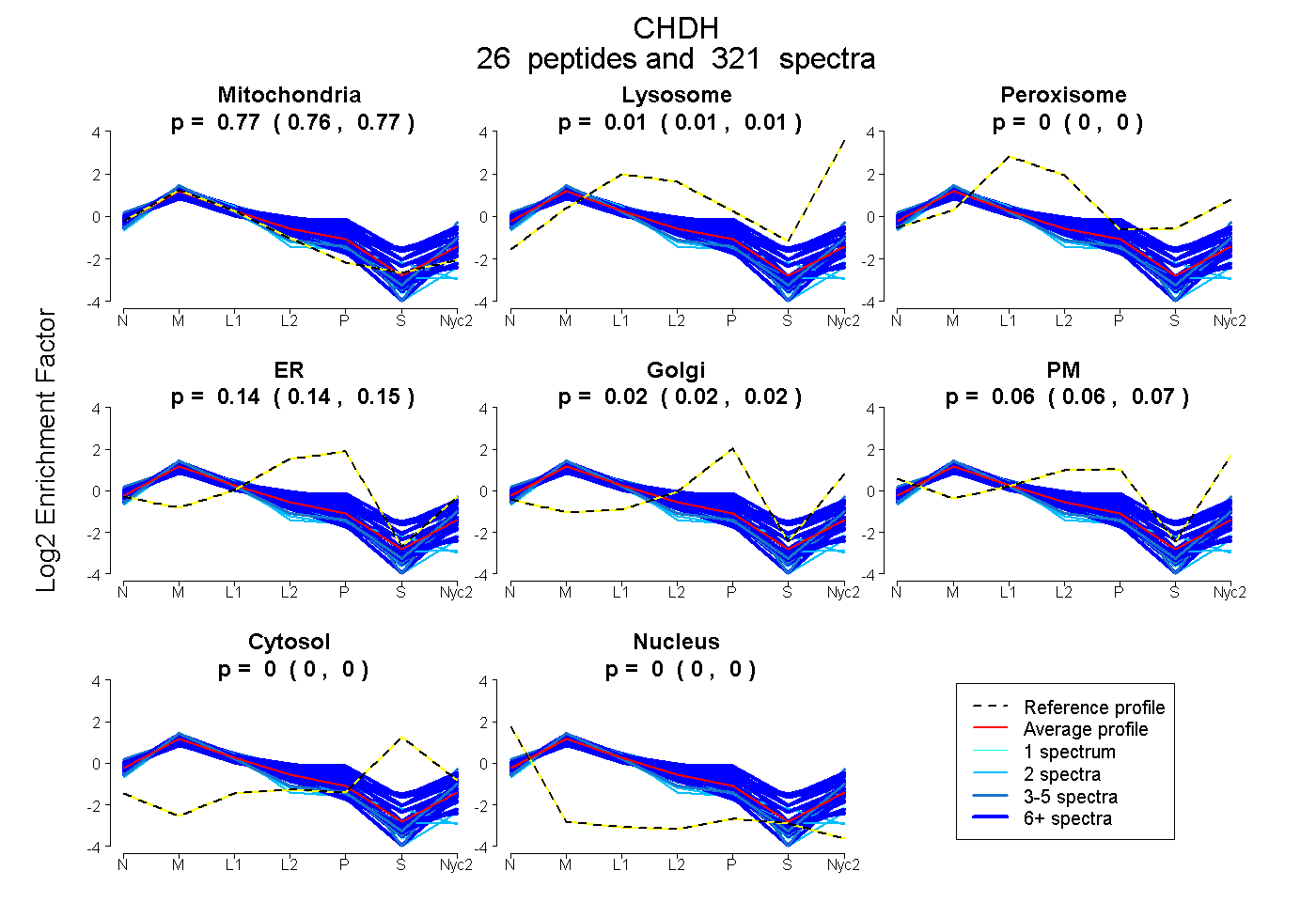
0.764 | 0.768
0.008 | 0.012
0.000 | 0.000
0.138 | 0.147
0.015 | 0.022
0.056 | 0.066
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
321 spectra |
 |
0.766 0.764 | 0.768 |
0.011 0.008 | 0.012 |
0.000 0.000 | 0.000 |
0.143 0.138 | 0.147 |
0.019 0.015 | 0.022 |
0.062 0.056 | 0.066 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 19 spectra, ATSVGWLK | 0.855 | 0.000 | 0.000 | 0.104 | 0.000 | 0.040 | 0.000 | 0.000 | ||
| 3 spectra, YNWYYHTEAQPGLDGR | 0.825 | 0.067 | 0.000 | 0.000 | 0.109 | 0.000 | 0.000 | 0.000 | ||
| 3 spectra, ELQPGSHVQSDK | 0.536 | 0.000 | 0.000 | 0.027 | 0.000 | 0.437 | 0.000 | 0.000 | ||
| 16 spectra, EIFAQEAFAPFR | 0.876 | 0.000 | 0.000 | 0.078 | 0.000 | 0.045 | 0.000 | 0.000 | ||
| 6 spectra, VWGGSSSLNAMVYIR | 0.508 | 0.000 | 0.154 | 0.007 | 0.251 | 0.080 | 0.000 | 0.000 | ||
| 21 spectra, TNHPLHQAFLQAAR | 0.683 | 0.000 | 0.000 | 0.317 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, STNPQDHPMINPNYLSTETDVEDFR | 0.975 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.025 | ||
| 8 spectra, GGDGPLHVSR | 0.609 | 0.000 | 0.113 | 0.000 | 0.197 | 0.081 | 0.000 | 0.000 | ||
| 2 spectra, AADVIK | 0.957 | 0.000 | 0.000 | 0.031 | 0.000 | 0.000 | 0.000 | 0.012 | ||
| 5 spectra, EIDAFVR | 0.846 | 0.005 | 0.000 | 0.000 | 0.069 | 0.080 | 0.000 | 0.000 | ||
| 6 spectra, LTEDPNHR | 0.696 | 0.006 | 0.012 | 0.099 | 0.119 | 0.069 | 0.000 | 0.000 | ||
| 11 spectra, FTGDGATAHLETGGFIR | 0.717 | 0.031 | 0.000 | 0.077 | 0.053 | 0.122 | 0.000 | 0.000 | ||
| 20 spectra, VIGVENLR | 0.782 | 0.000 | 0.000 | 0.000 | 0.000 | 0.218 | 0.000 | 0.000 | ||
| 1 spectrum, DGQSHK | 0.806 | 0.000 | 0.000 | 0.194 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, GCPALGDENVPVYKPQTLDTQR | 0.921 | 0.000 | 0.000 | 0.056 | 0.000 | 0.000 | 0.023 | 0.000 | ||
| 23 spectra, KPTQQEAYQVHVGTMR | 0.869 | 0.000 | 0.000 | 0.131 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 33 spectra, GHAEDYNR | 0.492 | 0.026 | 0.104 | 0.000 | 0.110 | 0.206 | 0.062 | 0.000 | ||
| 9 spectra, VLLLEAGPK | 0.550 | 0.017 | 0.148 | 0.000 | 0.110 | 0.083 | 0.092 | 0.000 | ||
| 19 spectra, VLFEGTR | 0.879 | 0.029 | 0.000 | 0.000 | 0.038 | 0.054 | 0.000 | 0.000 | ||
| 20 spectra, MGQPSDPTAVVDQQTR | 0.564 | 0.000 | 0.166 | 0.038 | 0.174 | 0.000 | 0.059 | 0.000 | ||
| 6 spectra, DLLMGSK | 0.868 | 0.000 | 0.000 | 0.108 | 0.024 | 0.000 | 0.000 | 0.000 | ||
| 17 spectra, VLYWPR | 0.876 | 0.016 | 0.000 | 0.003 | 0.000 | 0.105 | 0.000 | 0.000 | ||
| 31 spectra, AEVQTLVSR | 0.794 | 0.000 | 0.000 | 0.122 | 0.000 | 0.084 | 0.000 | 0.000 | ||
| 12 spectra, QGAEGWDYAHCLPYFR | 0.826 | 0.000 | 0.000 | 0.174 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 19 spectra, HELGANMYR | 0.462 | 0.000 | 0.187 | 0.000 | 0.340 | 0.000 | 0.011 | 0.000 | ||
| 7 spectra, AVGVEYIK | 0.814 | 0.000 | 0.054 | 0.114 | 0.000 | 0.000 | 0.018 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
213 spectra |
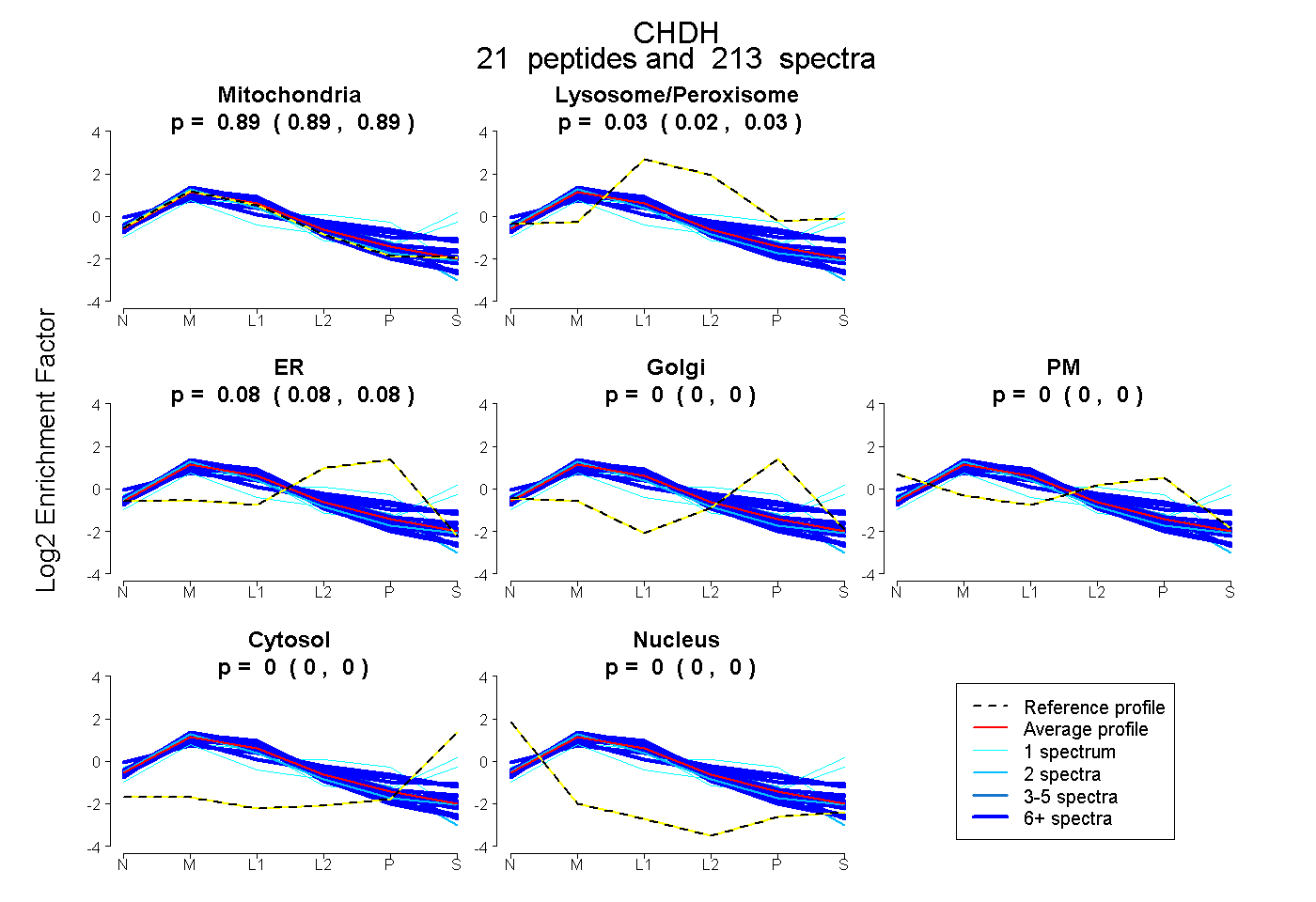 |
0.893 0.890 | 0.895 |
0.025 0.023 | 0.028 |
0.082 0.079 | 0.084 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
933 spectra |
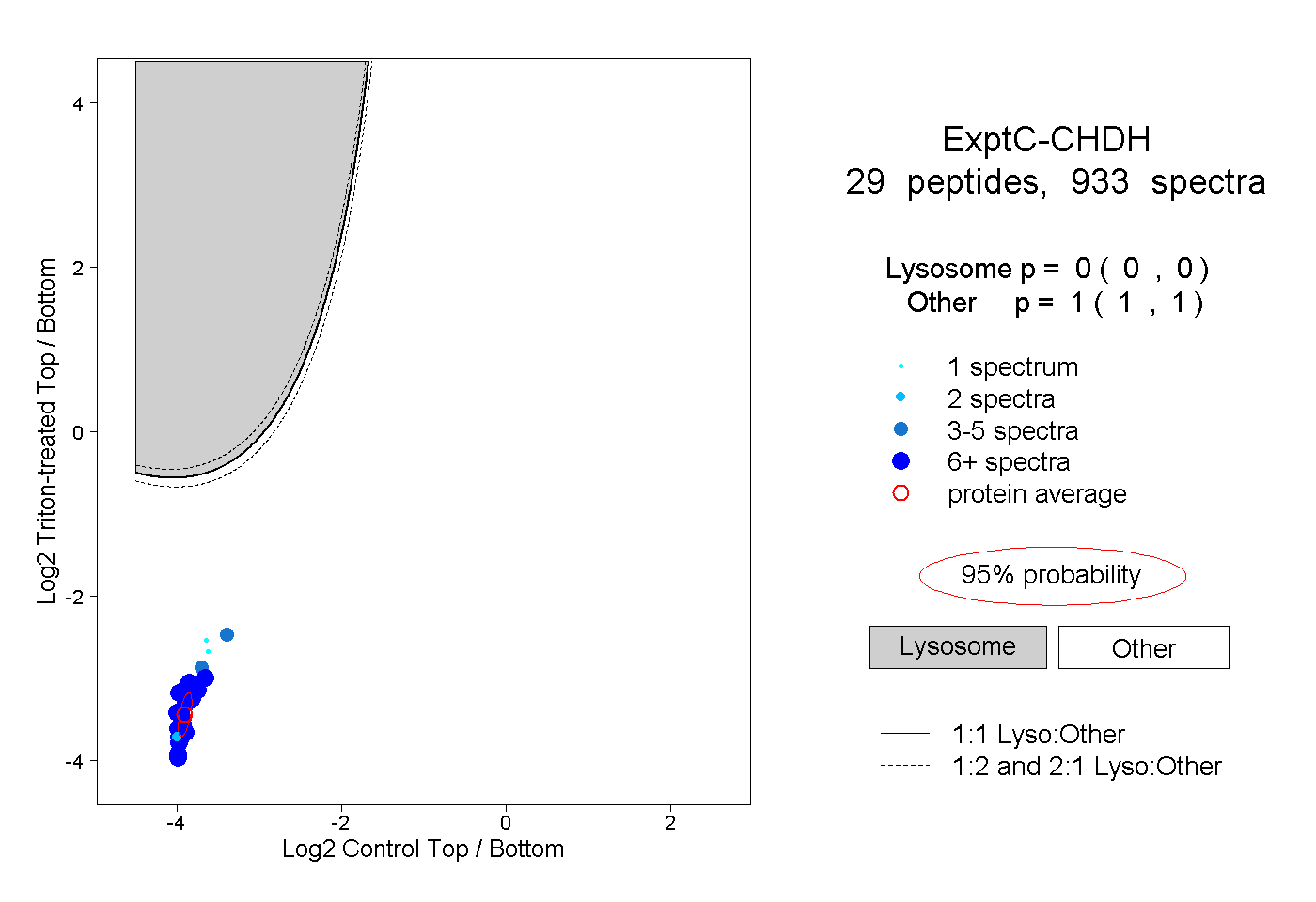 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
78 spectra |
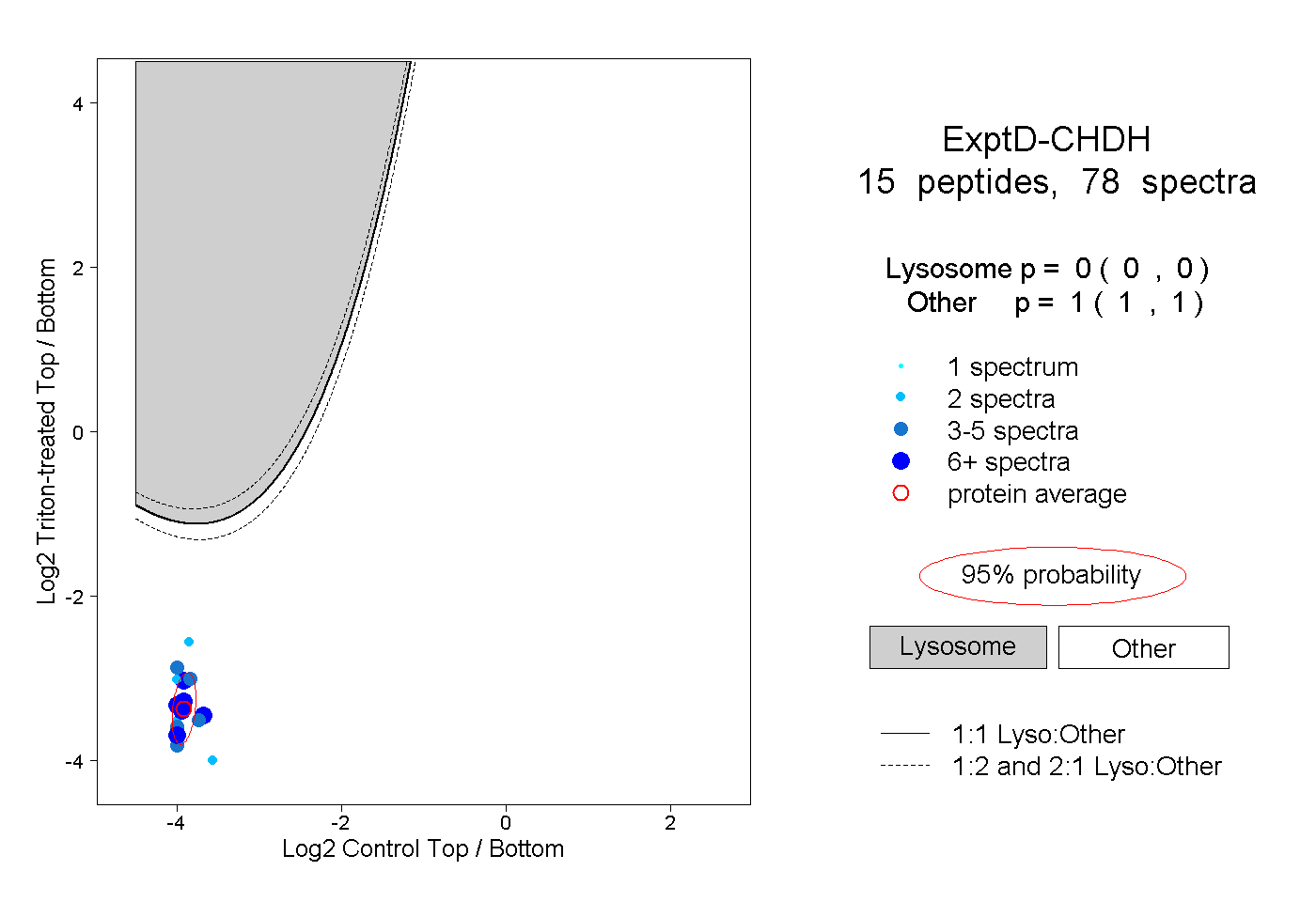 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |