peptides
spectra
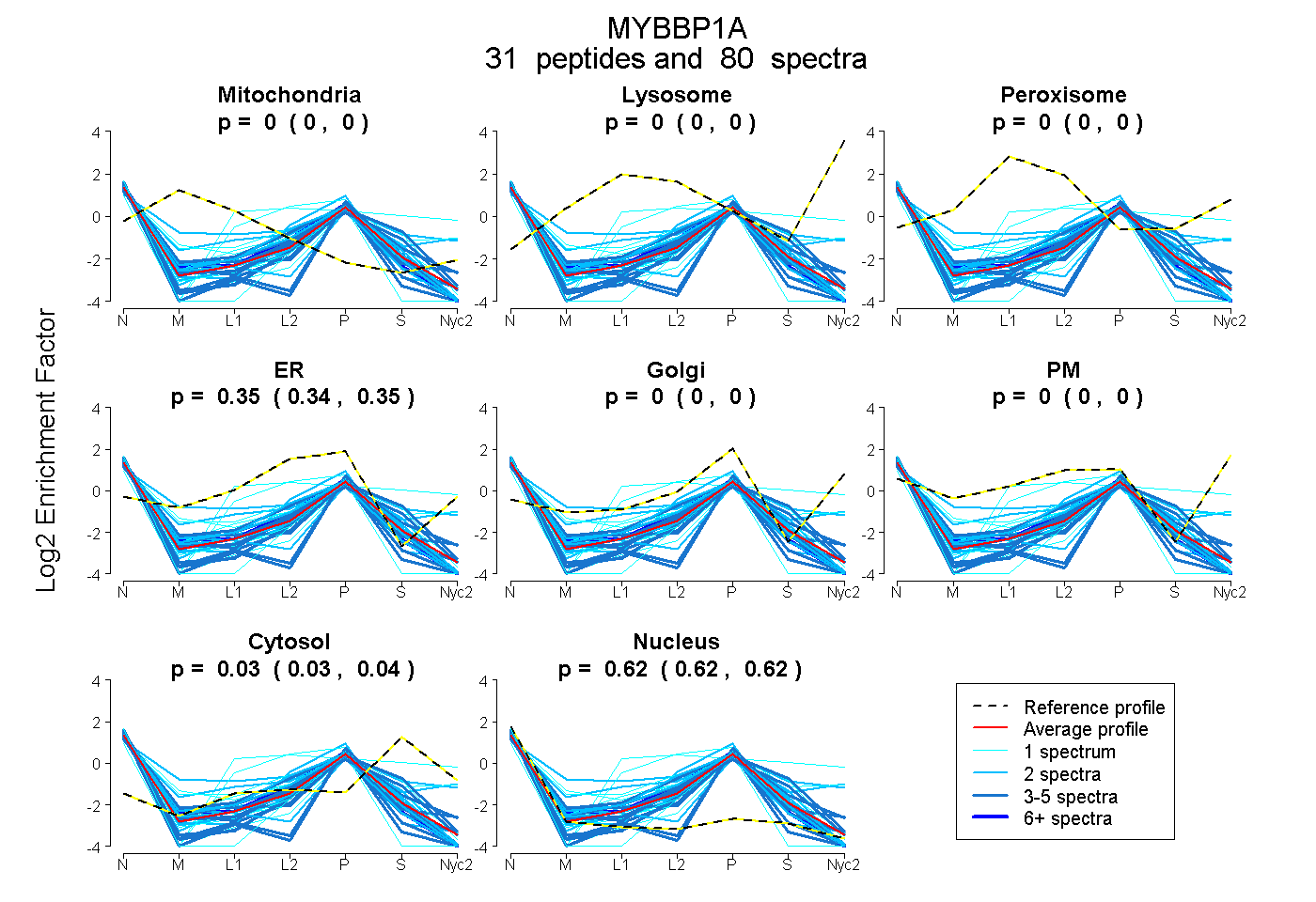
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.342 | 0.350
0.000 | 0.000
0.000 | 0.000
0.028 | 0.038
0.616 | 0.624
peptides
spectra
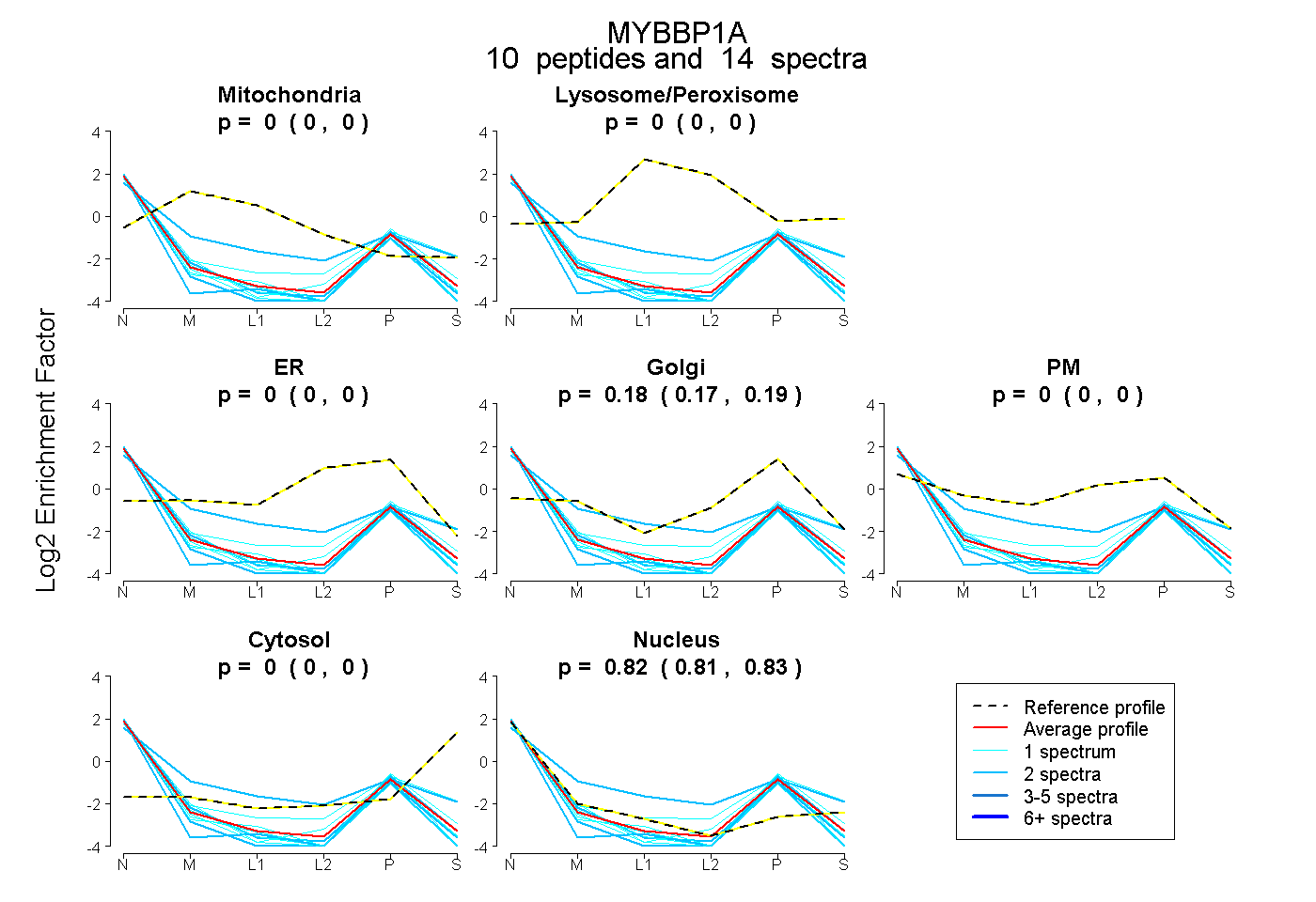
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.167 | 0.188
0.000 | 0.000
0.000 | 0.000
0.809 | 0.832
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
80 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.346 0.342 | 0.350 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.033 0.028 | 0.038 |
0.621 0.616 | 0.624 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
14 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.179 0.167 | 0.188 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.821 0.809 | 0.832 |
| 1 spectrum, SPSLLQSGIR | 0.000 | 0.000 | 0.000 | 0.169 | 0.000 | 0.000 | 0.831 | |||
| 1 spectrum, LLEYLR | 0.000 | 0.000 | 0.000 | 0.079 | 0.000 | 0.000 | 0.921 | |||
| 2 spectra, ALDLIEVLVTK | 0.000 | 0.000 | 0.000 | 0.063 | 0.000 | 0.000 | 0.937 | |||
| 1 spectrum, LVQLADMLLK | 0.000 | 0.000 | 0.000 | 0.215 | 0.000 | 0.000 | 0.785 | |||
| 1 spectrum, ELEAQSSETR | 0.000 | 0.000 | 0.000 | 0.322 | 0.000 | 0.000 | 0.678 | |||
| 1 spectrum, LPDVALNLLR | 0.000 | 0.000 | 0.000 | 0.130 | 0.000 | 0.000 | 0.870 | |||
| 2 spectra, LSLVSR | 0.000 | 0.000 | 0.000 | 0.095 | 0.000 | 0.000 | 0.905 | |||
| 1 spectrum, EVLEEGLLK | 0.000 | 0.000 | 0.000 | 0.139 | 0.000 | 0.000 | 0.861 | |||
| 2 spectra, LITGLGVGR | 0.000 | 0.000 | 0.000 | 0.136 | 0.000 | 0.000 | 0.864 | |||
| 2 spectra, NVANVTPLTAQQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.480 | 0.000 | 0.520 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
17 spectra |
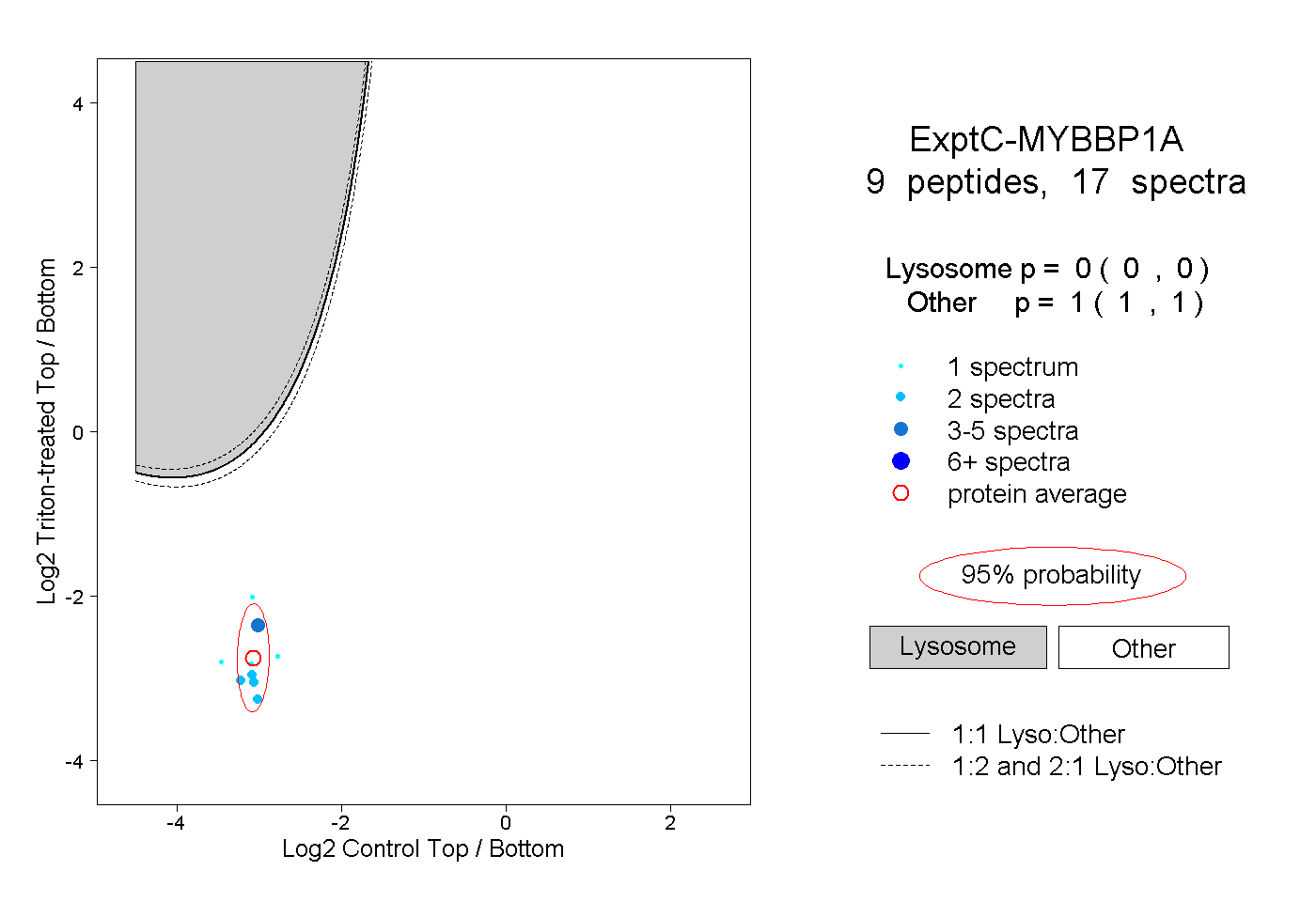 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
3 spectra |
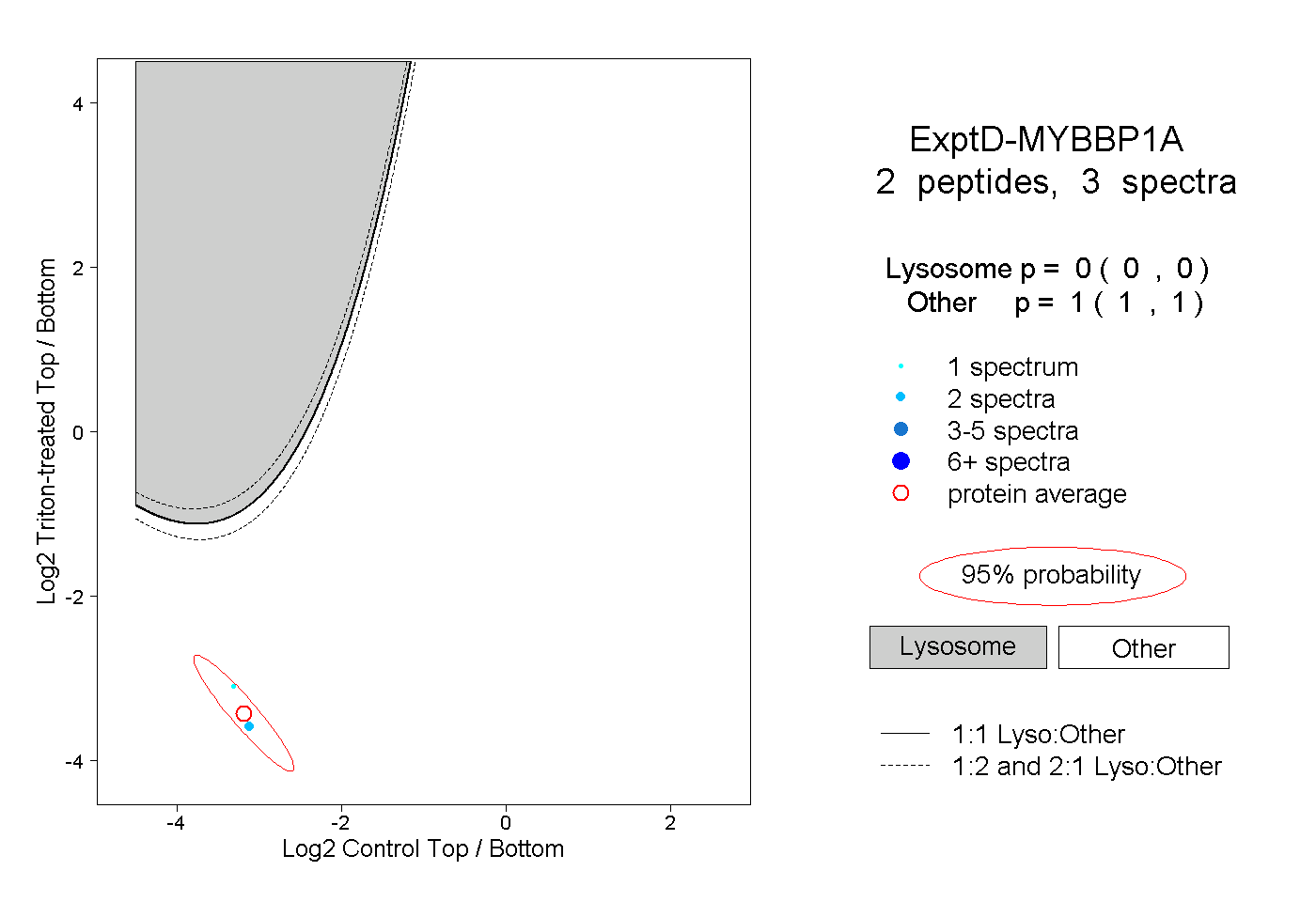 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |