peptides
spectra
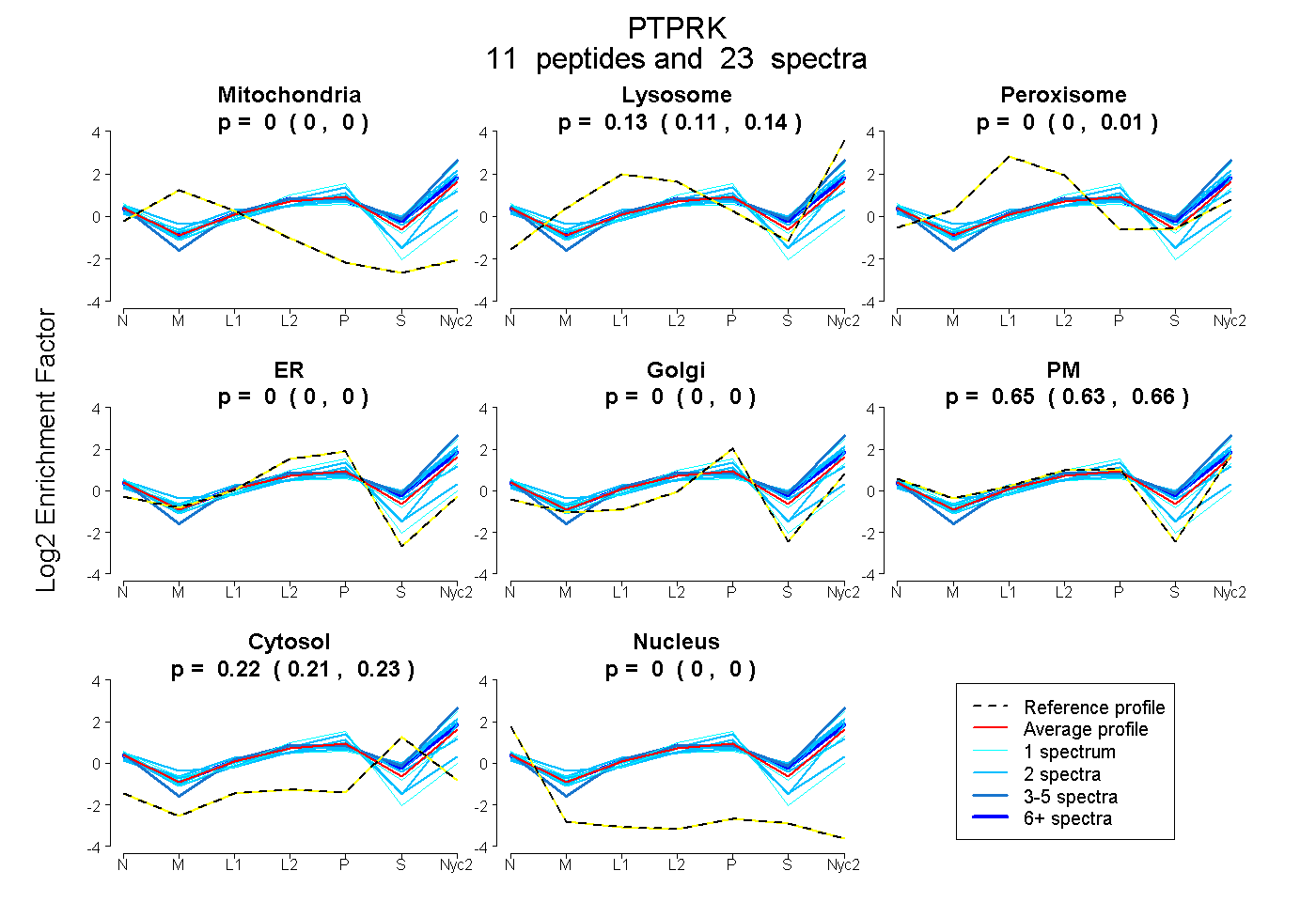
0.000 | 0.000
0.108 | 0.142
0.000 | 0.007
0.000 | 0.000
0.000 | 0.000
0.629 | 0.662
0.213 | 0.232
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
23 spectra |
 |
0.000 0.000 | 0.000 |
0.129 0.108 | 0.142 |
0.000 0.000 | 0.007 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.647 0.629 | 0.662 |
0.224 0.213 | 0.232 |
0.000 0.000 | 0.000 |
| 6 spectra, CVTQSER | 0.000 | 0.221 | 0.001 | 0.000 | 0.000 | 0.528 | 0.250 | 0.000 | ||
| 2 spectra, IAEIQAR | 0.000 | 0.205 | 0.000 | 0.000 | 0.000 | 0.513 | 0.282 | 0.000 | ||
| 2 spectra, GYNEIR | 0.000 | 0.067 | 0.147 | 0.000 | 0.094 | 0.470 | 0.222 | 0.000 | ||
| 1 spectrum, VTCVEMEPLAEYVVR | 0.000 | 0.000 | 0.000 | 0.594 | 0.000 | 0.299 | 0.048 | 0.059 | ||
| 1 spectrum, GLNPGTLNILVR | 0.000 | 0.241 | 0.000 | 0.000 | 0.000 | 0.551 | 0.209 | 0.000 | ||
| 2 spectra, MILTNPEGR | 0.000 | 0.305 | 0.000 | 0.000 | 0.000 | 0.418 | 0.277 | 0.000 | ||
| 2 spectra, LLDVPR | 0.000 | 0.064 | 0.000 | 0.000 | 0.092 | 0.759 | 0.086 | 0.000 | ||
| 3 spectra, VLLTRPGEGGTGLPGPPLITR | 0.000 | 0.283 | 0.000 | 0.000 | 0.000 | 0.483 | 0.234 | 0.000 | ||
| 1 spectrum, QNVVDVFHAVK | 0.000 | 0.011 | 0.034 | 0.000 | 0.000 | 0.743 | 0.212 | 0.000 | ||
| 2 spectra, LQAEDCSIACLPR | 0.048 | 0.000 | 0.000 | 0.280 | 0.011 | 0.499 | 0.154 | 0.008 | ||
| 1 spectrum, GSGVSNFAQLIVR | 0.000 | 0.333 | 0.000 | 0.000 | 0.000 | 0.409 | 0.258 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
1 spectrum |
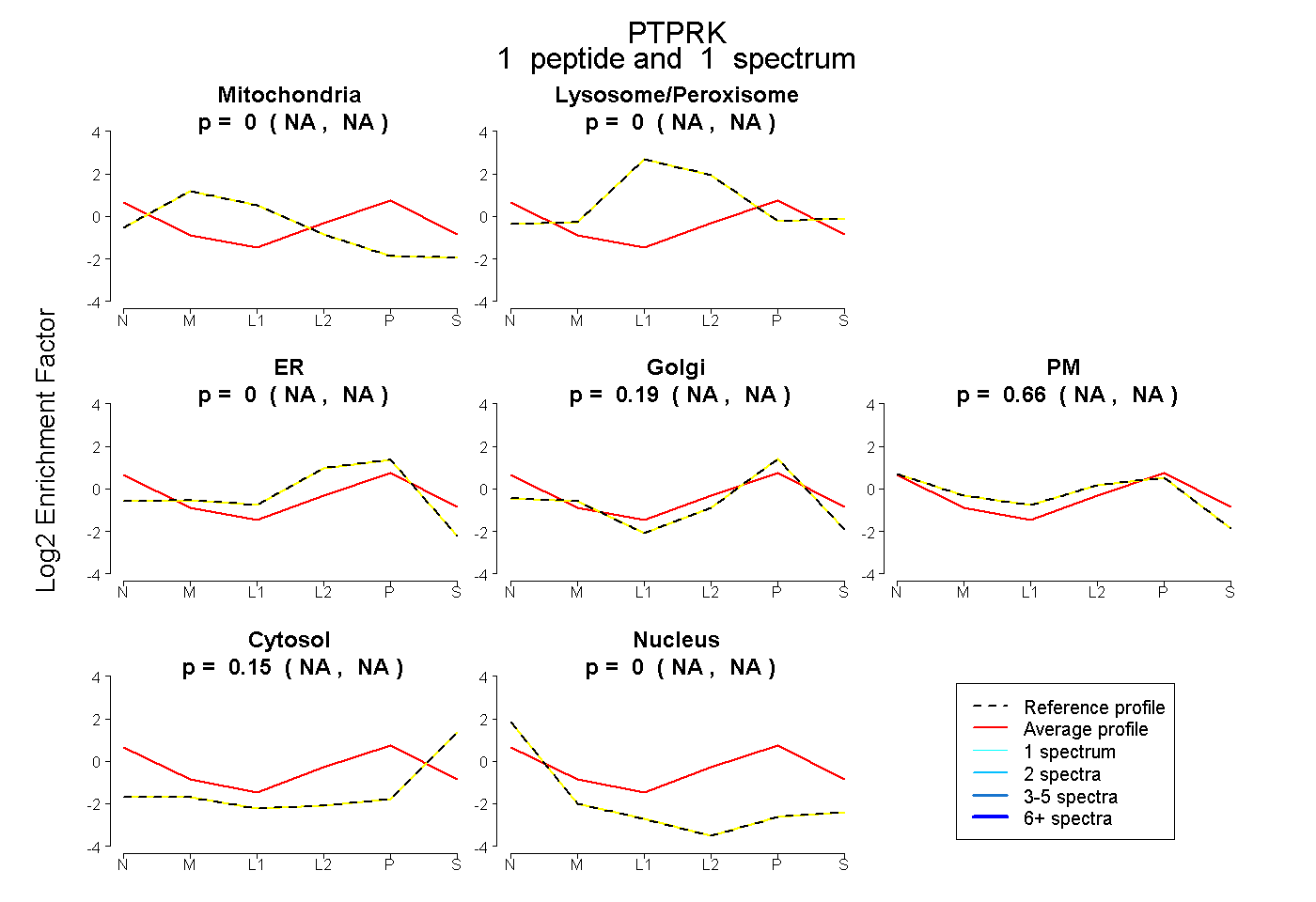 |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.188 NA | NA |
0.657 NA | NA |
0.155 NA | NA |
0.000 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
26 spectra |
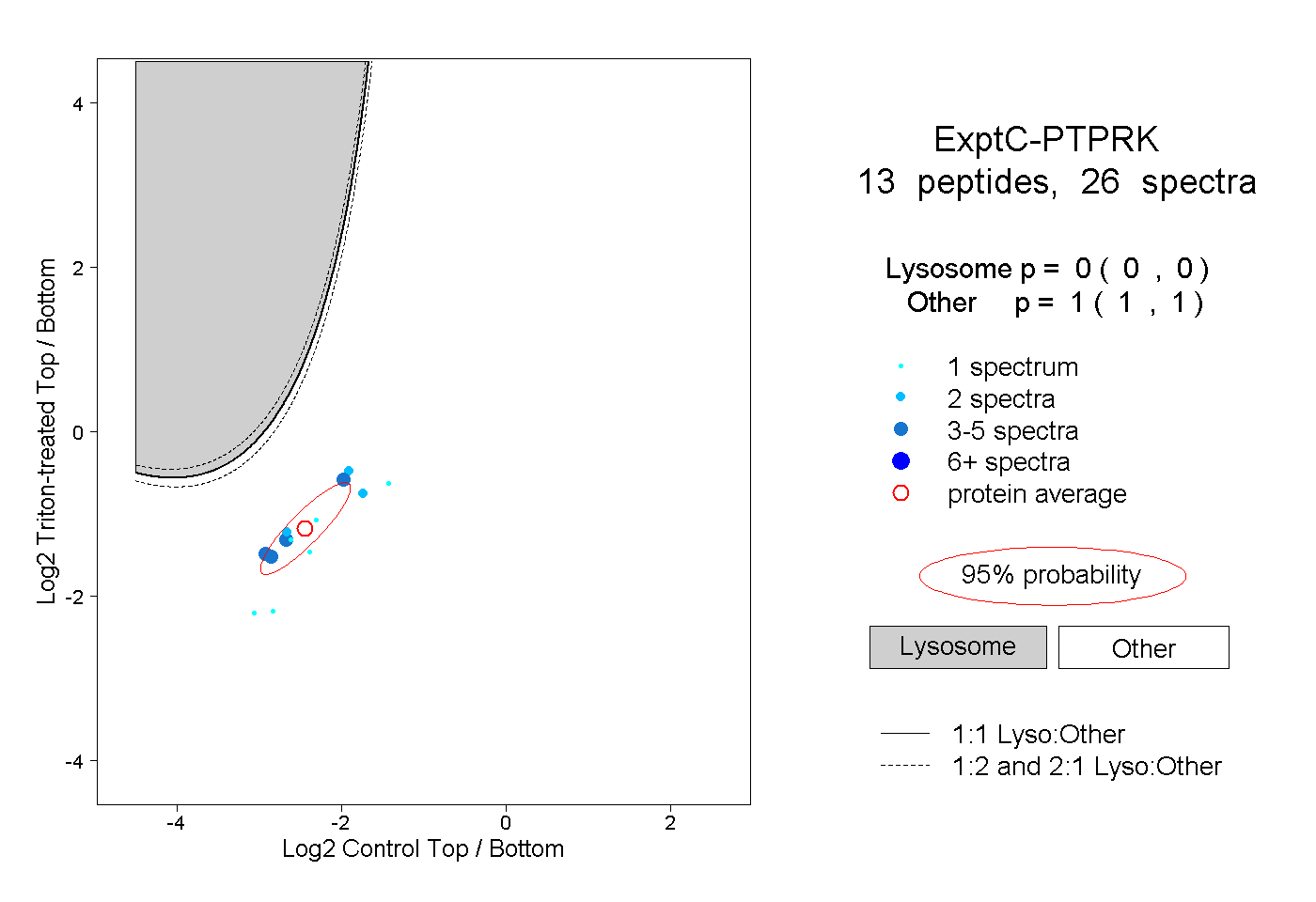 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
1 spectrum |
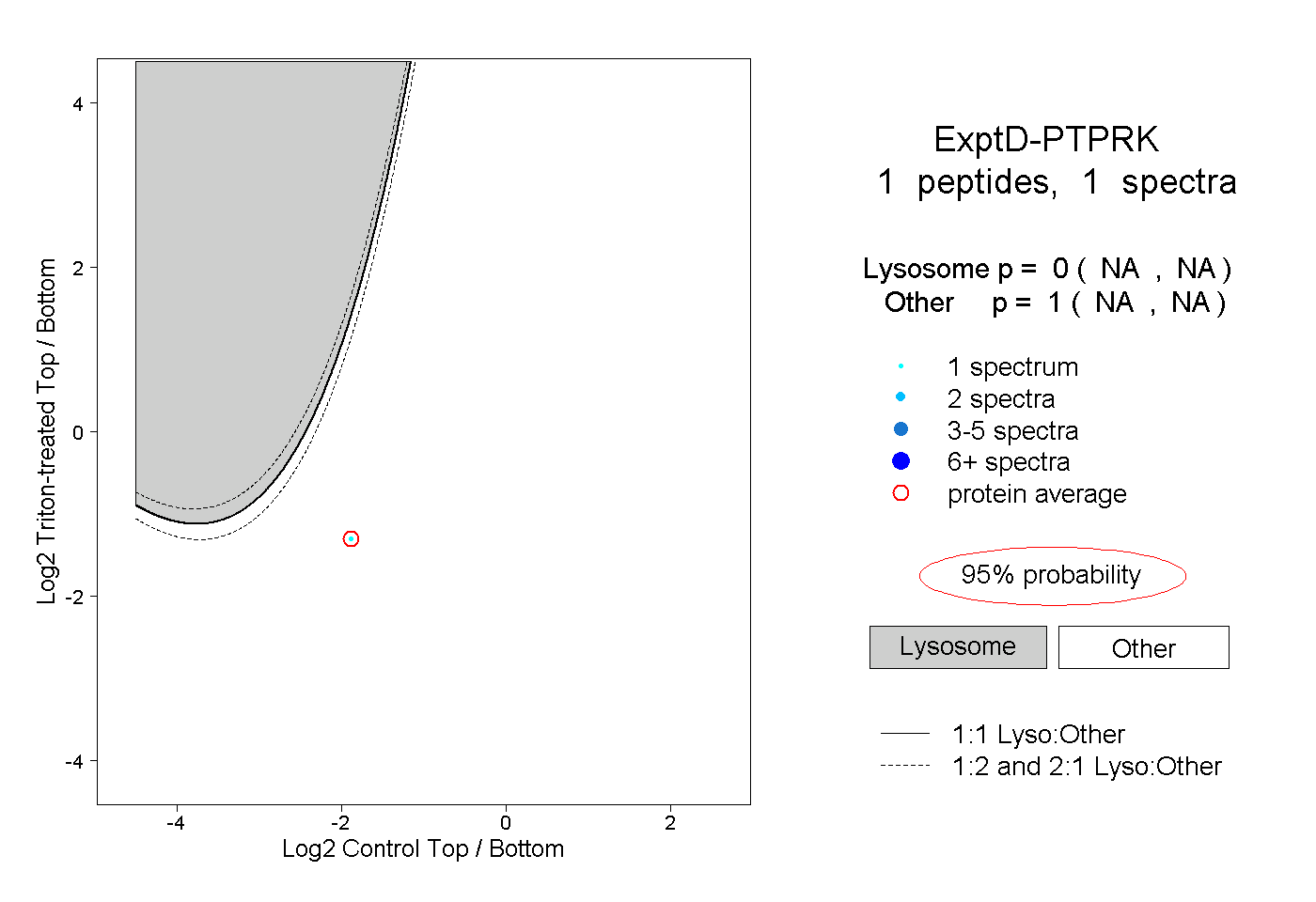 |
0.000 NA | NA |
1.000 NA | NA |