peptides
spectra
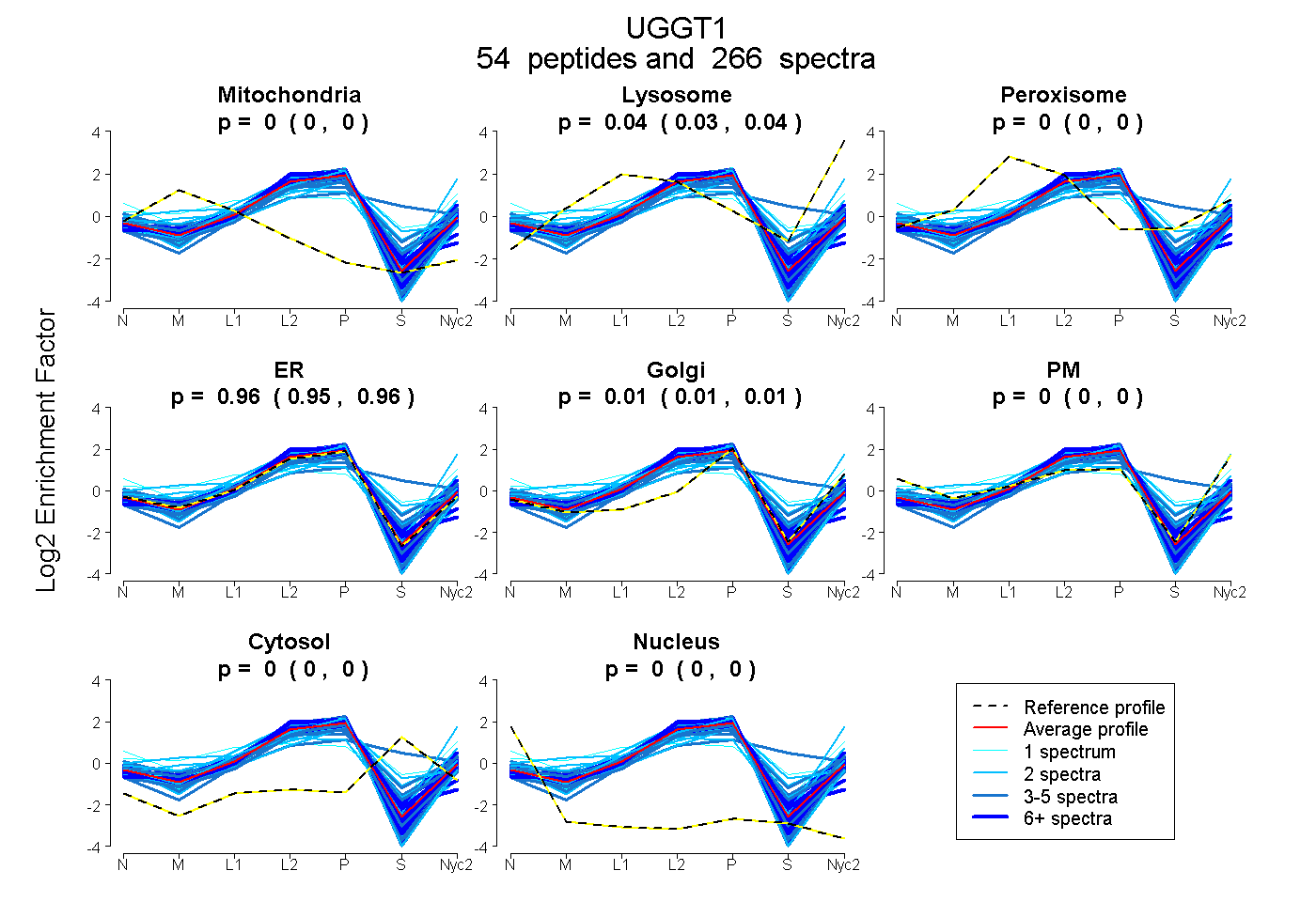
0.000 | 0.000
0.035 | 0.037
0.000 | 0.000
0.953 | 0.957
0.007 | 0.011
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
peptides
spectra
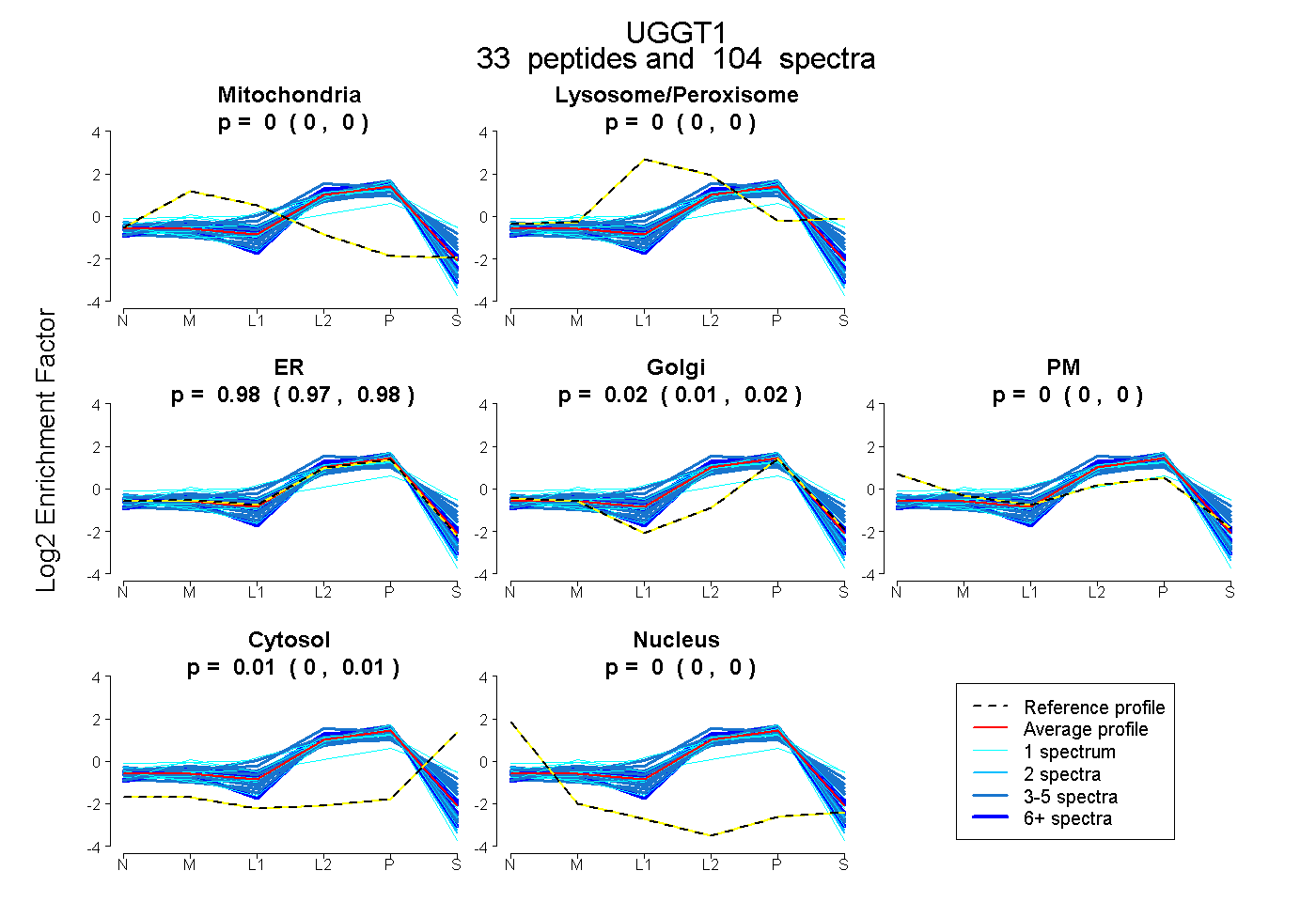
0.000 | 0.000
0.000 | 0.000
0.971 | 0.980
0.012 | 0.024
0.000 | 0.000
0.002 | 0.008
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
266 spectra |
 |
0.000 0.000 | 0.000 |
0.036 0.035 | 0.037 |
0.000 0.000 | 0.000 |
0.955 0.953 | 0.957 |
0.009 0.007 | 0.011 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
104 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.976 0.971 | 0.980 |
0.019 0.012 | 0.024 |
0.000 0.000 | 0.000 |
0.005 0.002 | 0.008 |
0.000 0.000 | 0.000 |
| 4 spectra, LGIEGLSLHNILK | 0.000 | 0.226 | 0.654 | 0.120 | 0.000 | 0.000 | 0.000 | |||
| 10 spectra, INYVFR | 0.000 | 0.077 | 0.835 | 0.089 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, ILETTTFFQR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, SYYDAILEAAFR | 0.000 | 0.000 | 0.827 | 0.173 | 0.000 | 0.000 | 0.000 | |||
| 9 spectra, IMMLSVLK | 0.000 | 0.056 | 0.944 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, VDALLSAQPK | 0.000 | 0.371 | 0.404 | 0.152 | 0.000 | 0.073 | 0.000 | |||
| 1 spectrum, SGYWASHLAGR | 0.000 | 0.141 | 0.817 | 0.005 | 0.000 | 0.036 | 0.000 | |||
| 1 spectrum, IVPEWQDYDQEIK | 0.074 | 0.126 | 0.800 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, AEVEENQK | 0.000 | 0.000 | 0.995 | 0.000 | 0.000 | 0.000 | 0.005 | |||
| 4 spectra, QLLYDAIK | 0.000 | 0.069 | 0.761 | 0.065 | 0.000 | 0.105 | 0.000 | |||
| 1 spectrum, VWQLQDLSFQTAAR | 0.000 | 0.000 | 0.928 | 0.025 | 0.000 | 0.047 | 0.000 | |||
| 1 spectrum, SPAISWVNNLEVDSR | 0.000 | 0.000 | 0.802 | 0.198 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, EQLDPDELETITMHK | 0.000 | 0.000 | 0.967 | 0.000 | 0.000 | 0.033 | 0.000 | |||
| 1 spectrum, AITTSLTTK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, FCLSLR | 0.000 | 0.000 | 0.875 | 0.125 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, LSDMPLK | 0.000 | 0.000 | 0.858 | 0.053 | 0.000 | 0.089 | 0.000 | |||
| 1 spectrum, AIWAALQTQTSNSAK | 0.000 | 0.310 | 0.000 | 0.348 | 0.229 | 0.113 | 0.000 | |||
| 3 spectra, TAVSAQLR | 0.000 | 0.000 | 0.893 | 0.015 | 0.000 | 0.092 | 0.000 | |||
| 1 spectrum, FLFVDADQIVR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, ISMINNPSR | 0.000 | 0.000 | 0.877 | 0.123 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, FLSPLQQNLLK | 0.000 | 0.000 | 0.979 | 0.000 | 0.021 | 0.000 | 0.000 | |||
| 3 spectra, NYLSPTFK | 0.000 | 0.242 | 0.396 | 0.326 | 0.000 | 0.036 | 0.000 | |||
| 2 spectra, LEAAVR | 0.000 | 0.001 | 0.949 | 0.036 | 0.000 | 0.014 | 0.000 | |||
| 1 spectrum, VEEDVASDLVMK | 0.074 | 0.021 | 0.905 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, ANPGAWILR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, VMEGLHR | 0.000 | 0.187 | 0.813 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, EISDSSTPVSR | 0.000 | 0.000 | 0.822 | 0.178 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, ILAAPVELALVVMK | 0.000 | 0.000 | 0.978 | 0.000 | 0.000 | 0.022 | 0.000 | |||
| 4 spectra, SDDIYR | 0.000 | 0.000 | 0.871 | 0.129 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, IEYQFFEDK | 0.000 | 0.000 | 0.983 | 0.017 | 0.000 | 0.000 | 0.000 | |||
| 8 spectra, EVFESSR | 0.000 | 0.000 | 0.882 | 0.118 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, TAAIANSMNYLTK | 0.000 | 0.293 | 0.385 | 0.259 | 0.000 | 0.063 | 0.000 | |||
| 9 spectra, MDFILSHALYCR | 0.012 | 0.049 | 0.900 | 0.040 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
359 spectra |
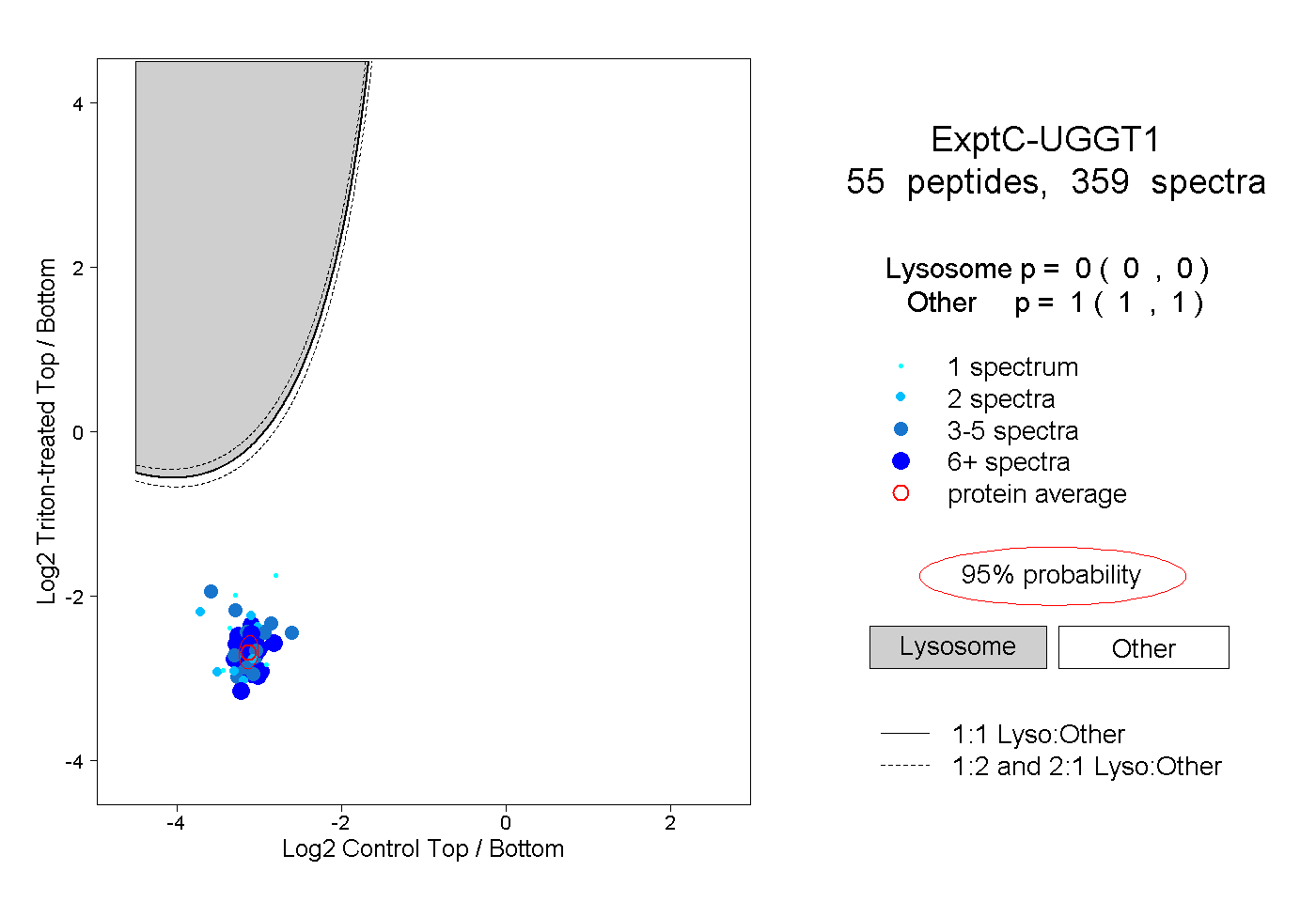 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
56 spectra |
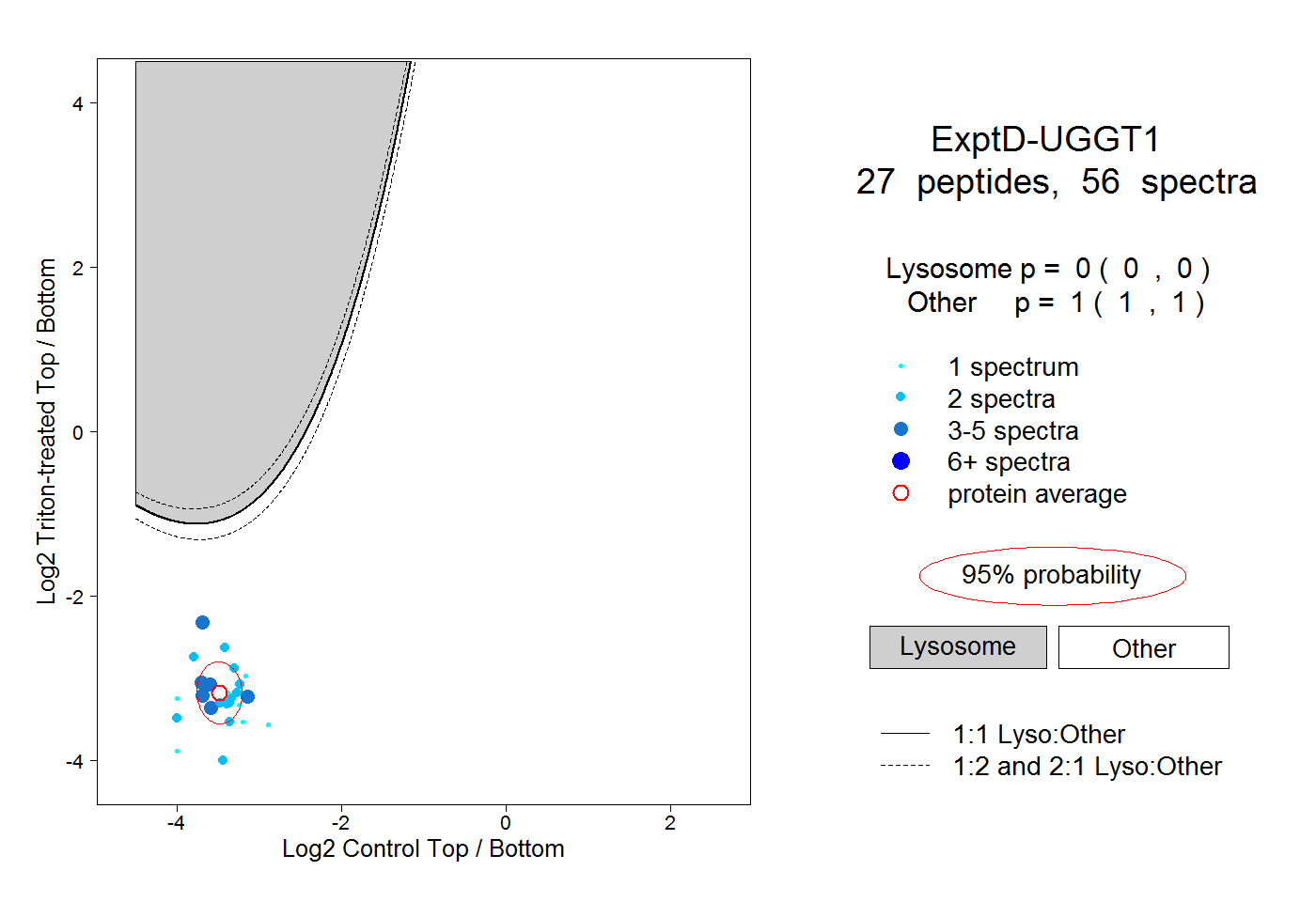 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |