peptides
spectra
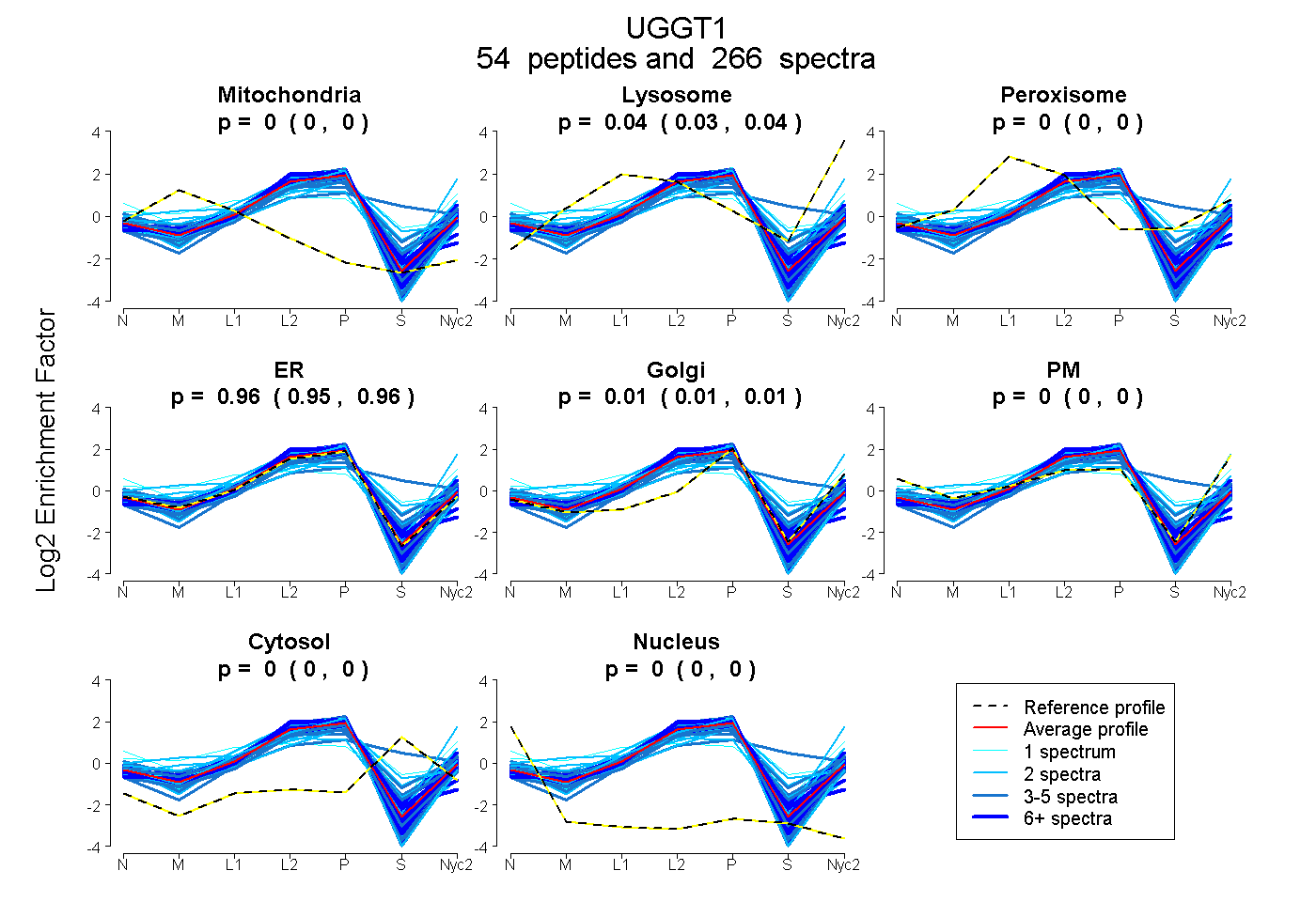
0.000 | 0.000
0.035 | 0.037
0.000 | 0.000
0.953 | 0.957
0.007 | 0.011
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
266 spectra |
 |
0.000 0.000 | 0.000 |
0.036 0.035 | 0.037 |
0.000 0.000 | 0.000 |
0.955 0.953 | 0.957 |
0.009 0.007 | 0.011 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 6 spectra, IIWGYK | 0.000 | 0.004 | 0.000 | 0.892 | 0.000 | 0.104 | 0.000 | 0.000 | ||
| 3 spectra, HYISNPR | 0.000 | 0.000 | 0.100 | 0.740 | 0.000 | 0.095 | 0.065 | 0.000 | ||
| 16 spectra, INYVFR | 0.000 | 0.106 | 0.000 | 0.793 | 0.051 | 0.000 | 0.049 | 0.000 | ||
| 6 spectra, ILETTTFFQR | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 5 spectra, SYYDAILEAAFR | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 10 spectra, IMMLSVLK | 0.000 | 0.055 | 0.000 | 0.901 | 0.031 | 0.000 | 0.012 | 0.000 | ||
| 3 spectra, HLVESTNEMAPLK | 0.000 | 0.000 | 0.000 | 0.823 | 0.000 | 0.160 | 0.018 | 0.000 | ||
| 2 spectra, DISQNFPTK | 0.000 | 0.000 | 0.223 | 0.438 | 0.248 | 0.000 | 0.091 | 0.000 | ||
| 3 spectra, SGYWASHLAGR | 0.000 | 0.108 | 0.059 | 0.397 | 0.000 | 0.000 | 0.436 | 0.000 | ||
| 2 spectra, IVPEWQDYDQEIK | 0.018 | 0.000 | 0.151 | 0.663 | 0.115 | 0.000 | 0.052 | 0.000 | ||
| 4 spectra, FSALDSR | 0.000 | 0.086 | 0.000 | 0.906 | 0.007 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, VEHVVSVLEK | 0.000 | 0.000 | 0.041 | 0.655 | 0.038 | 0.000 | 0.266 | 0.000 | ||
| 2 spectra, QLQTLFQEEK | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, LNIQPSETDYAVDIR | 0.099 | 0.000 | 0.317 | 0.316 | 0.075 | 0.135 | 0.058 | 0.000 | ||
| 3 spectra, AEVEENQK | 0.000 | 0.062 | 0.000 | 0.938 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, DFNLDGAPYGYTPFCDSR | 0.000 | 0.000 | 0.000 | 0.977 | 0.000 | 0.000 | 0.000 | 0.023 | ||
| 2 spectra, SHIQQLR | 0.025 | 0.192 | 0.000 | 0.133 | 0.000 | 0.650 | 0.000 | 0.000 | ||
| 3 spectra, QLLYDAIK | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 6 spectra, IAAGDR | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, VWQLQDLSFQTAAR | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 3 spectra, SPAISWVNNLEVDSR | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 8 spectra, EQLDPDELETITMHK | 0.000 | 0.007 | 0.000 | 0.985 | 0.000 | 0.008 | 0.000 | 0.000 | ||
| 4 spectra, VFMNCQSK | 0.000 | 0.042 | 0.000 | 0.778 | 0.030 | 0.000 | 0.150 | 0.000 | ||
| 2 spectra, YNFQYELVQYK | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 8 spectra, WGFSGQK | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 3 spectra, AITTSLTTK | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, EGETYYDVVAVVDPVTR | 0.000 | 0.084 | 0.000 | 0.916 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, EFIPYMAK | 0.000 | 0.075 | 0.000 | 0.791 | 0.000 | 0.060 | 0.074 | 0.000 | ||
| 7 spectra, EMDGYR | 0.000 | 0.044 | 0.042 | 0.824 | 0.000 | 0.000 | 0.090 | 0.000 | ||
| 13 spectra, FCLSLR | 0.000 | 0.000 | 0.000 | 0.938 | 0.000 | 0.000 | 0.062 | 0.000 | ||
| 4 spectra, LSDMPLK | 0.000 | 0.070 | 0.000 | 0.870 | 0.000 | 0.060 | 0.000 | 0.000 | ||
| 2 spectra, AIWAALQTQTSNSAK | 0.000 | 0.000 | 0.000 | 0.952 | 0.000 | 0.048 | 0.000 | 0.000 | ||
| 7 spectra, TAVSAQLR | 0.000 | 0.000 | 0.000 | 0.972 | 0.000 | 0.028 | 0.000 | 0.000 | ||
| 1 spectrum, ELGTLHEEETQEGSQK | 0.000 | 0.011 | 0.070 | 0.667 | 0.000 | 0.000 | 0.251 | 0.000 | ||
| 5 spectra, FLFVDADQIVR | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 22 spectra, ISMINNPSR | 0.000 | 0.035 | 0.000 | 0.965 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 4 spectra, NYLSPTFK | 0.000 | 0.000 | 0.000 | 0.984 | 0.000 | 0.000 | 0.016 | 0.000 | ||
| 3 spectra, FLSPLQQNLLK | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, ILTAK | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, ELYPSLEGQLK | 0.000 | 0.000 | 0.000 | 0.968 | 0.000 | 0.000 | 0.032 | 0.000 | ||
| 6 spectra, VEEDVASDLVMK | 0.009 | 0.024 | 0.000 | 0.967 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 5 spectra, ANPGAWILR | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, DDTQVK | 0.000 | 0.000 | 0.005 | 0.180 | 0.000 | 0.727 | 0.089 | 0.000 | ||
| 10 spectra, VMEGLHR | 0.000 | 0.037 | 0.047 | 0.900 | 0.000 | 0.000 | 0.016 | 0.000 | ||
| 8 spectra, EISDSSTPVSR | 0.000 | 0.000 | 0.000 | 0.979 | 0.015 | 0.000 | 0.000 | 0.005 | ||
| 3 spectra, WLHQQTEK | 0.034 | 0.000 | 0.000 | 0.966 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 7 spectra, ILAAPVELALVVMK | 0.000 | 0.034 | 0.000 | 0.932 | 0.034 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, TIDLCNNPMTK | 0.033 | 0.033 | 0.014 | 0.743 | 0.000 | 0.176 | 0.000 | 0.000 | ||
| 4 spectra, SDDIYR | 0.000 | 0.000 | 0.131 | 0.540 | 0.000 | 0.202 | 0.127 | 0.000 | ||
| 1 spectrum, EIYDDSFIRPVTFWIVGDFDSPSGR | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 11 spectra, IEYQFFEDK | 0.000 | 0.083 | 0.000 | 0.898 | 0.000 | 0.019 | 0.000 | 0.000 | ||
| 13 spectra, EVFESSR | 0.000 | 0.149 | 0.000 | 0.657 | 0.148 | 0.000 | 0.047 | 0.000 | ||
| 2 spectra, TAAIANSMNYLTK | 0.000 | 0.213 | 0.000 | 0.774 | 0.000 | 0.013 | 0.000 | 0.000 | ||
| 10 spectra, MDFILSHALYCR | 0.000 | 0.000 | 0.010 | 0.933 | 0.000 | 0.000 | 0.057 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
104 spectra |
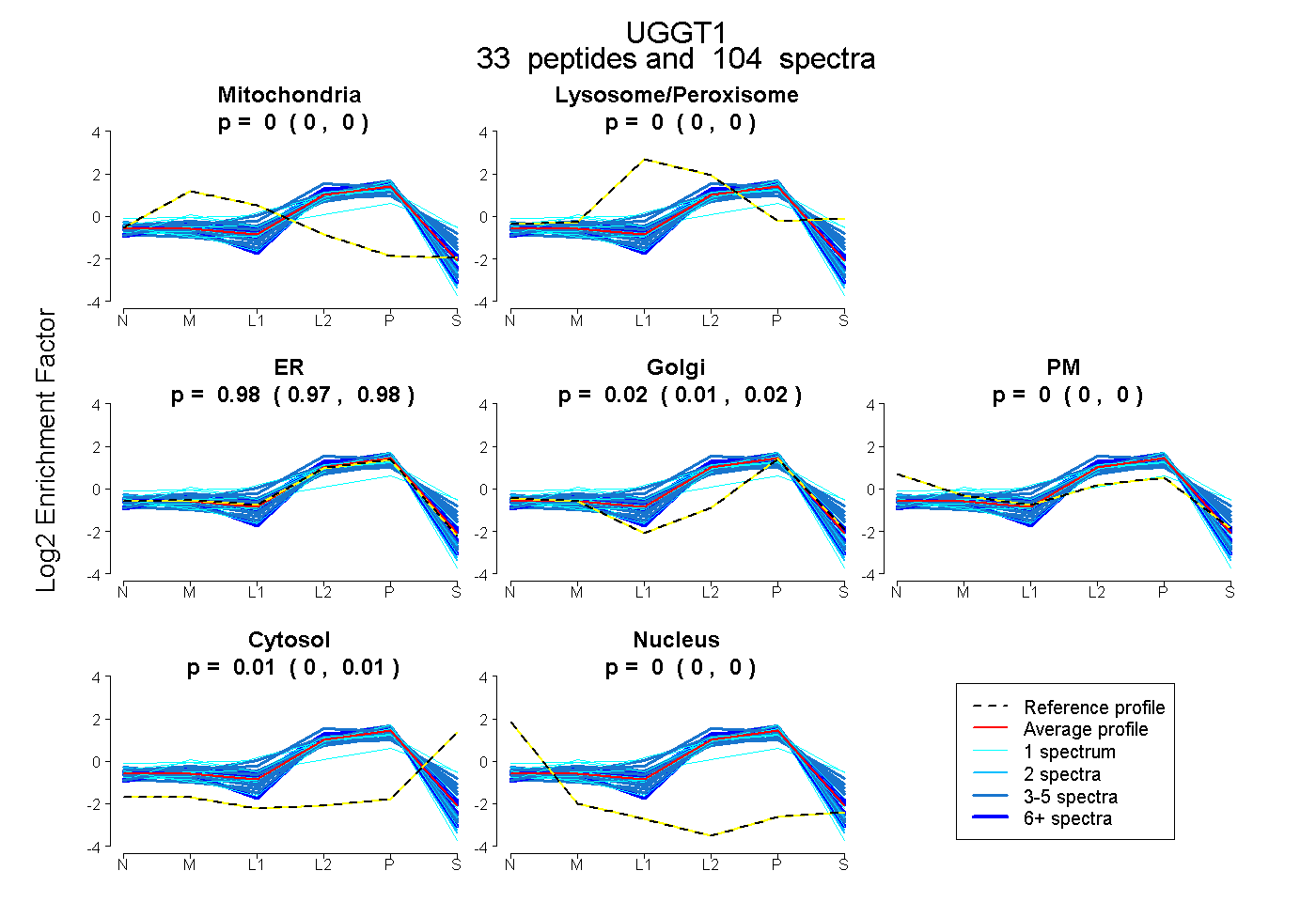 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.976 0.971 | 0.980 |
0.019 0.012 | 0.024 |
0.000 0.000 | 0.000 |
0.005 0.002 | 0.008 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
359 spectra |
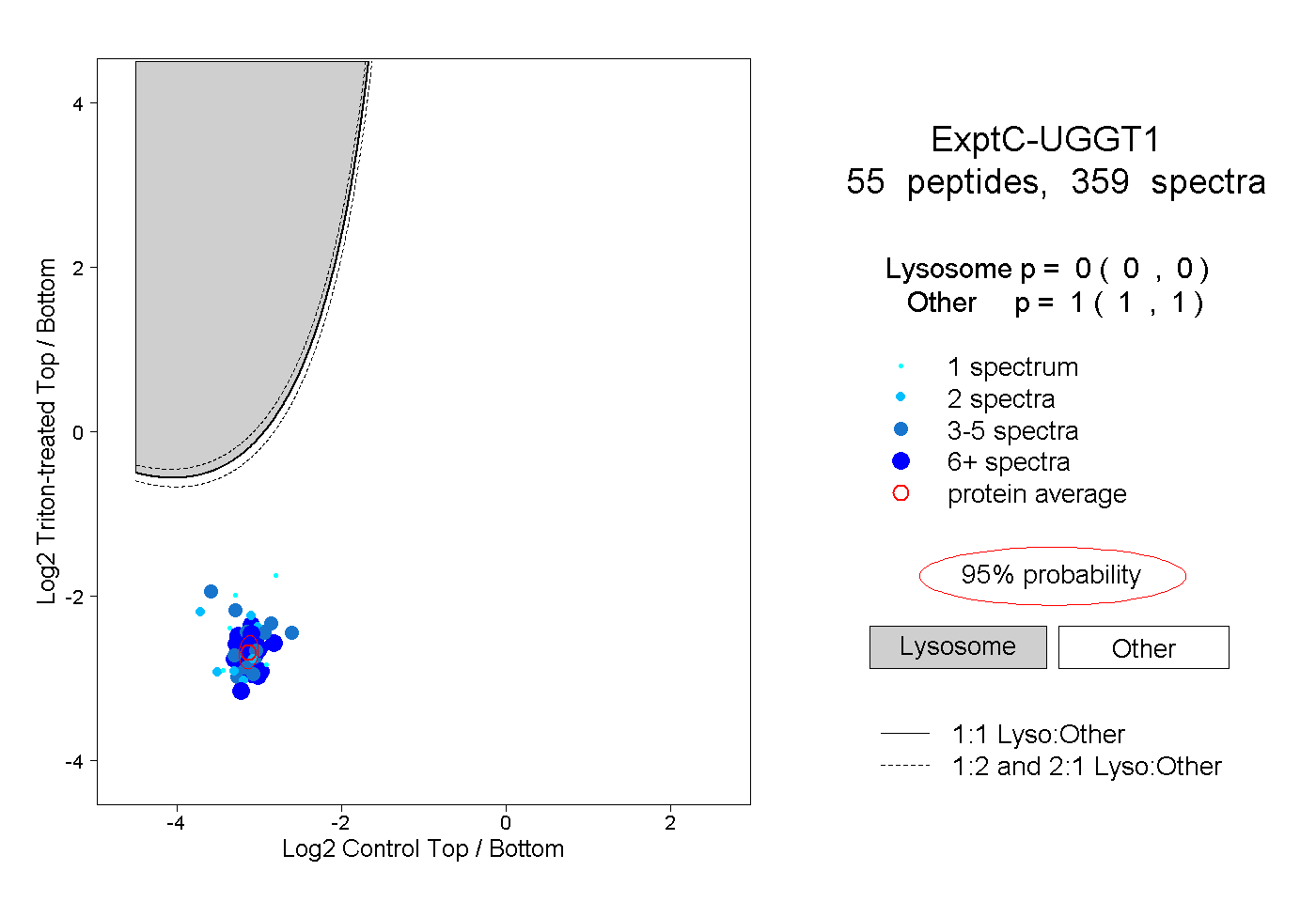 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
56 spectra |
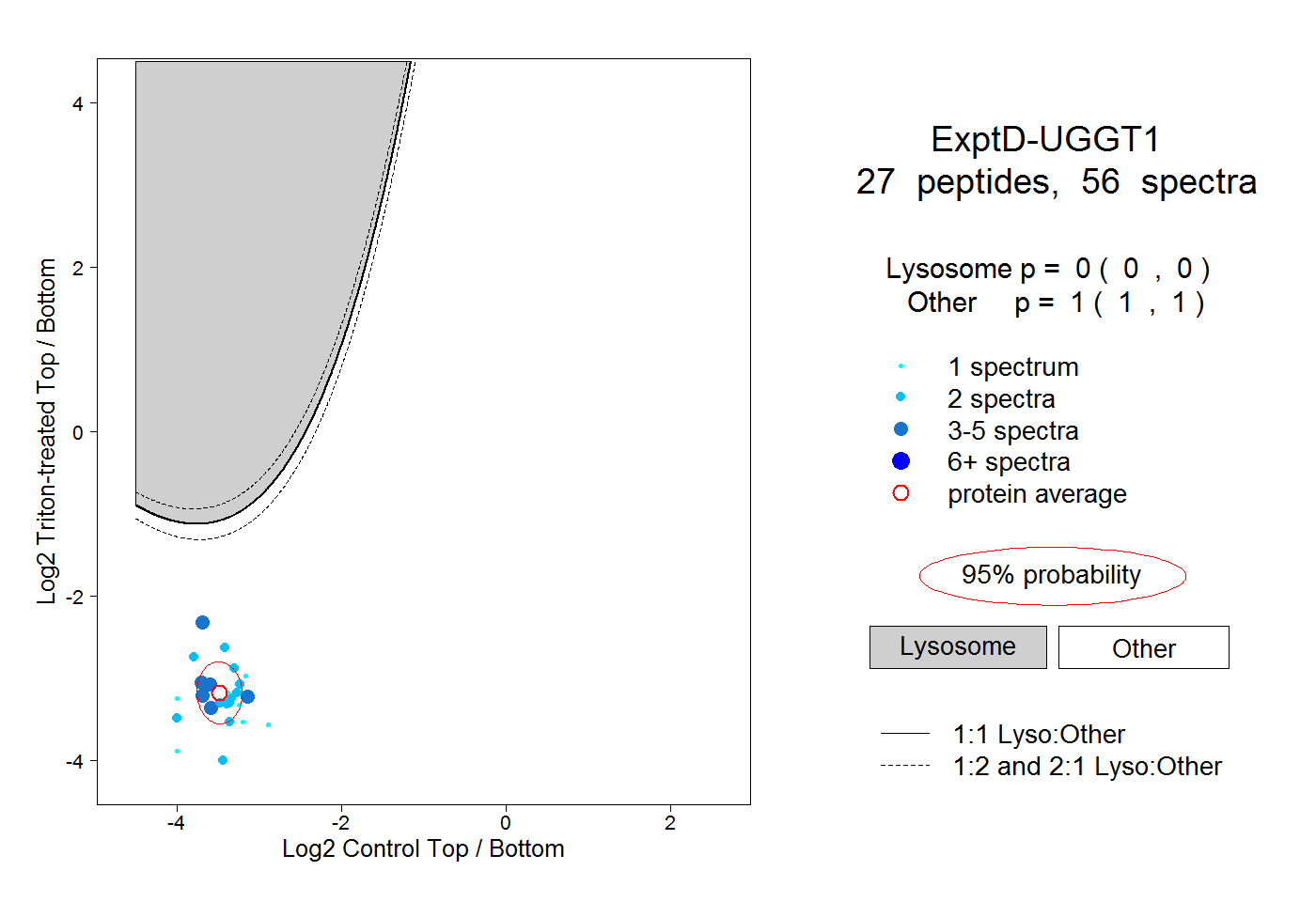 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |