peptides
spectra
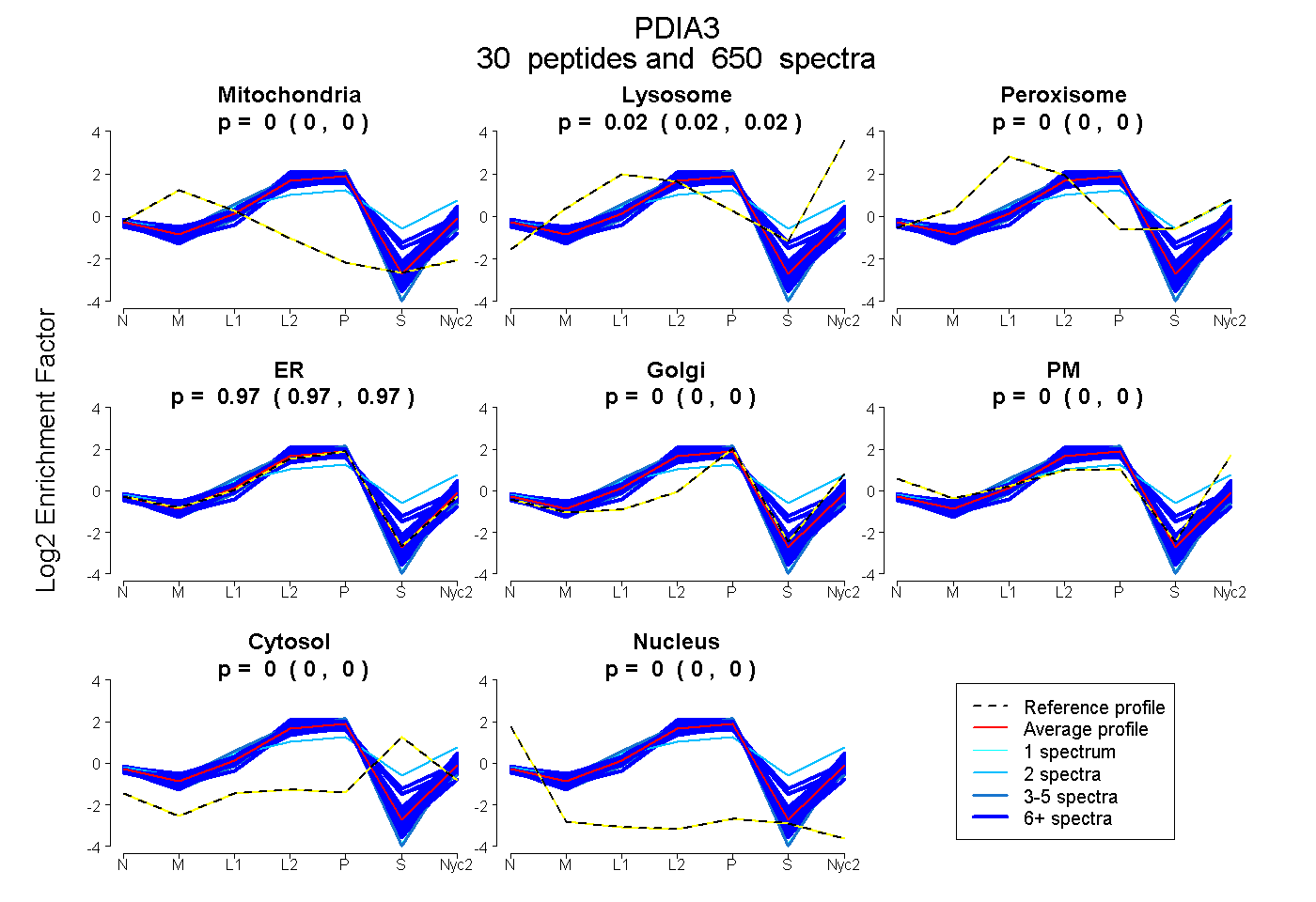
0.000 | 0.000
0.023 | 0.025
0.000 | 0.000
0.972 | 0.975
0.000 | 0.000
0.001 | 0.004
0.000 | 0.000
0.000 | 0.000
peptides
spectra
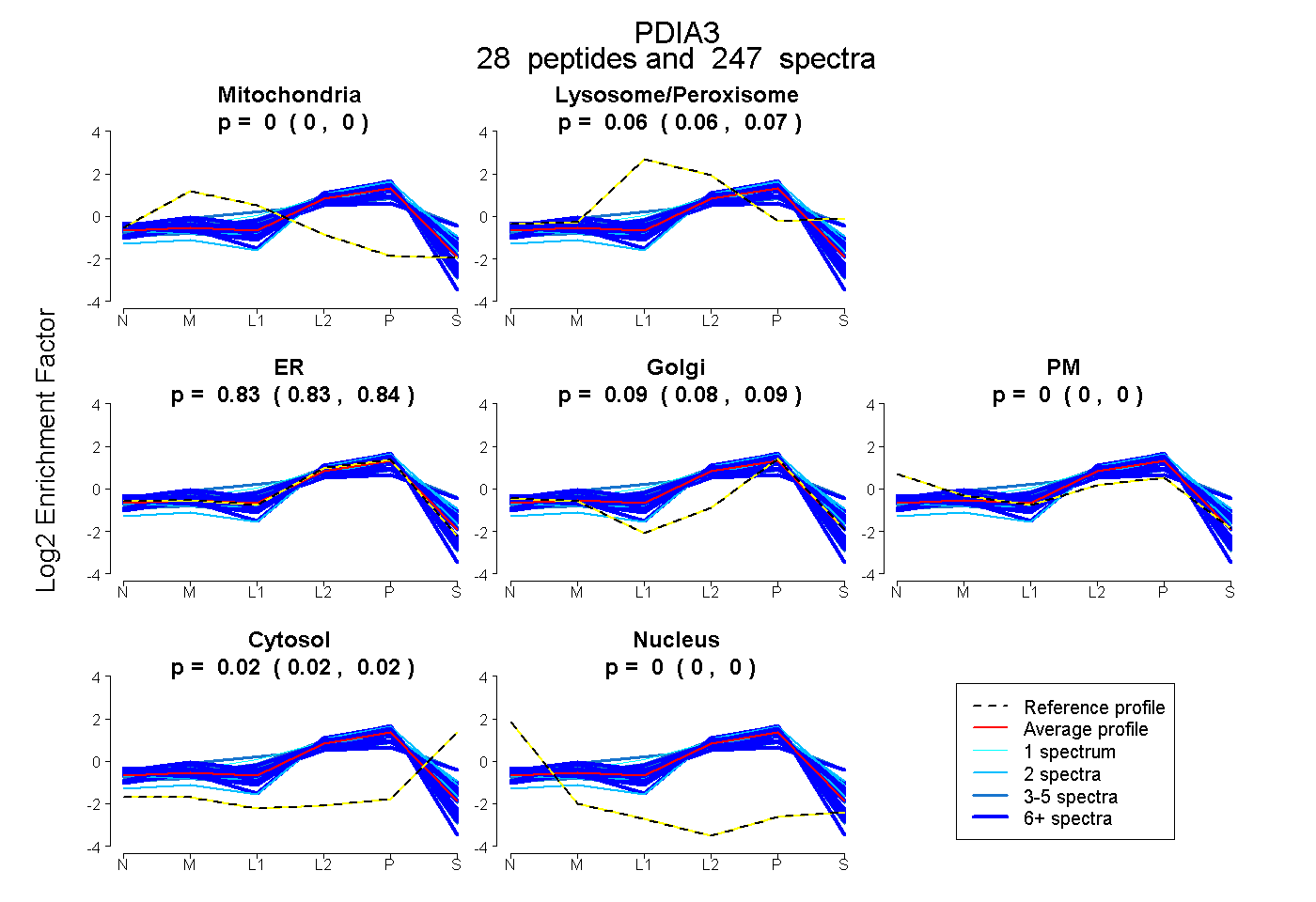
0.000 | 0.000
0.060 | 0.066
0.826 | 0.839
0.081 | 0.090
0.000 | 0.000
0.015 | 0.020
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
650 spectra |
 |
0.000 0.000 | 0.000 |
0.024 0.023 | 0.025 |
0.000 0.000 | 0.000 |
0.973 0.972 | 0.975 |
0.000 0.000 | 0.000 |
0.002 0.001 | 0.004 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
247 spectra |
 |
0.000 0.000 | 0.000 |
0.064 0.060 | 0.066 |
0.833 0.826 | 0.839 |
0.086 0.081 | 0.090 |
0.000 0.000 | 0.000 |
0.018 0.015 | 0.020 |
0.000 0.000 | 0.000 |
| 28 spectra, LAPEYEAAATR | 0.000 | 0.000 | 0.926 | 0.074 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, GSNYWR | 0.013 | 0.116 | 0.774 | 0.096 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, GIVPLAK | 0.000 | 0.375 | 0.337 | 0.284 | 0.000 | 0.004 | 0.000 | |||
| 7 spectra, MDATANDVPSPYEVK | 0.000 | 0.406 | 0.044 | 0.458 | 0.000 | 0.092 | 0.000 | |||
| 10 spectra, DGEEAGAYDGPR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, DPNIVIAK | 0.014 | 0.000 | 0.986 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, DASVVGFFR | 0.000 | 0.000 | 0.941 | 0.059 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, EATNPPIIQEEKPK | 0.000 | 0.128 | 0.674 | 0.198 | 0.000 | 0.000 | 0.000 | |||
| 9 spectra, TADGIVSHLK | 0.000 | 0.264 | 0.492 | 0.245 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, IVAYTEK | 0.000 | 0.000 | 0.904 | 0.030 | 0.000 | 0.066 | 0.000 | |||
| 2 spectra, TFSHELSDFGLESTTGEIPVVAIR | 0.000 | 0.091 | 0.723 | 0.047 | 0.000 | 0.138 | 0.000 | |||
| 11 spectra, VDCTANTNTCNK | 0.000 | 0.205 | 0.478 | 0.179 | 0.083 | 0.055 | 0.000 | |||
| 7 spectra, TFLDAGHK | 0.005 | 0.000 | 0.995 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 14 spectra, FVMQEEFSR | 0.000 | 0.000 | 0.888 | 0.112 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, EYDDNGEGITIFRPLHLANK | 0.000 | 0.146 | 0.830 | 0.024 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, AASNLR | 0.000 | 0.036 | 0.964 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 23 spectra, LNFAVASR | 0.006 | 0.000 | 0.983 | 0.011 | 0.000 | 0.000 | 0.000 | |||
| 15 spectra, QAGPASVPLR | 0.000 | 0.076 | 0.760 | 0.164 | 0.000 | 0.000 | 0.000 | |||
| 13 spectra, DLLTAYYDVDYEK | 0.000 | 0.207 | 0.452 | 0.261 | 0.000 | 0.081 | 0.000 | |||
| 4 spectra, FAHTNVESLVK | 0.000 | 0.495 | 0.000 | 0.452 | 0.000 | 0.053 | 0.000 | |||
| 8 spectra, VMMVAK | 0.019 | 0.002 | 0.943 | 0.000 | 0.000 | 0.036 | 0.000 | |||
| 7 spectra, YGVSGYPTLK | 0.000 | 0.000 | 0.891 | 0.109 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, TEDEFK | 0.000 | 0.000 | 0.849 | 0.000 | 0.000 | 0.151 | 0.000 | |||
| 10 spectra, GFPTIYFSPANK | 0.000 | 0.125 | 0.699 | 0.136 | 0.000 | 0.041 | 0.000 | |||
| 7 spectra, SEPIPETNEGPVK | 0.000 | 0.266 | 0.258 | 0.379 | 0.053 | 0.044 | 0.000 | |||
| 22 spectra, DLFSDGHSEFLK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 11 spectra, ELNDFISYLQR | 0.000 | 0.000 | 0.905 | 0.063 | 0.000 | 0.032 | 0.000 | |||
| 8 spectra, FLQEYFDGNLK | 0.000 | 0.148 | 0.694 | 0.126 | 0.000 | 0.032 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
1096 spectra |
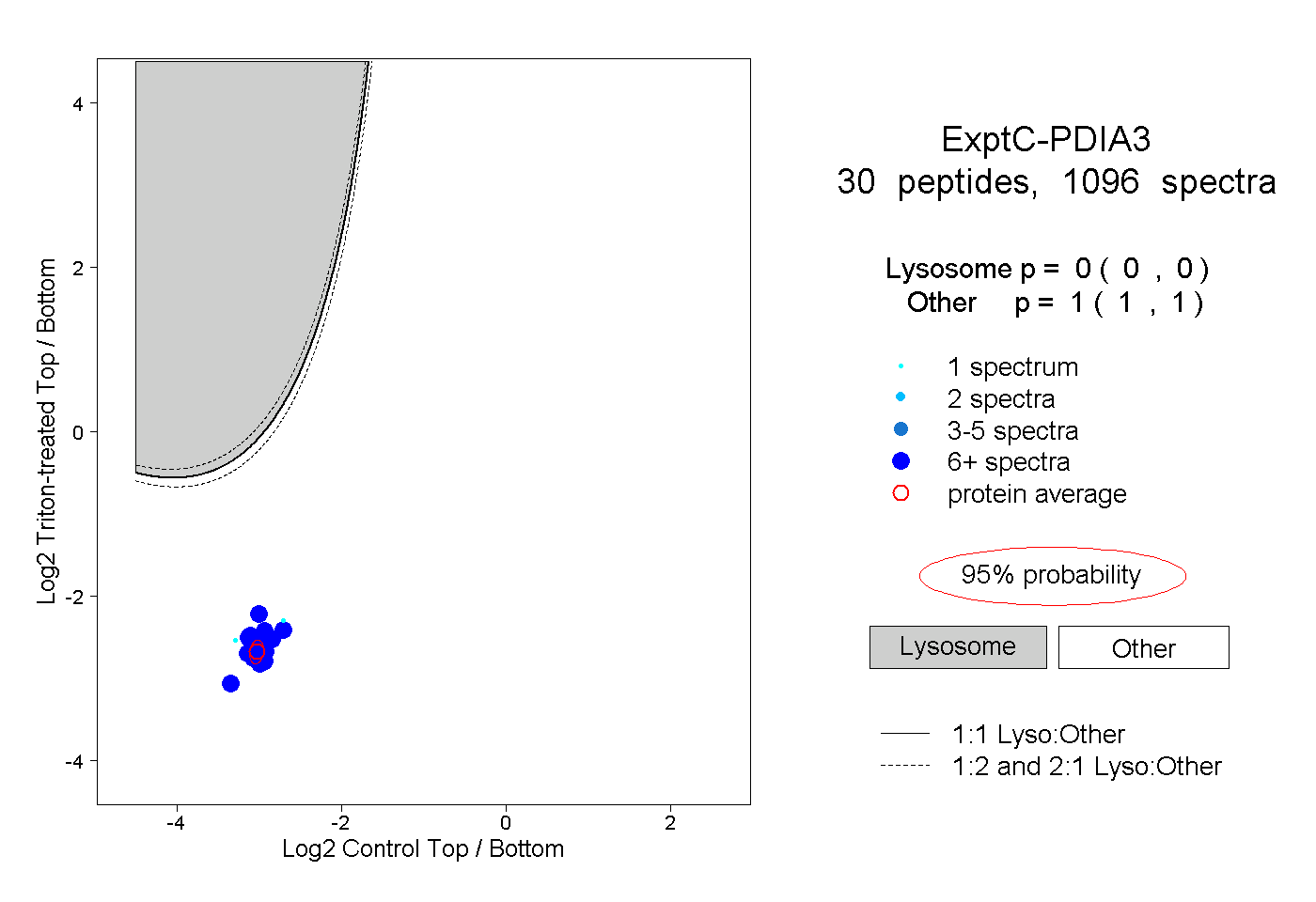 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
105 spectra |
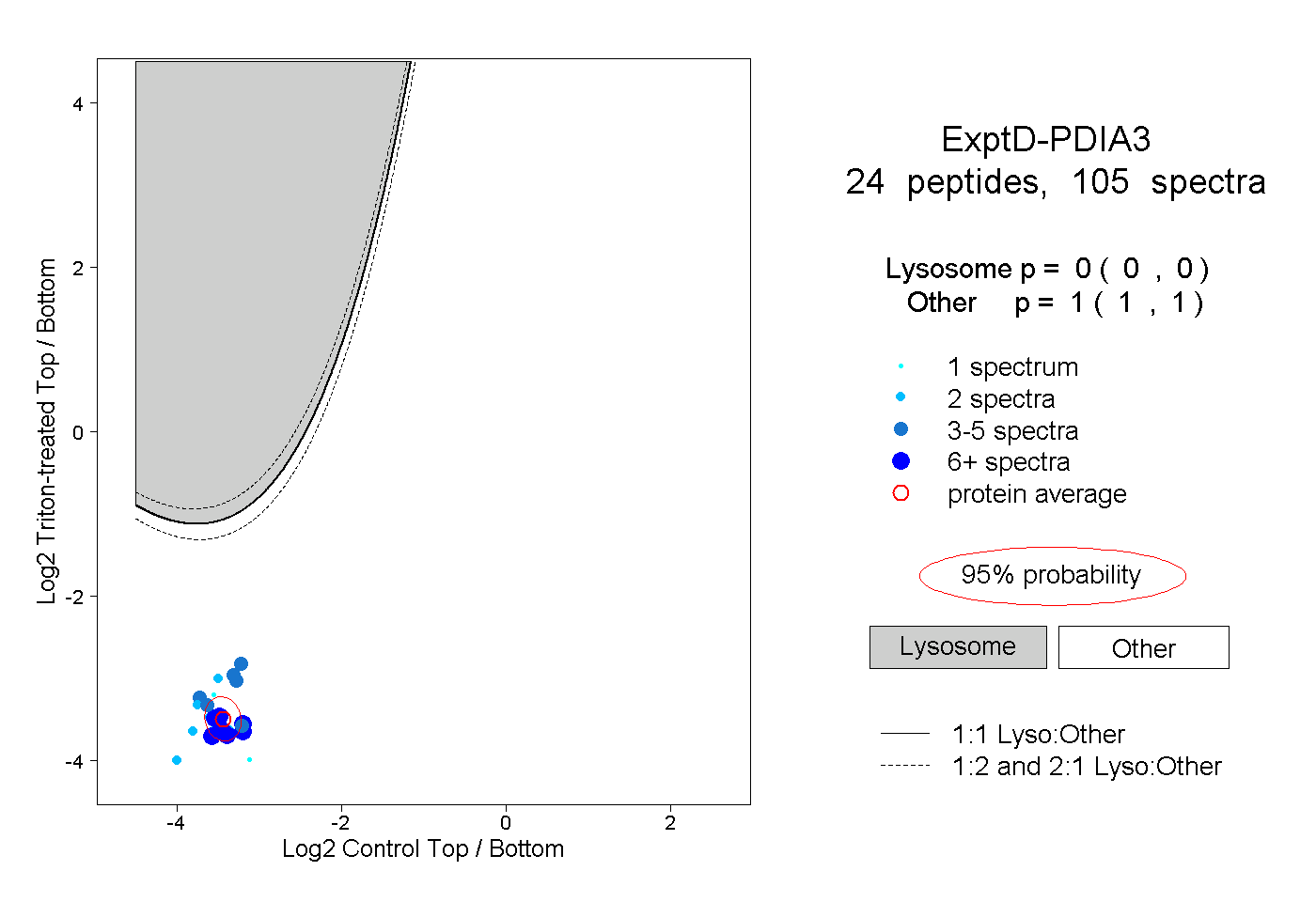 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |